Clear Sky Science · nl
Hoge bruikbaarheid van DNA‑barcoding voor soortidentificatie en cryptische diversiteit bij Koreaanse bladluizen (Hemiptera: Aphididae)
Waarom kleine plantenplagen ertoe doen
Bladluizen zijn kleine sapzuigende insecten die in stilte gewassen en tuinplanten kunnen verwoesten, maar ze zijn berucht moeilijk met het blote oog uit elkaar te houden. Veel soorten lijken vrijwel identiek en veranderen van vorm met de seizoenen, waardoor traditionele identificatie met microscopen traag en onzeker kan zijn. Deze studie laat zien hoe een genetische snelweg genaamd DNA‑barcoding Koreaanse bladluizen snel in soorten kan opdelen, verborgen dubbelgangers kan onthullen en ons vermogen kan verbeteren om plagen te monitoren en de landbouw te beschermen.
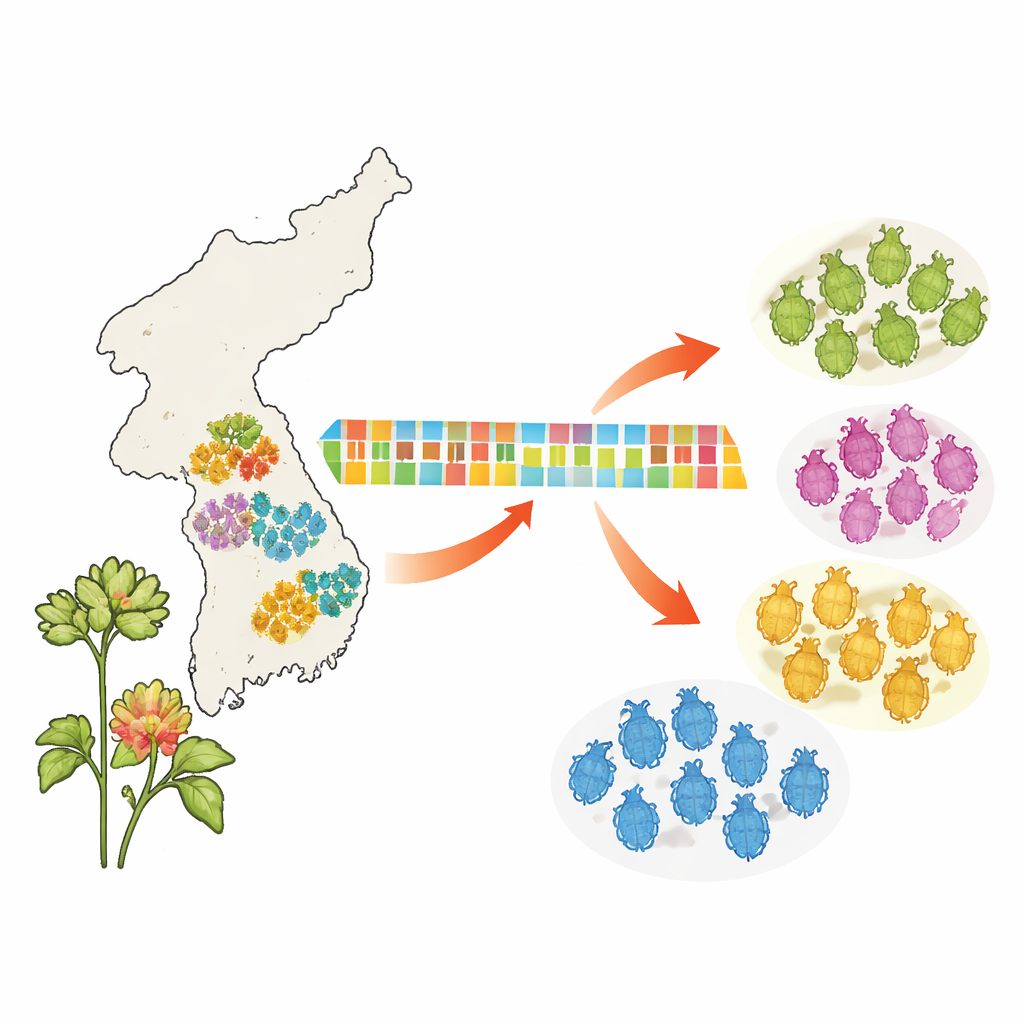
Onzichtbare verschillen bij look‑alike insecten
Op het Koreaanse schiereiland voeden honderden bladluissoorten zich met alles van groentegewassen tot bomen, en wereldwijd worden ongeveer 250 soorten als ernstige landbouwplagen beschouwd. Omdat bladluizen klein, zacht en vaak verborgen aan de onderkant van bladeren zijn, hebben specialisten doorgaans gedetailleerde lichaamsmetingen nodig om ze te benoemen, een proces dat uren per monster kan vergen. De onderzoekers wilden testen of een korte, gestandaardiseerde DNA‑reeks als betrouwbare "streepjescode" voor deze insecten kon dienen, waardoor een arbeidsintensieve identificatietaak veel sneller en consistenter kan worden uitgevoerd.
Een genetische identiteitskaart voor elke soort
Het team verzamelde 566 bladluizen van 85 locaties in Zuid‑Korea, die 125 groepen vertegenwoordigden die aanvankelijk op uiterlijk waren gesorteerd (zogenaamde morfosoorten). Van elk exemplaar sequentieerden ze een standaardsegment van een mitochondriaal gen dat veel wordt gebruikt bij barcoding van dieren. Vervolgens vergeleken ze hoe gelijk of verschillend deze DNA‑sequenties waren binnen een soort, tussen soorten binnen hetzelfde geslacht en tussen verder verwante soorten. Zoals verwacht waren de DNA‑verschillen binnen erkende soorten klein maar veel groter tussen soorten, waardoor er een meetbare "kloof" ontstond die gebruikt kan worden om soorten uit elkaar te houden.
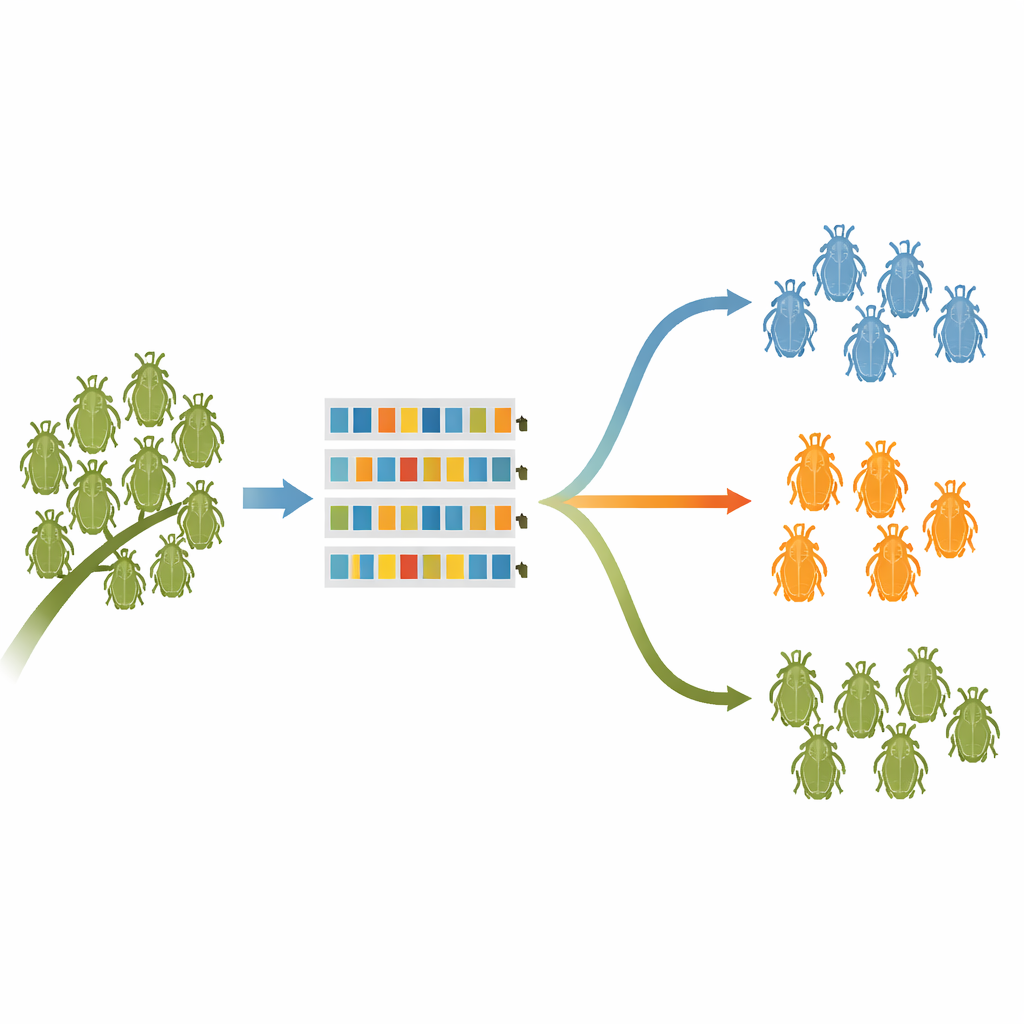
Verborgen lijnen en het testen van de grenzen
Om ruwe DNA‑verschillen om te zetten in praktische soortgrenzen pasten de onderzoekers vier veelgebruikte computer‑methoden toe, elk op een eigen manier snijdend in de genetische stamboom. Over deze benaderingen heen vonden ze dat een verschil van ongeveer 2% in het barcodegebied goed werkte als eerste afkappunt tussen soorten voor de meeste Koreaanse bladluizen. Ongeveer 70% van de morfosoorten werd consequent door alle methoden als afzonderlijke eenheden herkend, wat aangeeft dat barcodes en traditionele morfologie grotendeels overeenstemden. Er waren echter tientallen gevallen die minder goed overeenkwamen, wat duidt op ofwel verborgen diversiteit binnen wat voorheen als één soort werd gezien of, in enkele gevallen, zeer vergelijkbare soorten die mogelijk niet echt onderscheiden zijn.
Verborgen soorten en brede genetische variatie
Nadere bestudering van de niet‑overeenkomende gevallen onthulde verschillende intrigerende verhalen. Drie bladluissoorten, waaronder Eriosoma yangi en Greenidea kuwanai, splitsten zich in duidelijk verschillende genetische lijnen die ook subtiele maar consistente lichaamsverschillen of verschillende ecologische omstandigheden vertoonden—sterke aanwijzingen voor cryptische soorten die onopgemerkt waren gebleven. Bij andere soorten, zoals de graanplaag Sitobion avenae en de peulvruchtenplaag Aphis craccivora, lieten de barcodes verrassend hoge variatie over regio’s zien, maar groepeerden alle computermethoden ze nog steeds als één soort. Dit lijken genetisch rijke maar samenhangende soorten te zijn, een nuttige herinnering dat hoge DNA‑diversiteit niet altijd meerdere soorten betekent.
Wat dit betekent voor gewassen en biodiversiteit
Bladluizen leiden complexe levens, schakelen vaak van gastheer en planten zich deels door kloonen voort, wat de zuivere genetische grenzen waarop barcoding steunt kan vervagen. De auteurs waarschuwen dat DNA‑barcodes alleen in zulke groepen soms soorten kunnen oversplitsen of ondersplitsen, en pleiten voor het combineren van genetica met zorgvuldige morfologie en ecologische informatie. Desalniettemin toont hun uitgebreide Koreaanse dataset aan dat barcoding een krachtig praktisch hulpmiddel is: het versnelt routinematige identificaties, markeert gevallen waar verborgen soorten kunnen schuilen en helpt bij het opbouwen van referentiebibliotheken die boeren, quarantainefunctionarissen en ecologen kunnen gebruiken. Voor een algemeen publiek is de boodschap dat een korte DNA‑"tag" verrassend veel kan onthullen over de werkelijke diversiteit van kleine insecten die onze gewassen en ecosystemen vormen.
Bronvermelding: Kang, Y., Lee, H., Park, DK. et al. High utility of DNA barcoding for species identification and cryptic diversity in Korean aphids (Hemiptera: Aphididae). Sci Rep 16, 9307 (2026). https://doi.org/10.1038/s41598-026-38901-0
Trefwoorden: DNA‑barcoding, bladluizen, cryptische soorten, landbouwplagen, biodiversiteit