Clear Sky Science · nl
Nieuwe convolutionele neurale netwerk voor bacteriële identificatie van confocale microscopische datasets
Waarom sneller ziekteverwekkers zien ertoe doet
Wanneer artsen proberen te bepalen welke bacteriën een infectie veroorzaken, is tijd van essentieel belang. Traditionele laboratoriumtests kunnen uren of zelfs dagen duren en vereisen hoogopgeleide experts die microscoopbeelden met het blote oog beoordelen. Deze studie introduceert een nieuw computervisiesysteem, CM-Net genoemd, dat gespecialiseerde microscoopbeelden automatisch kan uitlezen en snel twee veelvoorkomende medisch relevante bacteriën van elkaar kan onderscheiden, terwijl het ook herkent welke cellen leven of dood zijn. Het werk wijst op een weg naar snellere, betrouwbaardere diagnostiek die op termijn in ziekenhuizen en onderzoekslaboratoria wereldwijd gebruikt zou kunnen worden.
Gloeiende microben omzetten in bruikbare beelden
De onderzoekers begonnen met een krachtig beeldvormingsinstrument dat bekendstaat als confocale laser scannende microscopie. Simpel gezegd gebruikt deze microscoop een gefocusseerde laser en fluorescerende kleurstoffen om bacteriën in verschillende kleuren te laten opgloeien, afhankelijk van of ze leven of dood zijn. Levende cellen verschijnen groen, terwijl dode cellen rood oplichten. Door het monster in zeer dunne lagen te scannen bouwt de microscoop scherpe, gedetailleerde beelden van de bacteriën op glazen objectglaasjes op. Het team werkte met twee goed onderzochte soorten die vaak ziekenhuisinfecties veroorzaken: staafvormige Escherichia coli en bolvormige Staphylococcus aureus. Deze hoogwaardige beelden vormen het ruwe materiaal dat CM-Net moet leren begrijpen.
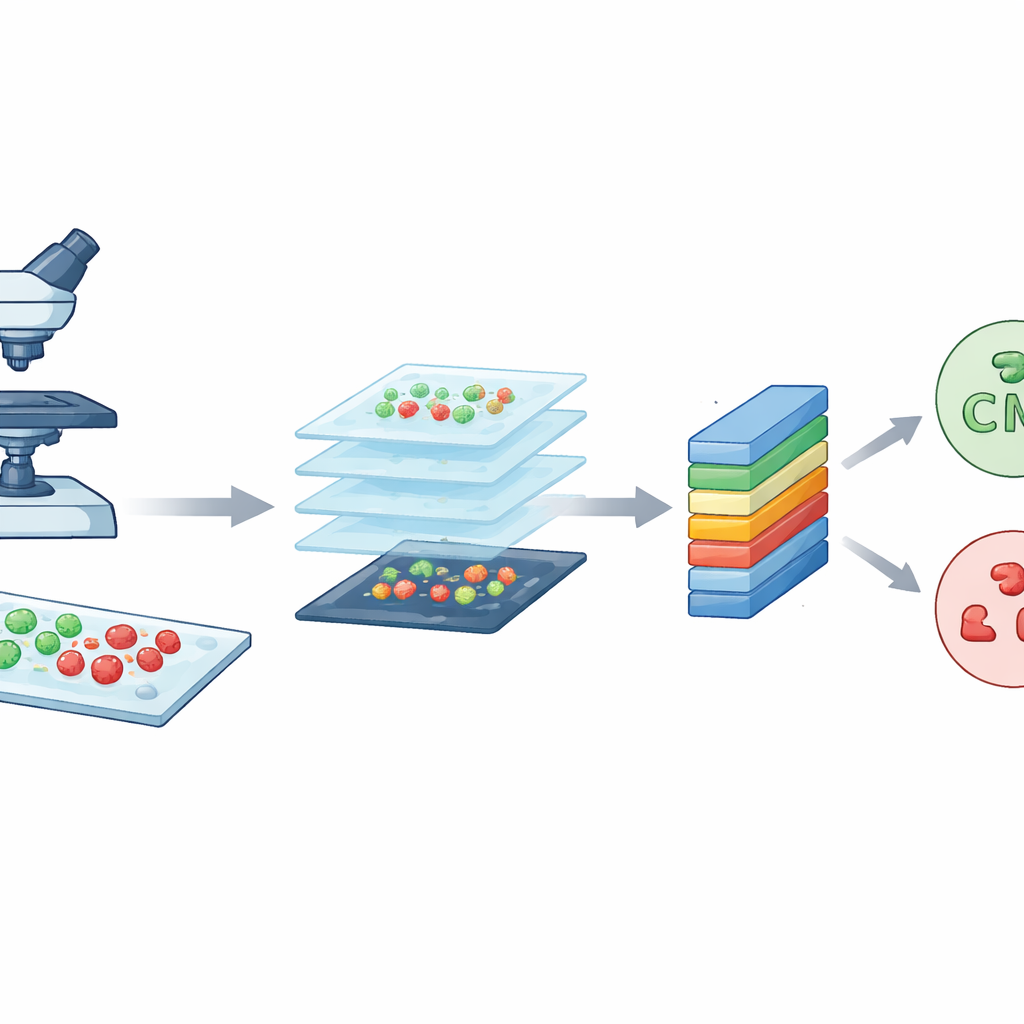
Van grote beelden naar veel kleine tegels
Hoewel elk confocaal beeld rijk aan details is, is het ook zeer groot, ongeveer 3000 bij 3000 pixels. Een computermodel direct op zulke enorme beelden trainen zou traag zijn en buitensporige rekenkracht vereisen. Om dit op te lossen sneed het team elk groot beeld in vele kleinere vierkante tegels, elk 224 bij 224 pixels, een standaardformaat in beeldanalyse. Dit proces, dat deel uitmaakt van data-augmentatie, vermindert zowel de technische belasting als het aantal trainingsvoorbeelden vergroot. Vanuit een oorspronkelijke set van 300 beelden per bacterietype genereerden ze in totaal 7.066 tegels. Deze tegels vangen lokale patronen van vormen, kleuren en texturen uit verschillende gebieden van de objectglaasjes, wat het model een diverse en evenwichtige verzameling voorbeelden geeft om van te leren.
Hoe de digitale waarnemer leert kijken
CM-Net is een zorgvuldig ontworpen deep-learningmodel dat specifiek is gebouwd voor bacteriële microscopie, in plaats van aangepast te zijn van algemene fotocollecties. Het is een soort convolutioneel neuraal netwerk, een klasse programma’s die uitblinken in het vinden van patronen in beelden. CM-Net verwerkt elke tegel via een reeks stadia. Vroege stadia zoeken naar eenvoudige visuele signalen zoals randen en vlekken; diepere stadia combineren deze tot complexere patronen die staven van bollen en levende van dode cellen onderscheiden. Het netwerk gebruikt technieken zoals batchnormalisatie, die de interne signalen goed laat verlopen, en een geklemde versie van zijn activatiefunctie, die extreme reacties voorkomt die het leren kunnen destabiliseren. Later lagen condenseren de geëxtraheerde informatie en nemen een definitieve beslissing over het bacterietype en de celtoestand.
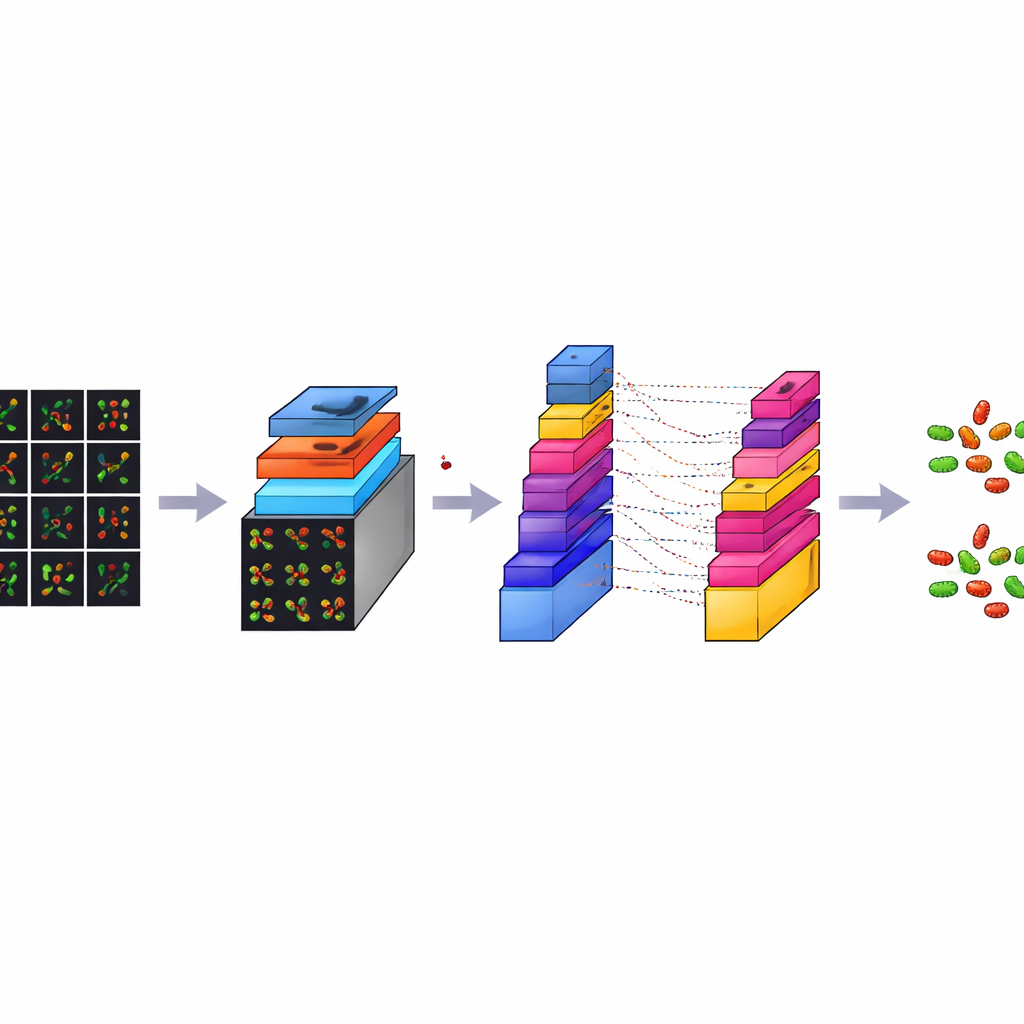
Beter presteren dan populaire kant-en-klare modellen
Om te beoordelen hoe goed CM-Net het doet, trainden en testten de auteurs het model 30 keer, telkens met een nieuwe verdeling van de data in trainings- en testgroepen. Ze maten nauwkeurigheid — hoe vaak het model het in het algemeen goed had; sensitiviteit — hoe goed het elke doelcategorie detecteerde; specificiteit — hoe goed het valse alarmen vermeed; en verschillende andere gangbare scores. CM-Net behaalde gemiddeld ongeveer 96% nauwkeurigheid, met sensitiviteit en specificiteit ook rond de 96%, en een sterke balans tussen de twee klassen. Het had bovendien minder interne parameters en minder geheugengebruik nodig dan verschillende wijdverbreide voorgetrainde modellen, waaronder GoogLeNet, MobileNetV2, ResNet18 en ShuffleNet, terwijl het ook sneller draaide. Visualisatietools toonden aan dat CM-Net zijn aandacht richt op de daadwerkelijke bacteriekernen in de beelden, in plaats van op willekeurige achtergrondkenmerken, wat de gedachte ondersteunt dat het biologische betekenisvolle aanwijzingen leert.
Wat dit betekent voor toekomstig laboratoriumwerk
In gewone woorden toont de studie aan dat een doelgericht deep-learningsysteem kan leren om complexe microscoopbeelden van bacteriën nauwkeurig, efficiënt en op een manier die aansluit bij wat menselijke experts belangrijk vinden, te “lezen”. Voorlopig is CM-Net echter alleen getraind op twee bacteriesoorten en op gegevens van één type microscoop, dus er is meer werk nodig voordat het als algemeen diagnostisch hulpmiddel kan worden gebruikt. De auteurs zijn van plan het uit te breiden naar meer soorten, verschillende celtoestanden en grotere, gevarieerdere datasets. Toch suggereren de resultaten dat systemen als CM-Net uiteindelijk laboratoria kunnen helpen infecties sneller te identificeren, behandelbeslissingen te sturen en geautomatiseerde analyse van microbiologische experimenten toegankelijker te maken voor gebruikers zonder gespecialiseerde beeldvormingsexpertise.
Bronvermelding: Al-Jumaili, A., Al-Jumaili, S., Alyassri, S. et al. Novel convolutional neural network for bacterial identification of confocal microscopic datasets. Sci Rep 16, 8123 (2026). https://doi.org/10.1038/s41598-026-38861-5
Trefwoorden: classificatie van bacteriebeelden, confocale microscopie, deep learning, convolutionele neurale netwerken, medische diagnostiek