Clear Sky Science · nl
Computationale optimalisatie van de oplosbaarheid van het DEK1-calpaindomein via geïntegreerde structurele modellering en data-gedreven gerichte mutagenese
Waarom het belangrijk is dat plantaardige eiwitten zich goed gedragen
Veel eiwitten die de groei van planten aansturen zijn grote, kwetsbare moleculen die zich niet laten oplossen wanneer wetenschappers ze in het laboratorium willen bestuderen. Een van die eiwitten, DEK1, helpt de vorming van plantlichamen te sturen vanaf het niveau van individuele cellen. Omdat een cruciaal deel van DEK1 echter samenklontert wanneer het in bacteriën wordt geproduceerd, bleef de 3D-structuur onbekend, wat de pogingen om het te begrijpen en te benutten vertraagde. Deze studie laat zien hoe computermodellering en slimme, data-gedreven ontwerpen dat lastige gebied kunnen herontwerpen zodat het beter oplost, zonder de bouwprincipes van het eiwit te verstoren — en biedt daarmee een algemeen recept om moeilijke eiwitten te temmen.
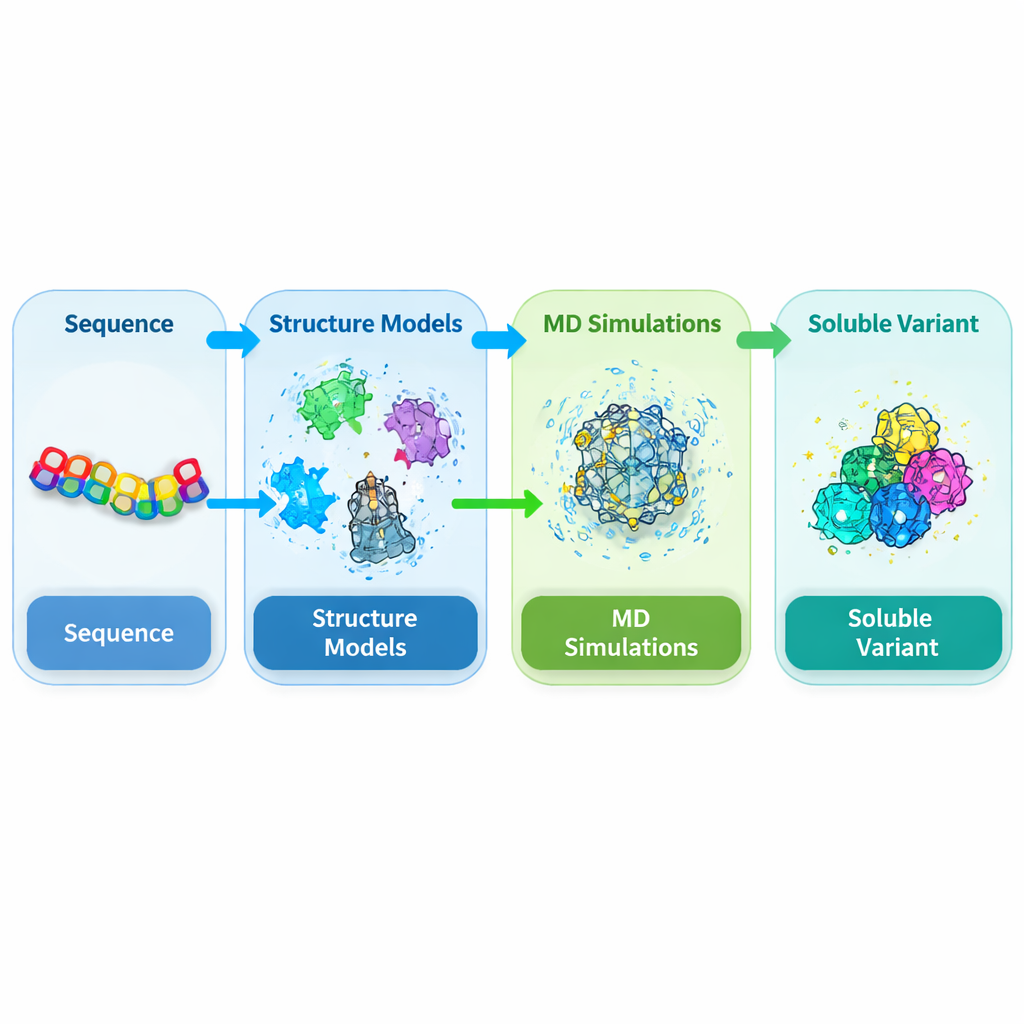
De probleemzone in een sleutel-eiwit van planten aanpakken
DEK1 is een uitzonderlijk groot eiwit dat in celmembranen zit en wordt afgesloten door een knipenzym-regio die bekendstaat als een calpaindomein. Genetisch onderzoek heeft aangetoond dat dit domein essentieel is voor normale ontwikkeling in planten zoals mossen en gewassen, maar de structuur is nog nooit experimenteel opgelost. Wanneer onderzoekers proberen deze calpain-kern (CysPc genoemd) in de gebruikelijke gastbacterie Escherichia coli te maken, wordt hij vaak onoplosbaar en vormt hij dichte inclusie lichaampjes. Daardoor is het vrijwel onmogelijk om het in de hoeveelheden en de zuiverheid te zuiveren die nodig zijn voor gedetailleerde structurele en functionele studies. De auteurs hebben zich daarom tot doel gesteld het CysPc-domein zo te herontwerpen dat het makkelijker oplost en tegelijkertijd zijn algemene vorm behoudt.
Een betrouwbaar 3D-model vanaf nul opbouwen
Aangezien er geen experimentele structuur bestaat voor deze plantaardige calpain, moest het team eerst de 3D-vorm voorspellen. Ze combineerden meerdere geavanceerde structuurvoorspellingsmethoden, waaronder AlphaFold2, SWISS-MODEL en I-TASSER, en verankerden deze voorspellingen aan bekende structuren van verwante calpains uit zoogdieren. Met een consensusbenadering verfijnden en controleerden ze de resulterende modellen met meerdere kwaliteitstests die de ruggengraatgeometrie, de opvulling en de overeenstemming met bekende structurele patronen beoordelen. Deze onafhankelijke controles toonden aan dat het geïntegreerde model van het CysPc-domein betrouwbaarder was dan elke afzonderlijke voorspelling, en zo een stevig startpunt bood om te onderzoeken hoe kleine wijzigingen in de aminozuursequentie de oplosbaarheid zouden kunnen verbeteren.
Virtuele mutaties testen in een gesimuleerde vloeistof
Met het 3D-model in handen voerden de auteurs uitgebreide moleculaire dynamica-simulaties uit, waarbij het eiwit en de omringende watermoleculen door de tijd op de computer werden gevolgd. Ze concentreerden zich op residuen aan het eiwitoppervlak die flexibel, hydrofoob of voorspeld waren om aggregatie te bevorderen. Kandidaatposities werden stuk voor stuk gemuteerd naar meer watervriendelijke aminozuren en vervolgens elk 200 nanoseconden gesimuleerd. Voor elke variant maten ze kenmerken die samenhangen met oplosbaarheid, zoals hoeveel oppervlak in contact staat met water, hoe compact het eiwit blijft en hoe sterk atomen fluctueren. Veel enkele mutaties verhoogden in bescheiden mate de blootstelling aan oplosmiddel of interne waterstofbrugvorming terwijl de algehele vouwing ongewijzigd bleef, wat suggereert dat het basale scaffold van CysPc zorgvuldig gekozen substituties kon verdragen.
Algoritmen laten zoeken in de mutatieruimte
Het veranderen van slechts één residu levert zelden grote verbeteringen in oplosbaarheid op, dus onderzochten de onderzoekers vervolgens combinaties van twee en drie mutaties. Ze genereerden een bibliotheek van dubbele en drievoudige varianten opgebouwd uit de beste enkele mutaties en simuleerden opnieuw elk van deze. Om deze ontwerpen eerlijk te scoren en te rangschikken, definieerden ze een gewogen index die meerdere simulatiekenmerken combineert die bekendstaan als correlaten van oplosbaarheid, en beloonden toegenomen hydratatie en interne binding terwijl overdreven flexibiliteit werd bestraft. Vervolgens gebruikten ze een reinforcement learning-algoritme (Proximal Policy Optimization) om door de enorme ruimte van mogelijke drievoudige mutants te navigeren en de meest veelbelovende combinaties voor te stellen. Deze data-gedreven zoektocht convergeerde op een specifieke drievoudige mutant, genoemd MUT347, als de topkandidaat.
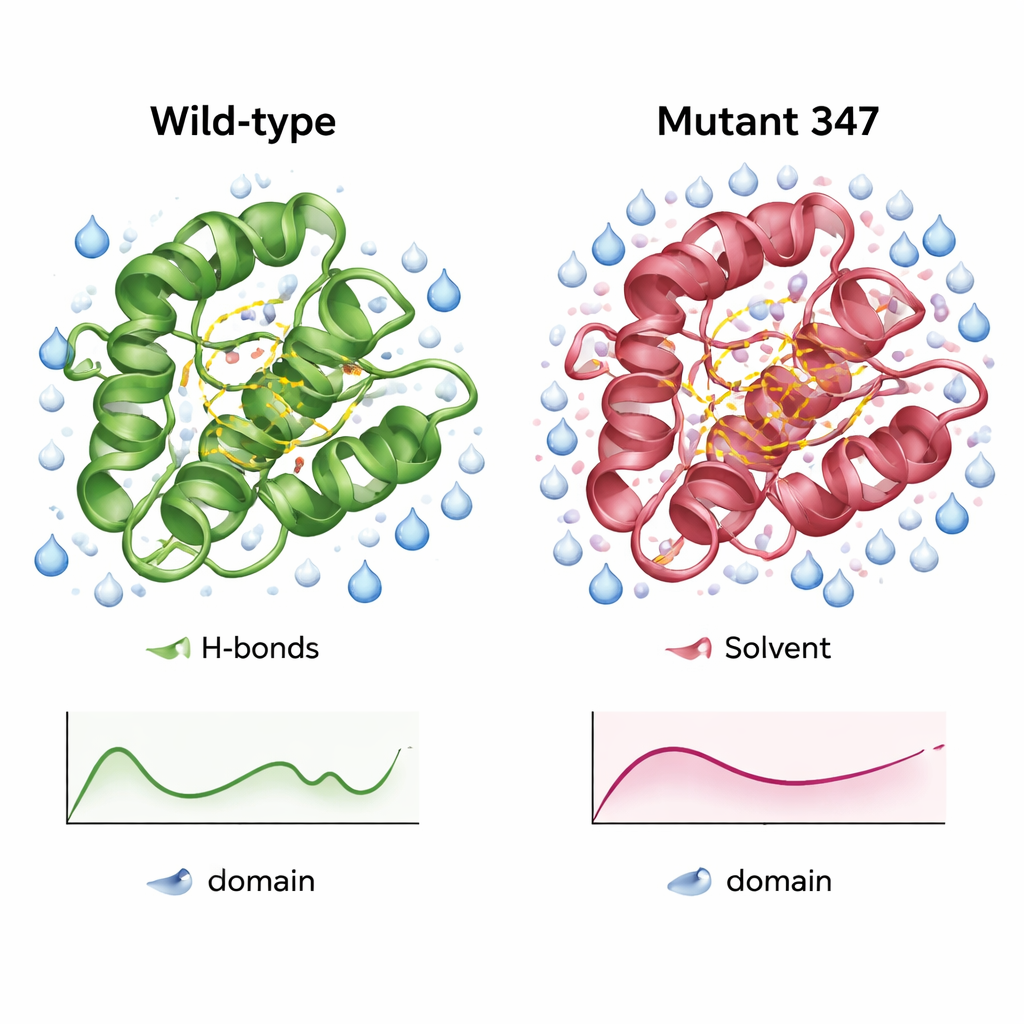
Een compacter, beter gehydrateerd versie van het enzym
Gedetailleerde simulaties van het wildtype CysPc-domein en MUT347 lieten zien hoe de ontworpen variant verschilde. MUT347 kwam sneller in evenwicht en vertoonde kleinere afwijkingen van de beginvorm, wat duidt op grotere structurele stabiliteit in oplossing. De lussen en ketentermen waren iets minder beweeglijk, terwijl het kern-katalytische gebied zijn oorspronkelijke flexibiliteit behield, wat suggereert dat functioneel belangrijke bewegingen behouden bleven. De drievoudige mutant vertoonde meer interne waterstofbruggen en een groter voor water toegankelijk oppervlak in sleutelregio's, signalen van een beter georganiseerde en meer gehydrateerde oppervlakte. Bij wisselende zoutconcentraties en pH-waarden hield MUT347 consequent lagere fluctuaties aan dan het oorspronkelijke eiwit, gedragskenmerken die samenhangen met een verminderde neiging tot klonteren.
Wat dit betekent voor het bestuderen en hergebruiken van eiwitten
De kernboodschap voor niet-specialisten is dat de auteurs grotendeels op basis van computers een recept hebben ontwikkeld om een moeilijk samenklonterend deel van een essentieel plantaardig eiwit om te vormen tot een beter oplosbare, betrouwbaardere versie, zonder eerst experimentele structurele informatie te hebben. Door moderne structuurvoorspelling, langtijdssimulaties en leeralgoritmen te combineren die veel ontwerpmogelijkheden tegelijk kunnen afwegen, identificeerden ze een drievoudige mutatie die naar verwachting de vouwing stabiliseert en het oppervlak gunstiger voor water blootlegt. Hoewel experimenteel werk nog nodig is om de verbeteringen in echte reageerbuizen te bevestigen, kan dit raamwerk breed inzetbaar zijn om andere eukaryote eiwitten die moeilijk te produceren zijn te redden, en uiteindelijk wetenschappers te helpen structuren en functies te ontsluiten die nu buiten bereik liggen.
Bronvermelding: Dabiri, M., Levarski, Z., Struhárňanská, E. et al. Computational optimization of DEK1 calpain domain solubility through integrated structural modelling and data-driven targeted mutagenesis. Sci Rep 16, 7767 (2026). https://doi.org/10.1038/s41598-026-38805-z
Trefwoorden: eiwitoplosbaarheid, computationele mutagenese, moleculaire dynamica, plantaardig calpain DEK1, eiwitengineering