Clear Sky Science · nl
Genoomsequencing van Bacillus daqingensis en Alkalicoccus luteus onthult taxonomische inzichten en adaptieve mechanismen
Leven op zoute plekken
Van zoutmeren tot alkalische grond: sommige microben gedijen in omstandigheden die de meeste andere levensvormen doen uitdrogen en doden. Deze studie duikt in het DNA van twee van zulke zoutminnende bacteriën om te begrijpen hoe ze extreme omgevingen doorstaan en om te verduidelijken waar ze echt thuishoren in de boom des levens. Door hun genomen gedetailleerd te vergelijken tonen de onderzoekers aan dat wat eerder voor aparte bacteriesoorten werd gehouden in feite hetzelfde soort organisme betreft, en ze onthullen de moleculaire trucs die deze microben gebruiken om intense zoutstress te weerstaan.
Waarom deze zoutliefhebbers ertoe doen
De bacteriën in het hart van dit werk werden oorspronkelijk Bacillus daqingensis en Alkalicoccus luteus genoemd. Beide zijn geïsoleerd uit zoute, alkalische omgevingen zoals soda-meren en zoute grond, waar de meeste levensvormen moeite mee hebben. Wetenschappers vermoedden dat Bacillus daqingensis mogelijk tot het geslacht Alkalicoccus behoort, maar de volledige genoomsequentie ontbrak, waardoor de officiële status in onzekerheid bleef. Door de complete genomen van deze microben te sequencen en te analyseren en ze te vergelijken met verwante soorten, wilden de auteurs deze taxonomische puzzel oplossen en tegelijkertijd leren hoe leden van het geslacht Alkalicoccus in staat zijn te overleven onder zulke harde omstandigheden.
Microbiële genomen lezen en vergelijken
Het team liet de bacteriën in het laboratorium groeien, extraheerde hun DNA en sequentieerde het met hoogdoorvoermethoden. Vervolgens plakten ze de miljoenen kleine DNA-fragmenten aan elkaar tot bijna-volledige genoomkaarten en controleerden ze de kwaliteit. Zowel Bacillus daqingensis als Alkalicoccus luteus bleken vergelijkbaar grote genomen te hebben van ongeveer 3,4 tot 3,5 miljoen basenparen, met nagenoeg identieke genetische inhoud en zeer hoge volledigheid. Een belangrijke genetische marker, het 16S rRNA-gen, was in wezen hetzelfde in beide organismen: één vergelijking vond 99,8 procent identiteit met eerdere laboratoriummetingen en, cruciaal, de 16S-sequenties van de twee stammen waren onderling een perfecte 100 procent match.
Ontcijferen van overleving bij zout en stress
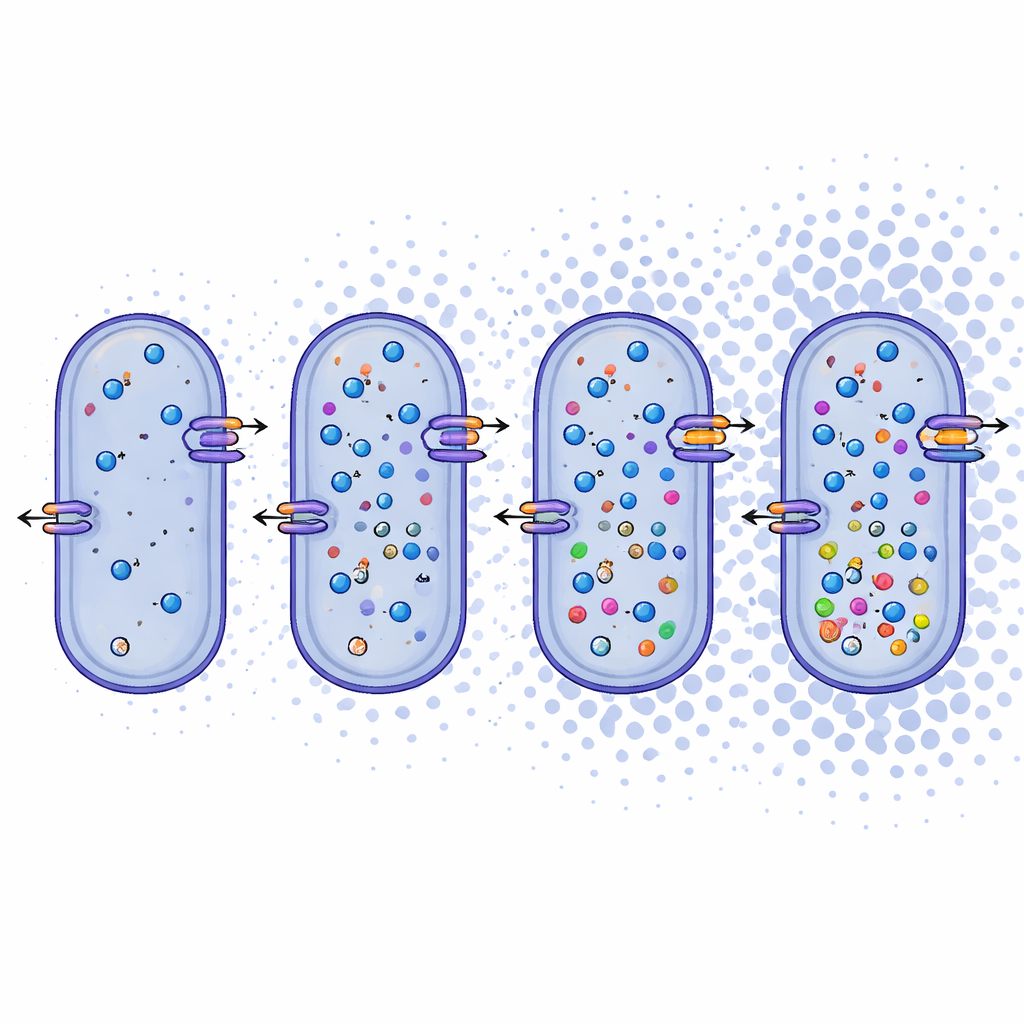
Kijkend voorbij namen onderzochten de onderzoekers wat de genomen onthullen over hoe deze microben hun bestaan onderhouden. Ze vonden dat Bacillus daqingensis en alle onderzochte Alkalicoccus-soorten gedeelde kernmetabole routes hebben, waaronder standaardpaden voor het afbreken van suikers en een gemodificeerde cyclus, het glyoxylaatshunt genoemd, die helpt koolstof te besparen onder stress. Het meest opvallend draagt het genoom een rijk arsenaal voor het omgaan met hoge zoutconcentraties. De bacteriën lijken twee complementaire tactieken te gebruiken: "salt-in" systemen die anorganische ionen zoals natrium en kalium over het celmembraan verplaatsen, en "salt-out" systemen die kleine organische moleculen produceren of importeren, zoals betaine, ectoine en bepaalde aminozuren, die als interne dempers tegen uitdroging fungeren. Genen voor ionentransporteurs, antiporters en de biosynthese van deze compatibele oplosmiddelen komen over het hele geslacht voor en wijzen op een robuuste, flexibele reactie op osmotische stress.
Bewijzen wie wie is
Om de taxonomische vraag te beslechten, vergeleken de auteurs volledige genomen met behulp van meerdere numerieke maatstaven die nu standaard zijn in de microbiële systematiek. Average nucleotide identity (ANI) meet hoe vergelijkbaar de DNA-sequenties over het hele genoom zijn, terwijl average amino acid identity (AAI) hetzelfde doet op eiwitniveau. Tussen Bacillus daqingensis en Alkalicoccus luteus bereikte de ANI 98,2 procent en de AAI 98,5 procent — ruim boven de gebruikelijke grenswaarden die worden gebruikt om dezelfde soort en zelfs hetzelfde geslacht te definiëren. Fylogenetische bomen opgebouwd uit vele genen, samen met vergelijkingen van gedeelde eiwitclusters, toonden aan dat deze twee stammen zich strak groeperen en meer genclusters met elkaar delen dan met enige andere Alkalicoccus-soort. Traditionele kenmerken zoals celvorm, vetzuurprofielen en belangrijke biochemische reacties waren ook in wezen identiek tussen hen.
Wat dit betekent voor microbinaire namen
Samengenomen alle bewijslijnen concludeert de studie dat Bacillus daqingensis geen distinct soort bacterie vertegenwoordigt. In plaats daarvan hoort het tot het geslacht Alkalicoccus en is het dezelfde soort als Alkalicoccus luteus, eerder bekend als Bacillus luteus. De auteurs stellen formeel de nieuwe combinatienaam Alkalicoccus daqingensis voor en behandelen deze, samen met de oudere Bacillus-naam, als latere synoniemen van Bacillus luteus/Alkalicoccus luteus. Voor niet-specialisten is de conclusie dat zorgvuldige genoomsequencing kan aantonen wanneer verschillende labels in feite voor hetzelfde microbe worden gebruikt, wat helpt het naamgevingssysteem op te schonen. Tegelijkertijd benadrukt het werk hoe deze zoutminnende bacteriën vertrouwen op een combinatie van ionenpompen en beschermende moleculen om te overleven in omgevingen die anders te zout zouden zijn voor leven.
Bronvermelding: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Trefwoorden: halofiele bacteriën, genoomsequencing, microbiële taxonomie, aanpassing aan zoutstress, Alkalicoccus luteus