Clear Sky Science · nl
Geautomatiseerde en robuuste niet-rigide registratie van seriële sectie-microscopiebeelden met PiCNoR
Weefsel driedimensionaal bekijken zonder details te verliezen
Moderne biologie berust vaak op het omzetten van dunne weefsellagen in volledige 3D-weergaven van organen en hersenen. Maar wanneer elke microscopische sectie wordt gesneden, gekleurd en gefotografeerd, kan ze uitrekken, scheuren of verschuiven. Als deze secties niet correct op elkaar worden uitgelijnd, kan het resulterende 3D-beeld misleidend zijn. Dit artikel introduceert een nieuwe computermethode genaamd PiCNoR die onderzoekers helpt dergelijke beelden nauwkeuriger en automatisch uit te lijnen, zodat fijne structuren in embryo’s en hersenen behouden blijven in 3D-reconstructies.
Waarom het uitlijnen van secties zo moeilijk is
Om een 3D-weergave te bouwen, fotograferen onderzoekers lange reeksen ultradunne secties die uit hetzelfde weefselstuk zijn genomen. In theorie zou elke sectie perfect boven de vorige moeten passen, als kaarten in een keurig gestapelde stapel. In de praktijk kan elke sectie tijdens het snijden en kleuren op een iets andere manier vervormen. Kleuren kunnen variëren, delen kunnen uitrekken en kenmerken kunnen verschuiven. Traditionele “rigide” uitlijningsmethoden veronderstellen dat een hele sectie slechts verschuift of roteert, wat vaak niet toereikend is. Flexibelere, “elastische” methoden bestaan, maar die kunnen traag zijn, vereisen zorgvuldige afstemming door experts of zijn sterk afhankelijk van beeldhelderheid, die van sectie tot sectie kan veranderen.
Een nieuwe aanpak: lokale stukjes die samenwerken
PiCNoR kiest een andere, meer lokale benadering van het probleem. In plaats van te proberen een heel beeld in één keer te buigen, verdeelt het eerst elke sectie in veel regio’s op basis van het patroon van kenmerken in het beeld. Binnen elke regio vindt de methode matchende punten tussen twee aangrenzende secties met behulp van robuuste feature-detectie en schat hoe die regio moet roteren en verschuiven om op elkaar uit te lijnen. Deze lokale bewegingen worden vervolgens gecontroleerd op plausibiliteit en zachtjes gecombineerd, zodat elke pixel in de sectie een beweging krijgt die informatie uit omliggende regio’s soepel mengt. Het resultaat is een flexibele, “niet-rigide” uitlijning die toch gecontroleerd en realistisch blijft.
Het de data laten kiezen van de juiste complexiteit
Een belangrijke uitdaging bij elke regiogebaseerde methode is beslissen hoeveel regio’s te gebruiken: te weinig en de methode kan fijne vervormingen niet corrigeren; te veel en hij wordt instabiel en traag. Eerdere benaderingen waren vaak afhankelijk van proef en fout en het herhaaldelijk visueel controleren van de resultaten. PiCNoR vermijdt deze handmatige afstemming door een statistisch hulpmiddel te gebruiken, het Bayesian information criterion, dat automatisch de hoeveelheid detail afstemt tegen het risico van overfitting. In de praktijk betekent dit dat het algoritme zelf kan beslissen hoeveel regio’s nodig zijn voor een gegeven dataset, zonder menselijke supervisie, wat tijd bespaart en biais vermindert.
Resultaten betrouwbaar en efficiënt houden
Niet elke geschatte lokale beweging is betrouwbaar—sommige kunnen vervormd worden door ruis of slechte matches. PiCNoR pakt dit aan door elke regio als een knooppunt in een graaf te representeren, waar aangrenzende regio’s elkaar beïnvloeden. Bewegingen die onrealistisch lijken qua rotatie of verschuiving worden vervangen door een gewogen gemiddelde van de betrouwbaardere bewegingen in de buurt. Een compacte wiskundige representatie helpt deze bewegingen efficiënt te combineren. Ten slotte wordt de verplaatsing van elke pixel berekend als een kansgewogen mengsel van de regionale bewegingen, waardoor overgangen tussen regio’s soepel blijven, zonder plotselinge knikken of plooien in het weefsel.
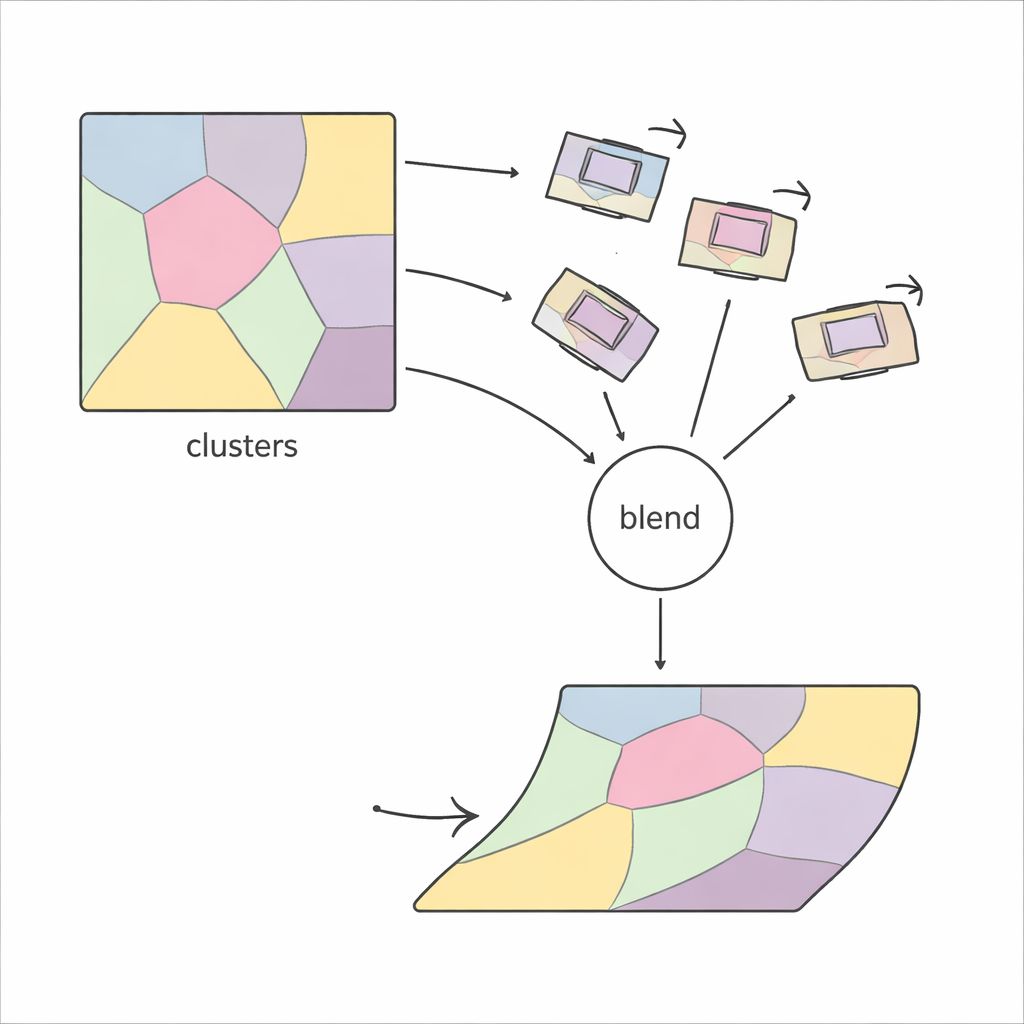
Aantonen dat het werkt op echte biologische data
De onderzoekers testten PiCNoR op drie zeer verschillende datasets: menselijke embryosecties uit de Kyoto-collectie, een elektronenmicroscopie-stack van een nervenstreng van de fruitvlieg, en een nieuwe lichtmicroscopie-stack van de hippocampus van een rattenbrein. Over deze voorbeelden heen produceerde PiCNoR consequent een betere overlap tussen secties dan standaard rigide en veelgebruikte niet-rigide methoden. Het behield de continuïteit van delicate structuren in 3D-weergaven en voorkwam de overdreven vervormingen die soms bij andere tools worden gezien. Belangrijk is dat het dit deed met minder lokale regio’s dan sommige concurrenten, en met rekenkosten die praktisch blijven voor grote stacks.
Wat dit betekent voor toekomstig 3D-microscopieonderzoek
Voor niet-specialisten is de kernboodschap dat PiCNoR een betrouwbaardere manier biedt om stapels 2D-microscoopbeelden om te zetten in getrouwe 3D-reconstructies. Door automatisch te bepalen hoe gedetailleerd de uitlijning moet zijn en door zich te beschermen tegen slechte lokale correcties, behoudt het de ware vormen van weefsels terwijl de verwerkingstijd beheersbaar blijft. Dit maakt het voor biologen en pathologen eenvoudiger om te vertrouwen op wat ze in 3D zien, of ze nu bestuderen hoe een embryo zich ontwikkelt of hoe hersencellen zijn gerangschikt, en het legt de basis voor nauwkeurigere, geautomatiseerde analyse van complexe microscopische datasets.
Bronvermelding: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Trefwoorden: 3D-microscopie, beeldregistratie, hersenbeeldvorming, histologie, niet-rigide uitlijning