Clear Sky Science · nl
Darmmicrobiota en resistoomprofielen van Zwitserse expatriates in Afrika onthuld door Nanopore‑metagenomica
Waarom je darmmicroben veranderen als je in het buitenland woont
Veel mensen wonen maanden of jaren in het buitenland, vaak op plaatsen waar antibioticum‑resistente bacteriën veel voorkomen. Deze studie stelt een eenvoudige maar belangrijke vraag: veranderen de gemeenschap van microben en de resistentiegenen in hun darmen op manieren die hun gezondheid en de bredere verspreiding van antimicrobiële resistentie kunnen beïnvloeden wanneer Zwitserse expatriates in Afrikaanse landen wonen met een hoge last van medicijnresistente infecties?
De onzichtbare gemeenschap in ons
In onze darmen leven biljoenen microben, voornamelijk bacteriën, die helpen bij de vertering van voedsel, het trainen van het immuunsysteem en het afweren van schadelijke microben. Naast deze nuttige microben bestaat het “resistoom” – de verzameling genen die bacteriën resistent maken tegen antibiotica. Ook gezonde mensen dragen veel van zulke genen. Wanneer mensen verhuizen naar of reizen door regio’s waar multiresistente bacteriën veel voorkomen, kunnen ze stilletjes nieuwe resistentiegenen en mobiele DNA‑elementen, plasmiden genoemd, oppikken die deze genen verspreiden. Begrijpen hoe dit gebeurt is essentieel om wereldwijde antibioticaresistentie te beheersen.
Vergelijking van expats in Europa en Afrika
De onderzoekers analyseerden stoelmonsters van 72 gezonde Zwitserse expatriates die naar Zwitserland terugkeerden: 39 hadden in Afrikaanse landen gewoond en 33 in andere Europese landen. In plaats van bacteriën in het laboratorium te kweken, gebruikten ze een lange‑read DNA‑sequencingtechniek genaamd Nanopore shotgun metagenomica, die al het genetisch materiaal in een monster tegelijk leest. Dit stelde hen in staat te registreren welke bacteriën aanwezig waren (het microbiota) en welke antibioticaresistentiegenen en plasmiden ze droegen (het resistoom en plasmidoom). Elk monster werd tweemaal gesequenced voor betrouwbaarheid, en geavanceerde software werd gebruikt om bacteriegroepen en resistentiegenen te identificeren en langere genoomfragmenten uit het gemengde DNA samen te stellen.
Verrassende stabiliteit van darmmicroben
Ondanks dat in eerder kweekgebaseerd testen meer mensen in de Afrika‑groep gekoloniseerd bleken met multiresistente darmbacteriën, leek de algehele samenstelling van hun darmmicrobiota opmerkelijk vergelijkbaar met die van expats die in Europa hadden gewoond. Maatstaven voor diversiteit – hoeveel verschillende soorten bacteriën aanwezig waren en hoe gelijkmatig ze waren vertegenwoordigd – verschilden niet per continent, en statistische analyses toonden geen duidelijke clustering van monsters uit Afrika versus Europa. In beide groepen domineerden bekende darmbewoners zoals Blautia, Faecalibacterium en Bacteroides, wat erop wijst dat langdurig verblijf in het buitenland niet per se de kernbacteriegemeenschap bij gezonde volwassenen ingrijpend verandert.
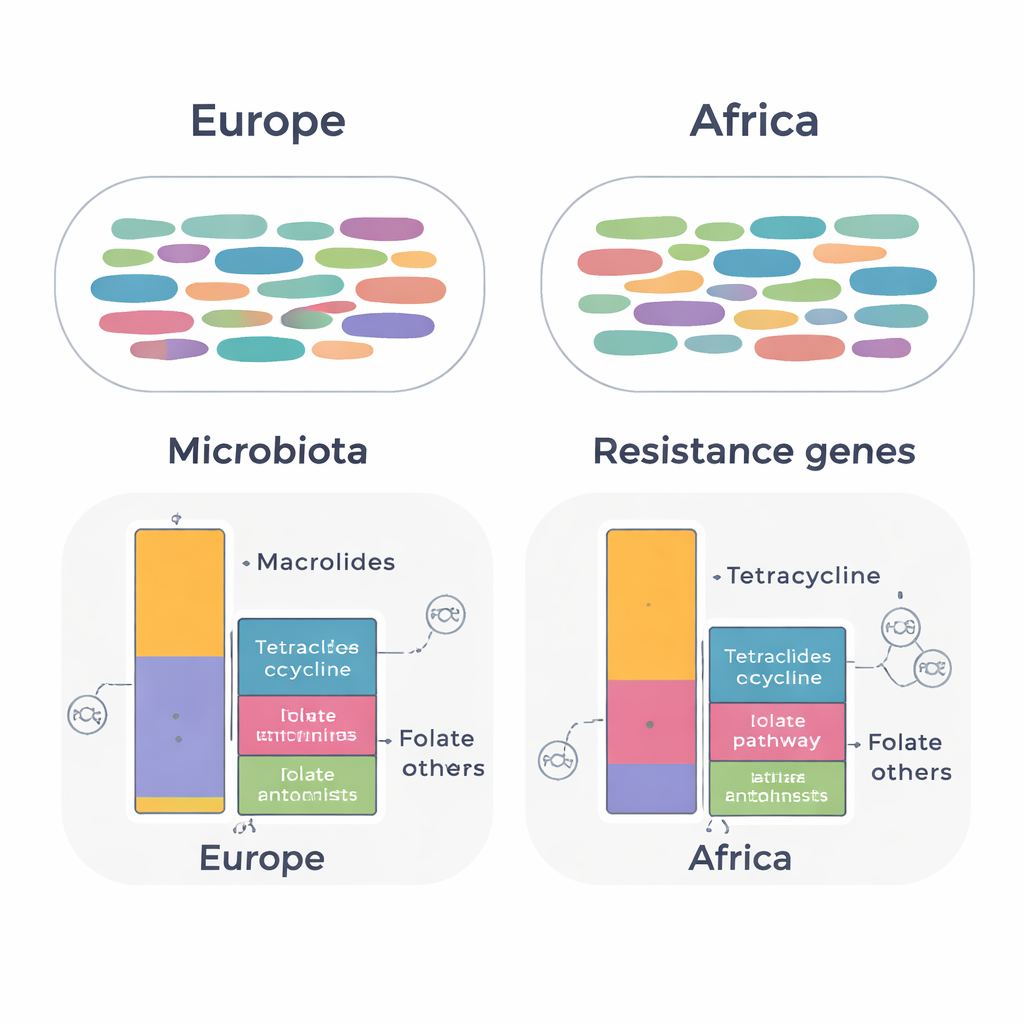
Resistentiegenen en mobiel DNA vertellen een ander verhaal
Toen het team zich richtte op resistentiegenen, kwamen subtielere maar belangrijke verschillen naar voren. In alle monsters samen vonden ze 134 verschillende resistentiegenen behorend tot 14 klassen antibiotica. Het totale patroon van genen was globaal vergelijkbaar tussen de continenten, maar expatriates die in Afrika hadden gewoond droegen hogere niveaus van genen die bacteriën beschermen tegen tetracyclines en middelen die de folaatroute targeten (zoals trimethoprim‑sulfamethoxazol). Ter vergelijking vertoonden expats uit Europese landen hogere niveaus van genen die resistentie tegen macrolide‑antibiotica confereren. Veel van deze genen waren gekoppeld aan veelvoorkomende darmbacteriën, waaronder Ruminococcoides, Bifidobacterium en Bacteroides. Klinisch belangrijke genen, zoals blaCTX‑M‑15, dat gevorderde cefalosporine‑antibiotica kan inactiveren, werden in Escherichia coli uit beide groepen gedetecteerd.
Plasmiden als wereldwijde shuttles voor resistentie
De studie volgde ook plasmiden – kleine, vaak overdraagbare DNA‑cirkels die resistentiegenen tussen bacteriën en door omgevingen transporteren. Met de lange DNA‑reads konden de onderzoekers soms resistentiegenen en plasmide “replicon” markers op hetzelfde geassembleerde DNA‑fragment zien, waarmee werd bevestigd dat ze samen reizen. Ze identificeerden 46 verschillende plasmidtypen, sommige uniek voor elk continent en andere gedeeld. Opvallend droegen bepaalde plasmiden meerdere resistentiegenen en leken op plasmiden die bekend zijn uit menselijke, dierlijke, voedsel‑ en afvalwaterbronnen in verschillende delen van de wereld. Eén plasmidtype dat vaak gekoppeld is aan Enterococcus‑bacteriën en in kippen en afvalwater is aangetroffen, kwam vaker voor in feces van expats in Afrika, wat benadrukt hoe voedsel, dieren en de omgeving allemaal kunnen bijdragen aan wat in onze darmen terechtkomt.
Wat dit betekent voor het dagelijks leven en de volksgezondheid
Voor een lezer zonder specialistische achtergrond is de kernboodschap dat alleen wonen in een risicovolle regio niet lijkt te leiden tot een ingrijpende herinrichting van welke darmbacteriën je herbergt, maar dat het wél de samenstelling van antibioticaresistentiegenen en de mobiele DNA‑elementen die ze verspreiden kan wijzigen. Deze verborgen veranderingen, deels gevormd door lokale patronen van antibioticagebruik, kunnen van belang zijn voor toekomstige infecties en voor hoe resistentiekenmerken zich verplaatsen tussen mensen, dieren en de omgeving. Het werk toont ook aan dat draagbare lange‑read sequencing kan fungeren als een vroegtijdig waarschuwingssysteem, dat laat zien hoe resistentiegenen en plasmiden circuleren bij gezonde reizigers en expatriates voordat ze ziekte veroorzaken.
Bronvermelding: Campos-Madueno, E.I., Aldeia, C. & Endimiani, A. Gut microbiota and resistome profiles of Swiss expatriates in Africa revealed by Nanopore metagenomics. Sci Rep 16, 7016 (2026). https://doi.org/10.1038/s41598-026-38302-3
Trefwoorden: darmmicrobioom, antibioticaresistentie, expatriates, plasmiden, metagenomica