Clear Sky Science · nl
Een methode voor het detecteren van structurele varianten met Hi-C-contactmatrix en neurale netwerken
Waarom het buigen van DNA in 3D ertoe doet
Ons DNA wordt vaak als een eenvoudige reeks letters afgebeeld, maar binnen elke cel vouwt het zich tot een complexe driedimensionale vorm. Wanneer grote stukken van deze keten worden verwijderd, omgekeerd of verplaatst — veranderingen die structurele variaties worden genoemd — kunnen ze genen verstoren en kanker bevorderen. Deze studie introduceert VarHiCNet, een nieuw kunstmatig-intelligentiesysteem dat 3D-kaarten van DNA-vouwing leest en deze risicovolle grootschalige veranderingen nauwkeuriger opspoort dan bestaande hulpmiddelen, en zo een nieuwe manier biedt om kankergenomen en andere ziekten te bestuderen.
Genoomveranderingen zien via 3D-contactkaarten
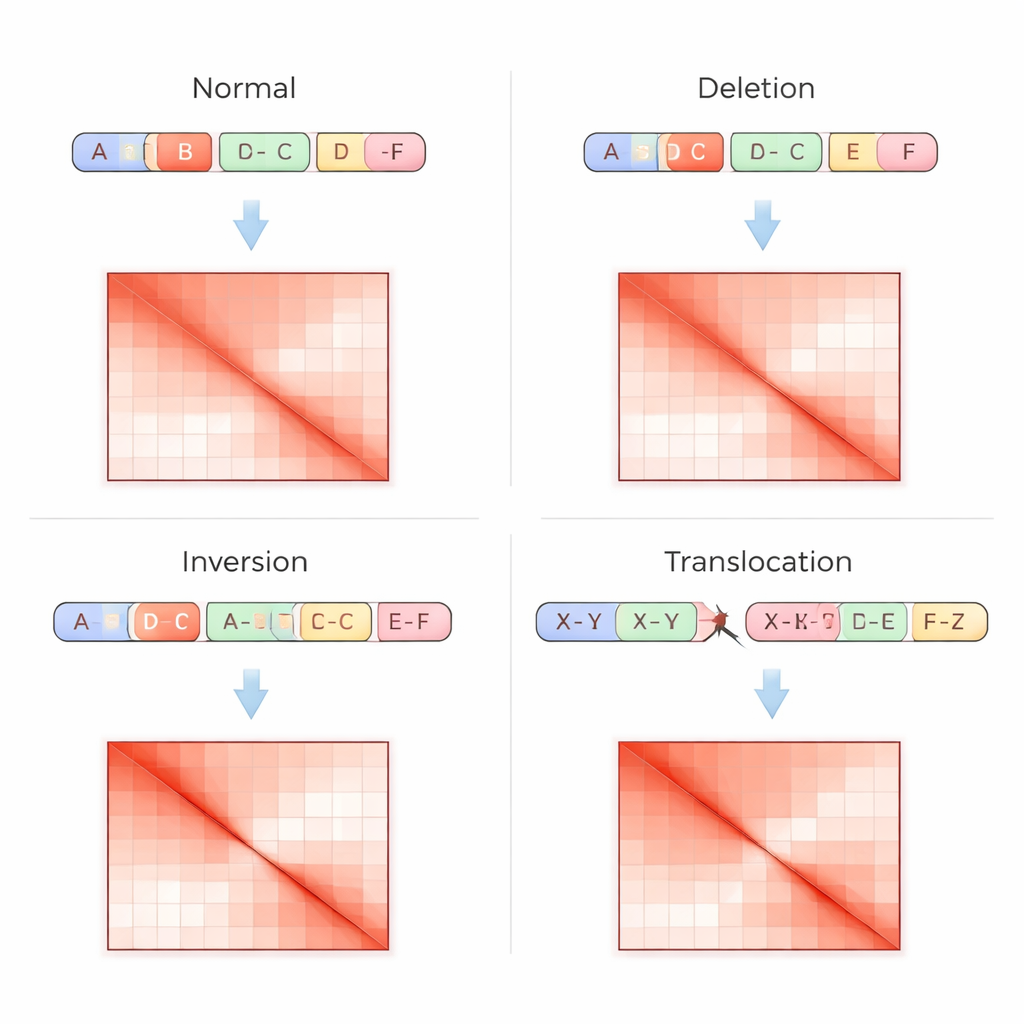
Traditionele genoomtests lezen DNA als een rechte volgorde, wat het moeilijk maakt complexe herschikkingen te herkennen, vooral in repetitieve regio’s of wanneer stukken worden verplaatst zonder kopieaantal te veranderen. De Hi-C-techniek pakt het probleem anders aan: ze meet hoe vaak verre delen van het DNA elkaar fysiek raken in de kern en registreert deze contacten als een raster, of contactmatrix, waarbij fellere plekken sterkere interactie aangeven. Structurele variaties laten kenmerkende vingerafdrukken achter in deze matrices — zoals ontbrekende strepen waar een regio is verwijderd, gespiegeld patroon wanneer een segment is omgekeerd, of niet-diagonale hotspots waar twee chromosomen zijn gefuseerd. VarHiCNet is ontworpen om deze visuele patronen automatisch te herkennen.
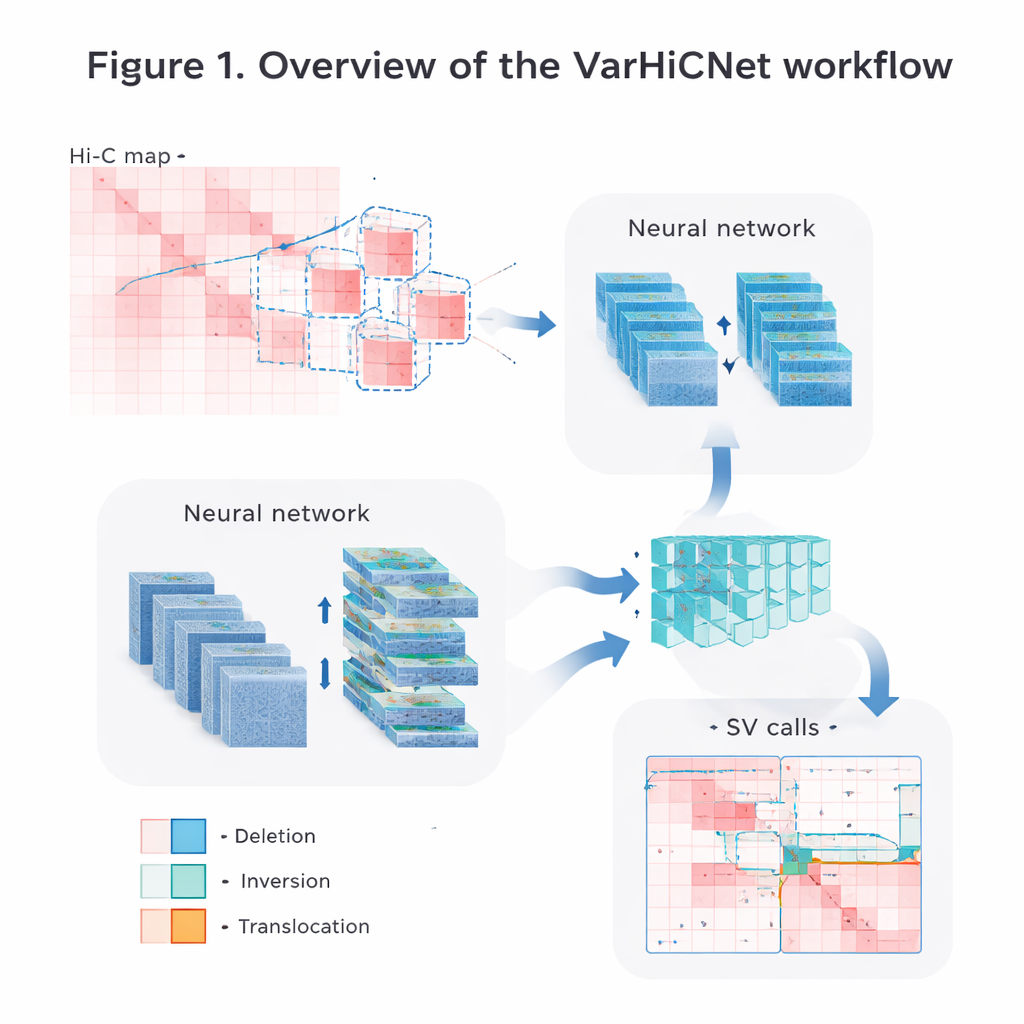
Genoomkaarten omzetten in afbeeldingen voor AI
De auteurs zetten de ruwe Hi-C-contactgegevens om in beelden die computervisiesystemen gemakkelijk kunnen verwerken. Eerst normaliseren ze de matrices zorgvuldig om de natuurlijke afname in contactfrequentie bij toenemende afstand te corrigeren, terwijl zowel nabij- als lange-afstandsinteracties behouden blijven. Daarna scannen ze elk chromosoom met overlappende vierkante vensters en knippen veel kleinere submatrices uit. Elke submatrix wordt geschaald naar een gestandaardiseerde kleurafbeelding van 800 bij 800 pixels, waarbij verschillende contactsterkten in roodachtige intensiteiten over drie kleurkanalen worden weergegeven. Deze afbeeldingsachtige representatie stelt het model in staat krachtige technieken te hergebruiken die oorspronkelijk zijn ontwikkeld voor het herkennen van objecten in foto’s.
Trucs lenen uit objectdetectie
VarHiCNet behandelt elke potentiële structurele variant alsof het een "object" in een afbeelding is. Het bouwt voort op een modern objectdetectieraamwerk genaamd RT-DETR, dat een combinatie van convolutionele neurale netwerken en Transformers gebruikt om belangrijke regio’s te markeren. Een ResNet-backbone haalt eerst multischalige kenmerken naar voren: ondiepe lagen behouden fijne details die nodig zijn om exacte breekpunten te lokaliseren, terwijl diepere lagen bredere patronen vangen die wijzen op grote gebeurtenissen. Een feature-fusiemodule mengt daarna informatie uit verschillende lagen zodat zowel lokale als globale aanwijzingen behouden blijven. Een ander aangepast blok, geïnspireerd door spatial pyramid pooling, past aan hoeveel van de omliggende regio het model tegelijk ‘ziet’, waardoor het gevoelig wordt voor varianten die alles kunnen overspannen van relatief kleine tot zeer grote stukken DNA.
Van kandidaatregio’s naar precieze varianttypes
Zodra VarHiCNet kandidaatregio’s in de Hi-C-afbeelding heeft voorgesteld, moet het deze verfijnen tot exacte breekpunten en specifieke varianttypes, zoals deleties, inversies, duplicaties of translocaties. Hiervoor zoemt het systeem in op de omgeving rond elk voorspeld breekpunt en reduceert de complexiteit met een wiskundige techniek genaamd hoofcomponentenanalyse (PCA), die uitlicht waar het contactpatroon het scherpst verandert. Deze compacte representaties worden vervolgens gevoed aan een Transformer-gebaseerde classifier die subtiele verschillen in de lokale patronen voor elk variantcategorie leert. Het resultaat is een gedetailleerde aanroep voor elk evenement: waar het in het genoom plaatsvindt en welk type structurele verandering het vertegenwoordigt.
Prestaties over verschillende kankercellijnen
De onderzoekers testten VarHiCNet op Hi-C-gegevens uit zes verschillende menselijke kankercellijnen, afkomstig van bloed-, borst-, hersen-, nier-, long- en prostaatstumoren. Met een hoogbetrouwbare catalogus van bekende structurele varianten als gouden standaard vergeleken ze hun methode met verschillende toonaangevende tools die ook Hi-C-gegevens analyseren. Zowel voor gebeurtenissen binnen hetzelfde chromosoom als tussen chromosomen behaalde VarHiCNet over het algemeen hogere of vergelijkbare F1-scores, wat betekent dat het de gevoeligheid en nauwkeurigheid beter in balans bracht dan andere benaderingen. Het was bijzonder sterk in het detecteren van gebalanceerde translocaties en inversies — herschikkingen die in standaard DNA-sequencing vaak weinig sporen achterlaten maar duidelijke 3D-vouwsignaturen zeigen. De auteurs toonden ook aan dat hun ontwerpkeuzes, zoals de beeldresolutie en feature-fusiemodules, de prestaties consequent verbeterden in gecontroleerde tests.
Wat dit betekent voor het begrijpen van ziekte
Simpel gezegd geeft VarHiCNet wetenschappers een slimmer manier om te "kijken" naar hoe het genoom in 3D vouwt en om grote, ziektegerelateerde herschikkingen op te sporen die conventionele sequencing mogelijk mist. Door complexe contactkaarten om te zetten in afbeeldingen en moderne vision-achtige neurale netwerken toe te passen, kan de methode veel soorten structurele variatie met hoge betrouwbaarheid detecteren en categoriseren in verschillende kankerceltypen. Hoewel het nog moeite heeft met sommige zeer kleine of sterk verwarde veranderingen en afhankelijk is van ruime trainingsdata, wijst VarHiCNet op een toekomst waarin 3D-genoomarchitectuur een routinematig onderdeel wordt van hoe we de genetische veranderingen lezen, interpreteren en uiteindelijk aanpakken die ten grondslag liggen aan kanker en andere aandoeningen.
Bronvermelding: Shen, J., Wang, H., Zhai, H. et al. A method for structural variant detection using Hi-C contact matrix and neural networks. Sci Rep 16, 7324 (2026). https://doi.org/10.1038/s41598-026-37678-6
Trefwoorden: structurele variatie, Hi-C, deep learning, kankergenomica, 3D-genoom