Clear Sky Science · nl
Een genoom-structuur adaptief kader voor ROH-gebaseerde inteeltinschatting in Penaeus vannamei
Waarom garnalenstambomen ertoe doen voor uw bord
Moderne garnalenkwekerijen leveren een groot deel van ’s werelds zeevruchten, maar het herhaald fokken binnen dezelfde familielijnen kan hun gezondheid langzaam aantasten. Wanneer nauwe verwanten zich voortplanten, kunnen schadelijke verborgen genen gekoppeld raken, wat groei, overleving en ziekteweerstand vermindert. Deze studie stelt een ogenschijnlijk eenvoudige vraag met grote implicaties voor de wereldwijde aquacultuur: hoe kunnen we inteelt bij gekweekte garnalen nauwkeurig meten zodat voorraden gezond en productief blijven?
Verborgen genetische sporen van inteelt
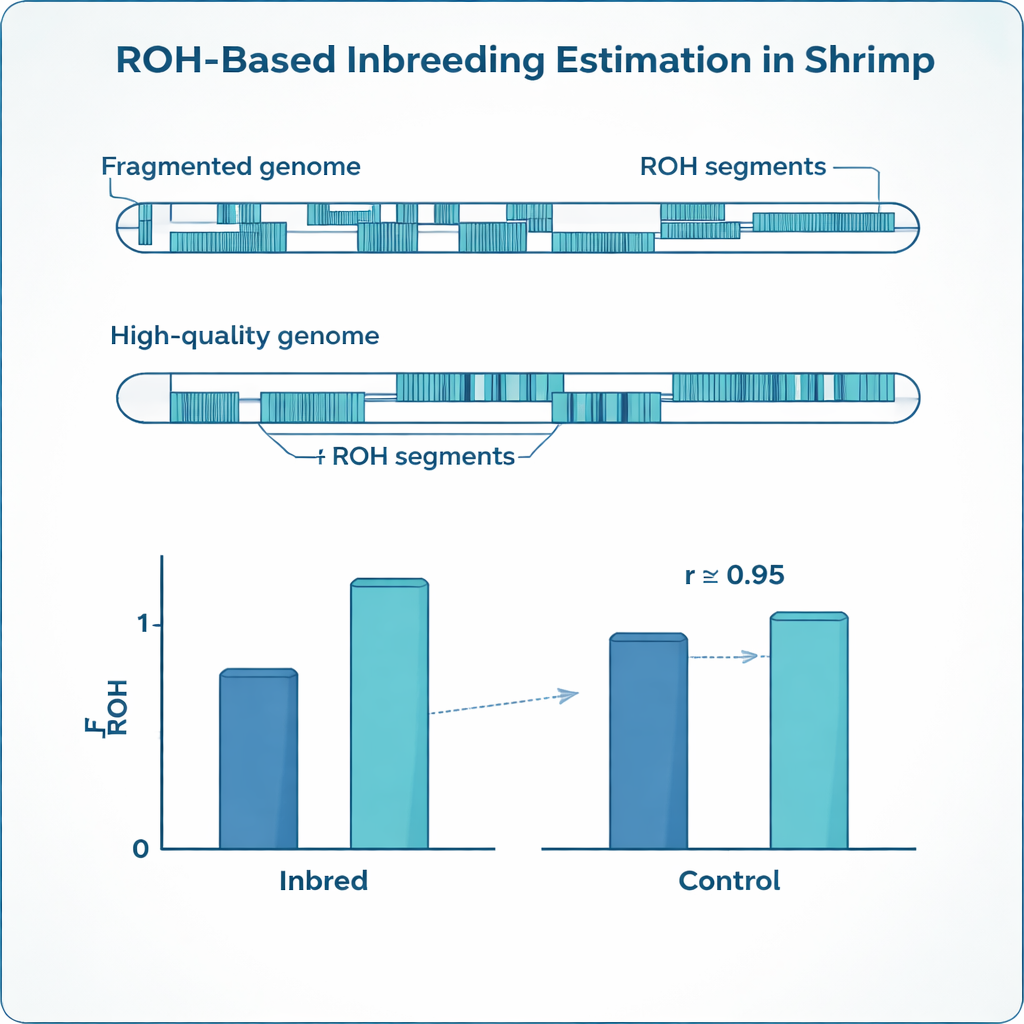
Inteelt laat karakteristieke sporen in het DNA achter. In plaats van twee licht verschillende versies van veel genen te dragen, hebben inteeltdieren vaak lange stukken waarbij beide kopieën identiek zijn. Genetici noemen deze stukken “runs of homozygosity” (ROH). Door op te tellen welk deel van het genoom van een dier binnen deze runs valt, kunnen onderzoekers het inteeltniveau preciezer inschatten dan met papieren stambomen, die vaak onvolledig zijn of fouten bevatten. Deze ROH-gebaseerde maat, bekend als FROH, is standaard geworden bij runderen, varkens en ander vee, maar garnaalgenomen vormen een speciale uitdaging waardoor kant-en-klare methoden onbetrouwbaar kunnen zijn.
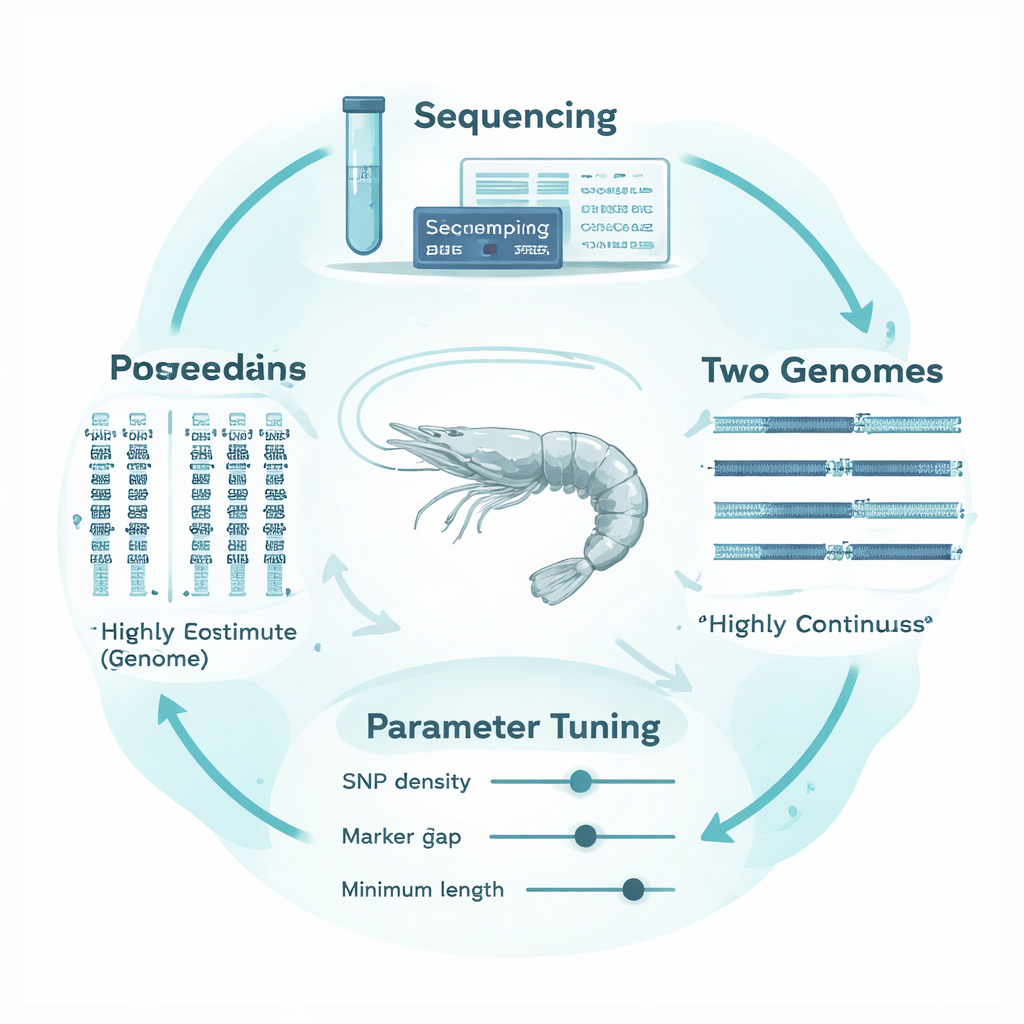
Waarom garnaalgenomen extra lastig zijn
De witte garnaal (Penaeus vannamei), de meest gekweekte garnaal ter wereld, heeft een sterk gefragmenteerd en complex genoom. In plaats van lange, continue chromosoomreeksen zijn veel beschikbare genoomkaarten gebroken in duizenden kleinere stukken, gescheiden door gaten en repetitieve regio’s. Genetische markers zijn ongelijkmatig verspreid over dit lappendeken, en de soort heeft een zeer hoge genetische diversiteit. Methoden en software-instellingen die oorspronkelijk zijn afgestemd op nette, goed in kaart gebrachte zoogdiergenomen kunnen daarom technische hiaten verwarren met echte onderbrekingen in ROH, of korte, achtergrondovereenkomsten aanzien voor echte tekenen van inteelt. Het resultaat is een groot risico op foutieve inschattingen van hoe inteelt een garnaal daadwerkelijk is.
Een genoom-bewuste meetlat bouwen
Om dit op te lossen ontwierpen de auteurs een “genoom-structuur adaptief” kader dat de ROH-analyse afstemt op de eigenaardigheden van garnaal-DNA. Ze creëerden dertien sterk inteeltfamilies onder gecontroleerde paringen en sekveneerden diep de genomen van vijf van deze families plus hun ouders. Cruciaal is dat ze dezelfde sequentiegegevens uitlijnden op twee verschillende referentiegenomen: één oudere, gefragmenteerde assemblage en een nieuwere, zeer continue versie. Met het veelgebruikte analysetool PLINK testten ze systematisch hoe acht kerninstellingen ROH-aanroepen beïnvloedden, met aandacht voor drie instellingen die bijzonder gevoelig zijn voor genoomstructuur: hoe dicht markers op elkaar moeten staan, hoe groot een gat tussen markers binnen een run mag zijn, en hoe lang een run minimaal moet zijn om te tellen. Ze bouwden empirische, niet-overlappende genomische vensters om lokale markerafstand en ontbrekende data bij te houden, en gebruikten de “genomische dekking” van deze vensters, samen met de stabiliteit van FROH en ROH-lengtes, als objectieve richtlijnen voor het kiezen van verstandige drempels.
Verschillende knoppen, hetzelfde beeld van inteelt
De geoptimaliseerde instellingen bleken sterk te verschillen tussen de twee referentiegenomen. Het gefragmenteerde genoom vereiste veel dichtere markers, kortere toegestane gaten en kortere minimale runlengtes dan het hoogwaardige genoom om te voorkomen dat echte ROH in veel kleine stukjes worden gebroken. Toch convergeerden na het apart afstemmen van deze instellingen de inteeltinschattingen van beide referenties: de gemiddelde FROH in de inteeltgarnalen was in beide gevallen ongeveer 0,24, wat goed overeenkomt met de verwachte waarde uit de geplande paringen en sterk met elkaar overeenstemde. Tegelijkertijd toonde het meer continue genoom minder maar veel langere ROH-segmenten, terwijl de gefragmenteerde kaart veel van die segmenten in korte stukjes sneed. De studie bracht ook opvallende verschillen aan het licht tussen volbloedbroers en -zussen: zelfs binnen dezelfde familie varieerden de inteeltniveaus sterk, iets wat eenvoudige stamboekgegevens niet kunnen vastleggen.
Scherpere instrumenten voor gezondere garnaalvoorraden
Voor niet-specialisten is de belangrijkste boodschap helder: inteelt meten aan de hand van DNA kan bij gekweekte garnalen zeer nauwkeurig zijn, maar alleen als de methode rekening houdt met de onderliggende genoomstructuur. Door een praktisch recept te bieden om ROH-analyse af te stemmen op gefragmenteerde kreeftachtige genomen, stelt dit werk fokkers in staat inteelt per dier te monitoren in plaats van te vertrouwen op onvolmaakte familiekaarten. Dat kan op zijn beurt helpen bij het ontwerpen van paringsplannen die de genetische diversiteit behouden terwijl groei en veerkracht worden verbeterd, wat bijdraagt aan duurzamere garnaalkweek en een model biedt voor andere aquacultuursoorten met vergelijkbare genoomuitdagingen.
Bronvermelding: Zou, X., Zhou, H., Liu, M. et al. A genome-structure adaptive framework for ROH-based inbreeding estimation in Penaeus vannamei. Sci Rep 16, 6769 (2026). https://doi.org/10.1038/s41598-026-37622-8
Trefwoorden: garnalenfokkerij, inteelt, genomische selectie, runs of homozygosity, aquacultuurgenetica