Clear Sky Science · nl
Snel leren-vrije organoïdekwantificatie en tracking met OrganoSeg2
Waarom klein in het lab gekweekt weefsel ertoe doet
In laboratoria over de hele wereld kweken wetenschappers nu miniatuurversies van menselijk weefsel, organoïden genoemd. Deze kleine, 3D-klompjes cellen kunnen nabootsen hoe echte organen of tumoren zich gedragen, waardoor ze krachtige instrumenten zijn om ziekte te bestuderen en behandelingen te testen. Maar er is een knelpunt: onderzoekers kunnen duizenden laagvergrotingsmicroscoopbeelden van organoïden verzamelen, maar worstelen met het meten hoe elk exemplaar groeit, van vorm verandert of sterft in de loop van de tijd. Dit artikel introduceert OrganoSeg2, een opnieuw ontworpen software die die simpele, grijze beelden omzet in rijke, betrouwbare metingen van elk individueel organoïde—zonder dat er kunstmatige intelligentie-training of dure beeldopstellingen nodig is.
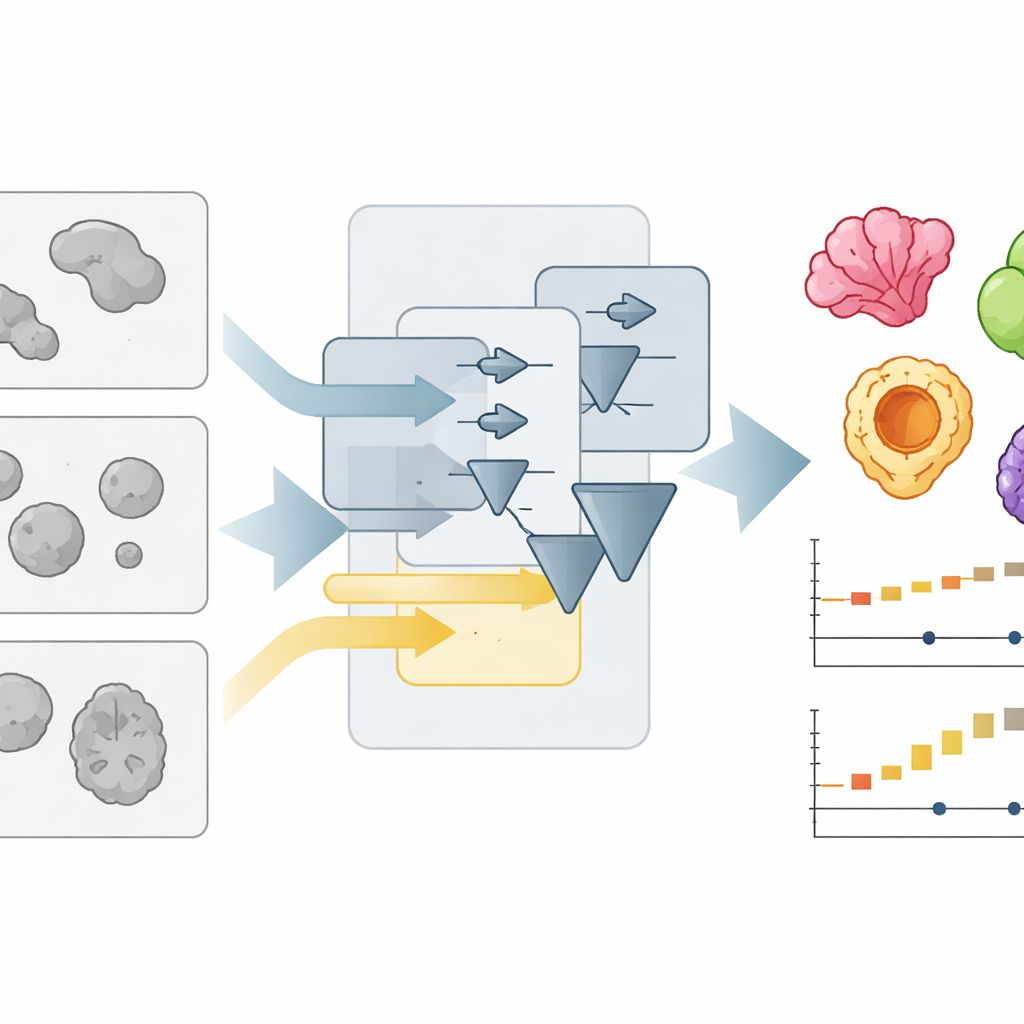
Een nieuwe manier om drukke microscoopbeelden te lezen
Organoïden worden meestal afgebeeld met eenvoudige brightfield-microscopen, waarbij ze verschijnen als vage, overlappende vlekken. Elk vlek automatisch afbakenen—het beeld "segmenteren"—is veel moeilijker dan het lijkt, vooral wanneer laboratoria verschillende kweekformaten, belichting of lenzen gebruiken. De auteurs maakten eerder OrganoSeg, een programma dat basissegmentatie kon verwerken maar traag en omslachtig werd wanneer beeldverzamelingen tot in de honderden groeiden. Met OrganoSeg2 hebben ze de software helemaal opnieuw opgebouwd met een moderne interface, de interne code gestroomlijnd en diverse verborgen instellingen zichtbaar gemaakt zodat gebruikers nauwkeurig kunnen afstemmen hoe het programma organoïden van de achtergrond scheidt, aangrenzende exemplaren splitst en artefacten aan de randen negeert. De app bewaart deze keuzes nu als metadata, zodat analyses reproduceerbaar en deelbaar zijn.
Sneller werken zonder details te verliezen
Buiten flexibiliteit legde het team sterk de nadruk op snelheid en gebruikerservaring. In eerdere versies berekende de software automatisch alle mogelijke metingen voor elk organoïde, zelfs wanneer er maar een paar nodig waren. OrganoSeg2 berekent in plaats daarvan alleen wat de gebruiker selecteert en herstructureert gerelateerde berekeningen zodat tijdrovende stappen efficiënt hergebruikt worden. Het vermindert ook hoeveel informatie op het scherm wordt weergegeven, toont labels alleen wanneer nodig en voegt sneltoetsen en interactieve hulpmiddelen toe om snel puin of niet-organoïde objecten te verwijderen. Deze ontwerpkeuzes verkorten veelvoorkomende handelingen—zoals beelden segmenteren, omtrekken weergeven en gegevens exporteren—ongeveer tien keer, waardoor het praktisch wordt om grote, tegelgewijze beelden en lange timelapse-experimenten op een gewone computer te verwerken.
Dezeert hoogtechnologische concurrenten op echte data
Om te testen hoe goed OrganoSeg2 werkt, vergeleken de auteurs het met meerdere andere segmentatietools, waaronder deep learning-systemen die getraind moeten worden op handmatig gelabelde voorbeelden. Ze stelden beeldsets samen uit zes verschillende bronnen—zoals colon-, long-, pancreas-, hersen- en borstkankerorganoïden, evenals embryoid bodies—waar menselijke experts al de grenzen van organoïden hadden getraceerd. Met een standaard nauwkeurigheidsscore die meet hoeveel de automatische omtrekken overlappen met de handmatige, deed OrganoSeg2 het even goed of beter dan gespecialiseerde tools in de meeste datasets en kwam duidelijk als beste uit de bus bij uitdagende borsttumorbeelden vol los materiaal en vreemd gevormde organoïden. Opmerkelijk is dat OrganoSeg2 deze prestaties bereikte zonder tienduizenden trainingsvoorbeelden en minstens even snel draaide als zijn concurrenten, ook die op basis van kunstmatige intelligentie.
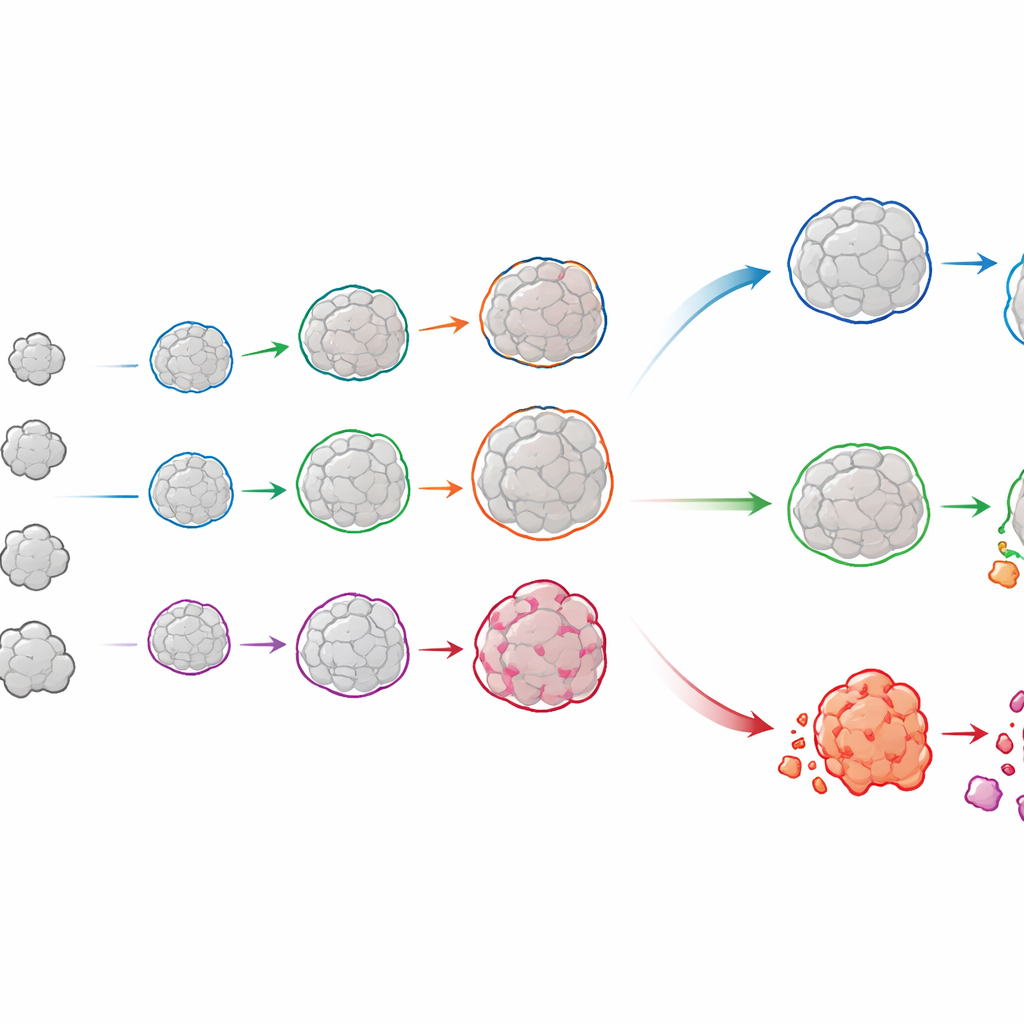
Het levensverhaal van elk organoïde volgen
OrganoSeg2 doet meer dan organoïden in losse snapshots omlijnen. Het kan beelden op verschillende dagen uitlijnen en hetzelfde organoïde door de tijd volgen, waardoor een groeigeschiedenis voor elk exemplaar wordt opgebouwd. Toen de auteurs dit toepasten op organoïden die direct uit patiënten met luminale borstkanker waren gekweekt, zagen ze dat individuele organoïden zelden vloeiend groeiden; veel vertraagden of bereikten een plateau, wat spiegelde hoe echte tumoren een mix van snel en langzaam groeiende regio’s bevatten. Door deze trajecten te passen op een eenvoudig groeimodel kon het team zowel kwantificeren hoe snel elk organoïde uitgroeide als hoe groot het waarschijnlijk zou worden. Vergelijking van deze patronen tussen patiënten toonde aan dat tumoren met vergelijkbare totale groei zeer verschillende samenstellingen van onderliggende gedragingen konden verbergen—verschillen die van belang kunnen zijn bij het voorspellen van therapierespons.
Kanker cellen zien leven en sterven onder straling
De software koppelt ook brightfield-beelden aan fluorescente kleurstoffen die de gezondheid van cellen aangeven. In nieuwe experimenten stelden de auteurs borstkankerorganoïden bloot aan stralingsdoses vergelijkbaar met die in de kliniek en kleurden ze met een live-cell marker die oplicht tijdens geprogrammeerde celdood, plus een tweede kleurstof die dode cellen op het eindpunt onthult. OrganoSeg2 gebruikte het brightfield-beeld om de organoïdevorm te definiëren en mat vervolgens de fluorescente signalen binnen elk exemplaar over meerdere dagen. Dit stelde het team in staat om, organoïde per organoïde, bij te houden wanneer straling celdood veroorzaakte en hoe sterk. Sommige patiëntenorganoïden reageerden nauwelijks, terwijl andere hoge gevoeligheid vertoonden zelfs bij lagere doses, wat de variabiliteit in tumorrespons onderstreept.
Wat dit betekent voor toekomstig onderzoek en zorg
Gezamenlijk laat het werk zien dat zorgvuldige, instelbare beeldverwerking kan wedijveren met of zelfs beter kan zijn dan complexe deep learning-methoden voor een breed scala aan organoïdebeelden, terwijl het transparant en makkelijk bij te stellen blijft. OrganoSeg2 zet eenvoudige, laagvergrotingsfilms van organoïden om in gedetailleerde registers van hoe elk klein weefsel groeit en overleeft onder verschillende omstandigheden. Voor fundamentele onderzoekers biedt het een robuuste manier om de verborgen diversiteit binnen organoïdeculturen te ontleden. Specifiek voor kankeronderzoek opent het de deur om patiënt-afgeleide organoïden niet alleen te gebruiken voor ja‑of‑nee medicatiescreenings, maar voor rijke, tijdsresolutie metingen van groei en celdood die op termijn kunnen helpen behandelingen preciezer af te stemmen.
Bronvermelding: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Trefwoorden: organoïden, beeldanalyse, kankeronderzoek, microscopie, stralingsrespons