Clear Sky Science · nl
Vergelijkende karyotype-analyse van elf Lilium-soorten uit China met FISH en rDNA-oligo-probes
Waarom leliechromosomen buiten het laboratorium ertoe doen
Tuinlelies zijn meer dan mooie bloemen en traditionele geneesmiddelen: ze zijn ook genetische modellen die onderzoekers helpen begrijpen hoe nieuwe plantensoorten ontstaan en hoe ze correct geclassificeerd moeten worden. Deze studie kijkt in de cellen van elf Chinese leliesoorten, waarvan vele als voedsel of medicijn worden gebruikt, om te zien hoe hun chromosomen zijn gerangschikt en gemarkeerd. Door deze verborgen structuren te vergelijken, verduidelijken de auteurs welke lelies werkelijk nauwe verwanten zijn en leveren ze bewijs om langlopende discussies over leliefamiliebanden te beslechten.
Een verwarrende lelie-stamboom ontwarren
Het geslacht Lilium omvat ongeveer 125 soorten verspreid over het noordelijk halfrond, waarbij China een van de belangrijkste centra van diversiteit is. Al meer dan een eeuw proberen botanisten deze soorten in natuurlijke secties te groeperen, grotendeels op basis van zichtbare kenmerken zoals bloemvorm. Maar bloemen die op elkaar lijken betekenen niet altijd nauwe verwantschap, en genetische studies van chloroplasten en kernen hebben soms tegenstrijdige antwoorden gegeven over hoe lelies verwant zijn. In het bijzonder is een groep genaamd Leucolirion en de twee subsecties daarvan (6a en 6b), plus enkele soorten uit zuidwest- en centraal-China, moeilijk met vertrouwen te plaatsen.
Barcodes lezen op chromosomen
Om dit probleem aan te pakken, wenden de auteurs zich tot cytogenetica, de studie van chromosomen. Alle elf bestudeerde soorten delen dezelfde basisset van twaalf chromosomen, gewoonlijk aanwezig als 24 in diploïden; twee populaties van Lilium lancifolium waren triploïd met 36 chromosomen. Onder de microscoop toont elke soort twee grotere chromosomen en tien kleinere, maar subtiele verschillen in vorm en lengte zijn met het blote oog moeilijk te zien. Het team heeft daarom chromosoomgroottes nauwkeurig gemeten en een techniek gebruikt die fluorescentie in situ hybridisatie (FISH) heet om gloeiende DNA-tags aan specifieke ribosomaal DNA (rDNA)-regio's te koppelen, die als heldere barcodes langs elk chromosoom fungeren.
Patronen vinden in lelie-genomen
De onderzoekers brachten twee typen rDNA—5S en 35S—op de chromosomen van elke soort in kaart. De meeste lelies hadden één 5S-locus en tussen twee en zes 35S-loci, vaak op karakteristieke posities. Bijvoorbeeld, vier soorten die traditioneel in subsectie Leucolirion 6a zijn geplaatst (L. leucanthum, L. sargentiae, L. sulphureum en L. regale) deelden zeer vergelijkbare patronen van rDNA-markeringen op dezelfde chromosomenparen, wat wijst op nauwe verwantschap, hoewel L. regale enkele extra veranderingen vertoonde. Daarentegen toonden soorten van de zustergroep 6b en sommige Sinomartagon-lelies duidelijk verschillende rDNA-arrangementen, wat een echte scheiding tussen deze twee groepen bevestigt. Buiten Leucolirion koppelden sterk gedeelde patronen de veel gekweekte L. lancifolium aan L. pumilum en L. davidii, in overeenstemming met eerdere DNA-sequentiestudies die hen samen groeperen.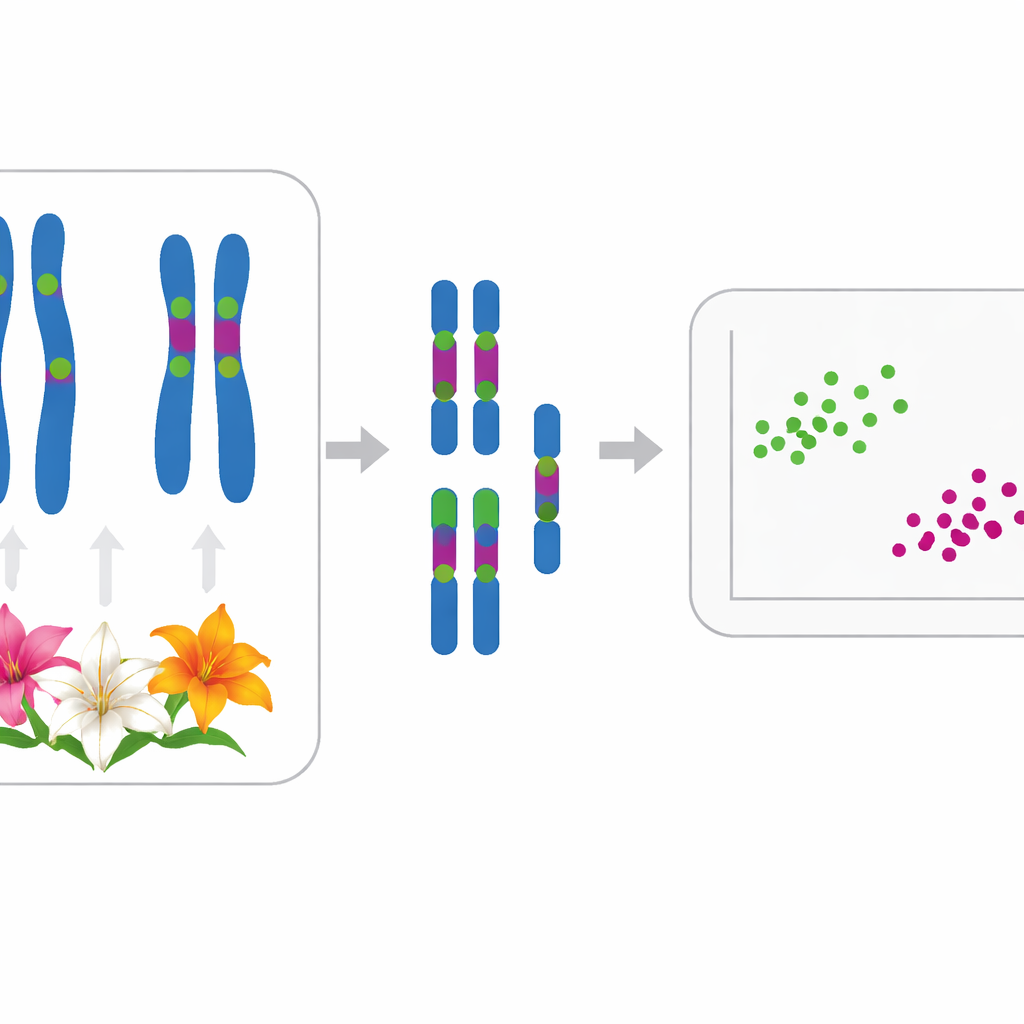
Metingen omzetten in een kaart van verwantschappen
Naast de barcode-posities kwantificeerde het team hoe ongelijk elk karyotype was—zowel in de posities van centromeren (de “taille” van het chromosoom) als in chromosoomlengtes. Ze gebruikten twee statistische indices, MCA en CVCL, om deze kenmerken vast te leggen en plaatsten de elf soorten in een tweedimensionale grafiek. Elke soort nam een eigen duidelijke positie in, wat aantoont dat zelfs ogenschijnlijk vergelijkbare karyotypen te onderscheiden zijn wanneer ze nauwkeurig worden gemeten. Een bredere statistische analyse (principale coördinatenanalyse) groepeerde vervolgens de lelies in twee hoofdclusters die goed overeenkomen met hun veronderstelde evolutionaire geschiedenis. De ene cluster omvatte L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale en de vormen van L. lancifolium en L. davidii; de andere groepering omvatte L. leucanthum, L. sargentiae, L. sulphureum, L. henryi en L. rosthornii.
Wat dit betekent voor naamgeving en gebruik van lelies
Door gedetailleerde chromosoommetingen te combineren met rDNA-barcodekaarten toont deze studie aan dat leliesoorten meer verschillen in hun karyotypen dan eerder gedacht en dat deze verschillen een duidelijk evolutionair signaal dragen. In praktische zin ondersteunt het werk het behandelen van subsectie Leucolirion 6a als een natuurlijke, goed afgebakende groep binnen het geslacht Lilium, in overeenstemming met recente classificatievoorstellen. Voor veredelaars, kruidkundigen en natuurbeschermingsplanners kan een nauwkeuriger beeld van wie met wie verwant is onder lelies kruisingsprogramma's sturen, genetische diversiteit beschermen en ervoor zorgen dat medicinale en eetbare variëteiten correct worden geïdentificeerd en gebruikt.
Bronvermelding: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Trefwoorden: Lilium, chromosomen, fluorescentie in situ hybridisatie, plantevolutie, cytotaxonomie