Clear Sky Science · nl
Geïntegreerde BSI-bacterie-identificator-op-chip met benaderende k-mer-vergelijking
Waarom snellere detectie van ziekteverwekkers ertoe doet
Voor patiënten die levensreddende stamceltransplantaties ondergaan, kunnen infecties in de bloedbaan binnen enkele uren van herstel een medische noodsituatie maken. Artsen weten dat elke minuut telt, maar de huidige laboratoriuminstrumenten om de schuldige bacterie te vinden kunnen traag zijn of krachtige computers vereisen. Deze studie presenteert een klein, energiezuinig computerchipje—PC-CAM genoemd—dat DNA uit patiëntmonsters snel kan scannen en gevaarlijke bacteriën in realtime kan signaleren, mogelijk direct aan het ziekenhuisbed.
Het infectierisico na een darmreddende behandeling
Sommige transplantatiepatiënten ontwikkelen een ernstige complicatie waarbij de gedoneerde immuuncellen de darm van de patiënt aanvallen. Een veelbelovende behandeling is fecale microbiota-transplantatie, waarbij gezonde darmmicroben van een donor in de patiënt worden ingebracht. Hoewel dit de darm kan redden, brengt het soms een extra risico met zich mee: schadelijke darmbacteriën kunnen in de bloedbaan terechtkomen en levensbedreigende infecties veroorzaken. Om deze infecties effectief te behandelen, moeten artsen snel vaststellen welke bacteriesoorten aanwezig zijn, maar traditionele tests kunnen uren tot dagen duren en onbekende stammen over het hoofd zien.
Van traag genoomherstel naar snelle DNA-fragmenten
Moderne DNA-sequencers kunnen genetisch materiaal bijna in realtime rechtstreeks uit bloed- of ontlastingsmonsters lezen. De bottleneck is niet langer het lezen van het DNA, maar het interpreteren ervan. Conventionele methoden proberen eerst volledige genomen te reconstrueren uit miljoenen korte DNA-fragmenten en vergelijken die samengestelde genomen vervolgens met een referentiebibliotheek—een rekenintensief proces. De auteurs vervangen dit door een eenvoudigere strategie: ze splitsen DNA in korte stukjes van vaste lengte, k-mers genoemd, en zoeken deze stukjes rechtstreeks in een database van bekende bacteriële sequenties. In plaats van te eisen dat elke letter exact overeenkomt, verdraagt hun systeem een bepaald aantal verschillen, waardoor het kan omgaan met de onvermijdelijke fouten van DNA-sequencing en natuurlijke mutaties. 
Een slimme geheugenchip gebouwd voor DNA-zoekopdrachten
In het hart van PC-CAM bevindt zich een speciaal type geheugen dat content-addressable memory heet en inkomende data tegelijk aan alles wat het opslaat kan vergelijken. De onderzoekers ontwierpen een "approximate search"-versie van dit geheugen (ACAM) die kan worden afgesteld om bijna-overeenkomsten in plaats van exacte overeenkomsten te accepteren. Elk kort DNA-fragment wordt gecodeerd en als een rij in dit geheugen opgeslagen. Wanneer een nieuw fragment uit een patiëntmonster binnenkomt, activeert de chip een zoeklijn door alle rijen tegelijk en meet hoe snel kleine elektrische signalen ontladen. Door twee stuurelementspanningen aan te passen, stelt het systeem een drempel in voor hoeveel mismatches het tolereert, waarmee het feitelijk instelt hoe vergevingsgezind de overeenkomst moet zijn. Deze vergelijking op hardwareniveau stelt de chip in staat patronen veel sneller en met minder energie te doorzoeken dan een algemene computer.
Hoe goed de chip echte bacteriën vindt
Het team testte PC-CAM op real-world datasets van patiënten die fecale microbiota-transplantatie hadden ondergaan en vergeleek de in hun bloed en ontlasting gedetecteerde bacteriën met de resultaten van een volledige, softwarematige genoomanalyse. Zelfs wanneer de chip slechts een kleine, zorgvuldig gekozen subset van DNA-fragmenten uit elk bacterieel genoom opsloeg, kwam de uitkomst grotendeels overeen met de meer rekenintensieve methode en identificeerde hij belangrijke pathogenen bij meerdere patiënten correct. In uitgebreide experimenten met gesimuleerde DNA-reads van verschillende bacteriën en verschillende foutpercentages nam de gevoeligheid van de chip (het vermogen om echte overeenkomsten te vinden) toe naarmate hij meer verschillen mocht tolereren, terwijl de specificiteit (het vermogen om valse alarmen te vermijden) daalde bij zeer hoge tolerantieniveaus. De auteurs tonen aan dat eenvoudige naverwerkingsstappen—zoals het vereisen van meerdere overeenkomende fragmenten of het weggooien van zwakke overeenkomsten—deze vals-positieven kunnen verminderen. 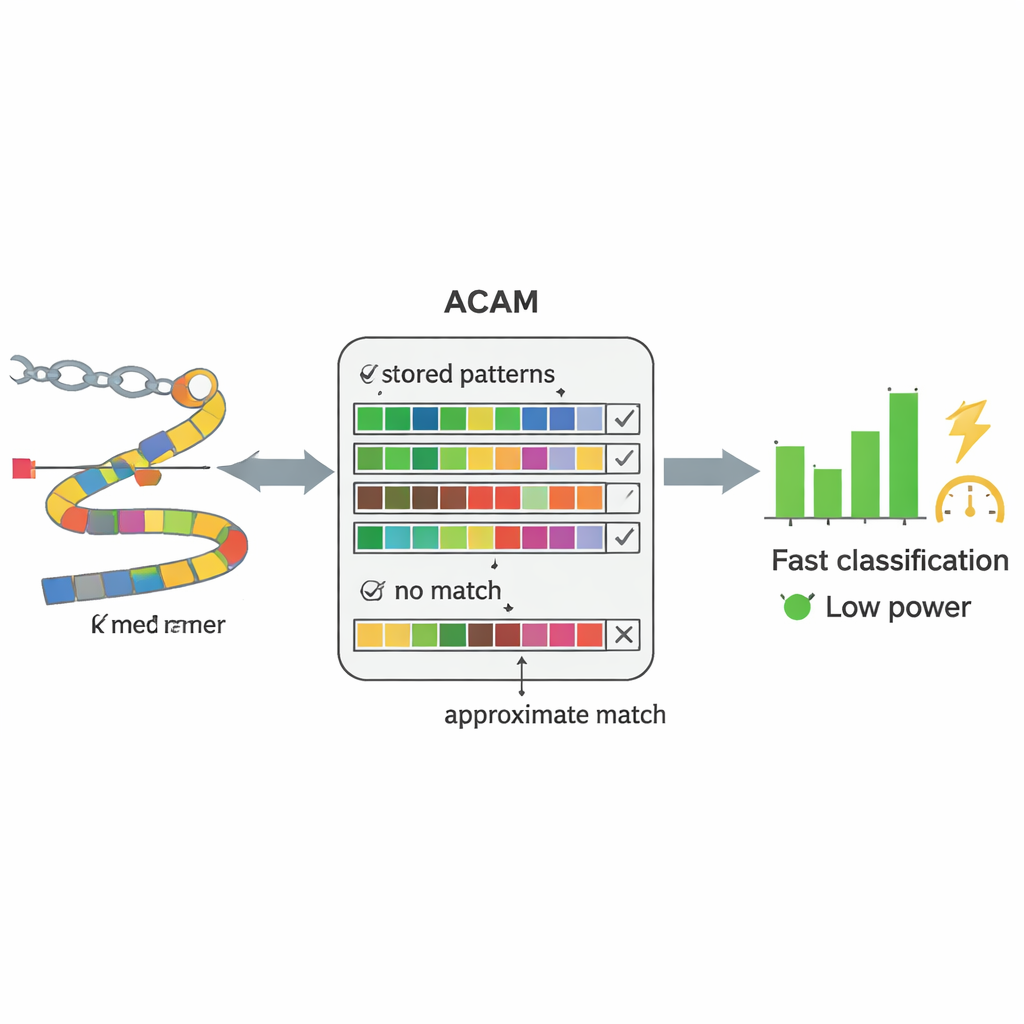
Kleine hardware met hoge snelheid en laag vermogen
PC-CAM integreert het ACAM-geheugen met een kleine RISC-V-processor op een chip van slechts enkele vierkante millimeters, gefabriceerd in een standaard 65-nanometer technologie. Metingen op echte hardware tonen aan dat hij ongeveer 960.000 korte DNA-reads per seconde kan classificeren terwijl hij ongeveer 1,27 milliwatt aan vermogen verbruikt—minder dan veel digitale polshorloges. Vergeleken met een toonaangevend softwaregereedschap dat op een high-end desktopprocessor draait, was de chip voor dit soort classificatietaken ongeveer 1.900 keer sneller. Hoewel de nauwkeurigheid iets is verminderd doordat hij een verdunde versie van elk genoom opslaat, stellen de auteurs dat deze afweging acceptabel is wanneer snelheid en energieverbruik de belangrijkste beperkingen zijn, zoals bij spoedeisende zorg of draagbare apparaten.
Wat dit betekent voor patiënten en verder
In eenvoudige bewoordingen laat de studie zien dat een klein, laagvermogen chipje kan fungeren als een gespecialiseerd zoekmachine voor bacterieel DNA en gevaarlijke ziekteverwekkers in bloed- of ontlastingsmonsters bijna onmiddellijk kan detecteren. Hoewel het geen volledige genetische analyse in een groot laboratorium vervangt, kan het snelle, ter plaatse bruikbare aanwijzingen geven over welke bacteriën aanwezig zijn, waardoor artsen eerder en nauwkeuriger antibiotica kunnen kiezen. Dezelfde benadering kan worden uitgebreid naar het monitoren van antibioticaresistentie, het controleren van voedsel en water op verontreiniging of het bewaken van gewassen op ziekten—allemaal met compacte hardware die geavanceerde DNA-analyse uit het datacenter haalt en dichter bij waar beslissingen genomen moeten worden brengt.
Bronvermelding: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Trefwoorden: bloedbaaninfectie, snelle detectie van ziekteverwekkers, DNA-sequencing, lab-op-een-chip, microbioom