Clear Sky Science · nl
Volledige-transcriptoomassemblage en ontwikkeling van SSR-markers voor Spinibarbus hollandi met PacBio SMRT-sequencing
Waarom een onopvallende rivier vis ertoe doet
Langs de rivieren in Zuid-China zwemt Spinibarbus hollandi, een karperachtige vis die zowel als tafelvlees als siervis gewaardeerd wordt. Telers willen de vis efficiënter kweken, maar hij groeit langzaam, wordt laat geslachtsrijp en produceert relatief weinig eieren. De hier beschreven studie gebruikt geavanceerde DNA- en RNA-sequencingtechnieken om een gedetailleerde genetische „onderdelenlijst” voor deze soort op te bouwen. Die genetische informatie kan uiteindelijk telers helpen robuustere, sneller groeiende vissen te selecteren en de instandhouding van wilde populaties ondersteunen.
Van veel weefsels naar een genetische kaart
Om zoveel mogelijk genetische informatie vast te leggen verzamelden de onderzoekers zes verschillende weefsels — hart, kieuw, hersenen, vin, lever en gonade — van zes volwassen mannetjes en vrouwtjes. Uit deze weefsels is RNA geëxtraheerd, het molecuul dat kopieën van actieve genen binnen cellen draagt. Met een technologie genaamd PacBio SMRT, die zeer lange stukken RNA-kopieën leest, stelden ze het eerste volledige transcriptoom voor S. hollandi samen. Simpel gezegd bouwden ze een hoge-resolutie catalogus van 15.197 onderscheiden genen en 23.403 transcripten, waarvan de meeste veel langer en vollediger zijn dan wat oudere kort-read methoden konden opleveren.
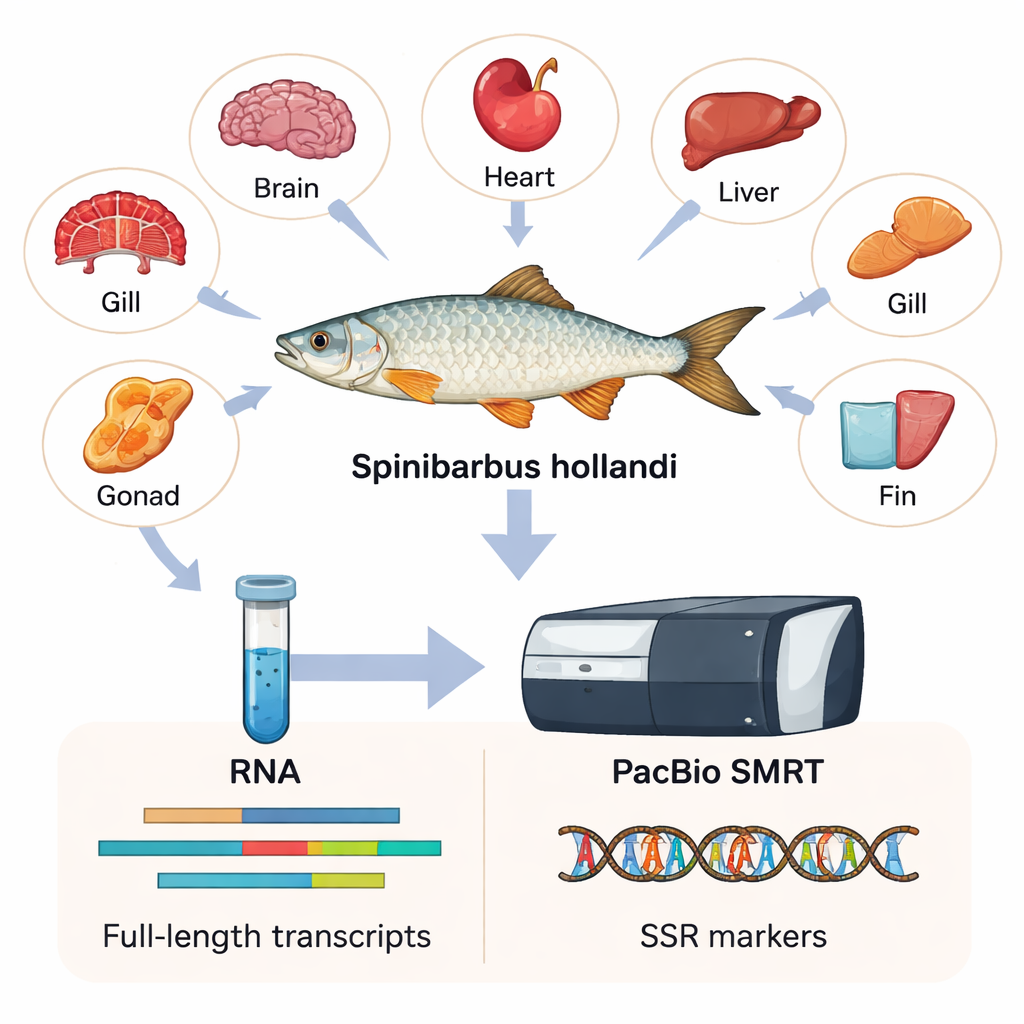
Wat de genen over de vis onthullen
Vervolgens vroeg het team wat deze genen daadwerkelijk doen. Ze vergeleken elke sequentie met grote openbare databanken die genen naar functie groeperen. Meer dan 95% van de genen kon worden gekoppeld aan bekende vermeldingen, een zeer hoge succesratio die wijst op goede datakwaliteit. Veel genen vielen in categorieën die verband houden met basiscelactiviteiten zoals metabolisme, signaaloverdracht en ontwikkeling, en leken het meest op genen van andere karperfamilie-vissoorten. Dit bevestigt dat het nieuwe transcriptoom biologisch solide is en een fundament biedt om genen te vinden die gekoppeld zijn aan eigenschappen als groeisnelheid, stressbestendigheid en voortplanting bij S. hollandi.
Verborgen lagen van regeling in RNA
Buiten het identificeren van genen onderzochten de wetenschappers ook hoe die genen worden gereguleerd. Ze vonden 373 gevallen van alternatieve splicing, waarbij hetzelfde gen op verschillende manieren wordt samengevoegd om verschillende RNA-boodschappen te maken. Het meest voorkomende patroon behield RNA-delen die vaak in andere soorten worden verwijderd, wat duidt op een bijzondere manier waarop deze vis zijn eiwitten fijn afstemt. Ze ontdekten ook 2.397 lange niet-coderende RNA’s — RNA-moleculen die geen eiwitten aanmaken maar kunnen regelen wanneer en waar andere genen worden aangezet. Gezamenlijk laten deze bevindingen zien dat S. hollandi een rijk scala aan RNA-niveau-regelmechanismen gebruikt die mogelijk invloed hebben op groei, seksuele rijping en aanpassing aan lokale omgevingen.
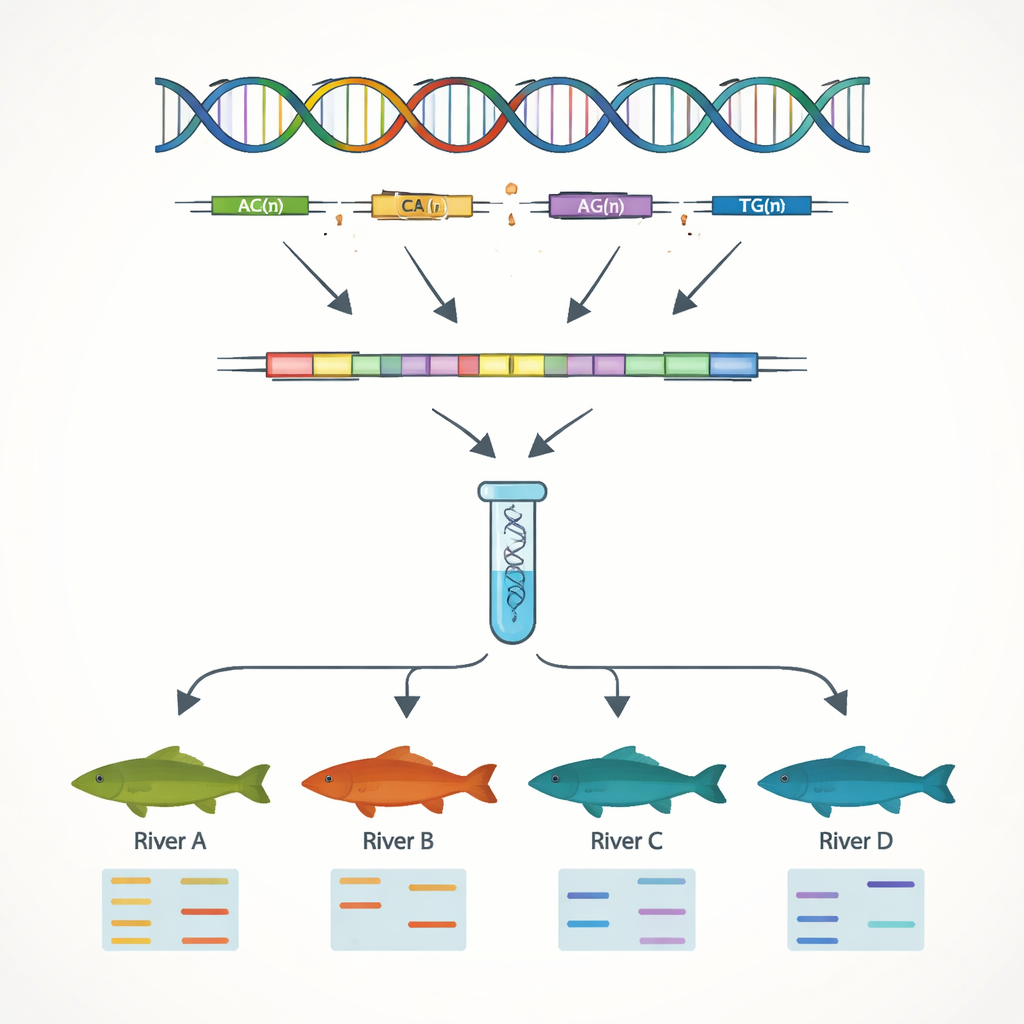
DNA-markeerlijnen bouwen voor fokkerij en behoud
Een belangrijk doel van het werk was het ontwikkelen van eenvoudige DNA-markers die individuele vissen en populaties van elkaar kunnen onderscheiden. Gericht op de genensequenties zochten de auteurs naar eenvoudige sequentieherhalingen, of SSR’s — korte DNA-motieven zoals “AC” of “AAT” die herhaald worden. Deze streken variëren vaak tussen individuen en zijn daardoor bruikbaar als genetische streepjescodes. Ze vonden 7.449 dergelijke SSR-loci en ontwierpen tientallen korte DNA-primers om ze in het laboratorium te amplificeren. Dertien van deze markers bleken zeer variabel en betrouwbaar bij tests in 51 vissen uit vier rivierstelsels. Met slechts deze 13 markers kon het team duidelijk genetische verschillen detecteren tussen populaties uit de Yangtze en die uit de Parelrivier, wat de bergketens weerspiegelt die natuurlijke uitwisseling tussen stroomgebieden beperken.
Wat dit betekent voor telers en rivieren
Voor niet-specialisten is de belangrijkste conclusie dat de auteurs een gedetailleerde, hoogwaardige genetische referentie voor S. hollandi en een set praktische DNA-markers hebben gecreëerd. Deze gereedschapskist zal onderzoekers helpen genen achter trage groei of lage vruchtbaarheid op te sporen, telers ondersteunen bij het selecteren van ouderdieren met gewenste eigenschappen, en natuurbeschermers in staat stellen genetische diversiteit over riviersystemen te volgen. Hoewel meer werk nodig is om specifieke genen te koppelen aan prestaties in vijvers of het wild, legt deze studie het moleculaire fundament om een traditionele riviervis om te vormen tot een moderne, duurzaam beheerde aquacultuursoort.
Bronvermelding: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Trefwoorden: Spinibarbus hollandi, vissen-transcriptoom, PacBio-sequencing, microsatellietmarkers, aquacultuurgenetica