Clear Sky Science · nl
Analyse op haplotype-niveau van milieudNA-metabarcoding onthulde de biogeografie en fylogeografie van zoetwatervissen op het Koreaanse schiereiland
Rivieren lezen via onzichtbare aanwijzingen
Rivieren en beken lijken met het blote oog vaak helder, maar ze zitten vol microscopische sporen van leven. Deze studie laat zien hoe wetenschappers die onzichtbare genetische "inkt" in water kunnen lezen om te ontdekken welke vissen waar leven, hoe hun populaties over het Koreaanse schiereiland met elkaar verbonden zijn, en zelfs of sommige vissen door mensen van het ene naar het andere gebied zijn verplaatst. Het werk geeft een voorproefje van hoe natuurbeheerders binnenkort biodiversiteit kunnen monitoren en zeldzame soorten kunnen beschermen zonder één net uit te gooien.
Vissen met DNA, niet met netten
In plaats van vissen te vangen verzamelden de onderzoekers simpele eenliterflessen water uit drie kleine beken — Seom, Gilan en Oshipcheon — elk gelegen in een ander biogeografisch gebied van Zuid-Korea. In deze monsters zochten ze naar milieudNA (eDNA): kleine fragmenten genetisch materiaal dat vissen verliezen via huid, afval en slijm. Met een techniek die metabarcoding heet, versterkten en sequentieerden ze een kort stukje vis-DNA en vergeleken miljoenen reads met referentiedatabases om te identificeren welke soorten — en zelfs welke genetische varianten, of haplotypen — in elke beek aanwezig waren.
Wie leeft waar in Korea’s beken?
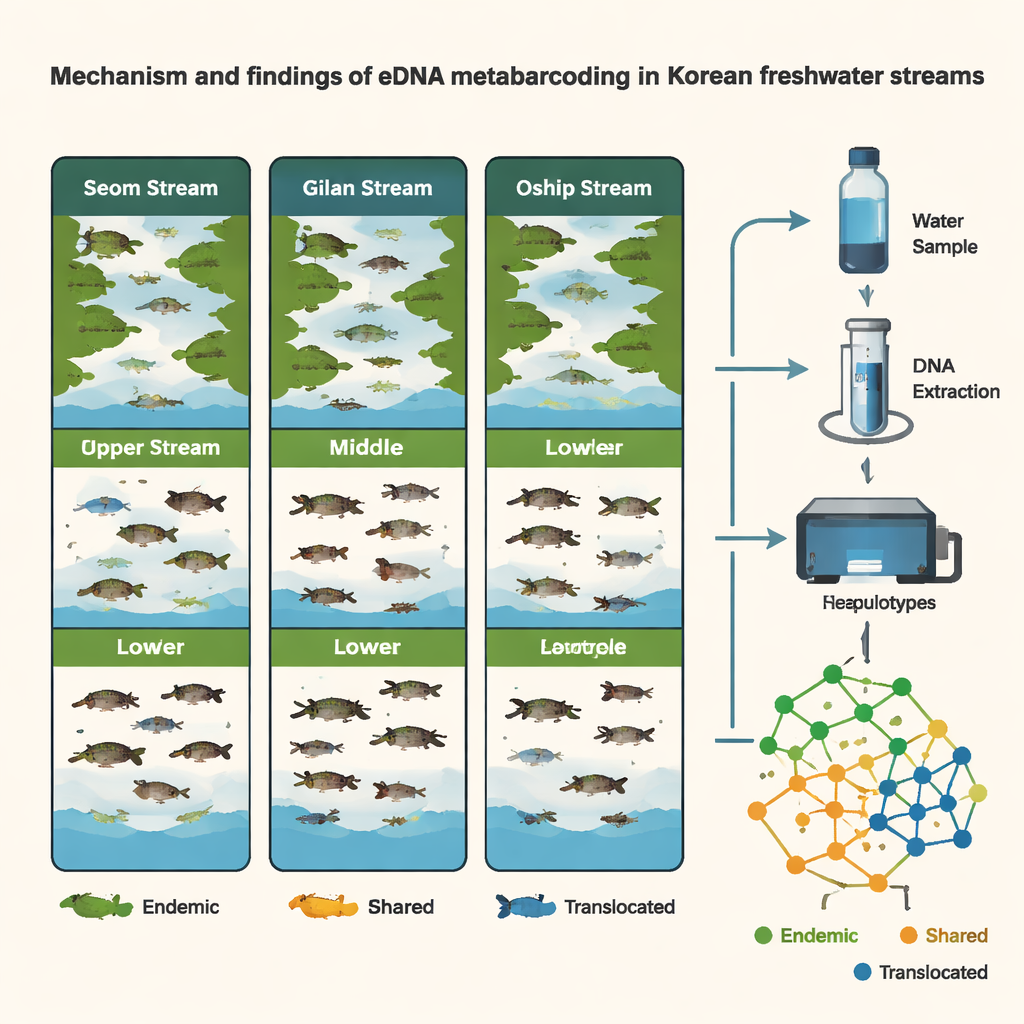
Uit slechts 54 watermonsters, genomen op negen locaties, detecteerde het team 107 verschillende DNA-varianten die 76 vissensoorten vertegenwoordigden — ongeveer een derde van alle zoetwatervissen die in Korea bekend zijn. De Seom-beek, een laaggelegen rivier verbonden met de Gele Zee, huisvestte de rijkste visgemeenschap met 49 soorten. Gilan en Oshipcheon, hoger gelegen en steilere zijrivieren die naar verschillende kusten stromen, telden elk 28 soorten. Veel vissen kwamen in meerdere beken voor, maar bijna 30 soorten bleken endemisch voor Korea’s zoetwaterhabitats, en elke beek had ook zijn eigen unieke soortenassortiment. In het algemeen kwamen de patronen overeen met de langbekende indeling dat Korea’s zoetwaterleven door bergketens en geologische geschiedenis in drie hoofdregio’s is verdeeld.
Genetische vingerafdrukken en verborgen verplaatsingen
Doordat de wetenschappers op haplotype-niveau werkten — de fijnmazige "smaken" van DNA binnen een soort — konden ze meer dan alleen soorten opsommen; ze konden populaties vergelijken. Verschillende algemeen voorkomende inheemse vissen toonden duidelijke genetische verschillen tussen regio’s, wat duidt op langdurige scheiding en beperkte natuurlijke uitwisseling over het schiereiland. Tegelijkertijd bracht de DNA-data waarschijnlijk gevallen van door mensen geholpen verplaatsing aan het licht. Voor soorten zoals Pungtungia herzi, Coreoleuciscus splendidus en Nipponocypris koreanus kwamen de haplotypepatronen in de oostelijke Oshipcheon-beek sterk overeen met die uit westelijke of zuidelijke rivieren, wat wijst op eerdere uitzettingen of verplaatsingen. Door de "stamboom" van deze DNA-varianten virtueel te reconstrueren, kon het team waarschijnlijke herkomstregio’s van verplaatste vissen afleiden — een soort genetische forensische methode voor rivierbeheer.
Seizoenen, habitats en bewegende doelen
De studie volgde ook hoe visgemeenschappen in tijd en ruimte veranderden. Door monsters te vergelijken die in de late winter (maart) en zomer (augustus) waren verzameld, vonden de onderzoekers een hogere soortenrijkdom in de zomer en duidelijke seizoensgebonden verschuivingen, vooral in de Seom-beek. In Oshipcheon verscheen en verdween eDNA van migrerende soorten — zoals zalmachtigen en andere vissen die tussen rivier en zee bewegen — op manieren die overeenkomen met hun bekende levenscycli. Verrassend genoeg lieten binnen elke locatie riffles, runs en poelen geen sterke verschillen in vis-DNA zien, waarschijnlijk omdat de waterstroom eDNA lateraal mengt over deze kleine kanalen. In plaats daarvan kwamen de belangrijkste verschillen voort uit verschillende secties van een beek (boven, midden, onder) en tussen de drie beken zelf, wat het belang benadrukt van waar langs een rivier monsters worden genomen.
Wat dit betekent voor de bescherming van zoetwaterleven
In eenvoudige bewoordingen toont dit onderzoek aan dat een fles rivierwater een gedetailleerde momentopname kan geven van wie er in de beek leeft, hoe lokale vispopulaties over grote regio’s met elkaar verwant zijn, en of mensen die patronen hebben veranderd door vissen te verplaatsen. Voor natuurbeheer betekent dit dat beheerders snel zeldzame en endemische soorten kunnen monitoren, invasieve en verplaatste vissen kunnen opsporen en seizoensgebonden verschuivingen in migrerende populaties kunnen volgen zonder intensief veldwerk of schade aan dieren. Hoewel eDNA nog niet volledig traditionele genetische studies kan vervangen, biedt het een krachtig, laag-impactinstrument om de biodiversiteit van zoetwaterecosystemen te bewaken in een opwarmende, intens beheerde wereld — en om te waarborgen dat Korea’s unieke rivier- vissen blijven gedijen in hun oorspronkelijke leefgebieden.
Bronvermelding: Amin, M.H.F., Kim, A.R., Jang, J.E. et al. Haplotype-level analysis of environmental DNA metabarcoding revealed the biogeography and phylogeography of freshwater fishes in Korean Peninsula. Sci Rep 16, 6955 (2026). https://doi.org/10.1038/s41598-026-36043-x
Trefwoorden: milieu-DNA, zoetwatervis, biodiversiteit, Koreaanse rivieren, conservatiegenetica