Clear Sky Science · nl
IL2Pepscan: Een machine-learningraamwerk voor het voorspellen van IL-2-inducerende peptiden en hun identificatie in wereldwijde virale proteomen
Het immuunsysteem leren met kleine eiwitfragmenten
Moderne vaccins en kankertherapieën vertrouwen steeds vaker op het subtiel bijsturen van het immuunsysteem in plaats van het bestrijden van ziekte met brede medicijnaanvallen. Deze studie onderzoekt hoe kleine eiwitfragmenten, peptiden genoemd, geselecteerd kunnen worden om een krachtige immuunboodschapper aan te zetten: interleukine‑2 (IL‑2). Met behulp van geavanceerde computermodellen doorzoeken de auteurs zowel bestaande immuungegevens als de proteïnekatalogi van duizenden virussen om die moleculaire “naalden” in een hooiberg te vinden die mogelijk kunnen helpen bij het ontwerpen van betere vaccins en immunotherapieën.
Waarom IL-2 belangrijk is voor gezondheid en ziekte
IL‑2 is een kleine signaalmolecule die werkt als een groeifactor voor belangrijke immuuncellen, de T‑cellen. Wanneer deze cellen voor het eerst een bedreiging tegenkomen — zoals een virus of een kankercel — kunnen ze IL‑2 afgeven, wat T‑cellen stimuleert om zich te vermenigvuldigen, te specialiseren en de indringer te herinneren. IL‑2 helpt ook bij het in stand houden van regulatorische T‑cellen die voorkomen dat het immuunsysteem tegen het eigen weefsel keert. Vanwege deze dubbele rol is IL‑2 als geneesmiddel gebruikt bij de behandeling van kankers zoals melanoom, en wordt het onderzocht voor auto-immuunziekten. Direct toedienen van IL‑2 kan echter zwaar zijn voor patiënten, waardoor er toenemende interesse is in het ontwerpen van veilige peptiden die het lichaam op een meer gecontroleerde, gerichte manier laten IL‑2 produceren.
Het "palet" van IL-2‑inducerende peptiden leren kennen
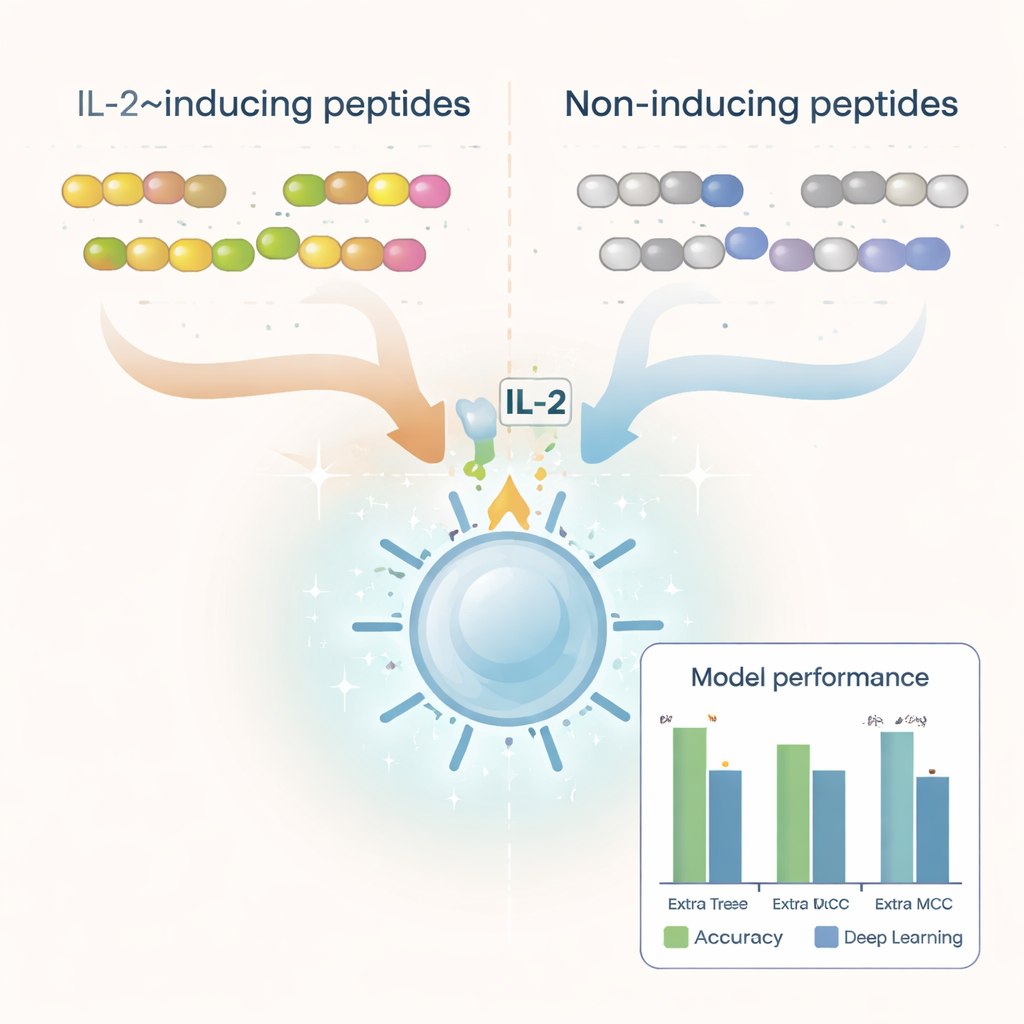
De onderzoekers startten met duizenden peptidesequenties die al in laboratoriumexperimenten waren getest en als IL‑2‑inducerend of niet were gelabeld. Ze schonen deze dataset op door duplicaten, ongewone bouwstenen en peptiden die te kort of te lang waren te verwijderen, en hielden zo meer dan 6.000 goed gekarakteriseerde voorbeelden over. Door de aminozuurbouwstenen van deze peptiden te analyseren, ontdekten ze duidelijke verschillen tussen de twee groepen. IL‑2‑inducerende peptiden leken rijker aan hydrofobe, waterafstotende aminozuren zoals leucine en alanine, terwijl niet‑inducerende peptiden meer neigden naar polaire en geladen residuen. Bepaalde korte patronen, of motieven, zoals "LEGS" en "ALEG", verschenen alleen in IL‑2‑inducerende peptiden, wat wijst op structurele signalen die immuunactivatie kunnen helpen uitlokken.
Machines trainen om immuunversterkende patronen te herkennen
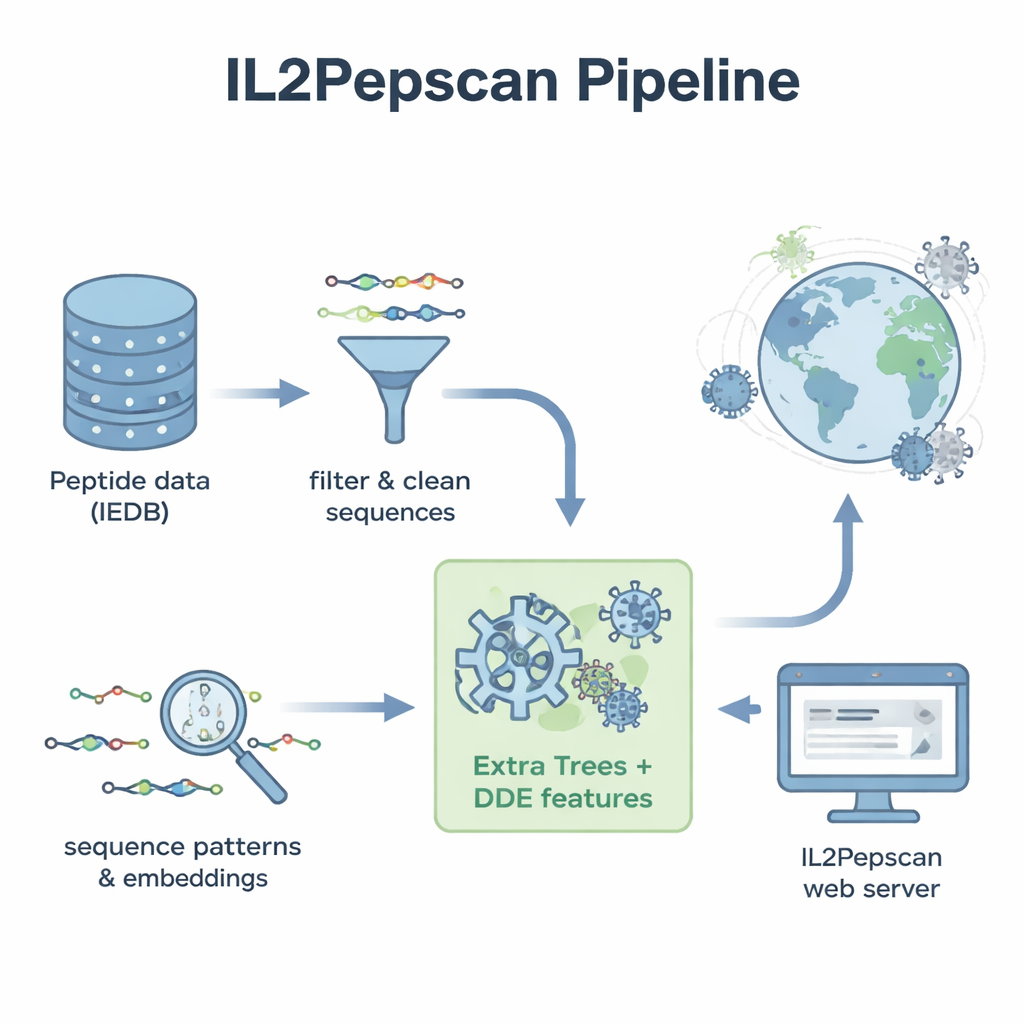
Om deze patronen om te zetten in een praktisch voorspellingstool, zetten het team elk peptide om in numerieke beschrijvingen die de samenstelling en de volgorde van aminozuren vastleggen. Ze testten een reeks machine‑learningmethoden — waaronder populaire algoritmen zoals random forests, support vector machines en boosted trees — naast deep‑learningarchitecturen die vaak worden gebruikt voor taal- en beeldtaken. Ze maakten ook gebruik van een groot eiwit‑"taalmodel" genaamd ProtBERT, oorspronkelijk getraind op honderden miljoenen eiwitsequenties, en verfijnen het om IL‑2‑gerelateerde signalen beter te herkennen. Na uitgebreid testen met kruisvalidatie en een onafhankelijke testset bleek een model genaamd Extra Trees in combinatie met een feature‑set bekend als dipeptide deviation from expected mean (DDE) het beste te presteren. Dit model behaalde bijna 80% nauwkeurigheid en een sterke correlatiescore, en overtrof meerdere deep‑learningbenaderingen.
De virale wereld scannen op verborgen immuuntriggers
Gewapend met hun beste model trokken de auteurs een veel bredere dataset. Ze verzamelden referentieproteïnes uit meer dan 14.000 virussen, verdeelden deze eiwitten in ongeveer 156 miljoen overlappende peptiden, en vroegen het model welke daarvan IL‑2 zouden kunnen induceren. Tot de hoogst scorende kandidaten behoorden peptiden uit bekende virale families, waaronder flavivirussen zoals West‑Nijl, Zika, Gele Koorts en Hepatitis C, evenals uit influenza en SARS‑CoV‑2. Veel veelbelovende peptiden kwamen uit virale omhullings‑ of nucleocapsideproteïnen — dezelfde typen eiwitten waarvan andere studies hebben laten zien dat ze IL‑2‑reacties in dieren kunnen oproepen. Het model wees ook potentiële IL‑2‑inducerende peptiden aan die gecodeerd zijn door bacteriofagen, virussen die bacteriën infecteren, wat wijst op een nog bredere reikwijdte van immuunrelevante sequenties.
Van algoritme naar toegankelijk gereedschap
Om hun werk buiten de computerfaciliteit bruikbaar te maken, bouwden de auteurs een publieke webserver genaamd IL2Pepscan. Onderzoekers kunnen peptiden of eiwitsequenties plakken op de site om hun IL‑2‑inductiepotentieel te schatten, nieuwe varianten te ontwerpen door posities te muteren, hele eiwitten te scannen op hotspots, of te zoeken naar bekende IL‑2‑gerelateerde motieven. Hoewel de studie nog niet elk voorspeld peptide experimenteel bevestigt, suggereert de overeenstemming met bestaande laboratoriumresultaten dat IL2Pepscan betrouwbaar kandidaten kan terugbrengen voor verder testen. Voor niet‑specialisten is de conclusie dat zorgvuldig getrainde algoritmen door enorme biologische datasets kunnen zeven om kleine eiwitfragmenten te identificeren die mogelijk op termijn vaccins en immunotherapieën helpen het immuunsysteem op een krachtigere — en preciezere — manier aan te zetten.
Bronvermelding: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
Trefwoorden: interleukine-2, peptidevaccins, machine learning, viraal proteoom, immunotherapie