Clear Sky Science · nl
Machine-learningkader voor mRNA-alternatieve-splijtanalyse identificeert een voortgangskenmerk bij colorectaal adenocarcinoom
Waarom dit onderzoek belangrijk is voor patiënten
Colorectale kanker is een van de meest voorkomende en dodelijke vormen van kanker, maar artsen hebben nog steeds moeite te voorspellen welke tumoren bij patiënten rustig onder controle blijven en welke na behandeling terugkomen. Deze studie introduceert een nieuwe manier om verborgen signalen in tumorrna te lezen — de boodschappen die cellen gebruiken om eiwitten te maken — en gebruikt machine learning om die signalen om te zetten in een eenvoudige risicoscore die kan helpen bepalen hoe agressief elke patiënt behandeld moet worden.
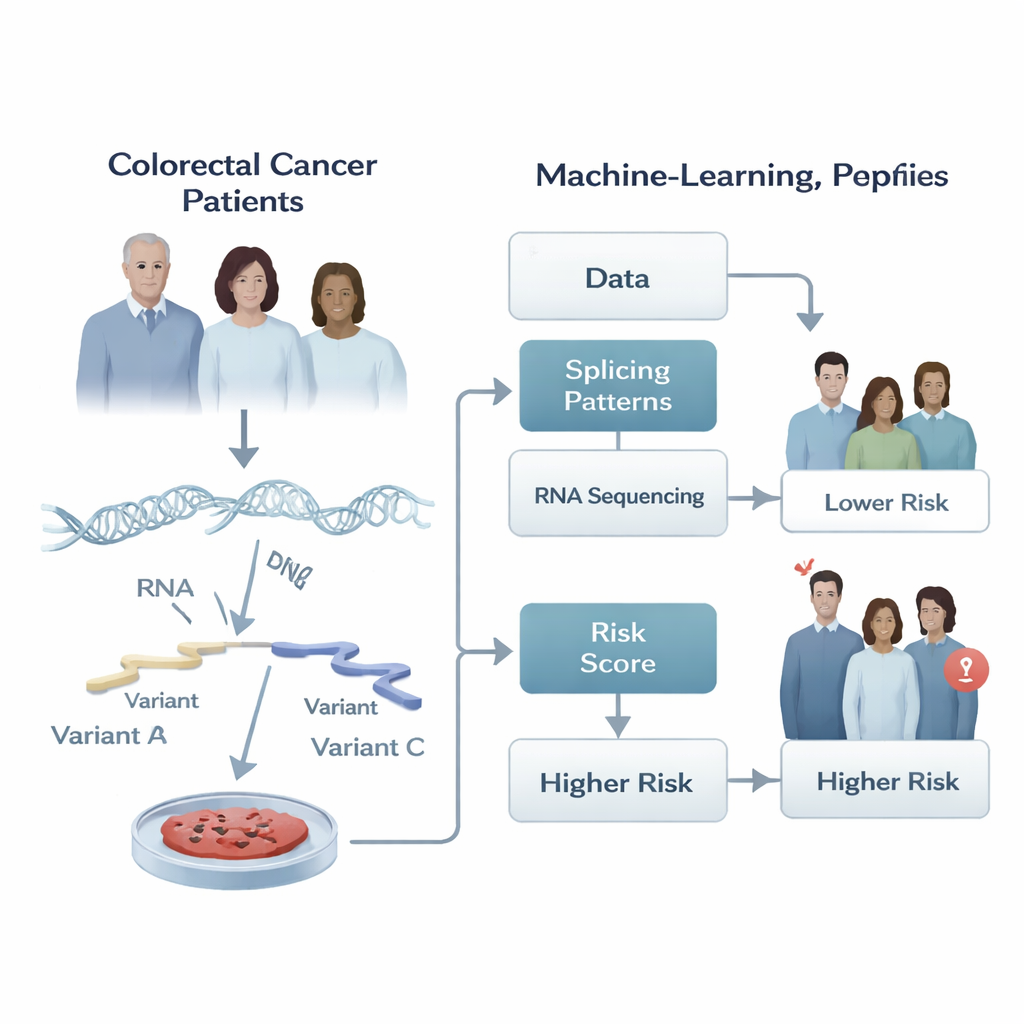
Verborgen knip- en plakwijzigingen in kankergenen
Onze genen worden niet op een vaste manier afgelezen. Wanneer een cel DNA naar RNA kopieert, kan zij stukken van het RNA-bericht op verschillende manieren knippen en plakken, een proces dat alternatieve splitsing wordt genoemd. Deze bewerking stelt één gen in staat meerdere varianten van een eiwit te produceren, als verschillende gereedschappen uit dezelfde gereedschapskist. In gezonde cellen is deze flexibiliteit strak gereguleerd. In kanker kan het knip- en plakproces echter ontsporen, waardoor eiwitvarianten ontstaan die tumoren helpen groeien, uitzaaien en therapie te weerstaan. De auteurs redeneerden dat het patroon van deze RNA-bewerkingen in een tumor sterke aanwijzingen kan bevatten over hoe die kanker zich waarschijnlijk zal gedragen in de loop van de tijd.
RNA-patronen omzetten in een risicoscore
De onderzoekers analyseerden RNA-sequencinggegevens van tumoren van 266 patiënten met colorectaal adenocarcinoom uit The Cancer Genome Atlas en nog eens 348 patiënten uit een onafhankelijke studie. Voor elke tumor kwantificeerden ze hoe vaak bepaalde splitsingskeuzes werden gebruikt, samengevat in een getal tussen nul en één. Vervolgens bouwden ze een stapsgewijze machine-learningpijplijn die eerst duizenden splitsingsevenementen screende op een verband met hoe lang patiënten vrij van tumorgroei bleven, en die de lijst daarna zorgvuldig terugbracht terwijl overlappingen en redundantie werden vermeden. Het eindresultaat was een compacte “handtekening” van slechts vijf specifieke splitsingsevenementen waarvan het gecombineerde gedrag het beste volgde of de kanker van een patiënt eerder of later progressie liet zien.
Patiënten indelen in lagere- en hogere-risicogroepen
Middels deze vijf-evenementenhandtekening definieerde het team voor elke patiënt een numerieke risicoscore door de splitsingsmetingen op te tellen, gewogen naar hoe sterk elk evenement met progressie samenhing. Patiënten waarvan de tumoren drie van de splitsingspatronen bevoordeelden, deden het doorgaans slechter, terwijl twee patronen aan betere uitkomsten waren gekoppeld. De score verdeelde patiënten duidelijk in laag- en hoogrisicogroepen: zowel in de oorspronkelijke cohort als in de onafhankelijke validatiegroep ervoeren degenen met hoge scores aanzienlijk vroeger tumorgroei. Toen de onderzoekers de tijd-tot-progressiekrommen plotten, scheidden de twee lijnen zich duidelijk, wat aangeeft dat deze kleine set RNA-bewerkingen betekenisvolle verschillen in tumorgedrag over honderden personen vastlegde.
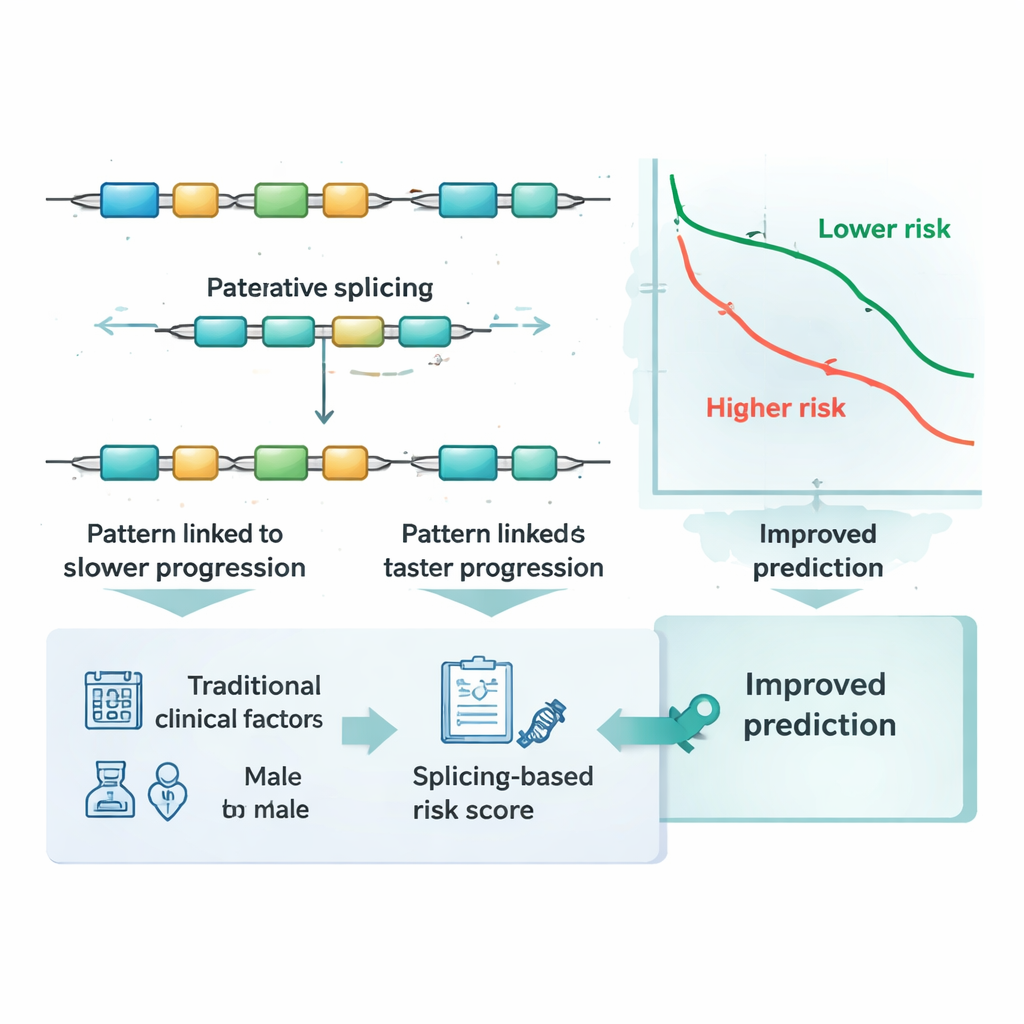
Verder dan standaardstadiering en bekende markers
Artsen baseren risicoschattingen momenteel op tumorstadium, leeftijd en andere klinische kenmerken, en soms op specifieke DNA-veranderingen of genexpressieniveaus. De onderzoekers vroegen zich af of hun op splitsing gebaseerde score iets toevoegde bovenop deze gevestigde maatstaven. Met tijdsafhankelijke nauwkeurigheidstests toonden ze aan dat voorspellingen die alleen op stadium, leeftijd en geslacht waren gebaseerd, duidelijk verbeterden wanneer de splitsingsrisicoscore werd toegevoegd. Ze vergeleken de score ook met tientallen bekende moleculaire markers bij colorectale kanker en met verschillende gangbare statistische modelleringsbenaderingen. In beide hoofdgroepen patiënten presteerde de vijf-evenementen-splitsingshandtekening gelijk aan of beter dan deze alternatieven, en verbeterde de voorspelling wanneer ze samen werden gebruikt, wat suggereert dat ze informatie vastlegt die andere markers missen.
Wat dit kan betekenen voor toekomstige zorg
Voor leken is de kernboodschap dat de manier waarop een tumor zijn RNA “bewerk t” kan onthullen hoe gevaarlijk hij waarschijnlijk is. Deze studie laat zien dat het volgen van slechts vijf specifieke RNA-bewerkingen in colorectale tumoren patiënten in groepen kan indelen die wezenlijk verschillen in hun kans om vrij van progressie te blijven. Hoewel dit werk nog moet worden vertaald naar praktische labtests en moet worden geëvalueerd in prospectieve klinische trials, wijst het op een toekomst waarin artsen zo’n score bij de diagnose kunnen gebruiken om te beslissen wie intensievere behandeling en nauwere opvolging nodig heeft en wie veilig overbehandeling kan vermijden. Breder gezien biedt het een herbruikbaar kader om RNA-splitsingspatronen in andere kankers te ontginnen, waarmee prognose kan worden verfijnd en echt gepersonaliseerde therapie kan worden aangestuurd.
Bronvermelding: Maimekov, U., Nosrati, M., Mahmoud, A. et al. Machine learning framework for mRNA alternative splicing analysis identifies a signature of progression in colorectal adenocarcinoma. Sci Rep 16, 7106 (2026). https://doi.org/10.1038/s41598-026-35903-w
Trefwoorden: colorectale kanker, alternatieve splitsing, RNA-sequencing, machine learning, kankerprognose