Clear Sky Science · nl
Ontwarren van directe en pleiotrope SNP-effecten in luzerne (Medicago sativa L.) met behulp van causale graafleer
Waarom dit van belang is voor boerderijen en voedsel
Luzerne is een pijler van de moderne landbouw: het voedt melkkoeien en helpt bij het opbouwen van gezonde bodems. Toch loopt het veredelen van betere luzerne — planten die de winter doorstaan, schade weerstaan en kwalitatief goed voer leveren — vast door de enorme complexiteit van het genoom. Deze studie introduceert een nieuwe manier om van lange, verwarrende lijsten met DNA-markers te komen tot heldere oorzaak-en-gevolgkaarten die laten zien welke delen van het genoom werkelijk belangrijke stamkenmerken aansturen en welke slechts mee-draaien.
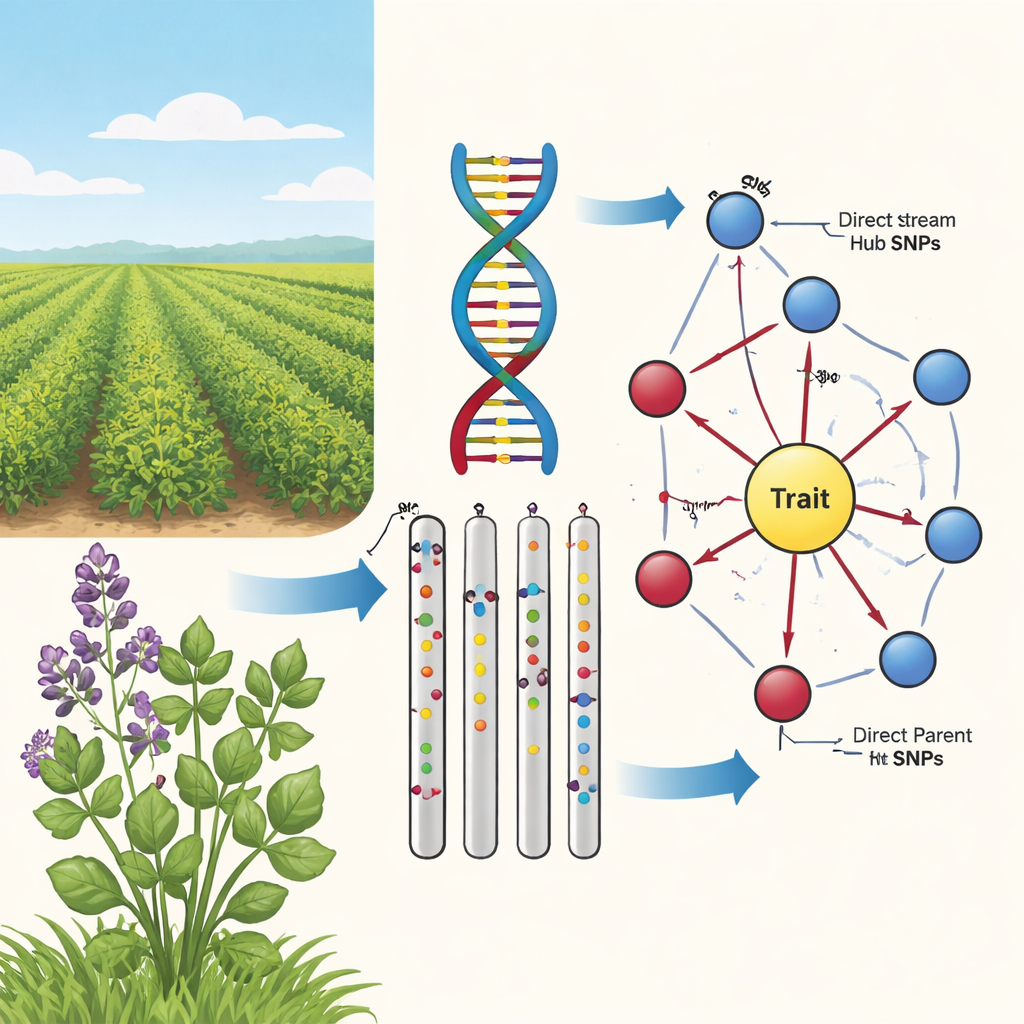
Van losse verbanden naar oorzaak-en-gevolg
Traditionele genome-wide associatieonderzoeken doorzoeken het genoom op DNA-variaties, SNPs genoemd, die samen voorkomen met een kenmerk, zoals stammkleur of winteroverleving. Bij luzerne is de situatie echter extra verwarrend: het heeft vier kopieën van elk chromosoom, grote DNA-stroken bewegen samen en populaties zijn genetisch sterk gemengd. Dat creëert een "nevel van correlatie" waarin veel markers belangrijk lijken, maar slechts enkelen daadwerkelijk het kenmerk beïnvloeden. De auteurs stellen dat veredelaars meer nodig hebben dan eenvoudige statistische verbanden; ze moeten weten welke markers daadwerkelijk op de causale paden van genotype naar zichtbare plantkenmerken liggen.
Hoe het nieuwe raamwerk werkt
De onderzoekers bouwden een tweefasenraamwerk dat moderne machine learning combineert met ideeën uit de causale graafleer. Eerst gebruikten ze een techniek genaamd Double Machine Learning om ongeveer 2.400 SNPs te screenen in 500 luzernegenotypen. Deze stap verwijdert de invloed van verborgen factoren zoals familieachtergrond en geografie, met behulp van hoofdcomponenten van het genoom als proxy's. Het resultaat is een schoner beeld van welke markers nog steeds een direct effect op kenmerken zoals stammkleur laten zien nadat voor deze verstorende invloeden is gecorrigeerd. In dit gefilterde beeld verschenen sterke, stabiele signaalpieken vooral op chromosoom 2 en 4, en toonden sleutelmarkers effectgroottes waarvan de betrouwbaarheidsintervallen duidelijk nul uitsloten, wat wijst op echte causale invloed.
Markers omzetten in genetische wegenkaarten
In de tweede fase gebruikte het team een algoritme voor causale graafleer, bekend als het PC-algoritme, om de veelbelovende markers te verbinden in een directioneel netwerk. In deze diagrammen vertegenwoordigen knopen SNPs en het kenmerk, en pijlen geven de meest waarschijnlijke richting van invloed aan. Door randen weg te halen die conflicteren met basisbiologie (bijvoorbeeld: kenmerken kunnen het onderliggende DNA niet veranderen) en alleen SNPs te behouden die in de richting van het kenmerk wijzen, kregen de auteurs compacte, biologisch plausibele kaarten. Deze "zonnebloem"-netwerken onthullen een gelaagde structuur: een binnenring van Directe Ouder-SNPs die direct naar het kenmerk lopen, en een buitenring van Opstroom-Knooppunt-SNPs die meerdere ouders beïnvloeden maar het kenmerk niet rechtstreeks raken.
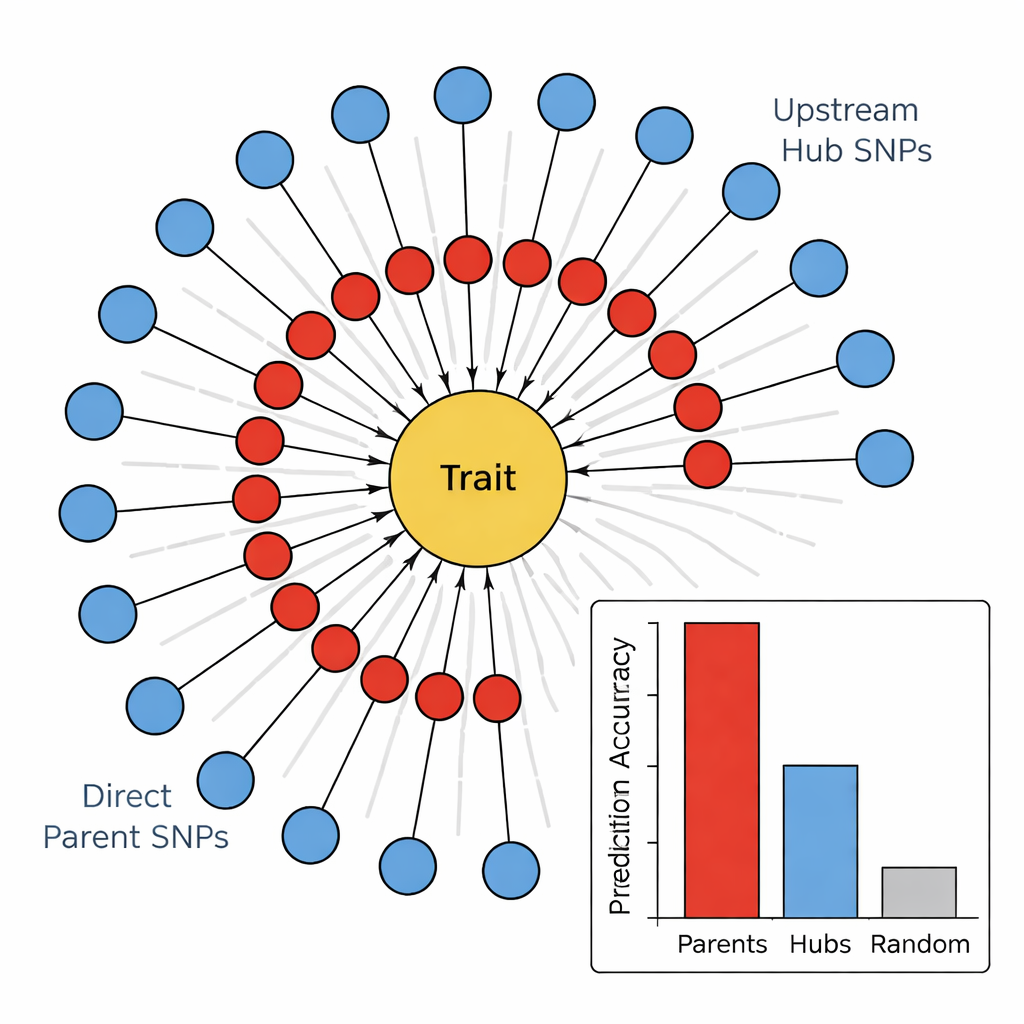
Uitvoerders versus regisseurs in het genoom
Om te testen of deze hiërarchie betekenisvol was, vergeleken de auteurs hoe goed verschillende groepen markers vier stamgerelateerde kenmerken konden voorspellen: stammkleur, stamvulling, stamsterkte en winterbeschadiging. Over alle kenmerken heen waren de Directe Ouder-SNPs consequent de beste voorspellers en verklaarden vaak meerdere malen meer variatie dan willekeurige markers of de Opstroom-Knooppunten. Daarentegen lieten de knooppunten zwakke of zelfs negatieve voorspellende kracht zien, ondanks hun hoge verbondenheid in het netwerk. Toen het team deze SNPs koppelde aan bekende genen, ontstond een patroon: Directe Ouders kwamen vaak overeen met enzymen of structurele eiwitten die direct werken aan celwanden, pigmenten of schade door stress, terwijl Knooppunten eerder overeenkwamen met transcriptiefactoren en regulatorische eiwitten die breedweg veel routes tegelijk bijsturen.
Wat dit betekent voor toekomstig luzerneveredelen
Voor veredelaars en genetici biedt de studie een manier om rumoerige associatieresultaten te doorsnijden en te focussen op DNA-veranderingen die echt het verschil maken voor specifieke kenmerken. De auteurs tonen aan dat het combineren van gedeconfounded screening met causale grafen kan dienen als ingebouwde bescherming tegen overfitting, waardoor lange kandidaatlijsten veranderen in kleine, interpreteerbare netwerken die aansluiten bij bekende biologie. In praktische termen worden Directe Ouder-SNPs hoogprecisie-markers voor het selecteren van planten met betere stengels of winteroverleving, terwijl Opstroom-Knooppunten wijzen op master-schakelaars die bredere stressreacties kunnen hervormen, maar met mogelijke trade-offs. Dit structurele beeld van het genoom legt een basis voor betrouwbaardere genomische selectie in complexe gewassen en voor het integreren van toekomstige datalagen, zoals genexpressie en metabolisme, in samenhangende oorzaak-en-gevolgmodellen van plantprestaties.
Bronvermelding: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Trefwoorden: luzernegenetica, causale graafleer, genomische selectie, plantenveredeling, polyploïde gewassen