Clear Sky Science · nl
Geordende dissociatieve PCA-methoden voor decompositie van hoogdimensionale neuroimaging-signalen
De verborgen signalen van de hersenen ontwarren
Moderne hersenscans kunnen elke seconde activiteit van honderdduizenden locaties registreren, maar van deze stroom cijfers heldere, betekenisvolle netwerken maken is buitengewoon lastig. Verschillende hersenprocessen overlappen vaak in ruimte en tijd, zoals meerdere radiostations die op nabijgelegen frequenties uitzenden. Dit artikel presenteert nieuwe wiskundige hulpmiddelen die helpen om deze verwarde signalen schoner van elkaar te scheiden, wat scherpere kaarten van hersenfunctie belooft voor zowel fundamenteel onderzoek als klinische studies.
Waarom gebruikelijke methoden tekortschieten
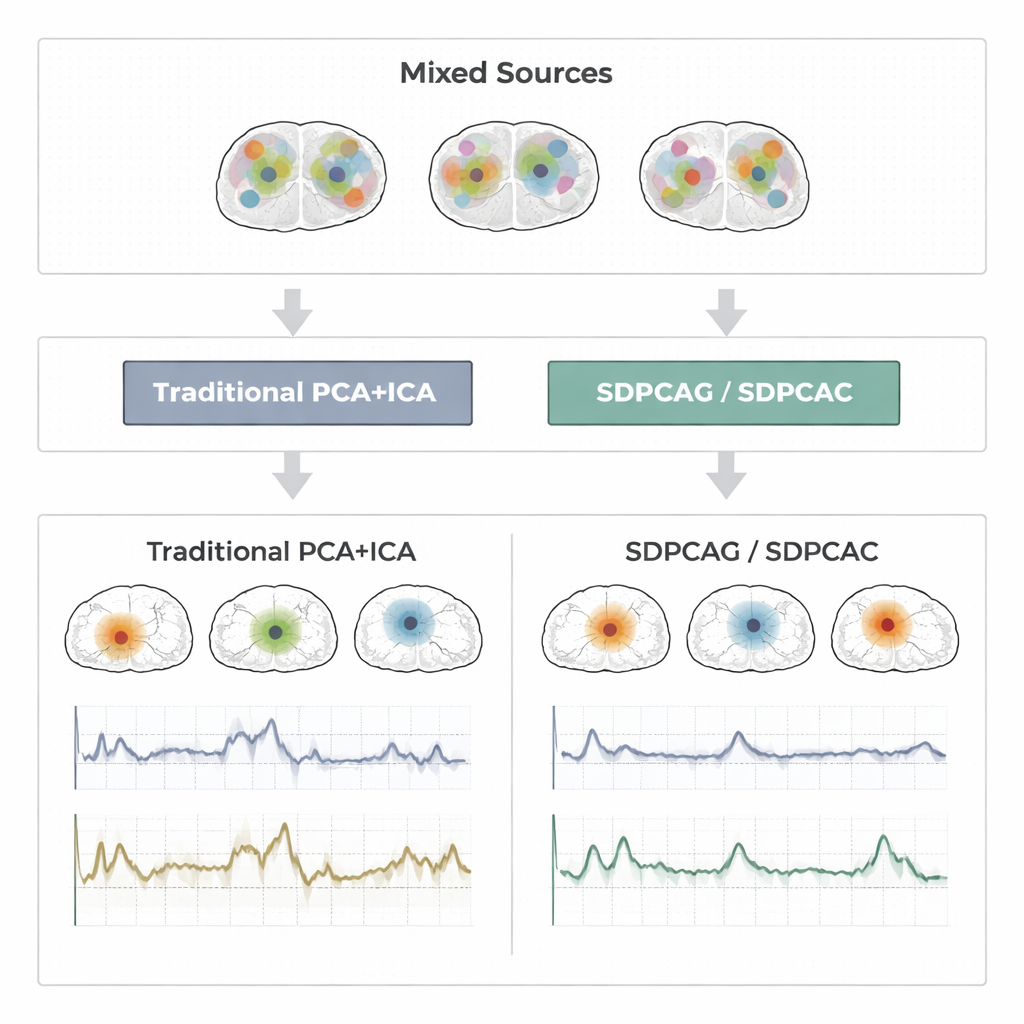
Decennialang vertrouwen onderzoekers op technieken zoals principal component analysis (PCA), sparse PCA en independent component analysis (ICA) om functionele MRI (fMRI)-gegevens te comprimeren en te scheiden. PCA vindt patronen die het merendeel van de variatie in de data verklaren, maar elk patroon mengt informatie uit vrijwel elke hersenlocatie, waardoor interpretatie moeilijk wordt. Sparse PCA probeert dit op te lossen door elk patroon te dwingen slechts een subset van locaties te gebruiken, en ICA gaat verder door aan te nemen dat de onderliggende hersensignalen statistisch onafhankelijk zijn. In de praktijk overlappen echte hersennetwerken echter en beïnvloeden ze elkaar. Wanneer dat gebeurt, vallen de onafhankelijkheids- en sparsity-veronderstellingen uiteen. Het resultaat kan gefragmenteerde kaarten en rumoerige tijdreeksen zijn die niet langer overeenkomen met het daadwerkelijke gedrag van hersennetwerken.
Een nieuwe manier om signalen te scheiden
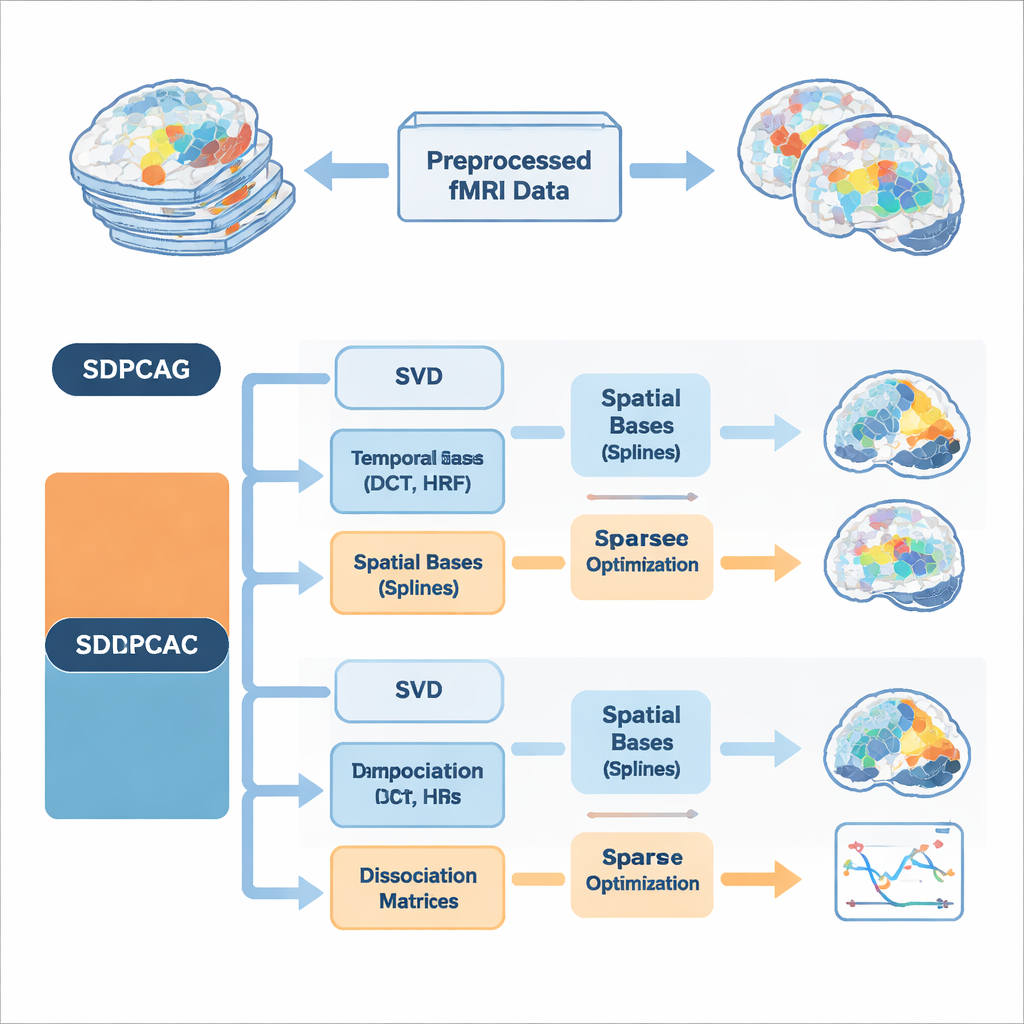
De auteurs stellen een verenigd kader voor, genoemd structured dissociative PCA, geïmplementeerd in twee algoritmen genaamd SDPCAG en SDPCAC. In plaats van ruimte en tijd apart te behandelen, herschikt de methode de volledige fMRI-dataset via een enkele, zorgvuldig ontworpen decompositie. Het begint met een standaard laag-rang-ontbinding van de data en introduceert vervolgens speciale "dissociatie"-matrices die zowel ruimtelijke kaarten als tijdreeksen herwegen en roteren. Tegelijkertijd representeert het deze componenten met sets vloeiende bouwstenen: cosinusachtige temporele golven, modellen van de bloedstroomrespons van de hersenen op neuronale activiteit en vloeiende ruimtelijke krommen genaamd splines. Door te leren hoe deze bouwstenen te combineren en tegelijkertijd sparsity af te dwingen—alleen de belangrijkste stukken te behouden—kan de methode overlappende netwerken uit elkaar halen zonder onrealistische onafhankelijkheidsveronderstellingen op te leggen.
Hersenkennis vanaf het begin inbouwen
Een belangrijke innovatie is dat de algoritmen voorkennis over hersensignalen direct in de decompositie verwerken, in plaats van die pas achteraf te corrigeren. Aan de temporele kant gebruiken ze discrete cosinusfuncties om vloeiende tijdreeksen te stimuleren en nemen ze standaardmodellen van de hemodynamische respons mee, het vertraagde bloed-zuurstofsignaal dat door fMRI wordt gemeten. Aan de ruimtelijke kant helpen spline-basen om aaneengesloten, coherente activatiepatronen te bevorderen in plaats van verspreide stippen. Extra beperkingen limiteren hoeveel temporele en ruimtelijke basisfuncties elke component mag gebruiken, wat overfitting aan ruis vermindert en het idee weerspiegelt dat echte hersennetwerken relatief compact zijn in zowel ruimte als tijd. Twee complementaire optimalisatiestrategieën worden gepresenteerd: SDPCAG werkt hele matrices in blokken bij, terwijl SDPCAC één component tegelijk verfijnt met behulp van residuele fouten, waarbij iets hogere kosten worden ingewisseld voor flexibelere aanpassingen.
De methode op de proef gesteld
Om te beoordelen hoe goed deze ideeën werken, voeren de auteurs uitgebreide tests uit op drie soorten data: zorgvuldig ontworpen synthetische fMRI-signalen met bekende grondwaarheid; een block-design motorisch experiment uit het Human Connectome Project; en een event-gerelateerde vinger-tapping studie van een onafhankelijk laboratorium. In deze settings vergelijken ze SDPCAG en SDPCAC met toonaangevende alternatieven die penalized matrix decomposition, sparse PCA, ICA en dictionary learning combineren. Ze meten hoe nauwkeurig herstelde tijdreeksen overeenkomen met bekende taakpatronen, hoe goed ruimtelijke kaarten samenvallen met gevestigde rust-netwerken en hoe nauwkeurig bronnen worden hersteld bij verschillende ruisniveaus. De nieuwe methoden produceren consequent schonere, meer gelokaliseerde hersenkaarten en minder rumoerige tijdreeksen, en behouden sterke prestaties zelfs wanneer de data zwaar gecorrumpeerd zijn. Een van de algoritmen, SDPCAG, verbetert de bronherstel-nauwkeurigheid met ongeveer 22% ten opzichte van een sterke concurrerende methode, terwijl het ook sneller draait dan zijn meer gedetailleerde partner SDPCAC.
Wat dit betekent voor hersenonderzoek
In eenvoudige termen biedt dit werk een betere manier om de signalen in fMRI-data te "ontmengen". Door ruimte en tijd gezamenlijk te modelleren, realistische voorkennis over hoe hersenactiviteit en bloedstroom zich gedragen te gebruiken, en intelligente sparsity af te dwingen, produceren SDPCAG en SDPCAC hersennetwerken die zowel scherper op de beelden zijn als truer zijn aan hun onderliggende tijdreeksen. Dit kan leiden tot betrouwbaardere detectie van taakgerelateerde activaties en preciezere mapping van rust-netwerken, wat op zijn beurt onderzoek naar aandoeningen zoals de ziekte van Alzheimer, psychiatrische stoornissen en andere hersenziekten ondersteunt. Hoewel er nog ruimte is om de aanpak te versnellen en uit te breiden—bijvoorbeeld naar studies met meerdere deelnemers of multimodale beeldvorming—vormt het een belangrijke stap in het omzetten van hoogdimensionale scangegevens in betrouwbare, interpreteerbare beelden van het werkende menselijke brein.
Bronvermelding: Khalid, M.U., Nauman, M.M., Rehman, S.U. et al. Structured dissociative PCA methods for high dimensional neuroimaging signal decomposition. Sci Rep 16, 6911 (2026). https://doi.org/10.1038/s41598-026-35764-3
Trefwoorden: fMRI-signaaldecompositie, spaarzame PCA, mapping van hersennetwerken, blinde bronseparatie, rusttoestandconnectiviteit