Clear Sky Science · nl
Een fysica‑geïnformeerd grafneuraal netwerk om docking‑gebaseerde bindingssterkte voor DYRK2 te benaderen bij het herbestemmen van Alzheimer‑geneesmiddelen
Waarom dit belangrijk is voor Alzheimer
De ziekte van Alzheimer neemt wereldwijd toe, terwijl de meeste huidige medicijnen slechts de symptomen verlichten en de ziekte niet stoppen. Het in het laboratorium testen van nieuwe middelen is traag en duur, vooral voor minder onderzochte herseneiwitten die mogelijk belangrijk zijn voor geheugen en zenuwgezondheid. Deze studie onderzoekt een slimme kortere weg: het gebruik van een fysica‑bewust kunstmatig intelligentiemodel om te voorspellen hoe goed bestaande Alzheimer‑middelen zich zouden binden aan een weinig onderzocht eiwit genaamd DYRK2, wat mogelijk nieuwe behandelrichtingen kan openen.
Een nieuwe kijk op oude medicijnen
In plaats van volledig nieuwe verbindingen vanaf nul te ontwerpen, richten de onderzoekers zich op drug repurposing — het vinden van nieuwe toepassingen voor medicijnen die al zijn goedgekeurd en waarvan de veiligheid gedeeltelijk bekend is. Ze onderzoeken vier bekende Alzheimer‑middelen (brexpiprazole, donepezil, galantamine en rivastigmine) en vragen hoe sterk elk van hen mogelijk aan DYRK2 bindt, een proteïnekinase dat betrokken is bij de groei en functie van zenuwcellen. DYRK2 is nauwelijks bestudeerd in de context van Alzheimer, maar vroege aanwijzingen verbinden het met synapsen, axonen en geheugen, wat het tot een intrigerend doelwit maakt dat bestaande therapieën zou kunnen aanvullen.
Moluculen omzetten in netwerken
Om deze geneesmiddel‑eiwitrelaties te onderzoeken, zetten de onderzoekers elk geneesmiddelmolecuul om in een graaf: atomen worden knooppunten en chemische bindingen lijnen die ze verbinden. Ze doen iets soortgelijks voor het DYRK2‑eiwit door de aminozuursequentie te representeren als een keten van verbonden eenheden. Een type machine‑learningmodel dat bekend staat als een graph neural network (GNN) kan van nature met dergelijke graafvormige input werken, en stuurt informatie langs de verbindingen om patronen in vorm en chemie te leren. Dit maakt het mogelijk dat het model, genaamd PhysDual‑GCN, zowel het geneesmiddel als DYRK2 ‘leest’ als interagerende netwerken in plaats van als eenvoudige strings of lijsten met kenmerken.
Fysica mengen met kunstmatige intelligentie
De meeste deep‑learningtools in geneesmiddelenonderzoek leren alleen uit data, waardoor hun interne werking moeilijk te interpreteren kan zijn. Hier weven de auteurs bewust basale fysische ideeën over atoominteracties in het model. Naast de geleerde graafeigenschappen berekent PhysDual‑GCN twee klassieke energietermen: één die elektrische aantrekking en afstoting tussen partiële ladingen vastlegt, en een andere die de aantrekkings‑ en afstotingscomponenten van van der Waals‑krachten beschrijft. Deze fysica‑gebaseerde energieën worden gecombineerd met de interne representatie van de GNN voordat een voorspelde bindingssterkte wordt uitgegeven. In feite wordt het model getraind om het gedrag van klassieke dockingprogramma’s — met name AutoDock Vina en aanverwante tools — na te bootsen, maar dan sneller, terwijl het verankerd blijft in vertrouwde fysische principes.
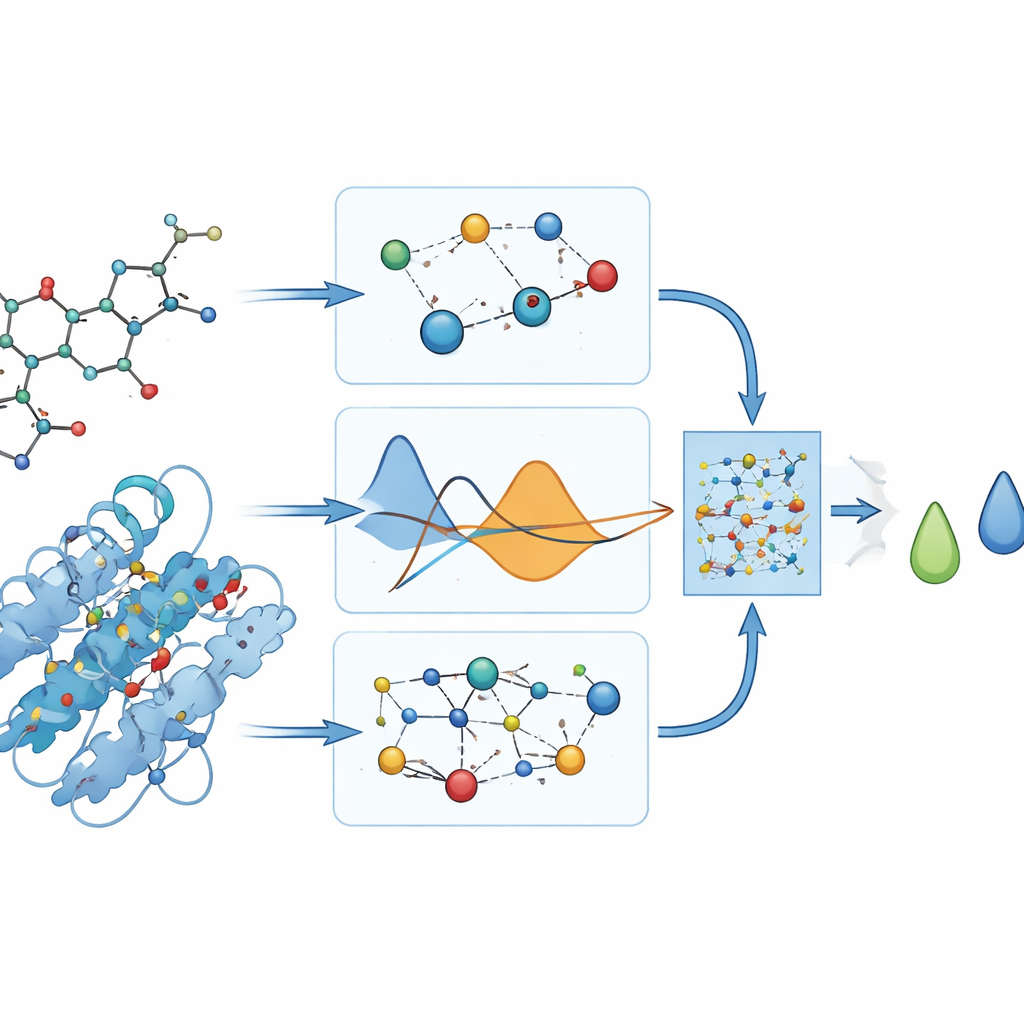
Wat het model daadwerkelijk voorspelt
Aangezien er geen laboratoriummetingen bestaan voor hoe sterk deze medicijnen aan DYRK2 binden, vertrouwen de auteurs op dockingprogramma’s om “referentie” bindingsscores in energietoestanden te leveren. Ze vermijden zorgvuldig om die scores in het trainingsproces te gebruiken en gebruiken ze alleen achteraf om te beoordelen hoe goed PhysDual‑GCN heeft geleerd. Voor de vier Alzheimermiddelen reproduceert het model de dockingwaarden met kleine gemiddelde fouten (ongeveer een derde kilocalorie per mol) en rangschikt het de verbindingen correct: donepezil en brexpiprazole komen naar voren als de sterkste binders, terwijl galantamine en rivastigmine zwakker lijken maar nog steeds redelijk stabiel. Deze resultaten tonen aan dat de fysica‑geïnformeerde GNN kan fungeren als een computationele surrogaat voor langzamere dockingruns.
Belofte en beperkingen van de aanpak
Ondanks deze bemoedigende cijfers benadrukken de auteurs dat hun studie strikte grenzen heeft. Slechts vier geneesmiddelen werden onderzocht en alle evaluaties steunen op andere computerprogramma’s in plaats van op echte biochemische experimenten. Het DYRK2‑eiwit wordt hoofdzakelijk gemodelleerd als een eendimensionale sequentiegraaf, niet als een volledige driedimensionale structuur, dus het model kan nog niet rekening houden met de gedetailleerde vorm van bindingspockets. De fysieke energieën zelf zijn vereenvoudigd en maken gebruik van standaard force‑fieldparameters en afkappunten. Als gevolg hiervan moet het werk gezien worden als een proof‑of‑concept: het toont aan dat fysica‑geleide grafneuronale netwerken klassieke docking‑scores in een lage‑data‑context nauw kunnen volgen, maar het bewijst nog niet dat de voorspellingen overeenkomen met de werkelijkheid in het laboratorium of de kliniek.
Wat dit betekent voor toekomstig Alzheimer‑onderzoek
Voor niet‑specialisten is de belangrijkste boodschap dat intelligente, fysica‑bewuste algoritmen onderzoekers kunnen helpen nieuwe Alzheimer‑doelen zoals DYRK2 veel sneller te verkennen dan traditionele methoden alleen. Door donepezil en brexpiprazole te benadrukken als veelbelovende DYRK2‑binders en een transparante manier te bieden om dockingresultaten te benaderen, levert PhysDual‑GCN een startpunt voor diepgaander laboratoriumonderzoek. Met grotere medicijnbibliotheken, rijkere 3D‑eiwitinformatie en experimentele validatie zou dit soort model een praktisch hulpmiddel kunnen worden voor het screenen van kandidaatbehandelingen en het sturen van herbestemmingsinspanningen gericht op het vertragen of veranderen van het beloop van de ziekte van Alzheimer.
Bronvermelding: Gider, V., Budak, C. A physics-informed graph neural network to approximate docking-based binding affinity for DYRK2 in Alzheimer’s drug repurposing. Sci Rep 16, 8357 (2026). https://doi.org/10.1038/s41598-026-35102-7
Trefwoorden: Ziekte van Alzheimer, herbestemming van geneesmiddelen, graph neural networks, eiwit–ligand binding, DYRK2‑kinase