Clear Sky Science · nl
Genetische diversiteit van Pseudomonas aeruginosa geïsoleerd uit klinische monsters met ISSR-moleculaire marker in een tertiair universitair ziekenhuis
Waarom ziekenhuiskiemen ons allemaal aangaan
Iemand die tijd in een ziekenhuis heeft doorgebracht — als patiënt of als bezoeker van een naaste — rekent erop dat antibiotica werken wanneer dat het hardst nodig is. Maar sommige kiemen worden zo taai dat zelfs onze krachtigste geneesmiddelen moeite hebben ze te stoppen. Dit artikel behandelt één van die probleemverwekkers, de bacterie Pseudomonas aeruginosa, en laat zien hoe wetenschappers in een ziekenhuis in India haar verborgen genetische variatie in kaart brachten om beter te begrijpen waarom ze zo moeilijk te beheersen is.
Een hardnekkige kiem in moderne ziekenhuizen
Pseudomonas aeruginosa is een glibberige tegenstander. Ze gedijt in vochtige omgevingen, van beademingsbuizen tot wondverbanden, en treft vooral mensen wier afweer al verzwakt is door ziekte, brandwonden of een langdurig verblijf in het ziekenhuis. Ze kan ernstige long-, bloed-, urine- en wondinfecties veroorzaken. Wat haar bijzonder gevaarlijk maakt, is het vermogen om tegen veel antibiotica tegelijk resistent te zijn, waardoor routinematige infecties levensbedreigende crises worden en de behandelingskosten en ligduur wereldwijd toenemen.
Onder de oppervlakte van infectie kijken
Om te zien hoe divers deze kiem binnen één ziekenhuis werkelijk is, verzamelden de onderzoekers 100 bacteriële monsters uit bloed, urine, sputum en wonduitstrijkjes die tijdens routinezorg werden genomen in een groot onderwijsziekenhuis in oostelijk India. Ze concentreerden zich op 18 stammen die multiresistent waren en testten hoe elk reageerde op een uitgebreid paneel van antibiotica. Zorgwekkend was dat meer dan vier van de vijf monsters resistent bleken tegen sleutelmedicijnen zoals cefoperazon, meropenem en imipenem — middelen die vaak als laatste redmiddel worden ingezet wanneer andere falen. Een paar antibiotica, waaronder enkele minder gebruikte, werkten nog beter, wat wijst op resterende maar krimpende behandelingsmogelijkheden. 
De „streepjescode” van de bacterie lezen
Uitsluitend tellen welke middelen faalden was maar de helft van het verhaal. Het team wilde ook weten of deze infecties voortkwamen uit één succesvolle ‘superstam’ die zich door het ziekenhuis verspreidde, of uit veel niet-verwante lijnen die onafhankelijk binnenkwamen en evolueerden. Hiervoor gebruikten ze een DNA‑vingerafdrukmethode genaamd ISSR, die de stukken genetische code tussen korte herhaalde sequenties zichtbaar maakt. Na PCR-amplificatie en scheiding op een gel vormen die stukken een patroon van banden dat als een streepjescode voor elke stam fungeert. Met 17 informatieve primers genereerden de onderzoekers 95 unieke DNA-banden en vergeleken ze vervolgens de patronen over alle 18 stammen met computertools die gelijkende vingerafdrukken groeperen.
Veel verre neven, geen één superbug
De genetische vergelijkingen toonden aan dat het ziekenhuis niet te maken had met één uit de hand gelopen kloon. In plaats daarvan vielen de stammen in meerdere aparte clusters, met overeenkomsten variërend van redelijk nauwe verwantschap tot sterk uiteenlopende verwanten. Sommige isolaten die in medicijntests gelijk leken te reageren, bleken genetisch verschillend, terwijl andere verwante stammen delen van resistentie gemeen hadden. Principal component-plots en boomachtige diagrammen versterkten het beeld van meerdere coördinerende lijnen die gelijktijdig in dezelfde instelling bestaan in plaats van één dominante stam die zich doorzet. Deze diversiteit ontstaat waarschijnlijk doordat de bacteriën genen uitwisselen, muteren en zich aanpassen onder voortdurende blootstelling aan antibiotica en het menselijke immuunsysteem. 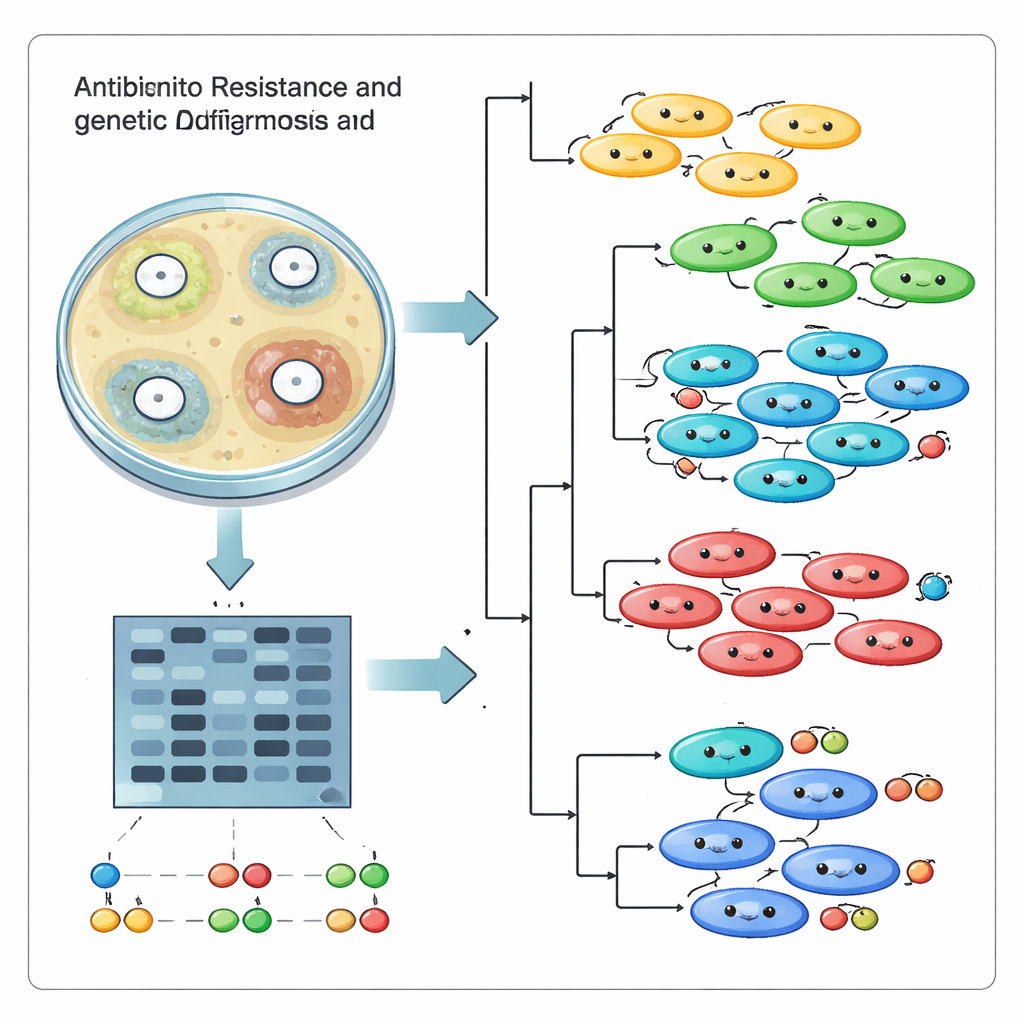
Wat dit betekent voor patiënten en ziekenhuizen
Voor ziekenhuizen brengen deze bevindingen een duidelijke boodschap: alleen bijhouden welke antibiotica falen is niet voldoende. Omdat genetisch verschillende stammen vergelijkbare resistentiepatronen kunnen delen — en nauwe verwanten zich anders kunnen gedragen — hebben zorgteams zowel routinematige gevoeligheidstests voor geneesmiddelen als periodieke genetische surveillances nodig om te zien hoe de bacteriële populatie in de loop van de tijd verschuift. De hier gebruikte ISSR-methode is relatief eenvoudig en goedkoop, wat haar aantrekkelijk maakt voor middelenarme omgevingen, hoewel de auteurs benadrukken dat het combineren met gedetailleerdere whole-genome sequencing in toekomstige studies een vollediger beeld zou geven.
Een verborgen landschap dat waakzaamheid vereist
Kort gezegd laat deze studie zien dat binnen één ziekenhuis Pseudomonas aeruginosa niet één vijand is maar een menigte verwante yet distincte probleemverwekkers, van wie vele al tegen meerdere antibiotica gewapend zijn. Door dit verborgen landschap van diversiteit in kaart te brengen, bieden de onderzoekers instrumenten en inzicht die artsen kunnen helpen gerichter te behandelen en infectiebestrijdingsteams slimmerere beheersstrategieën te ontwerpen. Continu toezicht op deze genetische patronen zal essentieel zijn om een stap voor te blijven op deze aanpasbare kiem en om de ziekenhuiszorg veilig te houden voor patiënten.
Bronvermelding: Mishra, P., Sahoo, D. & Sahu, M.C. Genetic diversity of Pseudomonas aeruginosa isolated from clinical samples with ISSR molecular marker in a tertiary care teaching hospital. Sci Rep 16, 5315 (2026). https://doi.org/10.1038/s41598-026-35090-8
Trefwoorden: Pseudomonas aeruginosa, antibioticaresistentie, ziekenhuisinfecties, genetische diversiteit, moleculaire typering