Clear Sky Science · nl
Een volledige mtDNA-dataset voor het bestuderen van genetische variatie over generaties en complexe familiestructuren
Familielijnen volgen via kleine energiecentrales
Iedereen van ons draagt een kleine ring van DNA in de energiecentrales van onze cellen, de mitochondriën, die vrijwel geheel van onze moeders afkomstig is. Deze genetische ring kan familiegeschiedenis onthullen, helpen misdaden op te lossen en licht werpen op ziekten — mits we hem nauwkeurig kunnen lezen. De hier beschreven studie levert een zorgvuldig gevalideerde verzameling volledige mitochondriale genomen uit echte families over meerdere generaties, en biedt een nieuw referentiemodel voor onderzoekers die willen volgen hoe dit bijzondere DNA verandert tijdens het doorgeven.
Waarom mitochondriaal DNA ertoe doet
Mitochondriën functioneren als kleine energiefabriekjes in onze cellen en bevatten hun eigen DNA, los van het DNA in de celkern. Omdat mitochondriaal DNA vrijwel uitsluitend via de moeder wordt doorgegeven en in vele kopieën per cel voorkomt, is het een belangrijk instrument geworden in disciplines variërend van evolutionaire biologie en medische genetica tot forensische wetenschap. Het kan overleven in beschadigde of oude monsters waar gewoon DNA faalt, en door de strikte moederlijke overerving is het een natuurlijke tracer van familielijnen en menselijke migraties door de tijd.
Het probleem van genetische echo’s op de verkeerde plek
Het volledig lezen van mitochondriaal DNA is niet eenvoudig. In de loop van evolutie zijn fragmenten van mitochondriaal DNA gekopieerd en in onze nucleaire chromosomen geplakt. Deze lijken sterk op echte mitochondriale sequenties en liggen verspreid door het genoom als misleidende echo’s. Wanneer wetenschappers standaard short-read sequencing gebruiken, kunnen deze nucleaire look‑alikes — NUMTs genoemd — worden aangezien voor echte mitochondriale varianten, waardoor het onduidelijk wordt welke veranderingen daadwerkelijk tot het mitochondriale genoom behoren, vooral bij het zoeken naar zeldzame mutaties of het reconstrueren van volledige moederlijke lijnen.

Een nieuwe manier om de hele ring in één keer te lezen
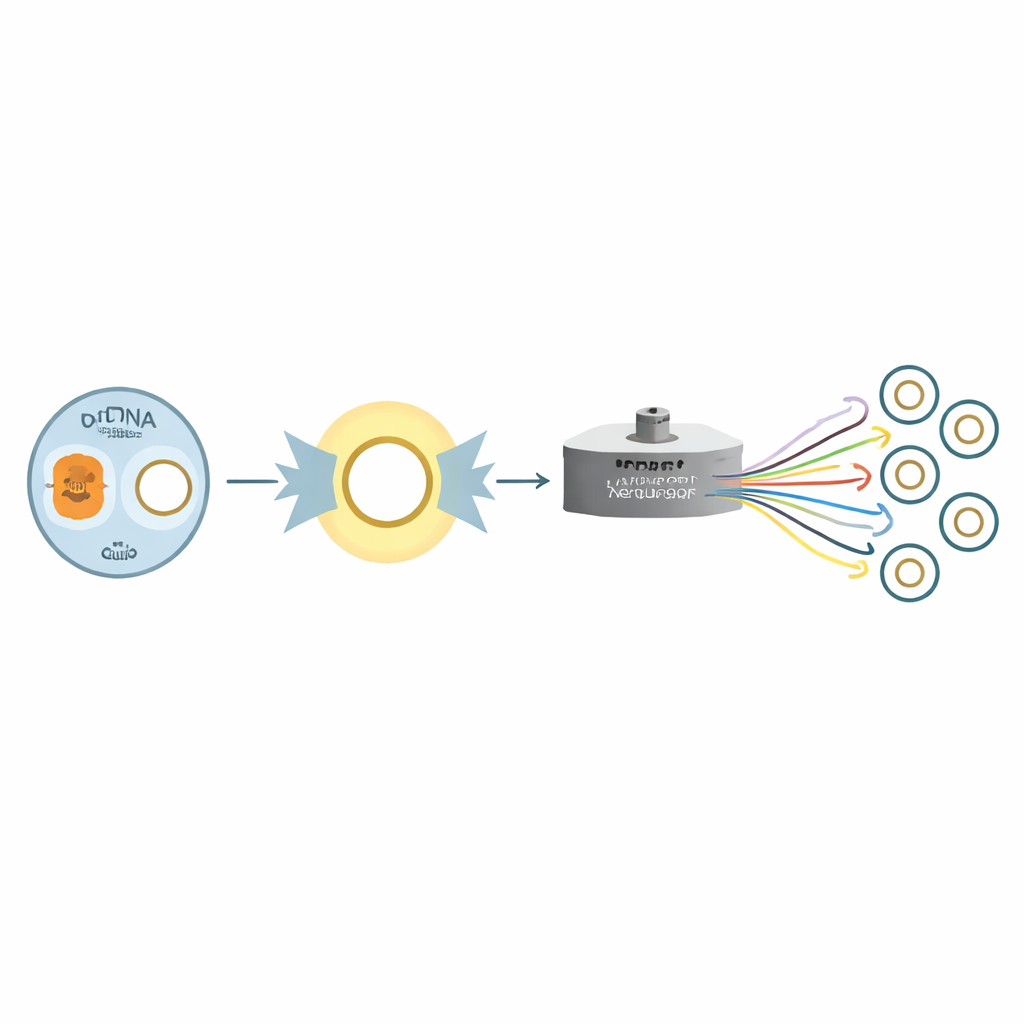
De onderzoekers pakten deze uitdaging aan met een derde-generatie nanopore-sequencingplatform gecombineerd met een slimme één-stuk amplificatiestrategie. In plaats van de mitochondriale ring in vele kleine fragmenten te knippen, gebruikten ze één primerpaar om vrijwel het hele circulaire molecuul in één lang stuk te kopiëren. Dit ontwerp geeft een voordeel aan echte circulaire mitochondriale DNA boven nucleaire echo’s en produceert lange reads die het hele genoom overspannen. Ze pasten deze aanpak toe op bloedmonsters van 106 personen uit acht families, inclusief meer-generatiehuishoudens en complexere patronen zoals halfbroers en -zussen, en creëerden daarmee een zeldzame dataset waarin moederlijke verwantschappen bekend zijn en gecontroleerd kunnen worden.
Opbouwen en controleren van een referentieset op familiebasis
Na het sequencen voerden de onderzoekers de data door een transparante, stapsgewijze analysepipeline. Ze filterden reads die te kort of te lang waren, controleerden de algemene kwaliteit en lijnden de resterende sequenties uit tegen een standaard mitochondriaal referentiegenoom. De dekking van het mitochondriale genoom bereikte 100 procent in alle individuen, met zeer hoge mappingpercentages. Vervolgens gebruikten ze gespecialiseerde software om varianten te identificeren, mitochondriale lijnen (haplogroepen) toe te wijzen en de volledige mitochondriale sequentie van elk persoon te reconstrueren. Omdat de monsters uit echte families kwamen, konden de onderzoekers testen of moeders en hun kinderen overeenkomende mitochondriale patronen droegen. In 73 van de 74 moederlijke lijnen kwamen de toegewezen haplogroepen overeen met de geregistreerde familiebanden, en de ene mismatch weerspiegelde waarschijnlijk een labelfout in plaats van een biologische verrassing.
Opletten voor verborgen foutbronnen
Om te waarborgen dat misleidende nucleaire echo’s de resultaten niet corrumpeerden, lijnden de onderzoekers de lange reads ook uit tegen het volledige menselijke genoom en zochten naar reads die zowel op mitochondriale als nucleaire locaties aansloegen. Dergelijke gebeurtenissen waren zeldzaam en deden zich voornamelijk voor in bekende NUMT-regio’s, wat de stelling ondersteunt dat hun strategie deze verwarringsbron sterk verminderde. Ze controleerden daarnaast op grote structurele veranderingen in het mitochondriale genoom en vonden niets boven hun detectiedrempel, consistent met de verwachte stabiliteit van dit DNA bij gezonde individuen. Tegelijk waarschuwden ze dat de onderliggende sequencingtechnologie nog een bescheiden foutpercentage heeft, en dat ultra‑zeldzame varianten en zeer lange nucleaire echo’s zonder aanvullende bevestiging moeilijk te onderscheiden kunnen blijven.
Wat dit betekent voor toekomstige studies
Uiteindelijk beweert dit werk niet alle technische obstakels in de mitochondriale genetica te hebben opgelost, maar het levert wel iets wat onderzoekers misten: een goed gedocumenteerde, familiegebaseerde verzameling volledige mitochondriale genomen geproduceerd met een modern long-read‑platform. Omdat de data openlijk worden gedeeld samen met gedetailleerde methoden en kwaliteitscontroles, kunnen andere wetenschappers deze bron gebruiken om nieuwe analysetools te testen, te onderzoeken hoe mitochondriale mutaties zich over generaties voordoen, afstamming beter te bepalen of forensische methoden te benchmarken. Voor niet‑specialisten is de conclusie dat we steeds beter worden in het nauwkeurig en verantwoordelijk lezen van deze kleine moederlijke DNA‑draad, waarmee nieuwe vensters op gezondheid, geschiedenis en identiteit worden geopend.
Bronvermelding: Liu, Y., Yang, Q., Xuan, Y. et al. A full-length mtDNA dataset for studying genetic variations across generations and complex family structures. Sci Data 13, 442 (2026). https://doi.org/10.1038/s41597-026-06824-0
Trefwoorden: mitochondriaal DNA, moederlijke overerving, familie-stamboom, long-read-sequencing, forensische genetica