Clear Sky Science · nl
Diepte-opgeloste metagenomische dataset van oppervlakte- en diepe-chlorofylmaximumlagen in de Westelijke Stille Oceaan
Waarom klein leven in de oceaan ertoe doet
Het heldere blauwe water van de open Stille Oceaan lijkt misschien leeg, maar het zit vol microscopisch leven dat stilletjes veel van de chemie van onze planeet aanstuurt. Deze drijvende microben helpen bij het verplaatsen van koolstof, stikstof en andere elementen door de oceaan en beïnvloeden zo alles van visbestanden tot het klimaat. Deze studie beschrijft niet alleen een paar nieuwe soorten — ze levert een grote, open dataset die vastlegt wie deze microben zijn en wat ze op verschillende dieptes kunnen doen in een afgelegen deel van de Westelijke Stille Oceaan. Die informatie wordt een gedeelde bron voor wetenschappers die proberen te begrijpen en te voorspellen hoe de oceaan zal reageren op een veranderend klimaat.
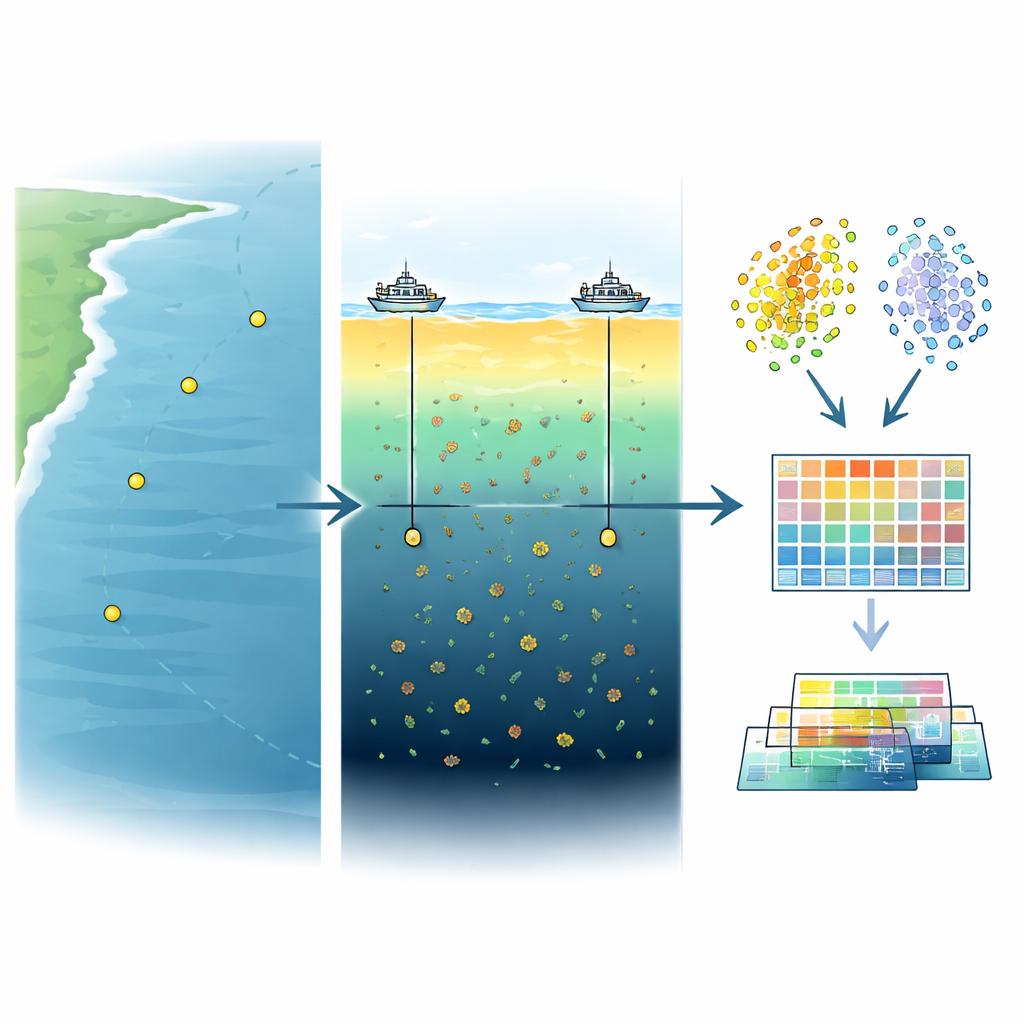
Kijken in een verborgen groene laag
De onderzoekers richtten zich op twee gelaagde lagen van de zee: het door zonlicht verlichte oppervlak, waar het licht het sterkst is, en een iets diepere band die het diepe chlorofylmaximum wordt genoemd. In deze verborgen groene laag, meestal 75 tot 100 meter diep, bereiken microscopische planten en andere kleine organismen vaak hun hoogste dichtheid, ondanks dat het zonlicht zwakker is. Door op vier stations, verspreid over ongeveer 800 kilometer van de Westelijke Stille Oceaan, beide lagen te bemonsteren, kon het team vergelijken hoe microbiële gemeenschappen veranderen met diepte en afstand. Deze regio is bijzonder belangrijk omdat ze gevoelig is voor verschuivingen in temperatuur en nutriënten als gevolg van klimaatverandering en oceaanstromingen.
Zeewater omzetten in digitale DNA
Om deze gemeenschappen vast te leggen filterde het team ongeveer 75 liter zeewater per monster om de microben te verzamelen, vroren de filters in en extraheerden later hun DNA onder zorgvuldig gecontroleerde laboratoriumomstandigheden om besmetting te voorkomen. Vervolgens gebruikten ze high-throughput DNA-sequencing om miljarden kleine fragmenten genetisch materiaal van acht monsters te lezen (vier van het oppervlak, vier uit de diepte). Na het schonen en controleren van de datakwaliteit maakten ze digitaal langere DNA-stukken door fragmenten aan elkaar te zetten en zochten ze naar genen. Het eindresultaat was een enorme verzameling van ongeveer 5,26 miljoen niet-redundante genen — een gigantische catalogus die de potentiële mogelijkheden van deze oceaanmicroben laat zien.
Wie leeft waar in de waterkolom
Toen het team het DNA sorteerde om te zien welke typen organismen aanwezig waren, vonden ze dat elk monster een opmerkelijk rijke mix van leven bevatte: tussen de 58 en 67 grote lijnen (phyla), meer dan 100 klassen en meer dan 6.000 soorten per station. Toch verschoof de balans met de diepte. Eukaryoten — organismen met complexere cellen, waaronder veel soorten microscopische algen — kwamen vaker voor in de diepere, chlorofylrijke laag, terwijl bepaalde bacteriën die floreren in helder, voedingsarm oppervlakwater minder talrijk werden met diepte. Andere bacteriegroepen waren juist verrijkt in de diepe laag, wat een duidelijk verticaal patroon onthult in wie elk deel van de waterkolom domineert.
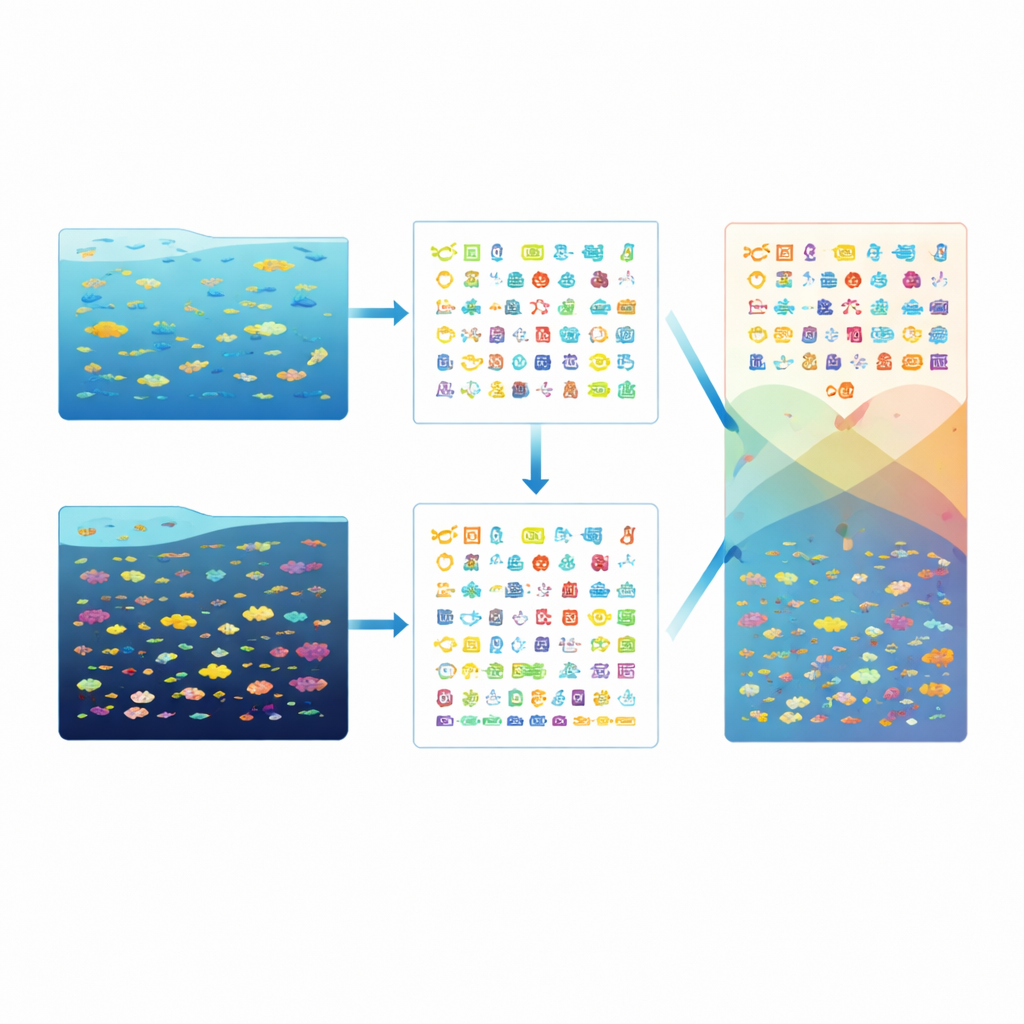
Wat microbiele genen onthullen over oceaanprocessen
Buiten het enkel tellen van soorten onderzochten de onderzoekers wat de genen zelf suggereren over hoe deze gemeenschappen functioneren. Door hun gencatalogus te vergelijken met meerdere referentiedatabases konden ze aan veel genen waarschijnlijke rollen toewijzen, inclusief genen betrokken bij het gebruik van verschillende vormen van koolstof, stikstof en zwavel. Statistische analyses zochten naar genen die op de ene diepte of bij het ene station vaker voorkwamen dan bij het andere, waarbij werd benadrukt hoe temperatuur, zuurstof en nutriëntenniveaus de “gereedschapskisten” die deze microben dragen kunnen vormen. De kwaliteitscontroles op sequencing, assemblage en annotatie lieten zien dat de dataset compleet en betrouwbaar genoeg is om door anderen als referentie te worden gebruikt.
Een gedeelde bron voor toekomstige oceaankwesties
In plaats van één smalle conclusie te trekken levert dit werk een goed gedocumenteerde, openbaar beschikbare DNA- en gencatalogus die anderen kunnen doorzoeken om vele vragen te beantwoorden. Het biedt een gedetailleerde momentopname van hoe microscopisch leven is gerangschikt van het oppervlak tot het diepe chlorofylmaximum in een sleutelregio van de Westelijke Stille Oceaan, samen met de genetische blauwdrukken die deze organismen in staat stellen vitale chemische cycli aan te sturen. Voor niet-specialisten is de kernboodschap eenvoudig: de ogenschijnlijk lege blauwe oceaan verbergt gelaagde, dynamische microbiële gemeenschappen, en deze open dataset geeft wetenschappers een krachtig nieuw venster om te volgen hoe die levende lagen kunnen veranderen naarmate de planeet opwarmt.
Bronvermelding: Thangaraj, S., Sun, J. Depth Resolved Metagenomic Dataset from Surface and Deep Chlorophyll Maximum Layers in the Western Pacific Ocean. Sci Data 13, 324 (2026). https://doi.org/10.1038/s41597-026-06706-5
Trefwoorden: marien microbioom, metagenomica, Westelijke Stille Oceaan, diep chlorofylmaximum, oceanische biogeochemie