Clear Sky Science · nl
Genoomsequencing, de novo-assemblage en annotatie van de commercieel belangrijke bamboe, Bambusa tulda Roxb
Een snelgroeiend gras met grote mogelijkheden
Bamboe lijkt misschien een eenvoudige tuinplant, maar is in feite een krachtige natuurlijke hulpbron voor bouwmaterialen, papier en zelfs toekomstige biobrandstoffen. Een veelgebruikte soort, Bambusa tulda of Bengalbamboe, groeit snel, slaat grote hoeveelheden houtig materiaal op en bloeit slechts zelden. Tot nu toe ontbrak wetenschappers een volledig "instructieboek" voor deze soort. Dit artikel beschrijft hoe onderzoekers de volledige DNA-volgorde van B. tulda hebben ontcijferd en georganiseerd, en zo een fundamentele bron hebben gecreëerd die zal helpen om bamboe te verbeteren voor industrie, natuurbehoud en klimaatsvriendelijke technologieën.
Waarom het DNA van bamboe ontcijferen?
Bambusa tulda komt veel voor op het Indiase subcontinent en in delen van Zuidoost-Azië, waar de stevige culms (stengels) worden gebruikt in plattelandsbouw, meubels en ambachtelijke producten. De soort wekt ook interesse als bron voor papierpulp en hernieuwbare energie. Toch vertoont B. tulda raadselachtig gedrag: hij kan zeer snel groeien, veel taai, houtig materiaal opslaan en dan ongeveer 50 jaar wachten voordat hij bloeit, waarbij soms alle planten in een gebied tegelijk bloeien. Zonder een volledig genoom konden wetenschappers alleen maar gissen welke genen deze eigenschappen regelen. Door het DNA te lezen en samen te voegen, wilden de auteurs een referentiekaart maken die toekomstige onderzoekers kunnen gebruiken om groei, bloei, ziektebestendigheid en meer te bestuderen.
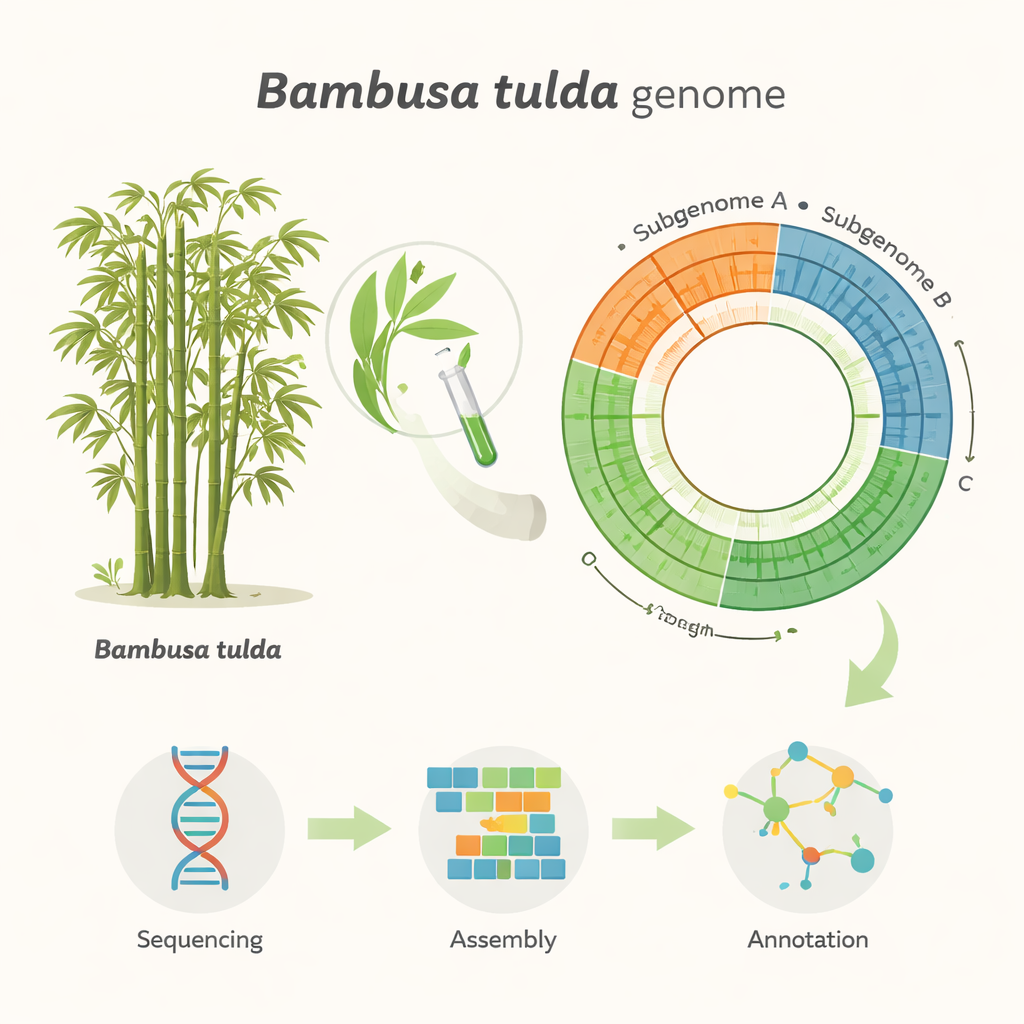
Een enorm genoom meten en lezen
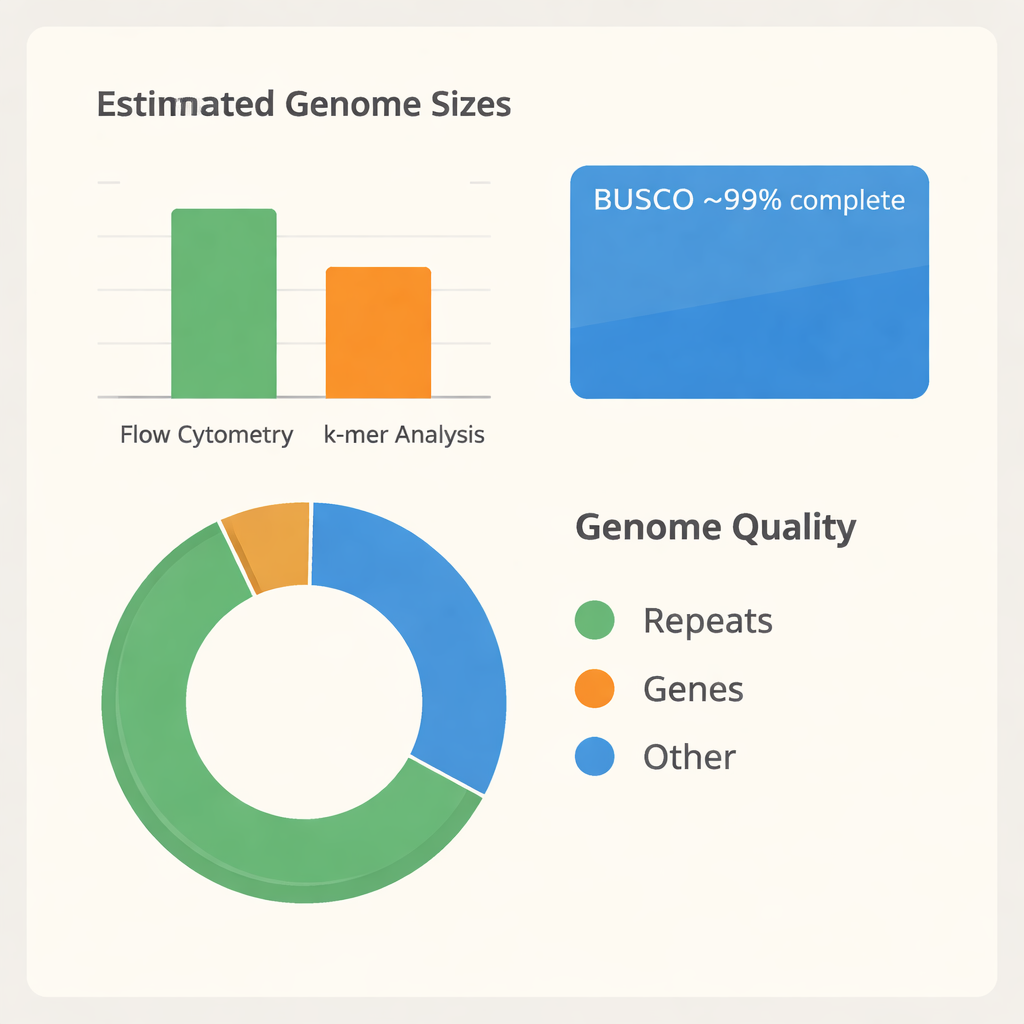
Het team moest eerst vaststellen hoe groot het genoom van B. tulda is. Met een techniek genaamd flowcytometrie vergeleken ze de DNA-inhoud van B. tuldabladcellen met die van tomaat en maïs, twee planten waarvan de genoomgroottes al bekend zijn. Dit suggereerde een diploïde genoomgrootte van ongeveer 3 miljard DNA-"letters." Vervolgens gebruikten ze een tweede, onafhankelijke methode gebaseerd op de overlap van korte DNA-fragmenten (k-meranalyse), die een iets kleinere omvang van ongeveer 2,34 miljard letters schatte en liet zien dat veel van het genoom repetitief en waarschijnlijk gedupliceerd is. Met deze schattingen in handen is zeer lang, hoogwaardig DNA uit jonge bladeren geëxtraheerd en met geavanceerde PacBio HiFi-technologie gesequenced, wat meer dan 116 miljard basen aan ruwe data opleverde—genoeg om het genoom tientallen keren te lezen.
Het blauwdruk van bamboe in elkaar zetten
Het omzetten van miljoenen DNA-reads in een geordend genoom is als het leggen van een enorme legpuzzel zonder afbeelding op de doos. De onderzoekers gebruikten gespecialiseerde software om zowel een gecombineerde primaire assemblage als twee afzonderlijke haplotypen te bouwen, die de twee ouderlijke kopieën van het genoom weerspiegelen. Na het verwijderen van dubbele en organel-afgeleide fragmenten kwamen ze uit op een gestroomlijnde "haploïde" assemblage van 43 grote segmenten, die ongeveer 1,37 miljard basen beslaan. Deze segmenten vallen in drie subgenomen, gelabeld A, B en C, wat overeenkomt met de complexe, polyploïde oorsprong van B. tulda. Een veelgebruikte kwaliteitscontrole genaamd BUSCO toonde aan dat ongeveer 99% van de verwachte plantengenen aanwezig en intact is, wat aangeeft dat de assemblage zowel compleet als betrouwbaar is voor vervolgonderzoek.
Genen, repetitieve elementen en evolutionaire aanwijzingen
Nadat het genoom was geassembleerd, was de volgende stap het identificeren van de werkende onderdelen. Door drie bewijslijnen te combineren—voorspellingen uit de DNA-volgorde zelf, overeenkomst met genen van andere bamboes en RNA-data van actief tot expressie komende genen—annoteerde het team 56.890 eiwitcoderende genen, die ruwweg een vijfde van het genoom innemen. Ze brachten ook grote aantallen niet-coderende RNA's in kaart, waaronder meer dan duizend transfer- en ribosomaal-RNA-genen die de eiwitproductie ondersteunen. Opvallend is dat ongeveer twee derde van het genoom bestaat uit repetitieve elementen, vooral mobiele DNA-segmenten die kopiëren en verplaatsen. Deze repetitievelden helpen verklaren waarom eerdere grootte-schattingen verschilden en wijzen op een dynamische evolutionaire geschiedenis. Vergelijking van eiwitfamilies over twaalf andere bamboesoorten, samen met maïs en banaan als verwanten, plaatste B. tulda duidelijk onder de paleotropische houtachtige bamboes met een hexaploïde achtergrond, waarmee wordt bevestigd dat zijn genoom is opgebouwd uit meerdere ancestrale kopieën.
Een nieuwe basis voor toekomstig bamboeonderzoek
Voor niet-specialisten is de belangrijkste uitkomst dat B. tulda nu een hoogwaardig referentiegenoom heeft—een geïndexeerde, doorzoekbare blauwdruk van zijn DNA. Deze bron stelt wetenschappers in staat genen te lokaliseren die snelle groei, houtigheid en vertraagde bloei regelen, en ze te vergelijken met die in andere grassen. Het zal ook inspanningen ondersteunen om bamboevariëteiten te kweken of te ontwerpen die beter geschikt zijn voor bouw, papier of energie, terwijl natuurlijke populaties behouden blijven. Kortom, door het genetische landschap van deze commercieel belangrijke bamboe in kaart te brengen, legt de studie de basis voor slimmer gebruik van een van ‘s werelds veelzijdigste planten.
Bronvermelding: Kundu, S., Rupp, O., Dey, S. et al. Genome sequencing, de novo assembly and annotation of the commercially important bamboo, Bambusa tulda Roxb. Sci Data 13, 175 (2026). https://doi.org/10.1038/s41597-026-06679-5
Trefwoorden: bamboegenoom, Bambusa tulda, planten-genetica, houtachtige grassen, hernieuwbare biomaterialen