Clear Sky Science · nl
Een chromosoomniveau-genoomassemblage van Homatula variegata uit het stroomgebied van de Yangtze
Een klein beekvisje met een groot genetisch verhaal
In de snelstromende, stenige beekjes die de bovenloop van China’s Yangtze voeden, leeft een kleine, gestreepte modderkruiper genaamd Homatula variegata. Hij wordt gewaardeerd zowel als voedsel als voor thuisaquaria, maar tot nu toe was er bijna niets bekend over zijn DNA‑blauwdruk. Deze studie levert de eerste bijna volledige, chromosoom‑voor‑chromosoom kaart van het genoom van de soort, waarmee de deur wordt geopend naar slimmer behoud, efficiëntere kweek en diepere inzichten in hoe leven zich aanpast aan koude, snelstromende bergwatertjes.
Waarom het DNA van een bescheiden uitziende vis in kaart brengen?
Hoewel deze modderkruiper slechts ongeveer 14 centimeter wordt, speelt hij een onevenredig grote rol in lokale rivierecosystemen en de regionale aquacultuur. Hij gedijt in mid‑hoogte beekjes met grindige bodems en constante stroming en voedt zich met insecten, organisch afval en kleine visjes. Omdat hij zowel smakelijk als kleurrijk is, groeit de belangstelling om hem als inheemse sier‑ en voedselsoort te fokken. Kweken en beschermen van een soort zijn echter veel lastiger zonder een nauwkeurige genetische referentie. Een compleet genoom werkt als een gedetailleerde onderdelenlijst en bedradingsschema, en onthult de genen die groei, kleur, weerstand tegen ziekten en het vermogen om met snel, koel water om te gaan bepalen. Tot nu toe had geen enkele modderkruiper in deze tak van de vissenfamilie zo’n hoogwaardige referentie, waardoor er een groot blind vak ontstond in de genetica van zoetwatervissen.
Een chromosoom‑voor‑chromosoom DNA‑kaart bouwen
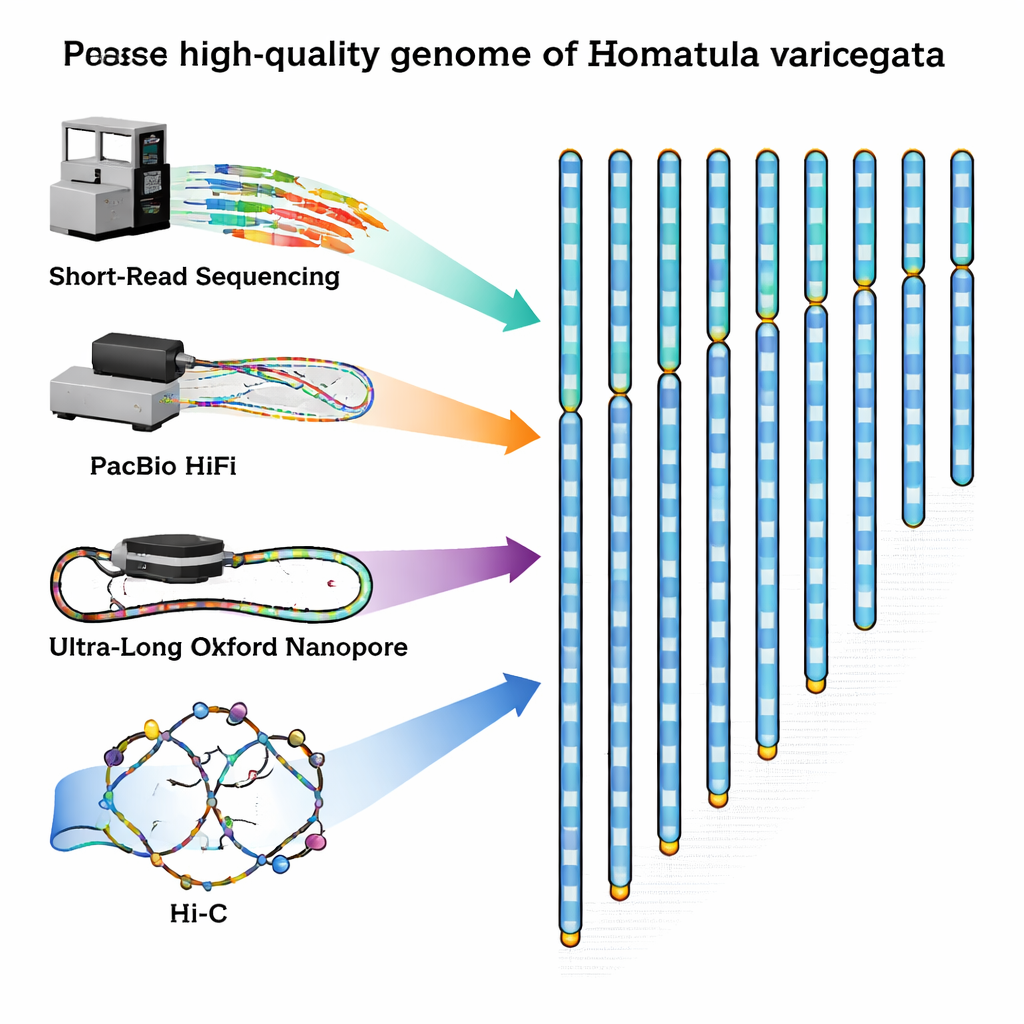
Om deze leemte te vullen, ving het onderzoeksteam een gezonde volwassen mannelijke modderkruiper in de Qingyi‑rivier, een zijrivier van de Yangtze, en extraheerde zorgvuldig DNA en RNA uit zijn bloed. Ze combineerden vervolgens meerdere geavanceerde sequencingmethoden, elk met verschillende sterke punten. Short‑read machines van Illumina leverden enorme aantallen zeer nauwkeurige DNA‑fragmentjes. PacBio HiFi‑technologie gaf wat langere fragmenten met uitstekende nauwkeurigheid, terwijl Oxford Nanopore‑apparaten ultralange strengen genereerden die over moeilijk te decoderen, repetitieve regio’s kunnen lopen. Ten slotte legde een methode genoemd Hi‑C vast hoe DNA‑strengen vouwen en met elkaar interageren in de celkern, en leverde zo een 3D‑contactkaart die helpt fragmenten in de juiste volgorde tot volledige chromosomen te verbinden.
Wat het nieuwe genoom onthult
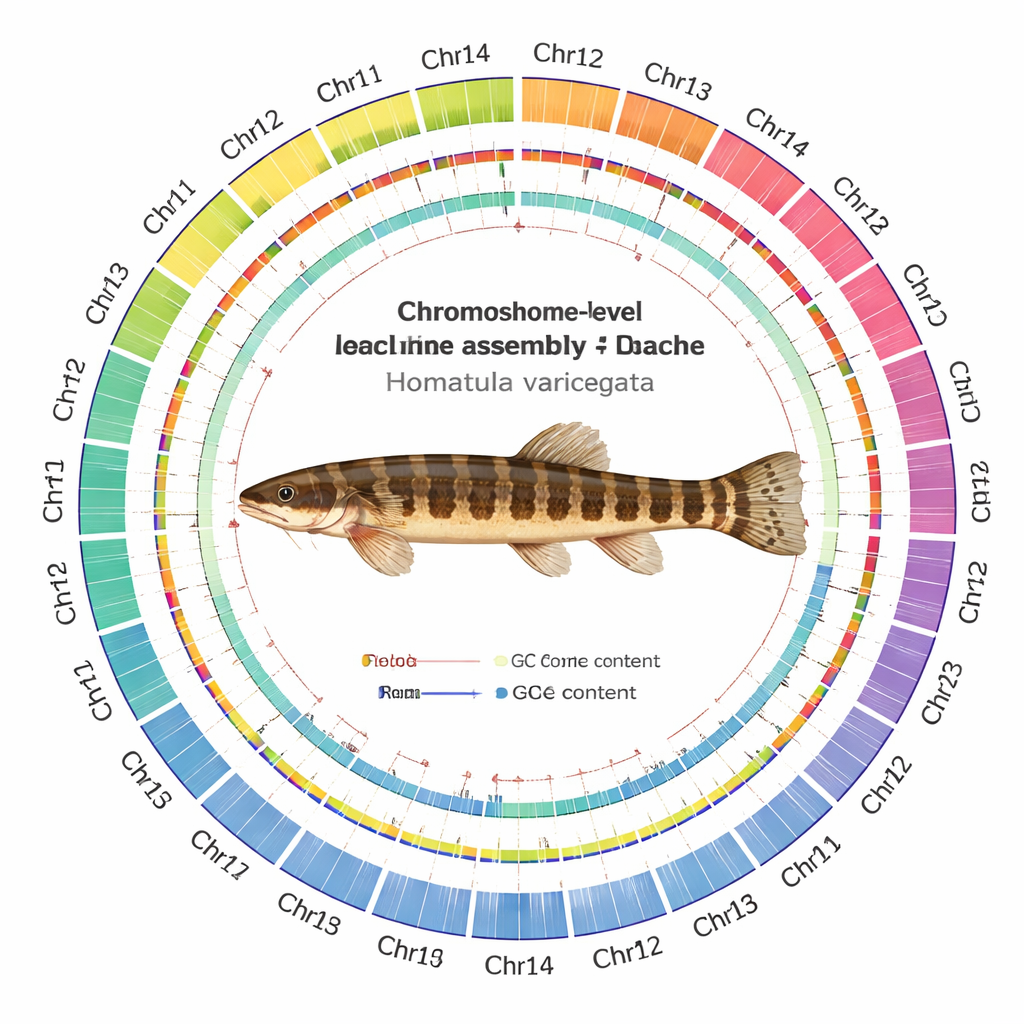
Door deze gegevens samen te weven met moderne assemblagesoftware en zorgvuldige kwaliteitscontroles, produceerde het team een genoom van 641 miljoen DNA‑letters, keurig georganiseerd in 24 chromosomen. Opmerkelijk is dat elk chromosoom als één enkele aaneengesloten eenheid is geassembleerd: 22 daarvan vertonen geen enkele gap en slechts twee bevatten zeer kleine hiaten. Ze konden 24 waarschijnlijke centromeren lokaliseren — de centrale “band” van elk chromosoom — en de meeste beschermende telomeerkapjes aan de chromosoomuiteinden detecteren. De wetenschappers registreerden 24.479 eiwitcodende genen en konden aan ongeveer 93% daarvan vermoedelijke functies toewijzen door vergelijking met grote internationale databanken. Ook brachten ze het landschap van herhaald DNA in kaart en vonden dat meer dan een kwart van het genoom uit mobiele genetische elementen bestaat, vooral DNA‑transposons, die door het genoom kunnen springen en soms evolutie aandrijven.
De kwaliteit onder de motorkap testen
Hoge‑niveau cijfers zijn alleen betekenisvol als de onderliggende kaart betrouwbaar is. Het team zette de assemblage daarom door een reeks tests. Reads van alle sequencingplatforms konden met zeer hoge percentages terug op het nieuwe genoom worden uitgelijnd, met vrijwel gelijkmatige dekking over de meeste chromosomen. Onafhankelijke tools die korte DNA‑patronen tellen, suggereerden dat bijna alle verwachte sequentieinhoud aanwezig is, en standaardtesten voor gencompleteit toonden aan dat de overgrote meerderheid van universele visgenen intact is. De Hi‑C‑contactkaarten vormden zuivere, vierkante patronen langs elk chromosoom, met weinig vreemd signaal ertussen, wat aangeeft dat segmenten correct zijn verbonden en niet door elkaar gehusseld.
Van DNA‑kaart naar impact in de praktijk
Voor een niet‑specialist klinkt dit werk misschien als een technische triomf op zichzelf, maar de implicaties zijn praktisch en breed. Het hebben van een bijna end‑to‑end genoom voor Homatula variegata geeft wetenschappers een referentie om wilde populaties mee te vergelijken, genetische diversiteit te volgen en tekenen van inteelt of lokale adaptatie te spotten. Kwekers kunnen zoeken naar DNA‑markers die gekoppeld zijn aan wenselijke eigenschappen zoals snelle groei, taaiheid of opvallende kleurpatronen, waardoor selectief fokken wordt versneld terwijl het natuurlijke karakter van de soort behouden blijft. Ecologen kunnen onderzoeken hoe deze modderkruiper is geëvolueerd om te leven in koele, snelstromende bergbeekjes — lessen die ook het beheer van verwante soorten kunnen informeren. Kortom, dit genoom op chromosoomniveau verandert een bescheiden riviervis in een krachtig model om het rijke leven van Aziatische zoetwaterecosystemen te begrijpen — en te beschermen.
Bronvermelding: Tang, Y., Wu, Q., Wang, Y. et al. A chromosome level genome assembly of Homatula variegata from the Yangtze River basin. Sci Data 13, 303 (2026). https://doi.org/10.1038/s41597-026-06667-9
Trefwoorden: visgenoom, chromosoomassemblage, zoetwater-biodiversiteit, aquacultuurgenetica, Yangtze‑meerval