Clear Sky Science · nl
Een gecureerde bron van chemolithoautotrofe genomen en markergenen voor voorspelling van CO₂-fixatiepaden
Microben die helpen het aardse koolstofbudget in evenwicht te houden
Verborgen in bodems, oceanen en extreme omgevingen kunnen bepaalde microben hun eigen biomassa opbouwen met kooldioxide (CO₂) als belangrijkste koolstofbron. Deze microscopische chemici zijn cruciaal om de koolstofkringloop van de aarde in balans te houden en kunnen ideeën opleveren voor nieuwe manieren om industrieel CO₂ af te vangen. Tot nu toe ontbrak het wetenschappers echter aan een eenvoudige, betrouwbare methode om in het DNA van een microbe te kijken en te bepalen welke CO₂-fixerende strategie hij gebruikt. Deze studie introduceert een gecureerde gencatalogus en een nieuw computergereedschap, AutoFixMark, dat die leemte vult.
Veel wegen om lucht in biomassa om te zetten
Niet alle organismen die CO₂ fixeren doen dat op dezelfde manier. Microben hebben minstens zeven natuurlijke paden ontwikkeld die CO₂ omzetten in organische stof. Sommige, zoals de Calvin–Benson–Bassham-cyclus die veel voorkomt in planten en veel bacteriën, zijn goed bestudeerd; andere, zoals het reductieve glycinepad dat pas in 2020 werd ontdekt, zijn nog slecht in kaart gebracht. Deze paden komen verspreid voor in vele takken van het leven en hergebruiken vaak vergelijkbare enzymen, wat het verrassend moeilijk maakt ze alleen op basis van genoomsequentie te onderscheiden. Bestaande software kan brede metabolische mogelijkheden voorspellen, maar is niet geoptimaliseerd of grondig getest om de exacte CO₂-fixatiepaden te identificeren.
Een schone referentiekaart van CO₂-fixerende microben opbouwen
De onderzoekers begonnen met het samenstellen van twee zorgvuldig gecontroleerde genoomverzamelingen. Eerst selecteerden ze 15 goed bestudeerde microben waarvan de CO₂-fixatiepaden in detail bekend zijn. Deze referentieorganismen, die meerdere bacteriële en archaeale groepen beslaan, dienden als blauwdrukken om de sleutelenzymen te definiëren die echt onderscheidend zijn voor elk pad. Vervolgens creëerden ze een benchmarkset van 347 chemolithoautotrofe genomen—microben die energie halen uit anorganische chemicaliën en biomassa opbouwen uit CO₂. Elk genoom in deze grotere set werd handmatig, op basis van de literatuur, gekoppeld aan specifieke CO₂-fixatiepaden, wat een solide waarheidset opleverde voor het testen van voorspellingen.
Markergenen en eenvoudige regels in plaats van zwarte dozen
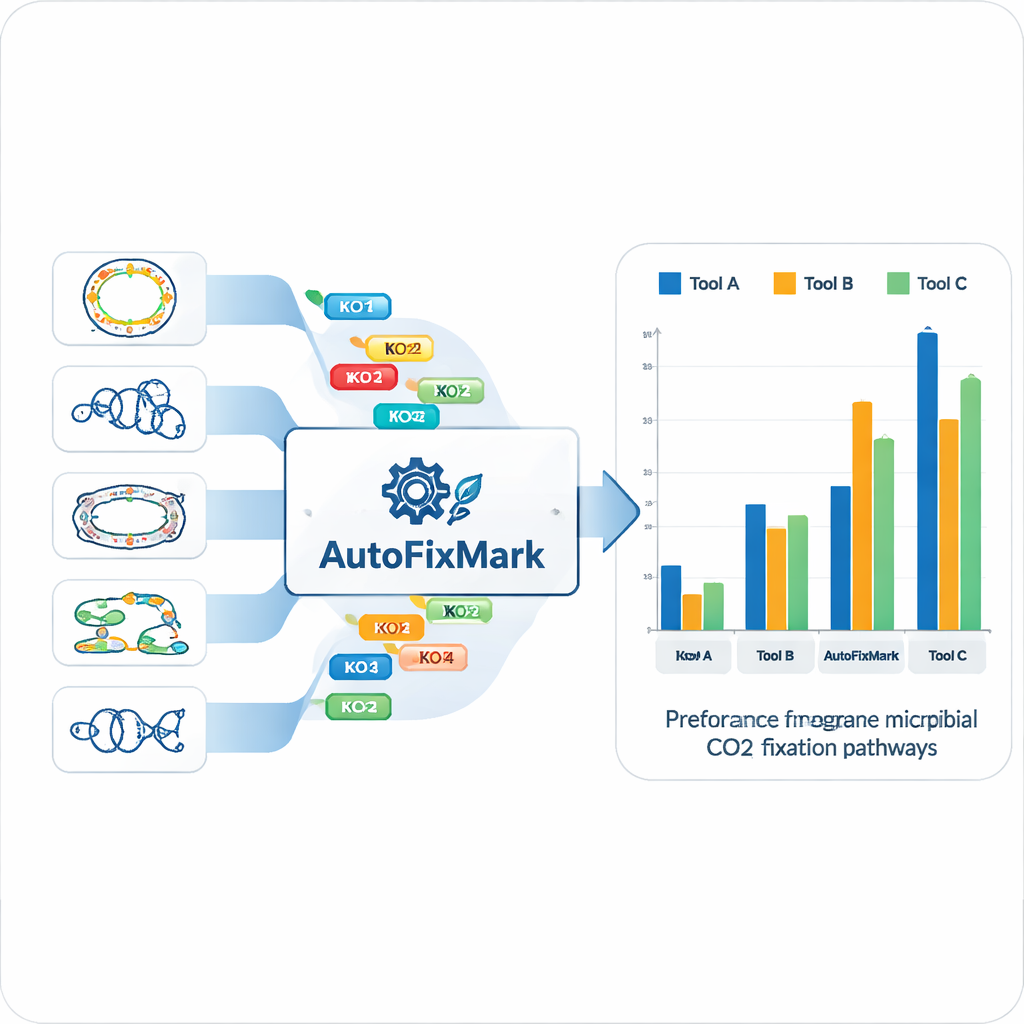
Met behulp van de 15 referentiegenomen identificeerde het team “markergenen” voor elk van de zeven CO₂-fixatiepaden en koppelde deze aan gestandaardiseerde KEGG Orthology (KO)-identifiers. In plaats van te vertrouwen op ondoorzichtige machine learning, codeerden ze transparante regels over hoe deze markers zich combineren. Sommige reacties kunnen worden uitgevoerd door een van meerdere alternatieve enzymen, wat wordt afgehandeld met een "one_of"-regel. Andere reacties berusten op multisubeenheidcomplexen en moeten "all_of" een gedefinieerde set KOs bevatten. Voor het reductieve glycinepad, waar niet alle componenten volledig begrepen zijn, gebruikt het gereedschap "at_least"-regels die een minimumaantal subunits vereisen. Deze logische regels zijn opgeslagen in een machineleesbaar JSON-bestand dat de kernkennisbasis voor AutoFixMark vormt.
Een lichtgewicht gereedschap dat gevestigde software overtreft
AutoFixMark zelf is een klein, regelgebaseerd programma geschreven in Python. Het neemt als invoer een lijst met KO-ID's van de genen in het genoom van een microbe, typisch geproduceerd door een apart hulpmiddel genaamd KofamScan, en controleert vervolgens welke markerregels voor elk van de zeven paden worden voldaan. De auteurs vergeleken AutoFixMark met twee veelgebruikte metabolische annotatietools, METABOLIC en gapseq, met behulp van hun 347-genoom benchmarkset. Alle drie de tools presteerden goed op klassieke paden zoals de Calvin-cyclus, de reductieve tricarboxylaatcyclus en het Wood–Ljungdahl-pad. AutoFixMark stak echter duidelijk uit boven de andere voor nieuwere of minder voorkomende paden zoals de 3-hydroxypropionaat/4-hydroxybutyraatcyclus, de dicarboxylaat/4-hydroxybutyraatcyclus en het reductieve glycinepad, waarvan sommige niet eens door concurrerende software worden gedekt.
Wat deze resultaten betekenen voor klimaat- en ecologiestudies
De gecureerde gensets, het AutoFixMark-programma en de volledige benchmarkgenoomverzameling zijn openbaar beschikbaar. Dit betekent dat onderzoekers nu zowel geïsoleerde microben als metagenoom-geassembleerde genomen kunnen screenen om te zien welke CO₂-fixatiestrategieën ze genetisch in huis hebben. Belangrijk is dat de auteurs benadrukken dat AutoFixMark de genetische potentie voorspelt, niet of een pad actief is onder werkelijke omstandigheden. Veel van deze biochemische routes kunnen omkeren, afhankelijk van de energiebalans van de cel. Desalniettemin zal een robuuste, transparante manier om CO₂-fixerende microben te signaleren wetenschappers helpen in kaart te brengen waar en hoe leven koolstof uit de atmosfeer verwijdert, experimenten met opkomende paden te sturen en het ontwerp van toekomstige CO₂-gebaseerde biotechnologieën te ondersteunen.
Bronvermelding: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Trefwoorden: microbiële koolstoffixatie, autotrofe stofwisseling, genoomannotatie, CO2-opslag, metagenomica