Clear Sky Science · nl
Genoomassemblage op chromosoomniveau van smalbladige katspaan (Sparganium angustifolium Michx., Typhaceae)
Een stille meerplant met een groot genomisch verhaal
Smalbladige katspaan is een onopvallende waterplant waar je misschien zonder tweede blik aan voorbij peddelt, maar die stilletjes het leven in veel noordelijke meren en vijvers vormgeeft. Hij biedt schuilplaatsen aan kleine vissen, voedt watervogels en bedekt het wateroppervlak met drijvende bladeren. In deze studie onthullen wetenschappers een gedetailleerd genetisch blauwdruk van deze plant, wat een nieuw venster opent op hoe planten zich aanpassen aan het leven onder water en een waardevolle referentie biedt voor zowel behoud als fundamentele biologie. 
Waarom deze onderwaterbewoner ertoe doet
Smalbladige katspaan (wetenschappelijke naam Sparganium angustifolium) komt veel voor in gematigde streken van het noordelijk halfrond. In tegenstelling tot rietachtige planten die meestal boven het water uitsteken, groeit deze soort in dieper water, met lange, slanke bladeren die grotendeels ondergedompeld of drijvend zijn. Zijn dichte velden vormen onderwaterbossen die schuilplaatsen bieden aan waterdieren, terwijl zijn vruchten en bladeren eenden en andere watervogels voeden. Omdat het zich dicht bij de basis van een belangrijk deel van de gras- en graanverwantschap bevindt (de orde Poales, waartoe ook gewassen als rijst en maïs behoren), biedt het een belangrijke vergelijkingspunt om te begrijpen hoe planten de sprong van land naar water maakten.
Het bouwen van een genetische blauwdruk met hoge resolutie
Om het genoom van de plant te ontcijferen, verzamelden onderzoekers een monster uit een rivier in Binnen-Mongolië, China, en gebruikten ze verschillende geavanceerde DNA-sequencingtechnieken. Ze combineerden lange, zeer nauwkeurige DNA-lezingen, kortere lezingen en een methode genaamd Hi-C, die vastlegt hoe verschillende DNA-regio’s ruimtelijk naast elkaar liggen in de cel. Door deze gegevens samen te weven, assembleerden ze het DNA in 15 chromosomen en dekten ze bijna het volledige genoom—ongeveer 487 miljoen “letters” genetische code. Maten voor de assemblagekwaliteit toonden aan dat grote stukken DNA aaneengeschakeld waren zonder onderbrekingen en dat meer dan 96% van de verwachte kernplantengenen aanwezig was, wat duidt op een zeer compleet en betrouwbaar referentiegenoom.
Repetitief DNA en duizenden genen
Nadat het genoom was samengevoegd, ging het team op zoek naar de belangrijkste kenmerken. Ze vonden 23.767 eiwit-coderende genen—DNA-segmenten die kunnen worden omgezet in eiwitten die de cellen van de plant opbouwen en laten functioneren. Om te begrijpen wat deze genen mogelijk doen, vergeleken ze ze met verschillende grote wetenschappelijke databases en konden ze waarschijnlijke functies toewijzen aan meer dan 96% ervan. De onderzoekers ontdekten ook dat het merendeel van het genoom—iets meer dan 70%—bestaat uit repetitief DNA, veelal in de vorm van springende genetische elementen die retrotransposons worden genoemd. Deze stukken coderen niet direct voor eiwitten, maar bepalen sterk de omvang en structuur van het genoom en kunnen beïnvloeden hoe nabije genen zich gedragen. 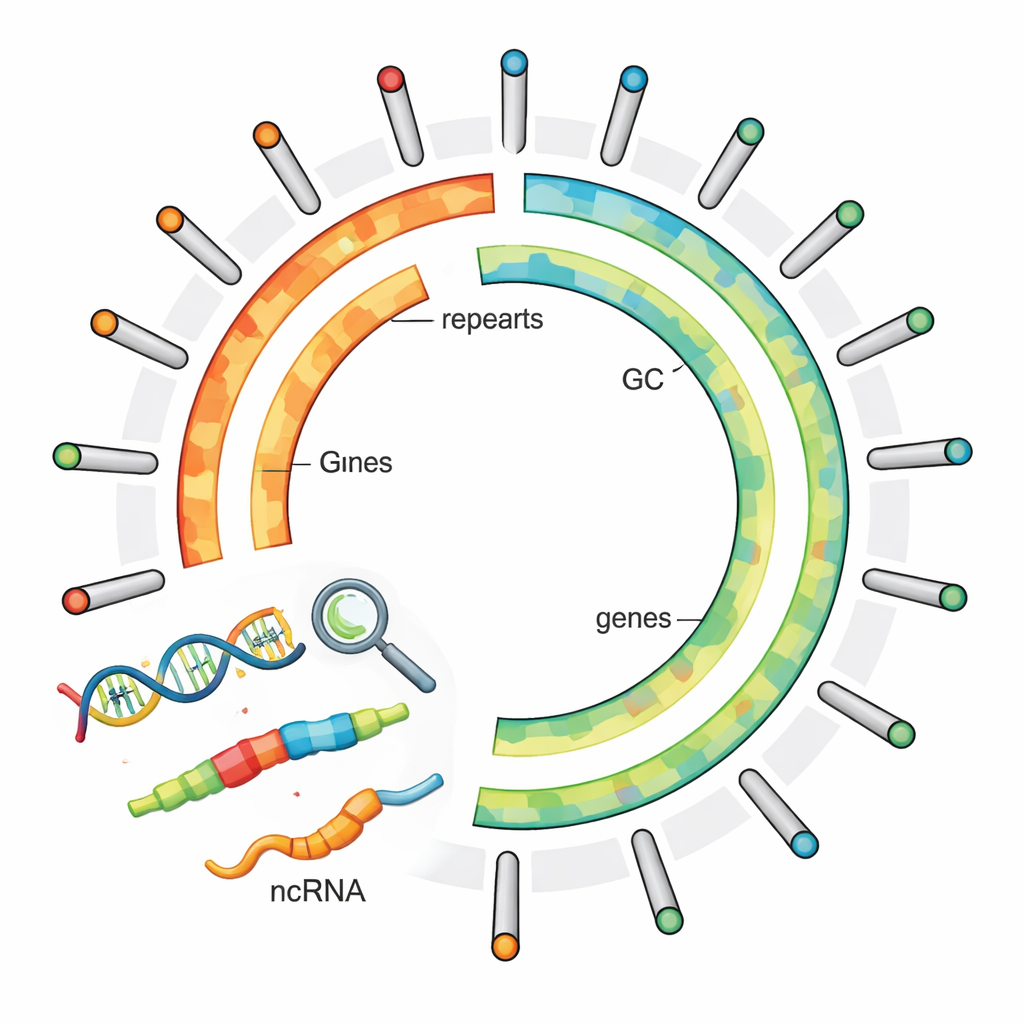
Het verborgen RNA-gereedschap van de plant
Naast genen die eiwitten maken, herbergt het genoom veel niet-coderende RNA’s, moleculen die helpen genactiviteit te reguleren en fijn af te stemmen. De onderzoekers identificeerden meer dan 3.300 dergelijke elementen, waaronder duizenden ribosomaal RNA’s die de kern vormen van de eiwitfabrieken van de cel, honderden transfer-RNA’s die bouwstenen voor nieuwe eiwitten aanleveren, en kleine RNA’s die kunnen sturen welke genen aan of uit worden gezet. Deze rijke RNA-arsenaal suggereert dat smalbladige katspaan meerdere lagen van regulatie heeft om te reageren op veranderingen in licht, zuurstof, temperatuur en waterbeweging in zijn aquatische habitat.
Van één plant naar een breder evolutionair beeld
Door dit chromosoomniveaureferentiegenoom openbaar beschikbaar te maken in internationale databanken, bieden de auteurs een krachtig nieuw hulpmiddel voor wetenschappers die bestuderen hoe planten zich aanpassen aan het leven in water. Het vergelijken van dit genoom met die van verwante soorten die langs de waterkant of op het land leven, kan aan het licht brengen welke genen en DNA-eigenschappen gedeeld worden en welke uniek zijn voor volledig aquatische levenswijzen. Voor niet-specialisten is de boodschap helder: door het genetische script van een ogenschijnlijk gewone meerplant te ontcijferen, hebben onderzoekers een basis gelegd om te begrijpen hoe planten zichzelf zodanig vormgeven dat ze onder water gedijen—kennis die uiteindelijk zowel moerasbehoud als het fokken van veerkrachtigere gewassen kan informeren.
Bronvermelding: Shi, X., Xue, J. & Xu, X. Chromosome-level genome assembly of narrow-leaf bur-reed (Sparganium angustifolium Michx., Typhaceae). Sci Data 13, 284 (2026). https://doi.org/10.1038/s41597-026-06640-6
Trefwoorden: waterplanten, genoomassemblage, moerasecologie, plantenontwikkeling, Sparganium