Clear Sky Science · nl
Chromosoom-niveau genoomassemblage van de steenvlieg Rhopalopsole triangulispina Mo en Li, 2025 (Plecoptera: Leuctridae)
Waarom een klein beekinsekt ertoe doet
In snelstromende bergbeken wereldwijd geven kleine, tere insecten die steenvliegen worden genoemd stilletjes aan hoe gezond het water is. Hun jeugdstadia, of nimfen, zijn zo gevoelig voor vervuiling dat hun aanwezigheid vaak betekent dat de beek schoon en goed geoxygeneerd is. Ondanks dit ecologische belang weten wetenschappers verrassend weinig over het gedetailleerde genetische profiel van veel steenvliegen. Deze studie levert een hoogwaardige, op chromosoomniveau gemaakte kaart van het DNA van een van die soorten, Rhopalopsole triangulispina, en opent een nieuw venster op hoe deze insecten zijn geëvolueerd en hoe ze ons kunnen helpen zoetwatersystemen beter te beschermen.
Leven in helder, snel stromend water
Steenvliegen in de superfamilie Nemouroidea behoren tot de meest diverse en talrijke groepen van deze insecten en leven in koude, schone beken, meren en vijvers—vaak verborgen tussen stenen of sedimenten. Hun nimfen zijn afhankelijk van goede waterkwaliteit: temperatuur, zuurstofniveaus, chemische vervuiling en zelfs het type bedding kunnen het verschil betekenen tussen floreren en verdwijnen. Vanwege deze gevoeligheid gebruiken wetenschappers ze als natuurlijke “milieusensoren” bij het beoordelen van de gezondheid van rivieren en beken. Binnen Nemouroidea zijn de familie Leuctridae en het geslacht Rhopalopsole vooral algemeen in Aziatische bergstreken, waaronder China, dat meer dan 60 bekende Rhopalopsole-soorten herbergt. Ondanks deze diversiteit ontbraken genetische referentiemappen, en vooral volledig geannoteerde genomen, wat onze mogelijkheid om hun evolutie te bestuderen of genomische instrumenten voor waterkwaliteitsmonitoring te gebruiken, beperkte.
Een genetische kaart vanaf nul opbouwen
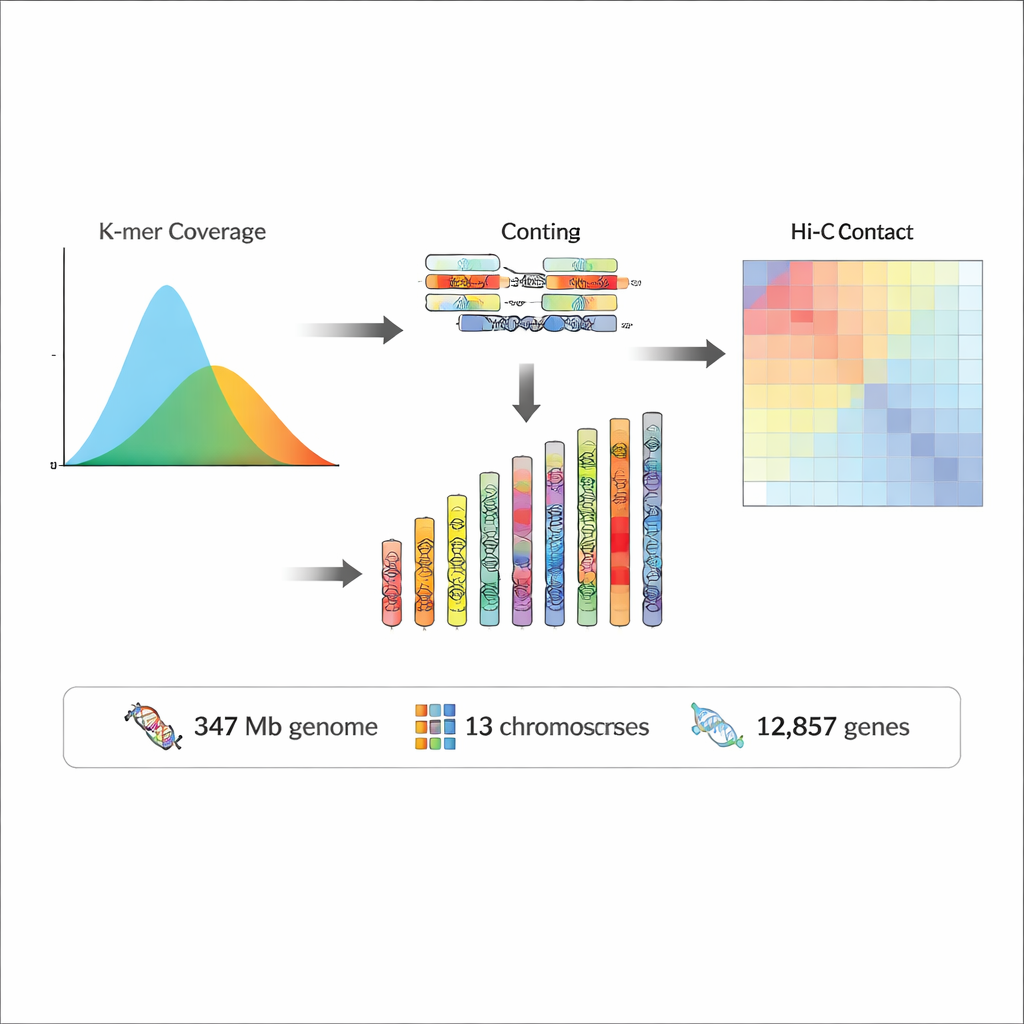
Om deze leemte aan te pakken verzamelden de onderzoekers volwassen Rhopalopsole triangulispina in een beschermd bergreservaat in Zuid-China. Na zorgvuldige conservering van de insecten is hoogwaardig DNA en RNA (het molecuul dat weergeeft welke genen actief zijn) geïsoleerd. Met meerdere geavanceerde sequencingtechnologieën genereerden ze verschillende gezichtspunten van het genoom: zeer nauwkeurige lange DNA-lezingen (PacBio HiFi), enorme aantallen korte lezingen (Illumina) en speciale data die vastleggen hoe DNA-stukken in de kern zijn gevouwen en met elkaar interageren (Hi-C). Gezamenlijk stelden deze datatypes het team in staat om het genetisch materiaal van het insect in lange, continue sequenties te assembleren en vervolgens de Hi-C-informatie te gebruiken om ze te rangschikken in 13 chromosoomachtige structuren, pseudochromosomen genoemd.
Wat het genoom onthult
Het voltooide genoom is ongeveer 347 miljoen “letters” DNA lang, waarbij bijna 97% ervan op de 13 pseudochromosomen is geplaatst. Kwaliteitscontroles toonden aan dat de assemblage zowel zeer volledig als buitengewoon nauwkeurig is, met foutpercentages die worden geschat op minder dan één op tien miljoen basen en meer dan 95% van alle sequence-lezingen die erop terug te mappen zijn. Bijna de helft van het genoom bestaat uit repetitief DNA—reeksen die veelvuldig voorkomen en vaak mobiele genetische elementen of “springende genen” weerspiegelen die het genoom in de loop van de evolutie hebben gevormd. Op deze basis voorspelde het team 12.857 eiwit-coderende genen en meer dan 2.400 niet-coderende RNA-genen, waaronder moleculen die betrokken zijn bij de opbouw van ribosomen, RNA-verwerking en het aansturen van eiwitsynthese. Door deze genen te vergelijken met grote internationale databanken konden ze aan de overgrote meerderheid waarschijnlijk functies toekennen en vele verbinden met bekende biologische paden.
Een nieuwe hulpbron voor evolutie en ecologie
Buiten het katalogiseren van genen fungeert dit genoom als naslagwerk voor toekomstige studies. Wetenschappers kunnen nu onderzoeken welke genen steenvliegen helpen zich aan te passen aan koud, snel stromend water, hoe ze op moleculair niveau reageren op vervuiling of klimaatverandering en hoe verschillende steenvliegenlijnen aan elkaar verwant zijn. Tot nu toe berustte het meeste evolutionaire werk aan Nemouroidea op morfologische kenmerken, mitochondriaal DNA of gedeeltelijke genensets. Dit complete, geannoteerde genoom biedt een veel rijkere en preciezere basis voor het reconstrueren van de stamboom van steenvliegen en voor het vergelijken van genomen tussen insecten, ook die met zeer verschillende levenswijzen. Omdat alle ruwe data en annotaties openbaar beschikbaar zijn, kunnen onderzoekers wereldwijd de informatie opnieuw analyseren, integreren met andere datasets en nieuwe instrumenten voor biomonitoring ontwikkelen.
Van DNA-blauwdruk naar schonere beken
Voor niet-specialisten is de kernboodschap dat we nu een gedetailleerde, op chromosoomniveau gebaseerde blauwdruk hebben van een steenvliegsoort die fungeert als voorpost voor de gezondheid van zoetwater. Dit genoom zal wetenschappers helpen te begrijpen hoe deze insecten leven en zich aanpassen, hun diepe evolutionaire geschiedenis te traceren en gevoeliger DNA-gebaseerde methoden te ontwikkelen om ze in rivieren en beken op te sporen. In de praktijk betekent dat betere vroegwaarschuwingssystemen voor vervuiling en milieuverandering. Door de genetische fundamenten van een klein insect in bergbeken te onthullen, draagt dit werk uiteindelijk bij aan het behoud van het schone water waarop mensen en ecosystemen vertrouwen.
Bronvermelding: Lin, A., Cao, J., Murányi, D. et al. Chromosome-level genome assembly of the stonefly Rhopalopsole triangulispina Mo and Li, 2025 (Plecoptera: Leuctridae). Sci Data 13, 292 (2026). https://doi.org/10.1038/s41597-026-06631-7
Trefwoorden: steenvlieggenoom, zoetwater-bio-indicatoren, assemblage op chromosoomniveau, insectenevolutie, milieu-DNA