Clear Sky Science · nl
Volledig-genoom herkartering en genetische diversiteit van vijf inheemse runderrassen uit China
Waarom lokale koeien ons allemaal aangaan
In de Chinese provincie Sichuan vertrouwen kleine boeren op robuuste gele runderen die gewend zijn aan steile hellingen, hete vochtige zomers en schraal voer. Deze dieren ondersteunen stilletjes de voedselzekerheid en het plattelandsinkomen, maar hun unieke eigenschappen lopen het risico verloren te gaan nu moderne rassen en kruisbestuiving zich verspreiden. Deze studie leest vrijwel elke letter van het DNA van meerdere Sichuan-runderrassen en creëert een gedetailleerde genetische kaart die kan helpen deze dieren te beschermen, de rundvleesproductie te verbeteren en vee voor te bereiden op een veranderend klimaat.
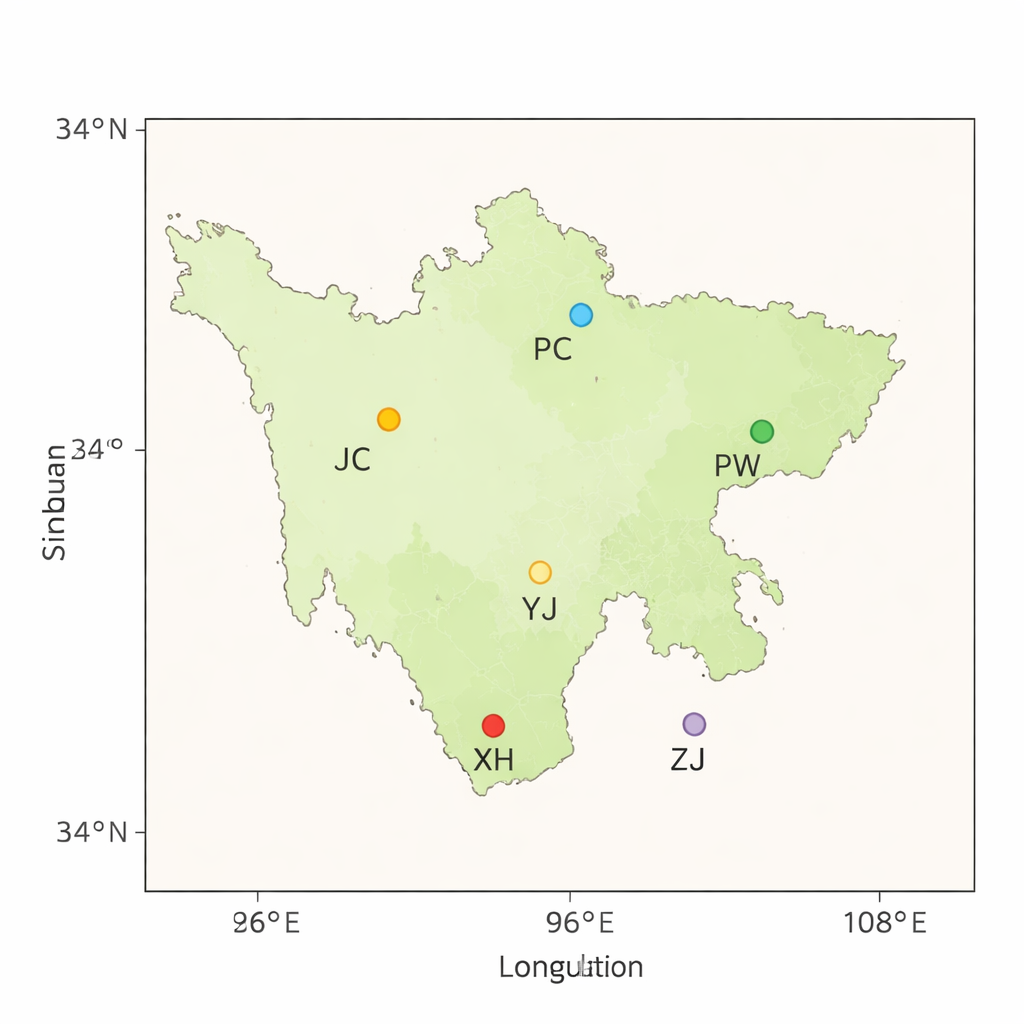
Runderen gebouwd voor ruig landschap
Sichuan is een van China’s hotspots voor runderven diversiteit, met miljoenen dieren verspreid over bekken, heuvels en hooglanden. Lokale gele runderen zijn gevormd door eeuwen van overleven in ruige omgevingen en door zorgvuldige selectie door boeren die waarde hechtten aan kracht, ziektebestendigheid en het vermogen te leven van ruw voer. Toch staan dezezelfde rassen nu onder druk door afnemende aantallen en genetische erosie. Ongecontroleerde kruisbestuiving, seizoensgebonden verplaatsing van kuddes, ziekte-uitbraken, overstromingen en de snelle vermenging van dieren door handel vervagen de grenzen tussen traditionele rassen. Zonder doelbewuste instandhouding kunnen de onderscheidende biologische kwaliteiten van deze runderen verdwijnen.
Het hele genetische verhaal lezen
Om deze diversiteit te begrijpen en te beschermen verzamelden de onderzoekers bloed van 56 gele runderen uit vijf Sichuan-gemeenten, elk representatief voor een lokaal ras. Ze namen ook DNA op van 10 hooglandyakken als vergelijkingsgroep, of outgroup, om het genoom van de runderen in een bredere evolutionaire context te plaatsen. Met moderne high-throughput sequencing genereerden ze ongeveer 2,3 terabyte aan DNA-gegevens, waarbij elk dierengenoom ruwweg 13 keer werd uitgelezen om nauwkeurigheid te waarborgen. De reads werden vervolgens uitgelijnd op een standaard referentiegenoom voor runderen, waarbij meer dan 99% op de juiste plaats terechtkwam — een teken van zeer hoge gegevenskwaliteit.
Miljoenen verschillen in de DNA-code
Nadat de genomen waren uitgelijnd, doorzochten de onderzoekers ze op verschillende soorten genetische variatie. Ze vonden ongeveer 31 miljoen enkelletterveranderingen in de DNA-sequentie, evenals meer dan twee miljoen kleine inserties en deleties, tienduizenden grotere structurele veranderingen en meer dan 240.000 regio’s waar stukken DNA ontbreken of gedupliceerd zijn. Het merendeel van deze verschillen ligt buiten de eiwitcoderende delen van genen, maar een substantieel aantal valt binnen of nabij genen die belangrijke eigenschappen kunnen beïnvloeden. Het patroon van veranderingen over de chromosomen, en in het bijzonder het afwijkende gedrag van het X-chromosoom, weerspiegelt zowel de biologie van runderen als de evolutionaire druk waarmee ze in de loop van de tijd geconfronteerd zijn geweest.
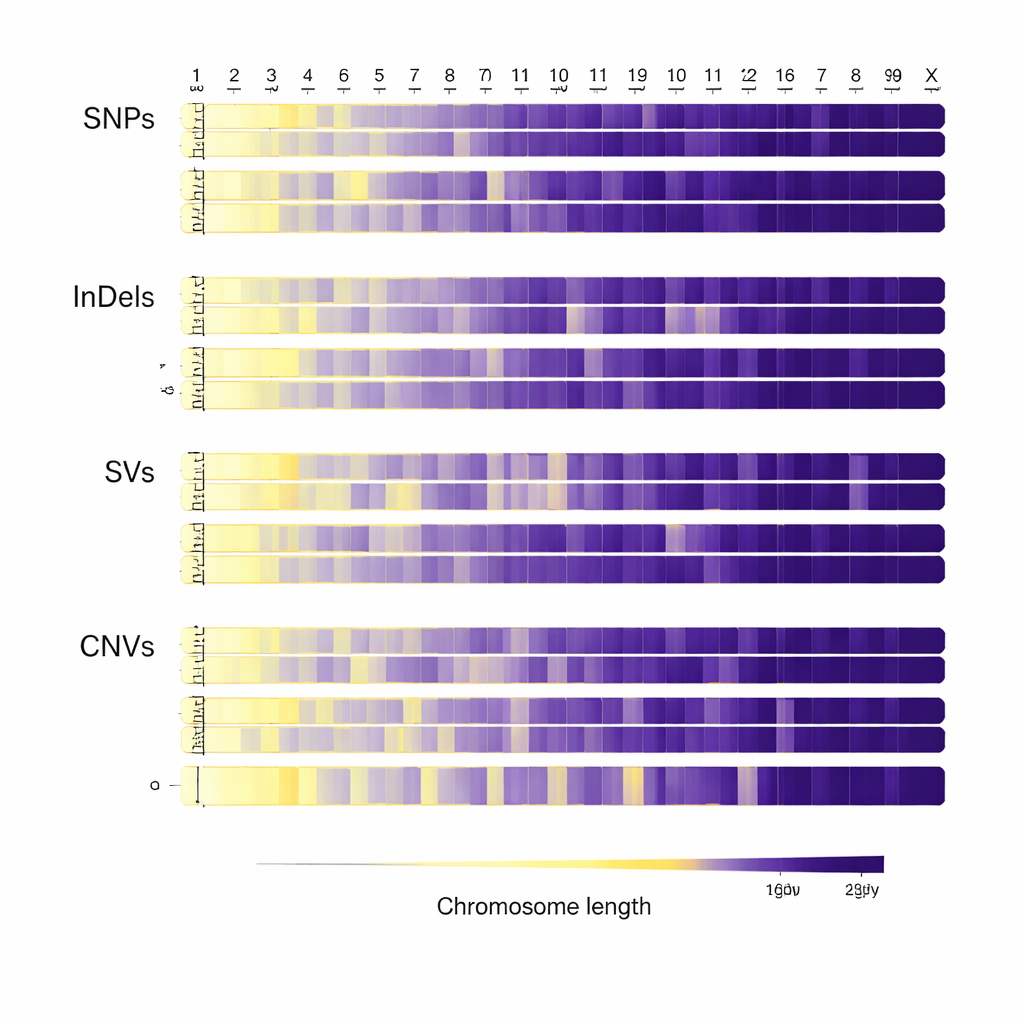
Ruwe data omzetten in biologische inzichten
Cruciaal is dat de onderzoekers meer deden dan alleen DNA-veranderingen tellen — ze annoteerden deze ook om mogelijke effecten op genfunctie te voorspellen. Met veelgebruikte bioinformatica-instrumenten koppelden ze elke variant aan zijn positie in of nabij genen en markeerden ze veranderingen die eiwitten kunnen verstoren of genregulatie kunnen wijzigen. Ze maakten vervolgens al het ruwe sequentiegegevens en de verwerkte variantlijsten vrij beschikbaar in internationale databanken. Deze openheid betekent dat wetenschappers wereldwijd de data kunnen doorzoeken naar genen die samenhangen met tolerantie voor hitte en vochtigheid, ziektebestendigheid, efficiënt gebruik van voer van lage kwaliteit en vleeskwaliteit, of om Sichuan-runderen met andere rassen te vergelijken.
Van verborgen code naar praktisch voordeel
Voor niet-specialisten kan dit werk worden gezien als het nemen van een genetische fotokopie met hoge resolutie van enkele van China’s meest robuuste runderen. Door hun DNA-verschillen in detail te catalogiseren en de resultaten open te delen, legt de studie essentieel fundament voor fokprogramma’s die de veerkracht van traditionele dieren behouden terwijl de productiviteit wordt verbeterd. In een toekomst met klimaatsstress en veranderende ziekten zal dergelijke informatie boeren en fokkers helpen hardere, lokaal aangepaste runderen te behouden die duurzame rundvleesproductie ondersteunen en een onvervangbaar stuk landbouw-erfgoed beschermen.
Bronvermelding: Wang, W., Li, L., Chen, Y. et al. Whole-genome resequencing and genetic diversity of five indigenous cattle breeds from China. Sci Data 13, 282 (2026). https://doi.org/10.1038/s41597-026-06610-y
Trefwoorden: rundergenetica, inheemse rassen, genetische diversiteit, volledig-genoomsequencing, veeteeltbehoud