Clear Sky Science · nl
Telomeer-tot-telomeer gap-vrije genoomassemblage van Opsariichthys evolans (Cypriniformes: Cyprinidae)
Een beekvis met een genomisch verhaal
Gierende bergbeken in het zuidoosten van China en Taiwan herbergen een kleine, kleurige vis genaamd Opsariichthys evolans. Hoewel buiten die regio weinig bekend, is deze soort een ecologische spil en een natuurwerkje, met felle strepen en opvallende paaikleuren. Meer dan een eeuw debatteerden wetenschappers over hoe ze deze soort moesten classificeren en waar ze thuishoort in de stamboom van zoetwatervissen. Deze studie levert een belangrijk puzzelstuk: het eerste volledige, gap-vrije genoom van O. evolans, gelezen van het ene chromosoomuiteinde naar het andere.
Waarom deze vis ertoe doet
O. evolans leeft in heldere, stromende beken, waar hij voedselnetwerken in balans houdt en fungeert als een gevoelige indicator van waterkwaliteit. Mannetjes krijgen tijdens het paaiseizoen levendige laterale strepen en korrelige knobbels op de kop en rond de ogen, samen met een donkere, zwart-paarsachtige snuit. Deze opvallende eigenschappen, gecombineerd met de voorkeur van de vis voor snelstromend water, maken hem tot een ideale soort om te bestuderen hoe dieren zich aanpassen aan hun omgeving. Tegelijkertijd krimpen de populaties door door de mens veroorzaakte veranderingen—vervuiling, habitatfragmentatie en invasieve soorten—waardoor het belangrijk is de biologie van de soort te begrijpen voor behoud.
Een jarenlang durende naamverwarring
Decennialang hadden biologen moeite te beslissen of O. evolans thuishoorde in het geslacht Opsariichthys of Zacco. Vroege taxonomen beschreven de soort als Zacco evolans, vooral gebaseerd op uiterlijke kenmerken zoals vinvorm en lichaamsstrepen. Latere, gedetailleerdere studies toonden aan dat het streeppatroon en de paaibultjes verschillen van die van het vergelijkbaar ogende Zacco platypus. Mitochondriaal DNA suggereerde dat O. evolans het beste past binnen Opsariichthys, maar sommige kern-gengegevens hintten op een nauwere verwantschap met Zacco. Zonder een compleet genoom bleef het evolutionaire beeld vaag en ging het debat over de juiste plek in de visstamboom door.

Elke letter van het genoom lezen
Om deze vragen te beslechten, verzamelden de onderzoekers een wilde mannelijke vis uit een rivier in de provincie Anhui, China, en conserveerden zorgvuldig negen verschillende weefsels. Ze combineerden vervolgens meerdere geavanceerde DNA-sequencingtechnologieën, elk met eigen sterke punten, om de genetische code van het dier te lezen. Korte, zeer nauwkeurige fragmenten hielpen de sequentie te polijsten, terwijl lange en ultralange reads van PacBio en Oxford Nanopore lastige regio’s overspanden en chromosomen van het ene uiteinde naar het andere samenvoegden. Hi-C-technologie, die vastlegt hoe DNA in de cel opvouwt, werd gebruikt om de stukken tot volledige chromosomen te ordenen. Het eindresultaat is een telomeer-tot-telomeer, gap-vrij genoom van ongeveer 0,89 miljard basenparen, keurig georganiseerd in 39 chromosomen met voor elk een continu DNA-stuk.
Wat het genoom onthult
Het voltooide genoom doorstond strenge kwaliteitscontroles, ving meer dan 99% van verwachte geconserveerde genen en sloot nauw aan bij bekende DNA-sequenties van verwante vissen. Bijna de helft van het genoom bestaat uit herhaalde sequenties, veel daarvan ‘‘springende genen’’ die kunnen verplaatsen en het genoom over evolutionaire tijd kunnen hervormen. Het team identificeerde bijna 30.000 eiwit-coderende genen en duizenden niet-coderende RNA’s, waarvan de meeste gekoppeld konden worden aan bekende functies met behulp van grote biologische databases. Door dit nieuwe genoom te vergelijken met dat van twee nauwe verwanten—Opsariichthys bidens en Zacco platypus—vonden de wetenschappers dat de algemene chromosoomstructuur sterk lijkt, wat nauwe evolutionaire banden bevestigt. Binnen dit raamwerk pinpointten ze kandidaatgenen en paden die waarschijnlijk betrokken zijn bij de lichaamsstrepen en aanpassingen aan leven in snelle stroming, wat aanwijzingen biedt voor hoe het karakteristieke uiterlijk en de levenswijze zijn geëvolueerd.
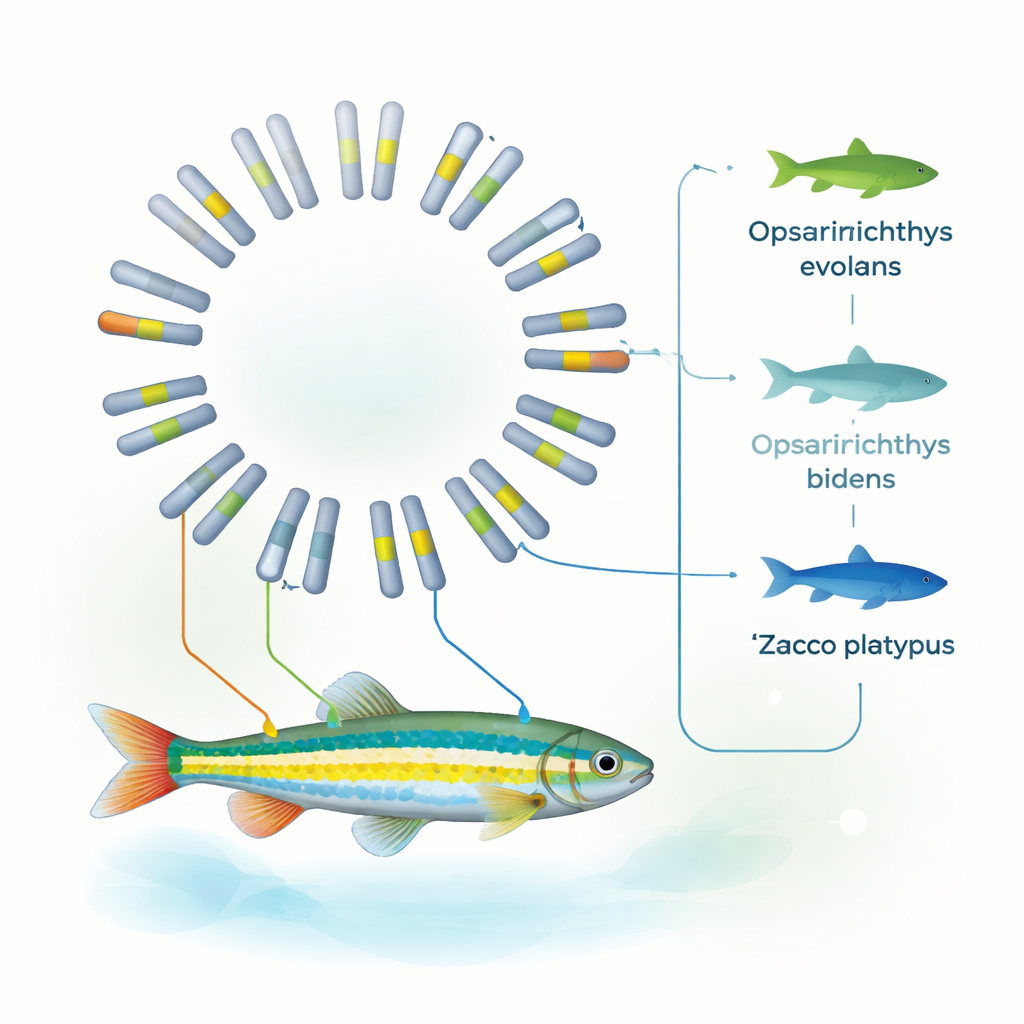
Zijn plek in de visstamboom verduidelijken
Met behulp van genfamilies die gedeeld worden door tien verschillende vissensoorten reconstrueerde het team een gedetailleerde evolutionaire boom. Hun analyse geeft aan dat O. evolans ongeveer 8 tot 19 miljoen jaar geleden afsplitste van Z. platypus en dat de genoomstructuur vooral nauw verwant is aan die van O. bidens. Samen met eerder mitochondriaal bewijs ondersteunen deze patronen het plaatsen van O. evolans stevig in het geslacht Opsariichthys, niet in Zacco. Met andere woorden: het volledige genoom bevestigt wat zorgvuldige observatie van strepen, snuitkleur en paaistructuren al suggereerde: uiterlijke schijn kan misleiden, maar wanneer morfologie en een compleet genoom overeenkomen, worden taxonomische grenzen veel duidelijker.
Waarom een compleet genoom het spel verandert
Voor niet-specialisten is de prestatie te vergelijken met het gaan van een wazige, gescheurde kaart naar een scherpe, volledige atlas van een soort. Met een compleet, gap-vrij genoom kunnen wetenschappers nu de oorsprong traceren van de opvallende kleuren van O. evolans, de gestroomlijnde vorm voor leven in snel water en de verwantschappen met andere Oost-Aziatische minnows met ongekende precisie. Deze hulpbron zal helpen de visclassificatie te verfijnen, het behoud van kwetsbare beekecosystemen sturen en ons begrip verdiepen van hoe kleine verschillen in DNA de rijke diversiteit in zoetwatervissen kunnen voortbrengen.
Bronvermelding: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Trefwoorden: genoomassemblage, zoetwatervis, telomeer-tot-telomeer, vis-evolutie, vergelijkende genomica