Clear Sky Science · nl
Metabarcoding- en metagenomische gegevens langs aquatische milieugradienten aan de kusten van Frankrijk en Chili
Verborgen leven in veranderende zeeën
Langs de kusten van de wereld, van rustige lagunes tot dramatische fjorden, past microscopisch leven zich voortdurend aan veranderende omstandigheden aan. Deze kleine organismen drijven de cycli van koolstof en voedingsstoffen aan die visserijen, waterkwaliteit en zelfs het klimaat ondersteunen. Toch zijn veel kustwateren, vooral complexe gebieden zoals lagunes en fjorden, op genetisch niveau nauwelijks onderzocht. Deze studie wilde daarin verandering brengen door een rijk, open dataset te creëren van kustmicroben uit Frankrijk en Chili, en zo een nieuw venster te bieden op hoe marien leven reageert op een voortdurend veranderende omgeving.
Kustlijnen als natuurlijke proeflaboratoria
Kustwateren zijn zelden constant. Regenbuien, rivierinvoer, verdamping en getijden kunnen temperatuur en zoutgehalte over korte afstanden en tijdschalen laten schommelen. Voedingsstoffen die microscopische algen voeden kunnen pieken of instorten en menselijke activiteiten brengen extra verstoring. Dergelijke variatie creëert een lappendeken van habitats die verschillende microbiële gemeenschappen selecteren en nieuwe aanpassingen stimuleren. Om deze complexiteit vast te leggen, bemonsterden de onderzoekers 26 locaties langs de Franse en Chileense kusten, waaronder lagunes, estuaria, fjorden, havens, stranden, kustwateren en één offshore locatie. Sommige Franse locaties werden maandelijks bezocht gedurende een jaar om de seizoenen te volgen, terwijl de Chileense locaties in de zuidelijke herfst werden bemonsterd, wat een brede momentopname van contrasterende kustwerelden oplevert. 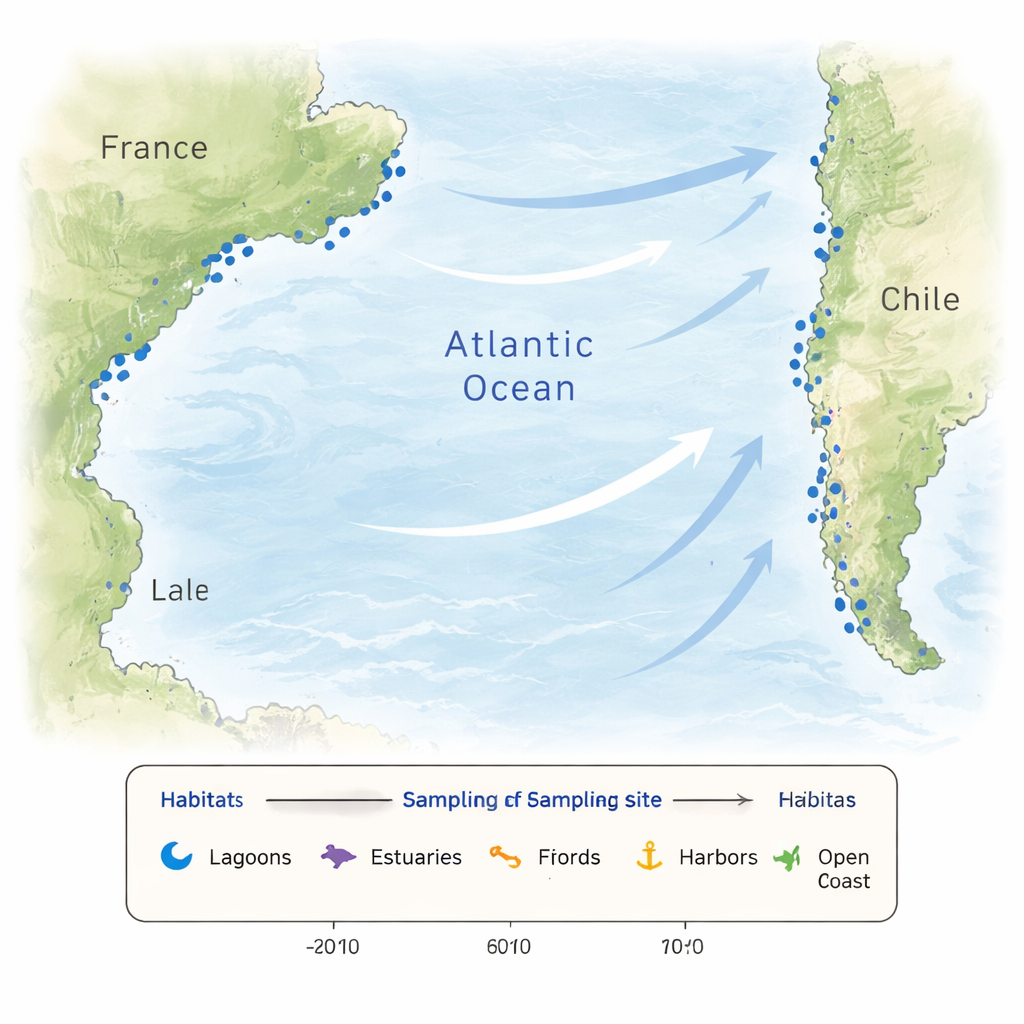
Van emmers water naar DNA‑vingerafdrukken
Op elke locatie verzamelde het team grote hoeveelheden zeewater, voornamelijk uit het verlichte oppervlak maar ook uit diepere lagen in geselecteerde fjorden en offshore-gebieden. Ze maten basisomgevingscondities zoals temperatuur, zoutgehalte en voedingsstoffen, naast indicatoren voor biologische activiteit zoals chlorofyl (een proxy voor algen), opgelost organisch materiaal, bacteriële productie en respiratie. Terug in het laboratorium werden microben geconcentreerd op fijne filters en werd hun DNA geëxtraheerd. Één reeks tests richtte zich op een standaard markergene (16S rRNA), dat fungeert als een barcode om bacteriën en archaea te identificeren. Deze metabarcoding-aanpak onthulde meer dan 53.000 verschillende DNA‑varianten en toonde aan dat sommige monsters nog maar drie gemeenschappelijke varianten deelden, wat benadrukt hoe verschillend naburige gemeenschappen kunnen zijn.
Genomen herbouwen uit een genetische 'soep'
De tweede analyseroute was ambitieuzer: shotgun-metagenomica, waarbij al het DNA in een monster in één keer wordt gesequenced. Met behulp van geavanceerde assemblage- en binningmethoden reconstrueerde het team 1.372 conceptgenomen, bekend als metagenoom-geassembleerde genomen of MAGs. Veel van deze genomen konden niet worden gekoppeld aan bekende soorten; slechts ongeveer 4% sloot aan bij formeel beschreven microbiële soorten. In sommige groepen, zoals bepaalde bacteriën en archaea die zijn aangepast aan ongewone omstandigheden, had meer dan de helft van de voorspelde eiwitten geen bekende functie. De onderzoekers bouwden ook een enorme genencatalogus van meer dan 23 miljoen niet-redundante genen en vonden dat ongeveer 31% geen overeenkomsten had in grote referentiedatabases. Dit wijst op een diepe voorraad ongekarakteriseerde biologie in kustwateren.
Extreme habitats, nieuwe hulpmiddelen
Sommige locaties, met name hypersaliene lagunes in Frankrijk, vielen op als hotspots van genetische nieuwigheid. Daar schommelden de zoutgehaltes in slechts enkele maanden van vrijwel normaal zeewater tot meer dan twee keer zo zout als de oceaan. Deze stressvolle omstandigheden kunnen zogenoemde extremotolerante microben bevoordelen die enzymen hebben die nog functioneren bij hoge zoutconcentraties of temperaturen. Dergelijke enzymen worden steeds vaker gezocht voor industrieel gebruik in wasmiddelen, biobrandstoffen, milieureiniging en voedselverwerking. Door gedetailleerde milieumetingen te koppelen aan gen- en genoomgegevens helpt deze dataset te lokaliseren waar zulke ongebruikelijke organismen en biochemische hulpmiddelen het meest waarschijnlijk voorkomen. 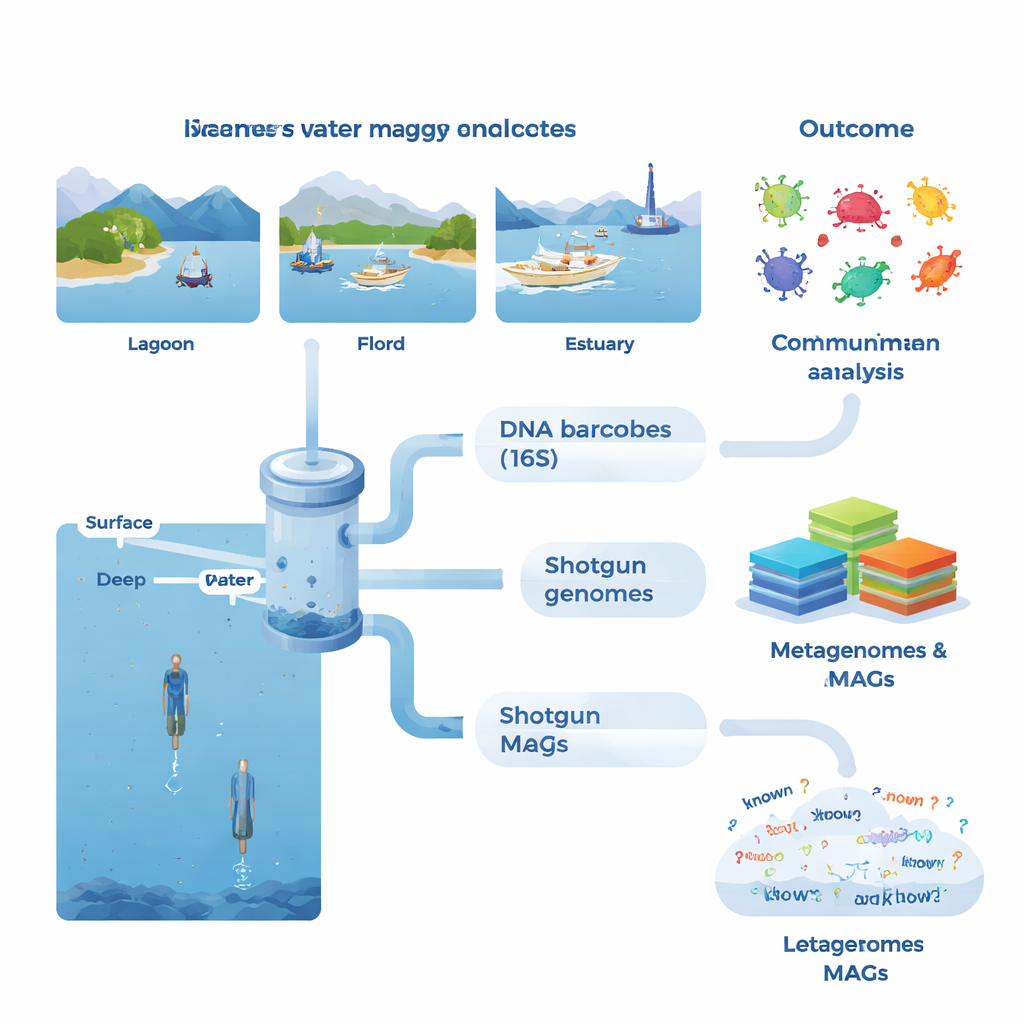
Een publiek hulpmiddel voor de toekomst van de oceaan
In plaats van één ontdekkingsresultaat te presenteren, levert dit werk een zorgvuldig gevalideerde, open hulpbron die andere wetenschappers kunnen gebruiken. Alle DNA-sequenties, genoomreconstructies, genencatalogi en milieumetingen zijn openbaar gearchiveerd, samen met de computercode die werd gebruikt om ze te verwerken. Voor niet‑specialisten is de kernboodschap dat kustmicroben zowel divers als vol verrassingen zijn, vooral in over het hoofd geziene omgevingen zoals lagunes en fjorden. Naarmate onderzoekers deze gegevens benutten, zullen ze beter in staat zijn te begrijpen hoe microscopisch leven langs onze kusten reageert op opwarming, vervuiling en verstoring — en om nieuwe genen te benutten die gunstig kunnen zijn voor biotechnologie en milieubeheer.
Bronvermelding: Maeke, M.D., Hassenrück, C., Aguilar-Muñoz, P. et al. Metabarcoding and metagenomic data across aquatic environmental gradients along the coasts of France and Chile. Sci Data 13, 29 (2026). https://doi.org/10.1038/s41597-026-06572-1
Trefwoorden: kustmicrobiomen, metagenomica, lagunes en fjorden, mariene biodiversiteit, omgevings-DNA