Clear Sky Science · nl
Hoge-resolutie reeksen bladbeelden met geometrische uitlijning voor dynamische fenotypering van bladaandoeningen
Plantenziekten in realtime zien ontstaan
Boeren en tuinders merken plantenziekten meestal pas op nadat bruine vlekken en gele strepen al zichtbaar zijn geworden. Maar wat als we die symptomen uur na uur konden volgen en precies konden leren hoe weer, plantvariëteit en verschillende ziekteverwekkers een uitbraak vormgeven? Dit artikel introduceert een openbare dataset die dat doet voor tarwe, een van ’s werelds belangrijkste voedselgewassen. Door individuele bladeren met een camera dagen en weken te volgen, openen de auteurs een nieuw venster op hoe bladaandoeningen beginnen, zich verspreiden en op elkaar inwerken.
Een nieuwe fotobibliotheek van zieke bladeren
De kern van het werk is een zorgvuldig samengestelde verzameling van 12.520 hoge-resolutie kleurenbeelden van tarwebladeren. Deze foto’s zijn gegroepeerd in 1.032 time-lapse reeksen, die elk hetzelfde blad ongeveer twee weken lang met bijna dagelijkse foto’s volgen. Veel bladeren tonen belangrijke tarweziekten zoals bruine roest, gele roest en Septoria tritici blotch. Door de beeldresolutie zeer fijn te houden (ongeveer drie honderdsten van een millimeter per pixel) legt de dataset kleine details vast zoals individuele letsels, roestpustels en kleine voortplantingslichamen waar schimmels sporen produceren.
Elk blad telkens op dezelfde plaats houden
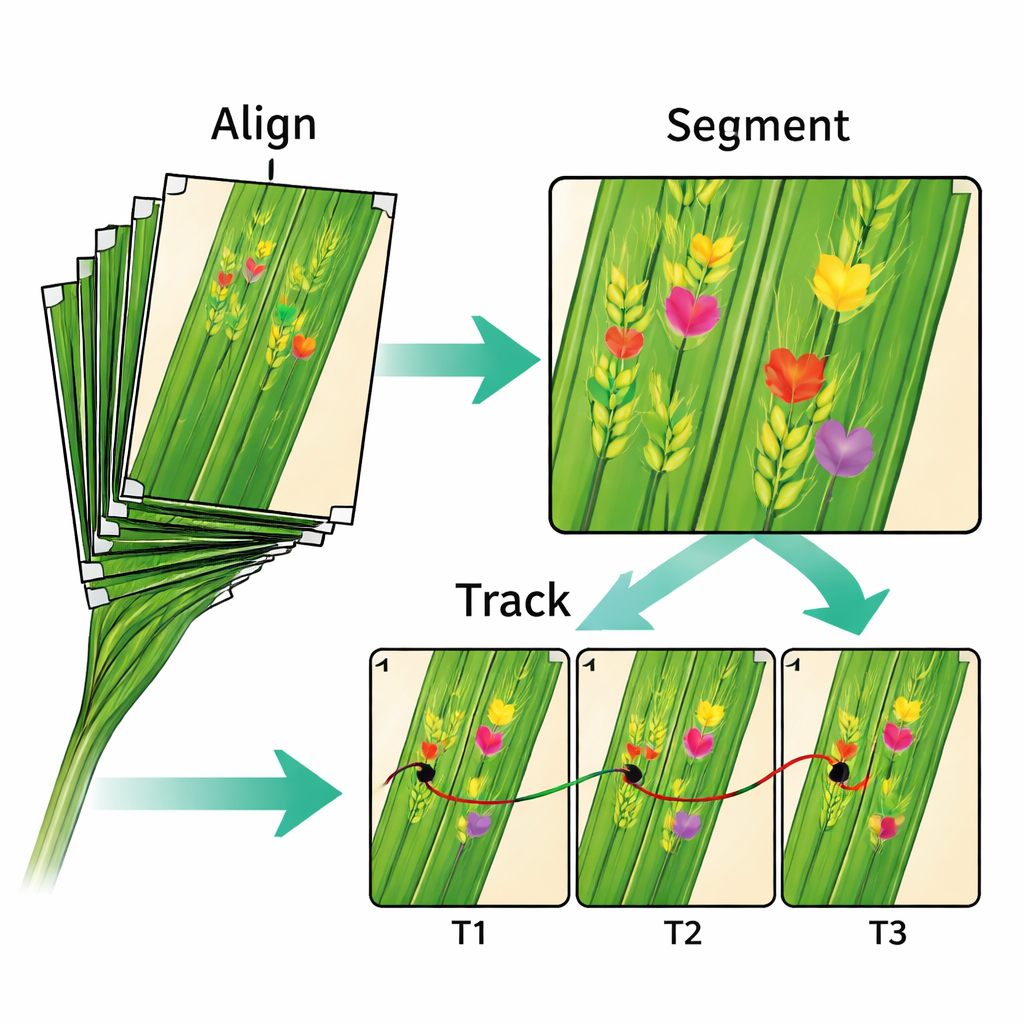
Een van de grootste technische hindernissen bij het bestuderen van dergelijke tijdreeksen is dat bladeren bewegen en van vorm veranderen. Om dit op te lossen hebben de onderzoekers elk blad zachtjes tegen een heldere plaat afgevlakt en kleine witte inktpunten als referentie aangebracht. Computer-vision software gebruikte deze markeringen vervolgens om alle beelden in een reeks uit te lijnen zodat hetzelfde stukje weefsel van dag tot dag op dezelfde plek verschijnt. De mediaan van de uitlijnfout is slechts 0,16 millimeter — goed genoeg om de meeste letsels te volgen terwijl ze uitbreiden. Naast de beelden levert het team ook de wiskundige transformaties die bij de uitlijning zijn gebruikt, zodat anderen alternatieve methoden kunnen testen of de bestaande kunnen verbeteren.
Van foto’s naar meetbare ziekte
Na uitlijning pasten de auteurs deep-learning modellen toe om symptomen op elk blad te lokaliseren en af te bakenen. De verwerkingspipeline detecteert sleutelpuntmarkeringen, segmenteert aangetaste gebieden en koppelt hetzelfde letsel over meerdere dagen op basis van hoeveel de afgebakende regio’s overlappen. Daardoor wordt het mogelijk om te meten hoe snel individuele vlekken groeien, wanneer nieuwe pustels verschijnen en hoeveel voortplantingslichamen zich ontwikkelen. De dataset bevat ook weersgegevens, informatie over fungicide- en inokulatietr Treatments (inokulatietr?) en details over 15 tarwecultivars met contrasterende bladvormen en resistentieniveaus. Deze extra gegevens stellen wetenschappers in staat te onderzoeken hoe ziekteontwikkeling afhangt van plantengenetica, beheerskeuzes en veranderende veldomstandigheden.
Slimmere beeldverwerking testen
Voorbij de plantgezondheid zelf is de dataset een speelveld voor informatici en ingenieurs. De auteurs tonen aan dat hun huidige stapsgewijze aanpak — eerst uitlijnen, dan segmenteren, dan volgen — redelijk goed werkt maar nog context mist en handmatige kwaliteitscontroles vereist. Ze betogen dat de echte kans ligt in meer geïntegreerde "end-to-end" systemen die uitlijning, symptoomdetectie en tracking tegelijk leren, geïnspireerd door vergelijkbare vooruitgangen in medische beeldvorming. Omdat de gegevens zowel ruwe beelden als verwerkte outputs zoals maskers en markercoördinaten bevatten, kunnen onderzoekers nieuwe algoritmen benchmarken en ze direct vergelijken met de bestaande pipeline.
Wat dit betekent voor toekomstige oogsten
Voor niet-specialisten is de praktische boodschap dat we leren plantenziekten te monitoren met dezelfde precisie en continuïteit die in de moderne geneeskunde wordt gebruikt. Door bladeren te veranderen in time-lapse verhalen in plaats van in losse momentopnames, helpt deze dataset wetenschappers vast te stellen welke soorten resistentie in het veld echt belangrijk zijn en onder welke weerspatronen uitbraken versnellen of afremmen. Hoewel de huidige data uit één locatie afkomstig zijn en zich op tarwe concentreerden, kunnen de methoden en tools worden aangepast aan andere gewassen en stressfactoren. Op de lange termijn kan zulke gedetailleerde monitoring fokkers richting duurzamere ziekteweerstand sturen en waarschuwingssystemen ondersteunen die opbrengsten beschermen voordat schade met het blote oog zichtbaar wordt.
Bronvermelding: Anderegg, J., McDonald, B.A. High-Resolution Leaf Image Sequences with Geometric Alignment for Dynamic Phenotyping of Foliar Diseases. Sci Data 13, 247 (2026). https://doi.org/10.1038/s41597-026-06567-y
Trefwoorden: ziekten aan tarwebladeren, time-lapse beeldvorming, plantfenotypering, digitale plantpathologie, weerstand tegen gewasziekten