Clear Sky Science · nl
Navigeren in het landschap van directe cellulaire herprogrammering met DiReG
Een celtype in een ander veranderen
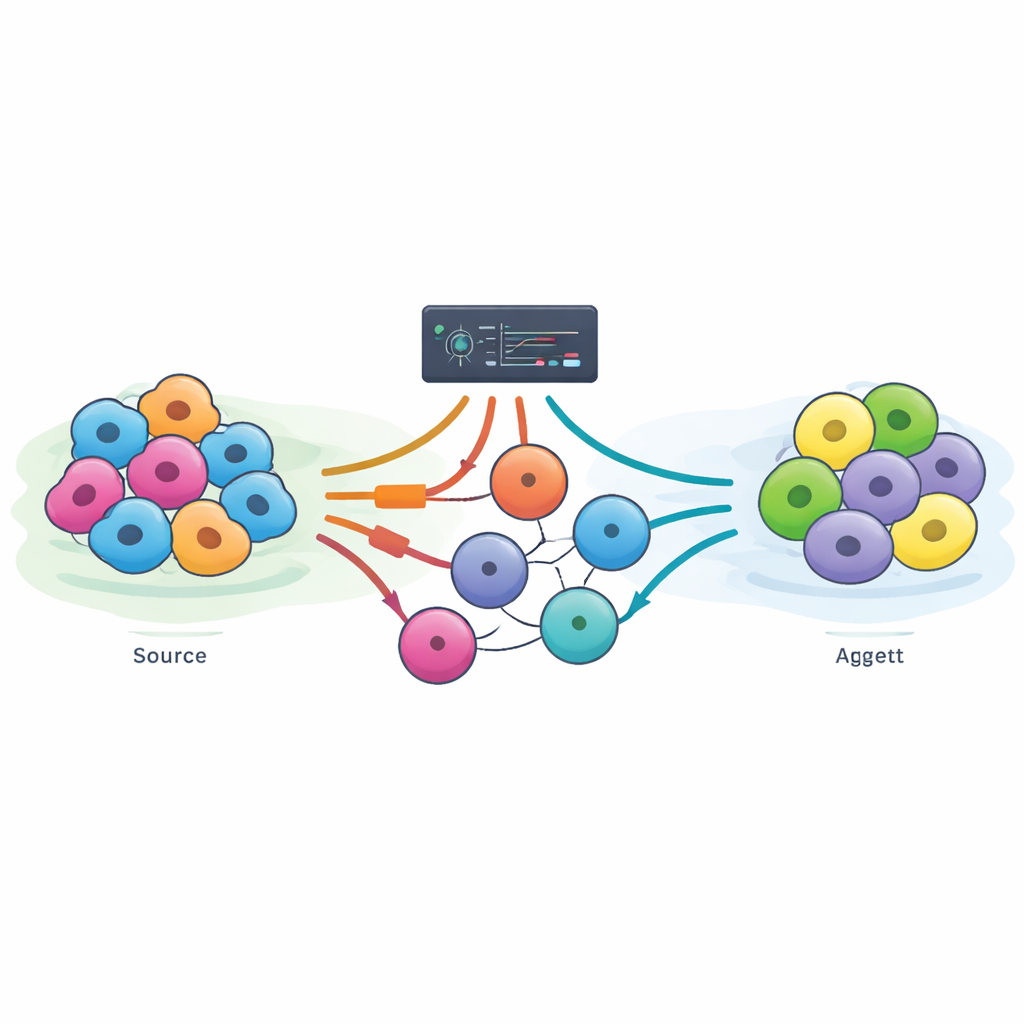
Stel je voor dat je een huidcel op verzoek in een hartcel of een levercel kunt veranderen. Dit soort directe transformatie, cellulaire herprogrammering genoemd, zou artsen in staat kunnen stellen vervangend weefsel te kweken, ziekten in het laboratorium na te bootsen en geneesmiddelen veiliger te testen. Maar het vinden van de juiste moleculaire “schakelaars” om in een cel om te zetten is vergelijkbaar met het raden van een kluiscombinatie: er zijn duizenden mogelijkheden en ze één voor één testen is traag en duur. Dit artikel legt uit hoe onderzoekers computers gebruiken om de opties te verkleinen en introduceert een nieuwe online gids, DiReG, die onderzoekers helpt herprogrammeringsrecepten slimmer te ontwerpen en te controleren.
Van toeval naar systematisch ontwerp
Het verhaal van celherprogrammering begon toen onderzoekers ontdekten dat het forceren van één gen, MyoD1, in bindweefselcellen deze in spiercellen kon veranderen. Later werden combinaties gevonden die neuronen of insulineproducerende cellen konden maken, en vier “Yamanaka‑factoren” die volwassen cellen terugdraaiden naar een stamcelachtig stadium. Deze doorbraken toonden wat mogelijk was, maar de manier waarop ze werden gevonden berustte zwaar op deskundige gokwerk en langdurig laboratoriumwerk. Directe herprogrammering—recht van het ene rijpe celtype naar het andere springen—blijft bijzonder lastig omdat veel pogingen halverwege vastlopen, instabiele “hybride” cellen opleveren, of er niet in slagen de vorige identiteit van de cel volledig te wissen.
Computers als receptzoekers
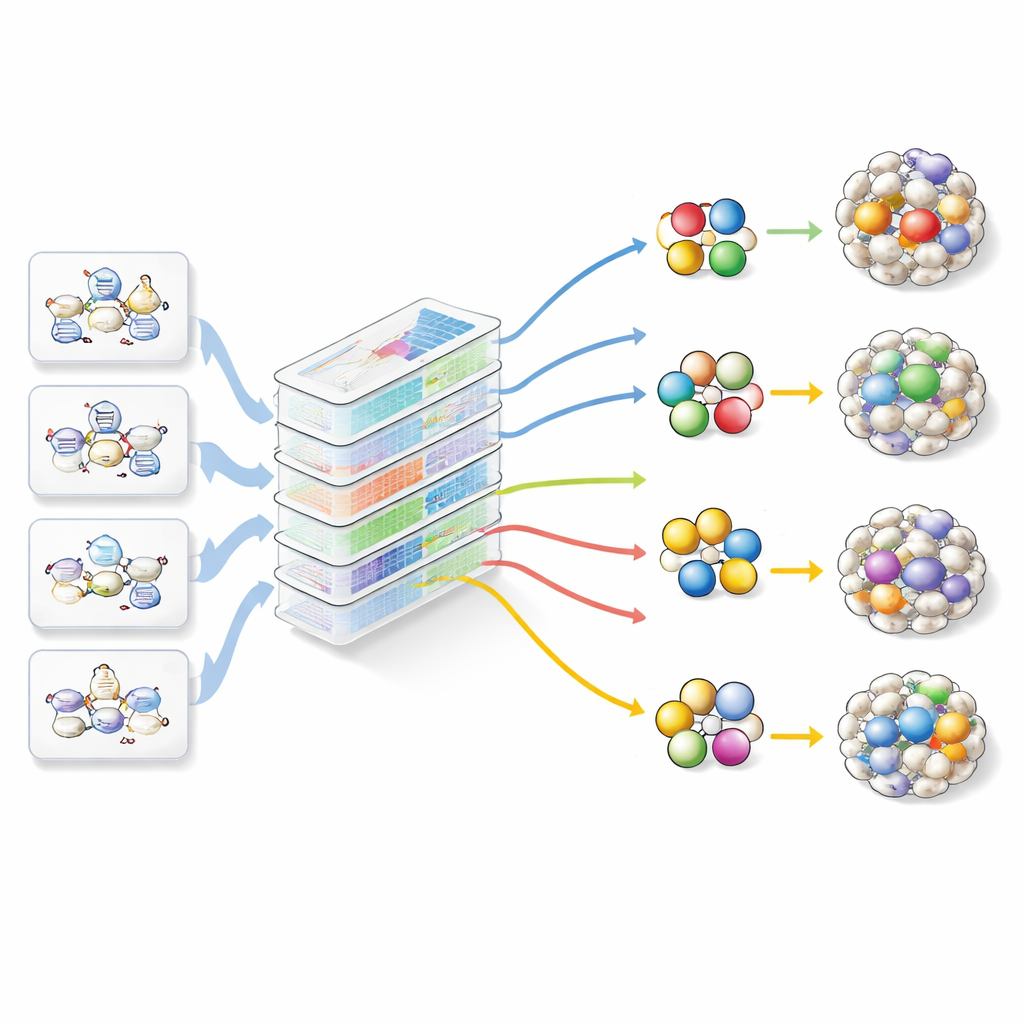
In het afgelopen decennium zijn verschillende computationele hulpmiddelen ontwikkeld om veelbelovende sets transcriptiefactoren te selecteren—degenen die als hoofdschakelaars voor celdentiteit fungeren. Het artikel bespreekt zes toonaangevende methoden die grote datasets van genexpressie en DNA‑regulatie doorzoeken om te suggereren welke factoren mogelijk een verandering van het ene celtype naar het andere kunnen aansturen. Sommige richten zich voornamelijk op welke genen aan of uit staan, anderen bouwen bedrading‑achtige regelnetwerken, en nieuwere methoden verwerken informatie over DNA‑toegankelijkheid en enhancers, waar veel schakelaren zitten. Elke stap vooruit voegt nuttige details toe, maar geen van de methoden is als duidelijke winnaar naar voren gekomen, deels omdat ze op verschillende datasets en onder uiteenlopende condities zijn getest, wat eerlijke vergelijkingen onmogelijk maakt.
Verborgen complexiteit in de cel
De auteurs wijzen erop dat alle huidige tools verschillende lagen biologische nuance over het hoofd zien. Een enkel “gen” kan in veel licht verschillende eiwitversies (isoformen) voorkomen die zich verschillend gedragen, en de huidige modellen behandelen die meestal als één. Chemische labels op DNA, zoals methylatie, kunnen controle-eiwitten blokkeren of aantrekken, maar de meeste algoritmen negeren of een doelplaats überhaupt bruikbaar is. Veel cruciale hulpstoffen—eiwitpartners, concurrerende familieleden die om dezelfde bindingsplaatsen vechten, en kleine regulerende RNA’s die ongewenste berichten stilleggen—worden ook weggelaten. Daarbovenop vertrouwen de meeste methoden op gemiddelde signalen uit mengsels van cellen en op RNA‑niveaus, die slechts globaal de werkelijke eiwitactiviteiten volgen die daadwerkelijk verandering aansturen.
Een nieuwe gids om de opties te verkennen
Om ondanks deze hiaten vooruitgang te boeken, bouwden de auteurs DiReG (Direct Reprogramming Guide), een webapplicatie die meer als een controlecentrum fungeert dan als een nieuw alleswetend algoritme. DiReG verzamelt voorspellingen van belangrijke bestaande tools, voegt een eenvoudige op motieven gebaseerde methode toe die direct werkt vanuit open‑chromatinegegevens, en koppelt dit aan een gecureerde bibliotheek van honderden herprogrammeringsartikelen. Met ingebouwde vraag‑en‑antwoordsystemen kunnen onderzoekers snel protocollen, factorcombinaties en experimentele details in de literatuur vinden. Ze kunnen vervolgens kandidaatfactorensets in een analyseruimte plaatsen waar DiReG hun regelnetwerken tekent, test of de beïnvloede genen lijken op die in het gewenste weefsel, controleert waar de factoren van nature actief zijn, en bekende interactiepartners en isoformen markeert die conversie kunnen stimuleren of belemmeren.
Een stap naar slimmer celomzetting
Voor niet‑specialisten is de kernboodschap dat dit werk nog niet een druk‑op‑de‑knoprecept oplevert om elke cel in elke andere te veranderen. In plaats daarvan biedt het een gecentraliseerde, interactieve kaart van wat bekend is, wat is geprobeerd en welke genetische schakelaars het waarschijnlijkst samen werken. Door onderzoekers te helpen computer‑voorspellingen snel met biologische context te combineren, streeft DiReG ernaar doodlopende experimenten te verminderen en protocolontwerp rationeler te maken. De auteurs schetsen ook wat nog ontbreekt—rijkere data over eiwitvormen, chemische markeringen, cel‑tot‑cel interacties en de werkelijke eiwitactiviteit. Naarmate opkomende technologieën deze lagen invullen, zouden toekomstige hulpmiddelen gebouwd op de hier getoonde ideeën directe cellulaire herprogrammering betrouwbaarder, veiliger en dichter bij medische toepassing in de praktijk kunnen maken.
Bronvermelding: Lauber, M., List, M. Navigating the landscape of direct cellular reprogramming with DiReG. npj Syst Biol Appl 12, 35 (2026). https://doi.org/10.1038/s41540-026-00652-z
Trefwoorden: cellulaire herprogrammering, transcriptiefactoren, computationele biologie, genregulatie-netwerken, regeneratieve geneeskunde