Clear Sky Science · nl
Simulatiegebaseerde inferentie van celmigratiedynamiek in complexe ruimtelijke omgevingen
Hoe immuuncellen hun weg vinden door druk weefsel
Onze immuuncellen moeten vaak door dicht, doolhofachtig weefsel knijpen om infectiehaarden of lymfeklieren te bereiken. Deze studie stelt een ogenschijnlijk eenvoudige vraag met grote implicaties: hoe navigeren deze cellen door zulke rommelige omgevingen, en hoe kunnen we hun gedrag betrouwbaar afleiden uit rommelige microscoopdata? Door precies geconstrueerde laboratorium“doolhoven” te combineren met geavanceerde computersimulaties en moderne machine‑learningtools, tonen de auteurs een nieuwe manier om de regels te ontcijferen die celbeweging in complexe omgevingen sturen.
Een piepklein doolhof bouwen voor immuuncellen
Om te onderzoeken hoe de omgeving beweging beïnvloedt, richtten de onderzoekers zich op dendritische cellen—immuunwachters die van perifeer weefsel naar lymfeklieren moeten reizen, geleid door chemische lokstoffen genaamd chemokinen. Ze bouwden een microgefabriceerd chip: een vlakke “pilaarbossen” van regelmatig geplaatste zuilen gemaakt van siliconenrubber (PDMS), met smalle openingen van 10 micrometer die de nauwe ruimten in echt weefsel nabootsen. Aan de ene kant van de chip werden tienduizenden dendritische cellen geplaatst; de tegenovergestelde kant bevatte een bron van de chemokine CCL19, die een stabiel gradiënt over de pilaren creëert. Met time‑lapsemicroscopie volgden ze de kernen van individuele cellen elke 30 seconden terwijl ze naar de chemokinebron probeerden te bewegen. 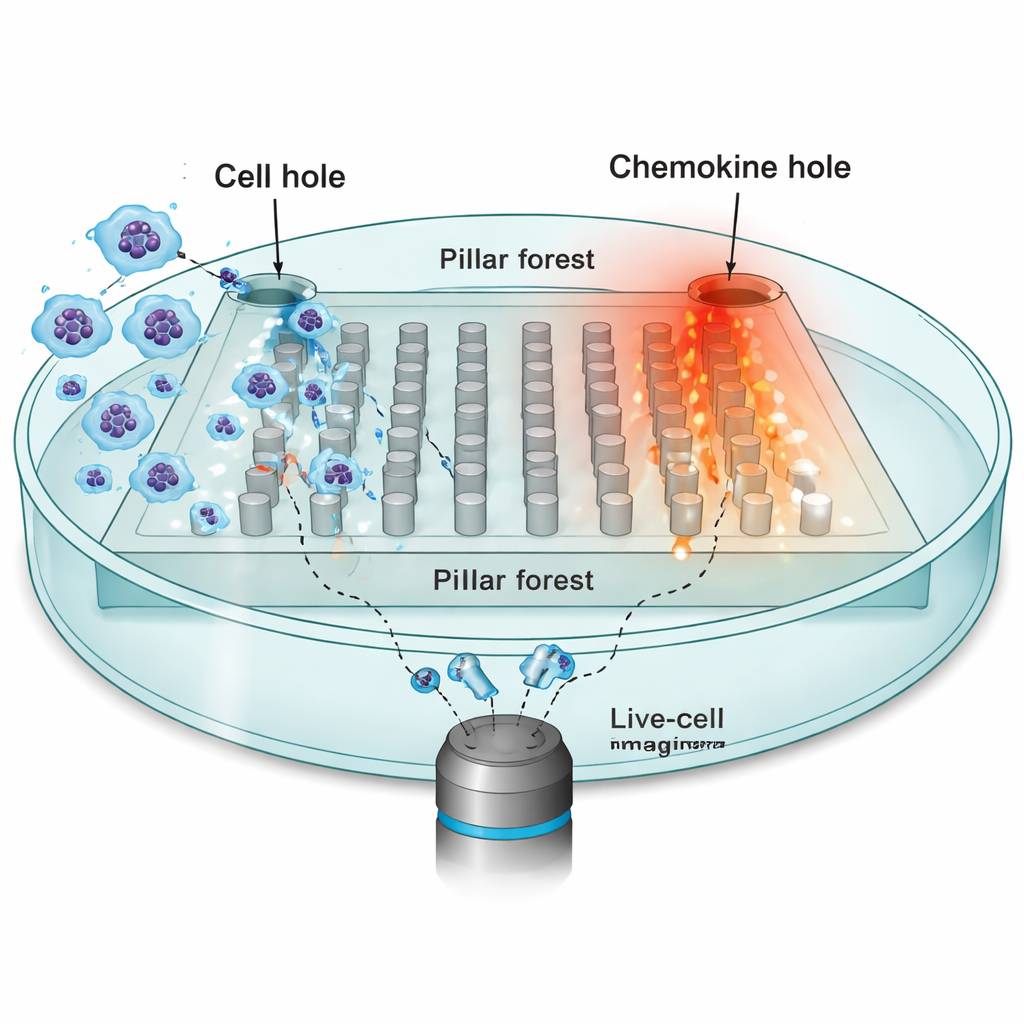
Biologie omzetten in een virtueel experiment
Om deze diversiteit te duiden, bouwde het team een gedetailleerd computationeel model van celmigratie met een kader dat bekend staat als het Cellular Potts‑model. In plaats van een cel als een eenvoudig punt te behandelen, representeert deze benadering elke cel als een uitgebreid vlak op een rooster, waardoor deze van vorm kan veranderen, tussen pilaren kan persen en op chemische signalen kan reageren. Het model omvat vier cruciale ingrediënten: hoe sterk een cel door het chemokinegradiënt wordt aangetrokken (mdir), hoeveel neiging hij heeft om in zijn huidige bewegingsrichting aan te houden (mrand), hoe vaak hij zich heroriënteert (vastgelegd door een snelheid λ), en zijn effectieve grootte (a). Door deze parameters aan te passen en simulaties uit te voeren, genereert het model synthetische sporen die direct vergeleken kunnen worden met de opgenomen celpaden in het pilaarbos.
Waarom handmatig gekozen maatstaven tekortschieten
Traditioneel vatten onderzoekers dergelijke bewegingsdata samen met een handvol vertrouwde statistieken—hoe ver een cel reist (verplaatsing), hoe snel hij beweegt (snelheid), en hoe zijn richting in de loop van de tijd verandert (draaihoeken). De auteurs gebruikten deze handgemaakte maten eerst binnen een techniek genaamd approximate Bayesian computation (ABC), die zoekt naar parameterinstellingen die gesimuleerde sporen op de experimentele laten lijken. Ze vonden dat hoewel deze samenvattingen brede trends vatten, ze veel van de fijnmazige structuur in de data missen. Daardoor bleven sommige modelparameters, vooral die welke de willekeurige persistentie en het timen van heroriëntatie bepalen, slecht geconstrueerd of zelfs bevooroordeeld. Bovendien vereiste ABC honderden duizenden simulaties en vele uren rekenwerk om acceptabele fits te bereiken.
De neurale netwerken laten leren wat telt
Om deze beperkingen te overwinnen, wendde de studie zich tot een nieuwere familie methoden genaamd neural posterior estimation (NPE). Hierbij wordt een neuraal netwerk direct getraind op veel paren van gesimuleerde data en onderliggende parameters. Een deel van het netwerk leert automatisch zijn eigen compacte set “samenvattende kenmerken” uit gehele verzamelingen celsporen; een ander deel leert hoe die kenmerken terug te koppelen zijn naar waarschijnlijke parameterwaarden. Cruciaal is dat deze geleerde kenmerken expliciet worden geoptimaliseerd voor nauwkeurige parameterinvoer, niet voor menselijke interpreteerbaarheid. De auteurs hergebruikten vervolgens de geleerde samenvattingen binnen een ABC‑kader, waardoor een hybride pijplijn ontstond die de robuustheid van ABC combineert met de flexibiliteit van neurale netwerken. 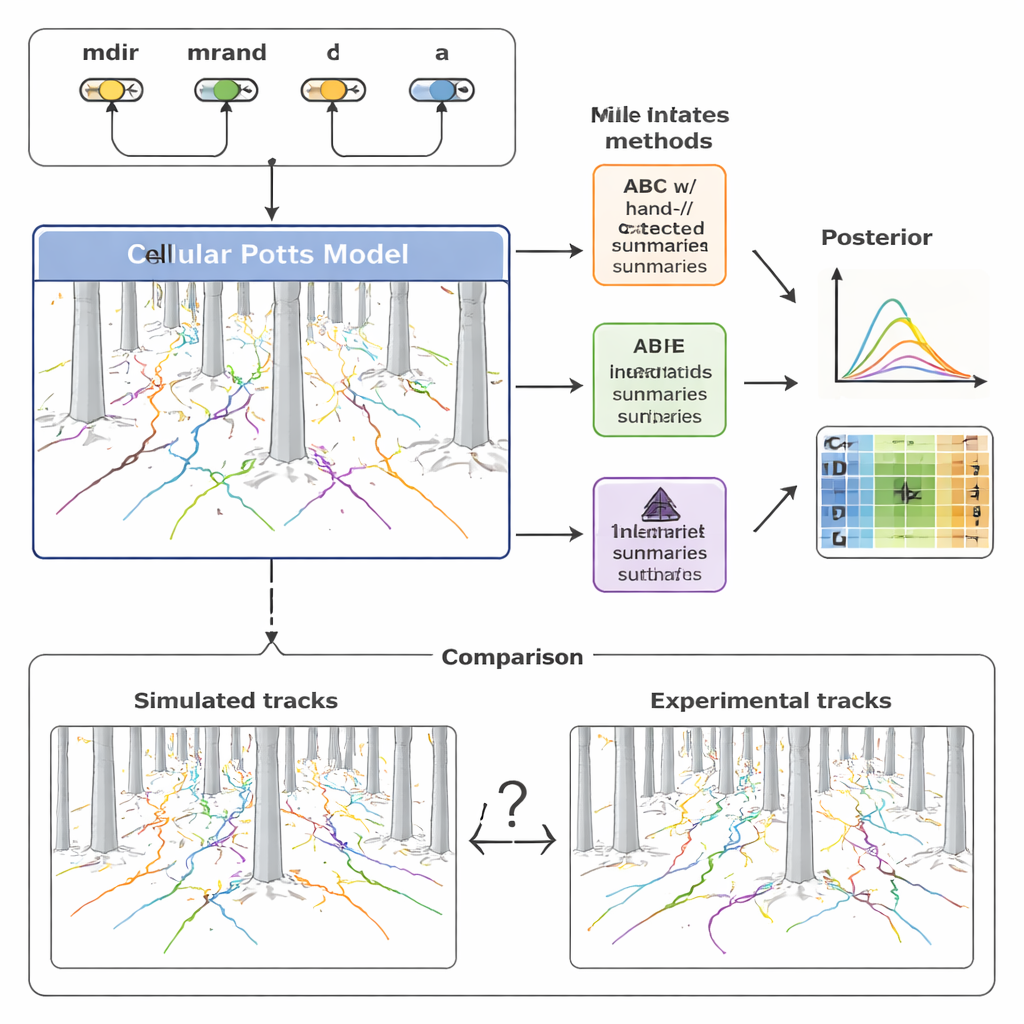
Wat de nieuwe aanpak onthult over celnavigatie
Met dit gekalibreerde model onderzochten de onderzoekers hoe chemokinesignalen en fysieke obstakels samen migratie vormen. De afgeleide celformaat suggereerde dat dendritische cellen effectief krimpen en vervormen om door de 10‑micrometer openingen te passen, in overeenstemming met hun bekende flexibiliteit. Simulaties gaven aan dat persistent willekeurig bewegen een belangrijke drijfveer is voor hoe wijd cellen zich verspreiden, zelfs zonder chemokine‑geleiding, en dat het pilaarbos cellen kan vasthouden wanneer sterke richtinggevende signalen en persistentie samenwerken. Verrassend genoeg voorspelt het model dat een chemokinesignaal dat in het begin kort actief is, in sommige gevallen meer cellen kan helpen het doel te bereiken dan een constant signaal, omdat langdurige aantrekking cellen binnen obstakels kan doen cirkelen in plaats van ze eruit te laten ontsnappen.
Waarom dit ertoe doet voor biologie en modellering
Voor niet‑specialisten is de kernboodschap tweeledig. Ten eerste is immuuncelmigratie in weefsels niet alleen het volgen van een chemisch spoor; het ontstaat uit een subtiele wisselwerking tussen geleidingssignalen, de eigen bewegingsneigingen van cellen en de fysieke indeling van hun omgeving. Ten tweede vereist het afleiden van deze regels uit beeldgegevens dat de computer leert welke patronen in de data het meest informatief zijn, in plaats van uitsluitend te vertrouwen op eenvoudige, door mensen ontworpen maatstaven. Door microgeëngineerde experimenten, vormresoluerende simulaties en neurale netwerkgebaseerde inferentie te integreren, biedt dit werk een krachtig sjabloon om te bestuderen hoe cellen van diverse typen door complexe omgevingen bewegen, met potentiële toepassingen variërend van het begrijpen van immuunsurveillance tot het ontwerpen van betere kankertherapieën.
Bronvermelding: Arruda, J., Alamoudi, E., Mueller, R. et al. Simulation-based inference of cell migration dynamics in complex spatial environments. npj Syst Biol Appl 12, 20 (2026). https://doi.org/10.1038/s41540-026-00648-9
Trefwoorden: celmigratie, dendritische cellen, chemokine‑gradiënten, simulatiegebaseerde inferentie, microfluidische pilaarbossen