Clear Sky Science · nl
SMART: ruimtelijke multi-omica-aggregatie met behulp van graf-neurale netwerken en metrisch leren
Weefsels zien als buurtenkaarten
Ons lichaam bestaat uit levendige cellulaire buurten, waarin genen, eiwitten en de verpakking van DNA nauwkeurig samenwerken op specifieke locaties. Nieuwe microscopen en sequentietechnieken kunnen nu veel van deze moleculaire lagen rechtstreeks in dunne weefselsneden aflezen, maar het omzetten van deze stortvloed aan gelaagde, ruimtelijke gegevens naar heldere beelden van hoe organen zijn georganiseerd, is een enorme computationele uitdaging. Deze studie introduceert SMART, een computermethode die onderzoekers helpt deze complexe signalen samen te voegen tot gedetailleerde kaarten van waar verschillende cellulaire gemeenschappen leven en hoe ze zijn gerangschikt.
Waarom het in kaart brengen van cellulaire buurten moeilijk is
Moderne "ruimtelijke multi-omica"-technologieën kunnen meerdere soorten moleculaire informatie tegelijk meten — zoals RNA, eiwitten aan het celoppervlak en hoe open of gesloten het DNA is — terwijl ze de exacte positie van elke meting in een weefselsnede bijhouden. Elk type, of "omische", biedt een ander perspectief op celgedrag, maar ze zijn lawaaierig, hoog-dimensionaal en lopen niet vanzelfsprekend in elkaar over. Daar komt bij dat cellen van hetzelfde type niet altijd bij elkaar geclusterd zijn; ze kunnen als verspreide eilanden door een orgaan voorkomen. Bestaande softwaretools negeren vaak de ruimtelijke indeling, vereenvoudigen hoe de verschillende omics zich tot elkaar verhouden, of hebben moeite om te schalen naar de zeer grote datasets die nieuwe instrumenten kunnen produceren.
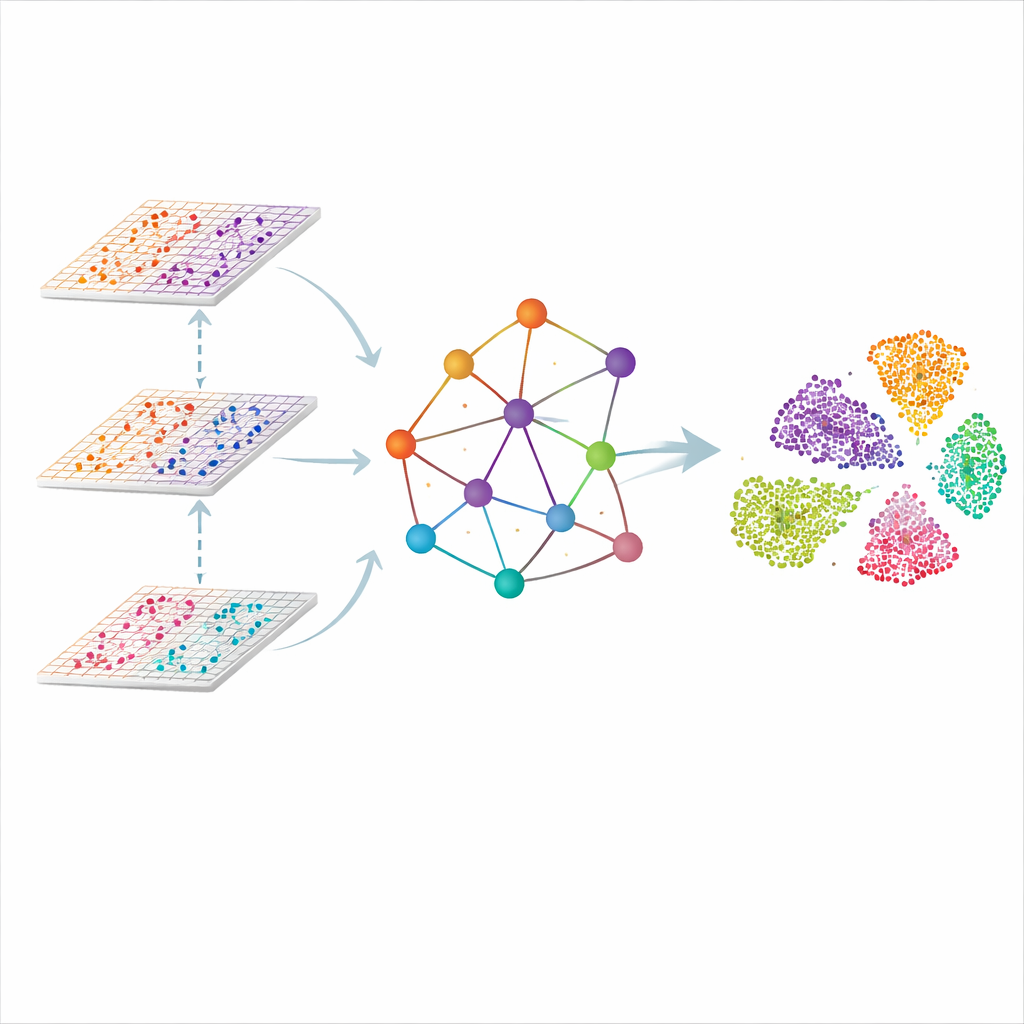
Een graaf van het weefsel, niet alleen een lijst met cellen
SMART benadert het probleem door elke meetplaats in het weefsel als een punt in een netwerk te behandelen. Nabije punten worden verbonden om een ruimtelijke graaf te vormen, en de moleculaire uitlezingen van elke omic worden eerst gecomprimeerd tot een kleinere set gecoördineerde kenmerken die algehele patronen vastleggen in plaats van individuele genen. Een soort neuraal netwerk dat is ontworpen voor grafen stuurt vervolgens informatie langs de verbindingen, waardoor elk punt naar zijn buren kan "luisteren" terwijl het bijhoudt hoe elke omic bijdraagt. Het resultaat is een gedeelde, laag-dimensionale representatie waarin vergelijkbare regio's in het weefsel — zoals verschillende lagen van de hersenen of zones van een lymfeklier — op natuurlijke wijze bij elkaar komen te liggen.
Het model leren wat vergelijkbaar moet zijn
Alleen fysieke buren volgen is niet genoeg, omdat cellen van hetzelfde type ver uit elkaar kunnen liggen. SMART voegt een tweede ingrediënt toe dat is geleend van gezichtsherkenningssystemen: metrisch leren met triplets. Voor elk punt vindt de methode automatisch een ander punt met zeer vergelijkbare moleculaire patronen (een "positief") en één die duidelijk verschillend is (een "negatief"). Vervolgens past het de interne representatie zo aan dat positief-voorbeelden dichterbij worden getrokken en negatief-voorbeelden verder weg worden geduwd, zelfs als ze ver uit elkaar liggen op de weefselsnede. Deze trek-tot-winst loopt naast een reconstructiestap die SMART dwingt de sleutelkenmerken van elke omic-laag te behouden, waardoor ruimtelijke continuïteit wordt gebalanceerd met moleculaire specificiteit.
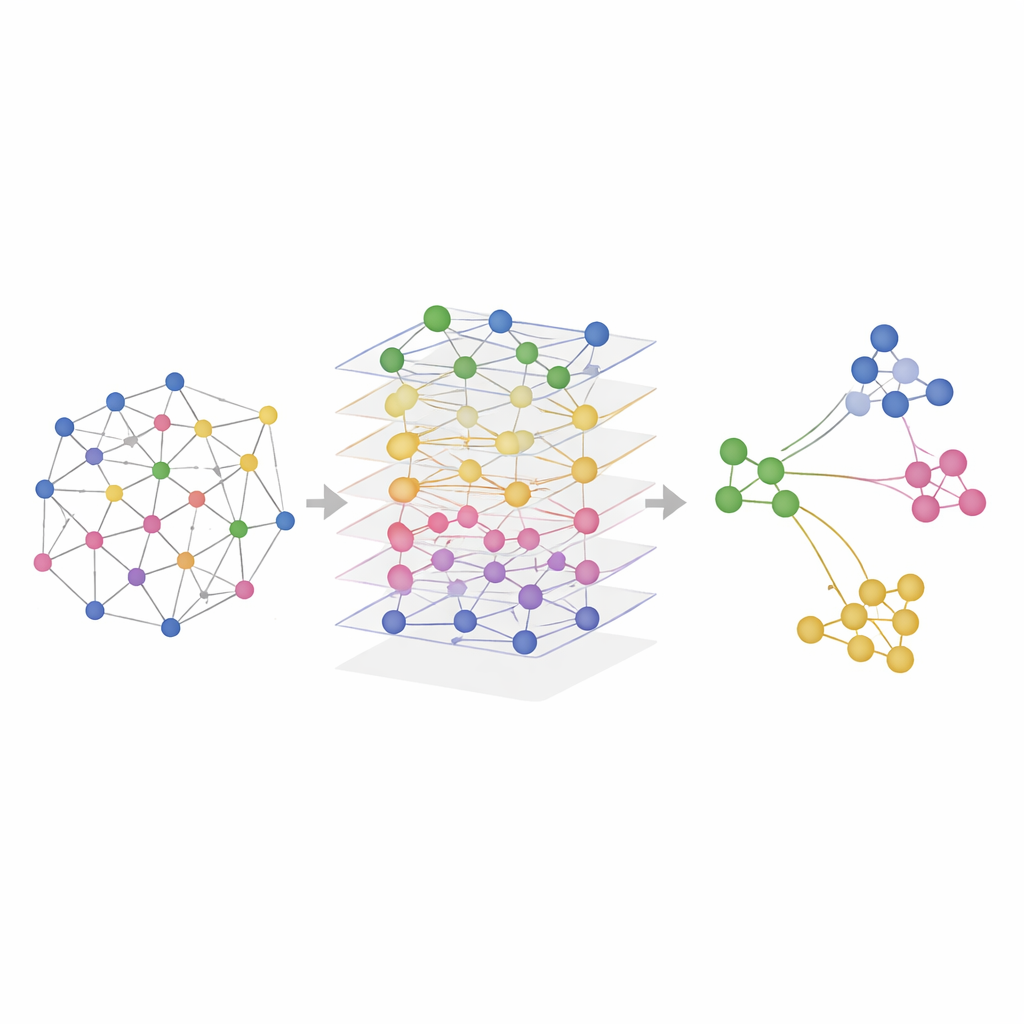
SMART testen in echte weefsels
De onderzoekers hebben SMART getest op zowel gesimuleerde gegevens als echte experimenten die combinaties van RNA, eiwitten en chromatintoegankelijkheid maten in muizenhersenen, muizensplezen, menselijke lymfeklieren en tonsillen. In gecontroleerde simulaties waarbij de werkelijke ruimtelijke regio's bekend waren, reconstrueerde SMART de grondwaarheids-patronen het nauwkeurigst en behield het de relaties die in elke omic-laag aanwezig waren. In echte datasets identificeerde SMART consequent fijne anatomische structuren — zoals specifieke hersenregio's of immuuncelzones in lymfoïde organen — scherper dan concurrerende methoden, terwijl de rekencapaciteit laag bleef. Een verwante versie, SMART-MS genoemd, breidt dezelfde ideeën uit over meerdere weefselsneden, door snedes van hetzelfde orgaan op elkaar af te stemmen en technische verschillen tussen experimenten te corrigeren.
Snel kaarten maken voor de volgende golf ruimtelijke biologie
In eenvoudige bewoordingen is SMART een kaartmaakmotor voor de volgende generatie moleculaire atlassen. Door netwerkachtige modellering van de weefsellay-out te combineren met een ingebouwd vermogen om te bepalen wat als "vergelijkbaar" moet gelden, kan het enorme, rommelige verzamelingen van ruimtelijke multi-omica-metingen omzetten in coherente buurtkaarten van organen. Dit stelt onderzoekers in staat makkelijker te zien waar bepaalde celtypen en microomgevingen zich bevinden, hoe ze veranderen tijdens ontwikkeling of ziekte, en hoe nieuwe experimentele technologieën samenhangen. Naarmate ruimtelijke gegevens blijven groeien in omvang en complexiteit, zullen tools als SMART en SMART-MS essentieel zijn om ruwe metingen om te zetten in biologische inzichten.
Bronvermelding: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Trefwoorden: ruimtelijke multi-omica, graf-neurale netwerken, weefselmicro-omgeving, gegevensintegratie, single-cell biologie