Clear Sky Science · nl
Data-efficiënte coarse-grained moleculaire dynamica leren uit krachten en ruis
Waarom het verkleinen van moleculen ertoe doet
Het simuleren van de onophoudelijke beweging van ieder atoom in een eiwit en het omringende water is een van onze beste middelen om te begrijpen hoe leven op moleculair niveau werkt. Maar deze all-atom simulaties zijn zo rekenintensief dat het volgen van een eiwit tijdens vouw-, ontvouw- of interactieprocessen op biologisch relevante tijden maanden op een supercomputer kan vergen. Dit artikel introduceert een nieuwe manier om snelle, vereenvoudigde modellen van eiwitten te bouwen die zich nog steeds gedragen als hun volledige atomistische tegenhangers, maar veel minder trainingsdata en rekenkracht vereisen dan voorheen.
Van elk atoom naar een eenvoudiger beeld
Traditionele moleculaire dynamica volgt elk atoom en berekent bij elke kleine tijdstap de krachten daartussen. Om het sneller te maken gebruiken wetenschappers vaak coarse-grained modellen, waarbij veel atomen worden samengevoegd tot een kleiner aantal ‘parels’. Deze gereduceerde modellen draaien veel sneller maar hebben historisch moeite gehad om de nauwkeurigheid van volledige atomistische simulaties te evenaren, vooral voor eiwitten met rijk vouwgedrag. Recente ontwikkelingen maken gebruik van machine learning om automatisch betere coarse-grained krachtvelden te vinden, maar het trainen van deze modellen vereiste doorgaans miljoenen gedetailleerde snapshots, elk gelabeld met de krachten op elk atoom—een enorme data- en rekenlast.
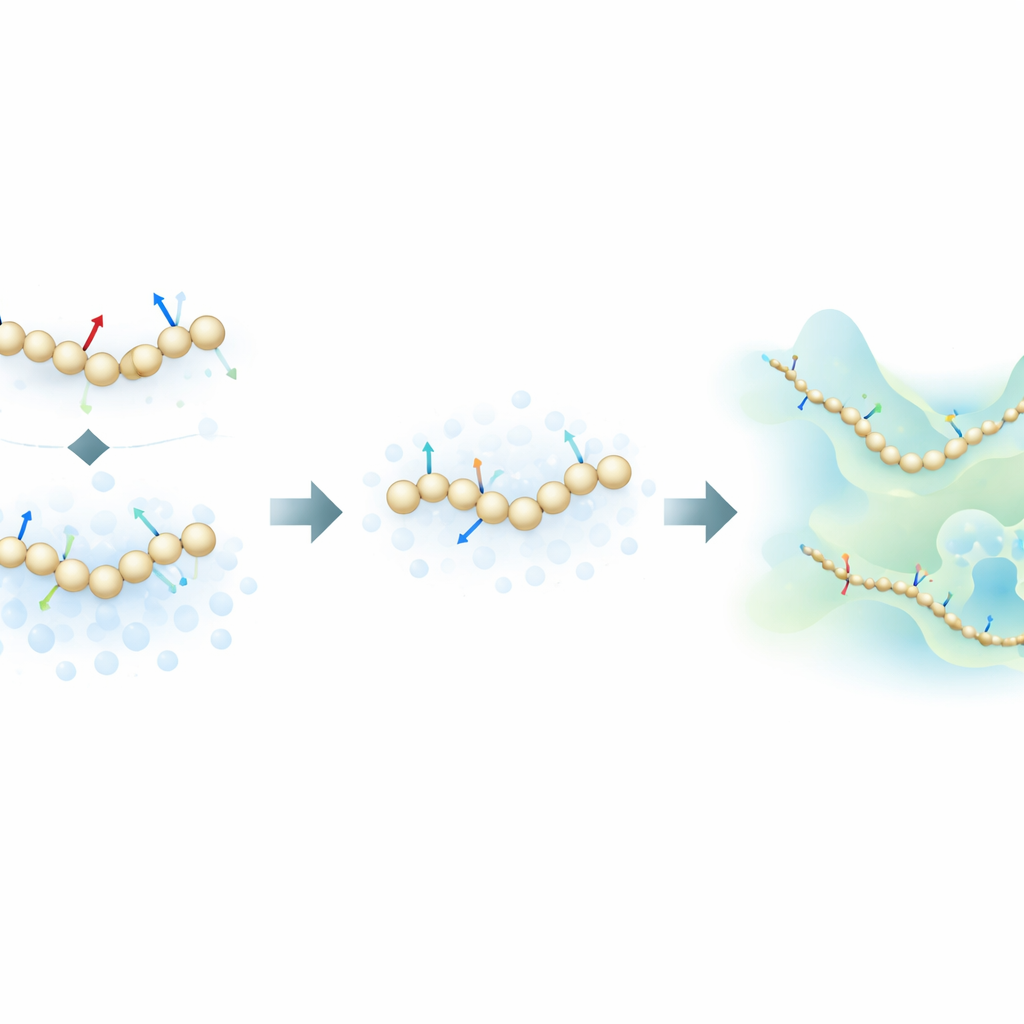
Fysische krachten mengen met informatieve ruis
De auteurs stellen een frisse trainingsstrategie voor die inspiratie haalt uit generatieve diffusiemodellen—dezelfde klasse algoritmen achter veel moderne AI-beeldgeneratoren. In plaats van alleen te leren van de fysische krachten berekend in atomistische simulaties, leert hun methode ook uit hoe moleculaire structuren ruimtelijk verdeeld zijn door gecontroleerd ruis toe te voegen aan coarse-grained configuraties. In dit kader is ruis niet louter een hinderlijke factor die verwijderd moet worden; het wordt een extra informatiebron. Door de traditionele ‘force matching’-aanpak wiskundig te verenigen met denoising-technieken uit diffusiemodellen kan de methode het onderliggende energielandschap van een eiwit afleiden met veel minder gelabelde voorbeelden.
Simpele modellen leren complexe eiwitten na te bootsen
Om hun idee te testen trainden de onderzoekers neurale-netwerk coarse-grained modellen voor meerdere eiwitten van toenemende complexiteit: de kleine miniproteïnes Chignolin en Trp-Cage, het iets grotere NTL9, en het 76-residu-eiwit Ubiquitine. Ze vergeleken drie trainingsmodi: alleen atomistische krachten gebruiken, alleen ruis-gebaseerde informatie, en een combinatie van beide. Voor de kleinere eiwitten lieten ze zien dat de nieuwe gecombineerde aanpak de belangrijkste kenmerken van het vouwlandschap kan reproduceren—zoals de relatieve stabiliteit van gevouwen en ontvouwen toestanden en de aanwezigheid van tussenstadia—met tot honderd keer minder trainingsdata dan standaard force-matching methoden. Verrassend genoeg haalden in regimes met weinig data zelfs modellen die alleen met ruis werden getraind vaak gelijkwaardige of betere nauwkeurigheid dan training op alleen krachten.
Grotere en zwaardere eiwitsystemen bereiken
Ubiquitine is een zwaardere proef: het vastleggen van zijn vouwen en ontvouwen bij realistische temperaturen vereiste historisch gespecialiseerde hardware en extreem lange atomistische runs. Hier trainen de auteurs coarse-grained modellen met een bescheiden dataset bestaande uit korte evenwichtssimulaties rond de gevouwen toestand plus niet-evenwichts ‘pulled’ simulaties die het eiwit geforceerd uitrekken. Ondanks deze bevooroordeelde trainingsset en het ontbreken van een perfecte atomistische referentie onder dezelfde condities, herstelt het model dat op zowel krachten als ruis is getraind een realistisch beeld waarin gevouwen en ontvouwen toestanden naast elkaar bestaan, met een voorkeur voor de gevouwen toestand qua stabiliteit. Daarentegen slaagt een uitsluitend op krachten getraind model er helemaal niet in de gevouwen toestand te stabiliseren, terwijl een alleen-ruis model de voorkeur geeft aan ontvouwen structuren. Opmerkelijk is dat geen van de coarse-grained modellen simpelweg de extreem uitgerekte vormen uit de trainingsdata memoriseert, wat erop wijst dat het geleerde energielandschap fysisch betekenisvol is en niet slechts een afdruk van de inputtrajecten.
Wat dit betekent voor toekomstige simulaties
Door ruis tot een trainingssignaal te maken en het te verenigen met fysieke krachten toont dit werk aan dat nauwkeurige coarse-grained modellen van eiwitten gebouwd kunnen worden uit veel kleinere en minder ideale datasets dan eerder gedacht. In de praktijk betekent dat dat onderzoekers mogelijk geen milliseconde-lange atomistische simulaties op gespecialiseerde supercomputers meer nodig hebben voordat ze het gedrag van een biomolecuul met machine-geleerde coarse-grained dynamica kunnen verkennen. In plaats daarvan kunnen meer bescheiden simulaties op algemeen beschikbare hardware voldoende zijn om krachtige gereduceerde modellen te trainen die belangrijke vouwpaden en thermodynamische verhoudingen vastleggen. Hoewel vragen blijven over hoe de toegevoegde ruis het beste gekozen en geïnterpreteerd kan worden en hoe de methode zich houdt op nog grotere, complexere biomoleculaire assemblages, verlaagt deze aanpak de drempel aanzienlijk om data-gedreven coarse-grained simulaties als een routinehulpmiddel in de moleculaire wetenschap te gebruiken.
Bronvermelding: Durumeric, A.E.P., Chen, Y., Pasos-Trejo, A.S. et al. Learning data-efficient coarse-grained molecular dynamics from forces and noise. Nat Commun 17, 2493 (2026). https://doi.org/10.1038/s41467-026-70818-0
Trefwoorden: coarse-grained moleculaire dynamica, machine learning krachtvelden, eiwitvouwing simulaties, diffusiemodellen in scheikunde, data-efficiënte simulatie