Clear Sky Science · nl
Niet-lineaire genomische selectie-index versnelt verbetering van gewassen met meerdere eigenschappen
Slimmer veredelen voor een hongerigere wereld
Naarmate de wereldbevolking groeit en klimaten onvoorspelbaarder worden, moeten plantenveredelaars meerdere gewaseigenschappen tegelijk verbeteren—zoals opbrengst, hoogte en bloeiwijze—sneller dan ooit. Dit artikel presenteert een nieuw wiskundig hulpmiddel dat veredelaars precies daarmee helpt door DNA-informatie op een realistischer manier te gebruiken, waarbij niet alleen individuele geneffecten worden vastgelegd maar ook hun onderlinge interacties. De benadering belooft het maken van betere maïs- en tarwerassen te versnellen zonder dat elk plantje in het veld gemeten hoeft te worden.
Waarom het combineren van veel eigenschappen zo moeilijk is
Veredelaars geven zelden alleen om één eigenschap. Ze willen bijvoorbeeld een hogere korrelopbrengst, maar ook kortere, steviger planten die op het juiste moment bloeien. Klassieke “selectie-indexen” zetten meerdere eigenschappen om in één score om planten te rangschikken. Traditioneel veronderstellen deze indexen dat elke eigenschap op een eenvoudige, lineaire manier bijdraagt en dat de effecten van verschillende eigenschappen gewoon optellen. De echte biologie is rommeliger: eigenschappen beïnvloeden elkaar en er kunnen optimale zones bestaan waar “meer” niet langer beter is. Het negeren van deze niet-lineaire interacties kan de genetische vooruitgang vertragen en zelfs de veredeling in de verkeerde richting duwen.
Van rechte lijnen naar flexibele krommen
Eerdere genomische hulpmiddelen stelden veredelaars in staat om met DNA-markers verspreid over het genoom te voorspellen hoe goed de nakomelingen van een plant zouden zijn, wat leidde tot zogenaamde lineaire genomische selectie-indexen. Die werken goed wanneer geneffecten grotendeels additief zijn. De auteurs breiden een flexibeler, ouder idee uit—de kwadratische fenotypische selectie-index, die al kwadratische termen en interacties tussen eigenschappen toestond—naar het DNA-tijdperk. Hun nieuwe hulpmiddel, de Quadratic Genomic Selection Index (QGSI), gebruikt voorspellingen van genomische fokwaarden en combineert die via zowel lineaire als gebogen (kwadratische) termen. Hiermee kan de index complexe patronen vastleggen zoals gen‑geninteracties en optimale combinatie van eigenschappen, zelfs wanneer veldmetingen niet voor elke cyclus beschikbaar zijn.
De nieuwe index op de proef stellen
Om te beoordelen of deze extra complexiteit rendeert, vergeleken de onderzoekers QGSI met zowel lineaire als kwadratische indexen die alleen veldgegevens gebruiken, en met lineaire genomische indexen die DNA gebruiken maar eenvoudig blijven. Ze voerden computersimulaties van maïskweek uit over 10 selectiecycli en analyseerden bovendien twee echte maïs- en vijf tarwe‑datasets van internationale veredelingsprogramma’s. Twee manieren om genetische waarde uit DNA te voorspellen werden getest: een standaard additief model en een flexibeler Gaussiaans kernel-model dat subtiele geninteracties kan opvangen. Over deze instellingen heen produceerde QGSI consequent grotere selectieresponsen—dat wil zeggen: grotere totale verbetering over eigenschappen—dan de lineaire indexen, en over het algemeen was het resultaat beter dan bij de kwadratische fenotypische index.
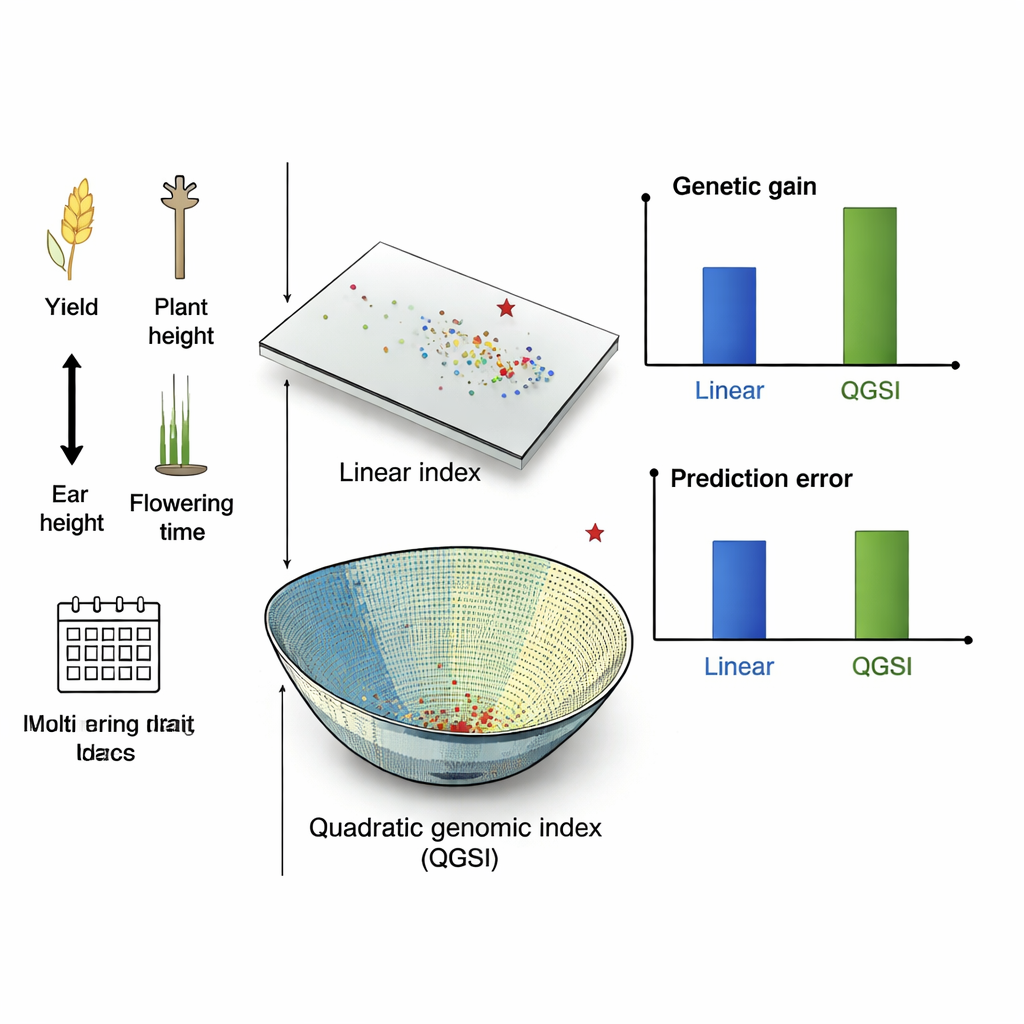
Betere opbrengsten, minder fouten, meer balans
In de gesimuleerde maïscycli leverde QGSI de grootste opbrengsten en bleef het zowel de lineaire genomische indexen als de kwadratische indexen die alleen op veldmetingen leunden, voor. Het had ook de neiging lagere voorspellingsfouten te hebben, wat betekent dat de scores betrouwbaardere richtlijnen waren voor het kiezen van ouderplanten. In echte maïspopulaties uit Mexico en Zimbabwe behaalde QGSI 80–90% hogere opbrengsten dan lineaire genomische indexen wanneer meerdere eigenschappen samen werden verbeterd. In tarweproeven onder verschillende irrigatie- en neerslagomstandigheden was het patroon vergelijkbaar: kwadratische indexen presteerden beter dan lineaire, en het combineren van QGSI met het Gaussiaanse kernel-model gaf de sterkste en meest stabiele verbeteringen over omgevingen heen, vooral voor korrelopbrengst terwijl plantlengte en bloeitijd binnen acceptabele grenzen bleven.
Wat dit betekent voor toekomstige gewassen
Voor niet‑specialisten is de kernboodschap dat veredelaars nu een realistischer scoresysteem hebben dat weerspiegelt hoe genen en eigenschappen écht met elkaar omgaan, in plaats van ze in een rechte-lijnmodel te dwingen. De auteurs raden aan de kwadratische fenotypische index te gebruiken wanneer in vroege stadia alleen veldgegevens beschikbaar zijn, en over te schakelen naar de QGSI zodra genomische gegevens en snelle selectiecycli aanwezig zijn. Door niet-lineaire genetische relaties beter vast te leggen, kan QGSI de verbetering van meerdere eigenschappen in gewassen versnellen en helpen nieuwe maïs- en tarwerassen te leveren die hogere opbrengst hebben, veerkrachtiger zijn en beter aangepast aan uitdagende omgevingen.
Bronvermelding: Jesús Cerón-Rojas, J., Montesinos-López, O.A., Montesinos-López, A. et al. Nonlinear genomic selection index accelerates multi-trait crop improvement. Nat Commun 17, 1991 (2026). https://doi.org/10.1038/s41467-026-69890-3
Trefwoorden: genomische selectie, gewaskweek, maïs, tarwe, verbetering van meerdere eigenschappen