Clear Sky Science · nl
XL-MSDigger: een deep learning-gebaseerde, veelzijdige oplossing voor cross-linking massaspectrometrie
Inzicht in hoe eiwitten samenhouden
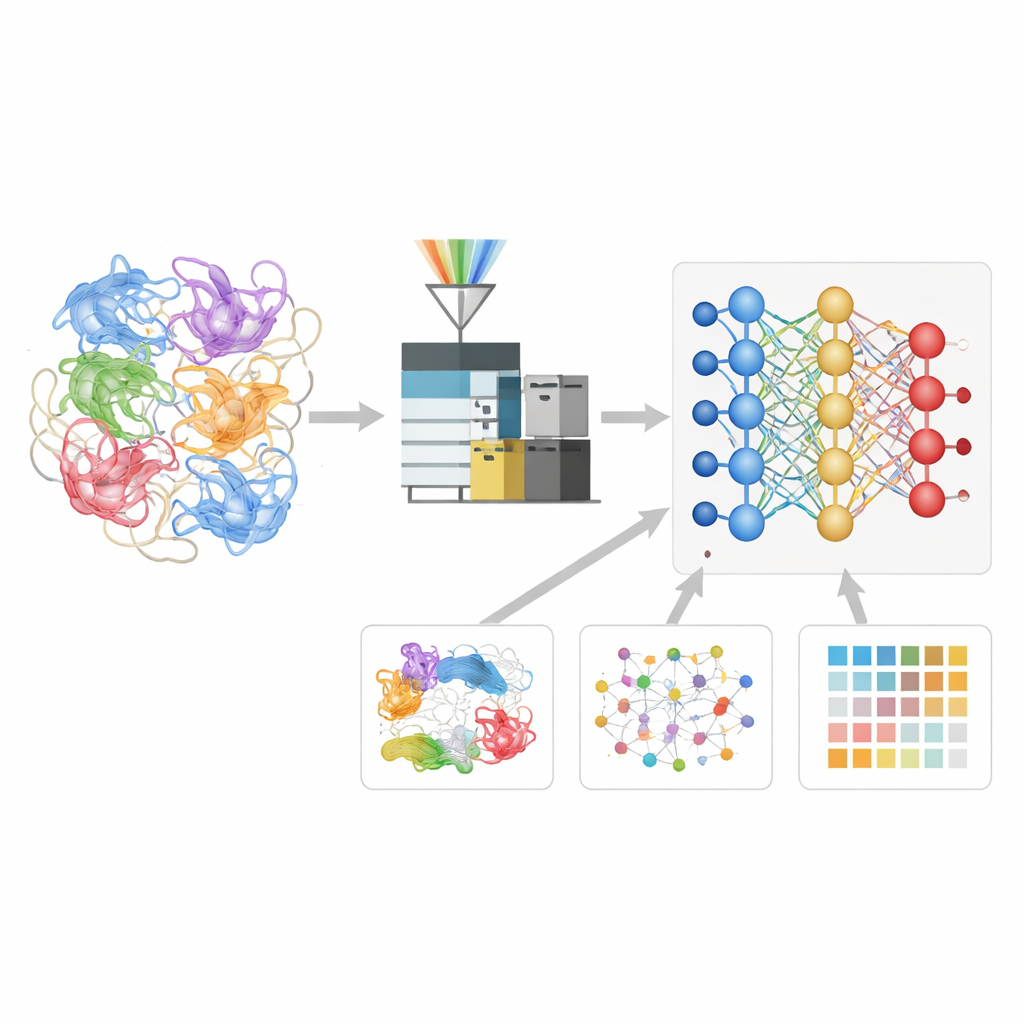
Elk proces in ons lichaam hangt ervan af dat eiwitten niet alleen in de juiste vormen vouwen, maar ook de juiste partners vinden. Deze moleculaire relaties in actie observeren is echter berucht lastig. Deze studie introduceert XL-MSDigger, een softwareplatform dat moderne kunstmatige intelligentie gebruikt om veel duidelijkere signalen uit een rumoerige experimentele techniek — cross-linking massaspectrometrie — te halen, waardoor wetenschappers kunnen uittekenen hoe eiwitten zijn gerangschikt en met wie ze in de cel interageren.
Een druk moleculair landschap ontwarren
Om te achterhalen hoe eiwitten zijn opgebouwd en hoe ze verbindingen vormen, gebruiken onderzoekers vaak cross-linking massaspectrometrie. In deze aanpak verbinden kleine chemische “bruggen” nabijgelegen delen van eiwitten met elkaar. De gekoppelde stukken worden vervolgens in fragmenten gebroken en in een massaspectrometer gewogen. In principe onthult het fragmentpatroon welke eiwitdelen in elkaars nabijheid zaten, vergelijkbaar met het vinden van welke pagina’s van een boek aan elkaar vastgeknepen waren. In de praktijk zijn de resulterende gegevens echter extreem complex. Bestaande computerhulpmiddelen kijken meestal alleen naar de basismassa-informatie en hebben moeite met het enorme aantal mogelijke combinaties, wat leidt tot gemiste verbindingen en valse matches.
Een neurale netwerk de taal van eiwitfragmenten leren
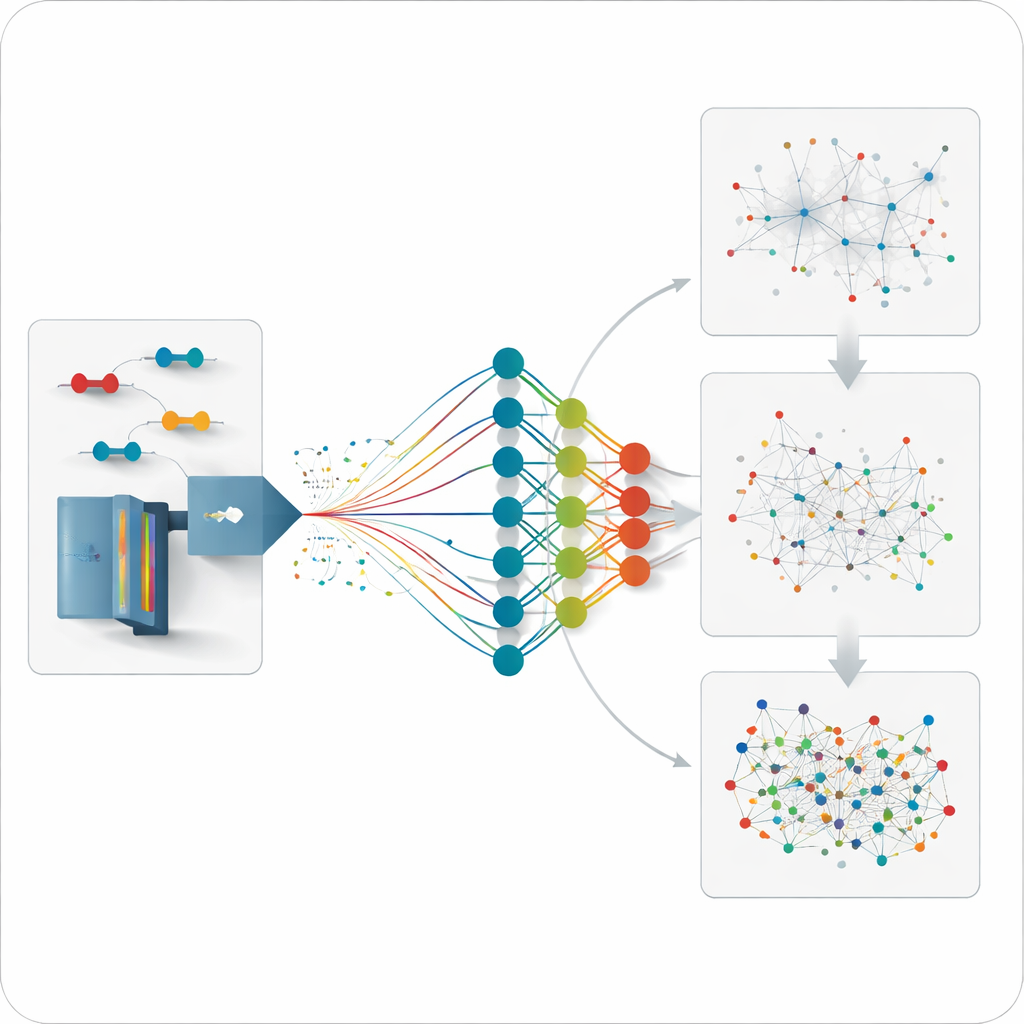
De auteurs ontwikkelden een deep learning-model genaamd Deep4D-XL om deze cross-linking-experimenten beter te interpreteren. Ze creëerden eerst een grote referentieset door eiwitten uit menselijke cellen te cross-linken, ze in peptiden te breken en niet alleen hun massa’s op te nemen, maar ook hoe lang ze erover deden om door het instrument te reizen en hoe ze zich gedroegen in een ion-mobiliteitskamer. Elk cross-gelinkt paar werd gecodeerd voor het model, dat een tweeling-«Siamese» ontwerp gebruikt om beide peptidepartners te lezen en een cross-attention stap om hun informatie te combineren. Hieruit leert het netwerk drie sleutel-eigenschappen van elk nieuw cross-gelinkt peptide te voorspellen: wanneer het zou moeten verschijnen in het experiment, hoe het zich zou moeten verplaatsen, en hoe het fragmentatiepatroon eruit zou moeten zien.
Voorspellingen omzetten in zuiverdere signalen
XL-MSDigger verpakt deze voorspellingsmotor in analysetrajecten voor twee belangrijke dataverzamelstijlen. In de traditionele, gerichte stijl neemt het instrument selectief fragmenten op van ionen die het ter plekke kiest. XL-MSDigger neemt de initiële matches van gevestigde zoeksoftware en evalueert ze opnieuw met behulp van het door het model voorspelde gedrag voor elke kandidaat. Een tweede neuraal netwerk vergelijkt voorspelling en experiment langs meerdere dimensies en kent verbeterde scores toe. Deze herscoring verdubbelt bijna het aantal met vertrouwen gedetecteerde verbindingen tussen verschillende eiwitten in gist- en menselijke monsters, terwijl de foutpercentages laag blijven, en onthult veel meer eiwit–eiwitinteracties dan voorheen.
Betekenis geven aan overvloed aan onbevooroordeelde gegevens
Een nieuwere manier om deze instrumenten te gebruiken, data-onafhankelijke acquisitie genoemd, registreert fragmenten van vrijwel alles in een monster, wat de dekking verbetert maar overweldigende data genereert. Tot nu toe was er geen goede manier om in te schatten hoeveel van de resulterende cross-links echt waren. XL-MSDigger gebruikt Deep4D-XL om een zorgvuldig afgestemde “decoy”-bibliotheek van nep-cross-links op te bouwen en analyseert vervolgens echte en decoy-entries samen. Door te kijken hoe vaak decoys doorheen glippen, kan de software de false discovery rate inschatten en een ander neuraal netwerk trainen om echte van valse matches te onderscheiden. Deze herscoring verhoogt het aantal betrouwbare cross-linked signalen met ongeveer vijfvoud en produceert een duidelijke scheiding tussen echte en decoy-patronen.
Voorspellen wat nog niet gemeten is
Aangezien het model kan voorspellen hoe elk plausibel cross-gelinkt peptide zich zou moeten gedragen, kan het team een stap verder gaan en data analyseren voor verbindingen die nooit direct zijn gemeten. Ze genereren middelgrote voorspelde bibliotheken gericht op geselecteerde eiwitten of interactienetwerken en doorzoeken de onbevooroordeelde data tegen deze bibliotheken. Deze strategie onthult extra verbindingen binnen individuele eiwitten en tussen partners van belangrijke chaperonne-eiwitten, met afstanden die goed overeenkomen met bekende driedimensionale structuren. Ook herstelt het interacties die gemist werden door de traditionele, meer beperkte experimentele bibliotheken, vooral voor verbindingen met lage abundanties.
Een helderder venster op eiwitpartnerschappen openen
Voor niet-specialisten is de kernboodschap dat XL-MSDigger fungeert als een sterk getrainde patroonherkenner bovenop een al krachtig experimenteel hulpmiddel. Door te leren hoe echte cross-linked signalen er in meerdere dimensies tegelijk uit moeten zien, kan het enorme, rommelige datasets doorsorteren, waarschijnlijke impostors wegfilteren en echte maar eerder verborgen eiwitverbindingen redden. Hoewel volledige, proteoombrede toepassingen nog steeds grote rekenkracht vergen, laat dit werk zien dat het combineren van cross-linking-experimenten met deep learning onze blik op hoe eiwitten zijn gerangschikt en met wie ze in de cel samenkomen, aanzienlijk kan verscherpen.
Bronvermelding: Chen, M., Hao, Y., Huang, X. et al. XL-MSDigger: a deep learning-based, versatile solution for cross-linking mass spectrometry. Nat Commun 17, 2554 (2026). https://doi.org/10.1038/s41467-026-69489-8
Trefwoorden: eiwitinteracties, cross-linking massaspectrometrie, deep learning, proteomics, data-onafhankelijke acquisitie