Clear Sky Science · nl
eQTL in ziek colonweefsel identificeert potentiële doelfgenen geassocieerd met IBD
Waarom dit onderzoek belangrijk is voor darmgezondheid
Inflammatoire darmziekten (IBD) zoals de ziekte van Crohn en colitis ulcerosa treffen miljoenen mensen wereldwijd, vaak op jonge volwassen leeftijd, en veroorzaken levenslange spijsverteringsproblemen. Uit grootschalige genetische studies weten we dat honderden plekken in ons DNA het risico op het krijgen van IBD beïnvloeden, maar voor het merendeel van deze regio’s weten we nog niet welke genen ze aansturen of hoe ze de darm veranderen. Deze studie pakt dat mysterie aan door direct colongewebe van mensen met IBD te onderzoeken om te zien hoe hun genetische varianten de genactiviteit veranderen, en onthult mogelijke zwakke plekken in de darmbarrière en het immuunsysteem die in de toekomst door therapieën gericht kunnen worden.
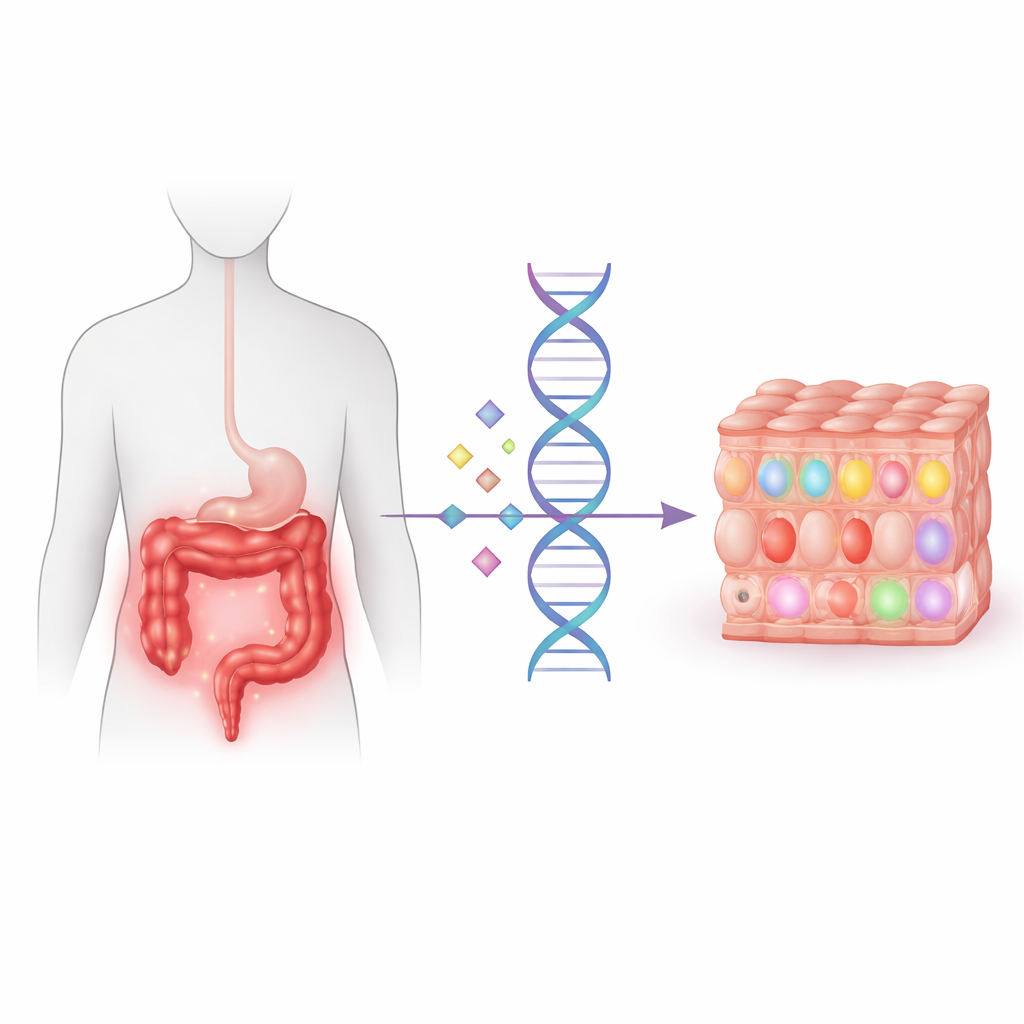
De genetische aan/uit-schakelaars lezen in het zieke colon
De onderzoekers concentreerden zich op “aan/uit-schakelaars” in het genoom: plaatsen waar DNA-varianten nabijgelegen genen subtiel omhoog of omlaag bijsturen. Deze worden expression quantitative trait loci genoemd, of eQTL, en ze zijn het gemakkelijkst te detecteren als je de genactiviteit meet in het juiste weefsel. In plaats van alleen gezonde donors te bestuderen, verzamelde het team niet-geïnflammeerde colonmonsters van 252 IBD-patiënten. Ze maten welke genen in elk monster actief waren en vergeleken dit met ieders DNA, waarbij ze meer dan acht miljoen varianten over meer dan dertigduizend genen scanden om varianten te vinden die consequent de genactiviteit in het colon veranderden.
IBD-weefsel vergelijken met gezond colon
Om te begrijpen wat er speciaal is aan ziek weefsel, vergeleek het team hun bevindingen met twee grote referentieprojecten die eQTL in colon van mensen zonder IBD in kaart brachten. De meeste genetische regelsignalen waren gedeeld: ruwweg 88% van de eQTL die in IBD-colon werden gedetecteerd, kwam overeen met die in gezond colon, en hun effecten waren sterk gecorreleerd. Dit suggereert dat het kernregulatieprogramma van het colon grotendeels intact blijft, zelfs bij IBD-patiënten. Toch kwam ongeveer 5–10% van de signalen in de IBD-cohort niet overeen met de gezonde referenties, ondanks dat die studies meer deelnemers en dus meer statistische power hadden. Deze “alleen-in-IBD” signalen wijzen op regulatoire veranderingen die alleen zichtbaar worden, of sterker zijn, in de context van ziekte.
Risico-DNA koppelen aan specifieke colongenen
De cruciale stap was het verbinden van deze aan/uit-schakelaars met de 320 genomische regio’s die eerder in genome-wide associatiestudies aan IBD-risico zijn gekoppeld. Door te onderzoeken waar ziektegebonden varianten en colon eQTL hetzelfde onderliggende DNA-signaal deelden, identificeerden de auteurs 194 potentiële doelfgenen voor 108 van deze risicoregionen, waarmee het aandeel IBD-loci met concrete genkandidaten uit colonweefsel werd verhoogd tot ongeveer een derde. Veel genen vielen in categorieën die biologisch logisch zijn voor IBD: immuunrespons, celadhesie, celgroei en signaalroutes die reguleren hoe darmcellen op microben reageren. Sommige genen, zoals FUT2, ELMO1 en verschillende immuunregulatoren in het HLA-gebied, waren al eerder in verband gebracht met intestinale verdediging, maar andere traden naar voren als nieuwe of sterkere kandidaten zodra ziek weefsel werd meegewogen.
Nieuwe aanwijzingen van bloedgroep ABO en TNFRSF14
Twee bijzonder opvallende voorbeelden tonen aan hoe het bestuderen van IBD-weefsel verbanden onthult die in gezond weefsel onopgemerkt bleven. In een Crohn’s disease-risicoregion vlak bij het ABO-bloedgroepgen bleek een bekend variant dat het bloedtype bepaalt ook de ABO-activiteit specifiek in IBD-colon te regelen, maar niet in de datasets van gezond colon. Mensen die de versie dragen die gekoppeld is aan bloedgroep O—al verondersteld enigszins beschermend te zijn—tonen gereduceerde ABO-expressie, wat een model ondersteunt waarin bloedgroepsuikers aan de colonoppervlakte de microbiota en immuunreacties beïnvloeden. In een andere regio geassocieerd met colitis ulcerosa wees het IBD-weefsel naar TNFRSF14, een receptor die helpt immuunreacties in het darmslijmvlies in balans te houden. In gezonde colondata wezen nabije maar verschillende signalen in plaats daarvan naar andere genen met onduidelijke relevantie. In dierstudies verergert het verlies van deze receptor experimentele colitis, dus het vinden van een genetische koppeling met zijn expressie in menselijk colon versterkt het bewijs dat het een sleutelrol in de ziekte kan spelen.
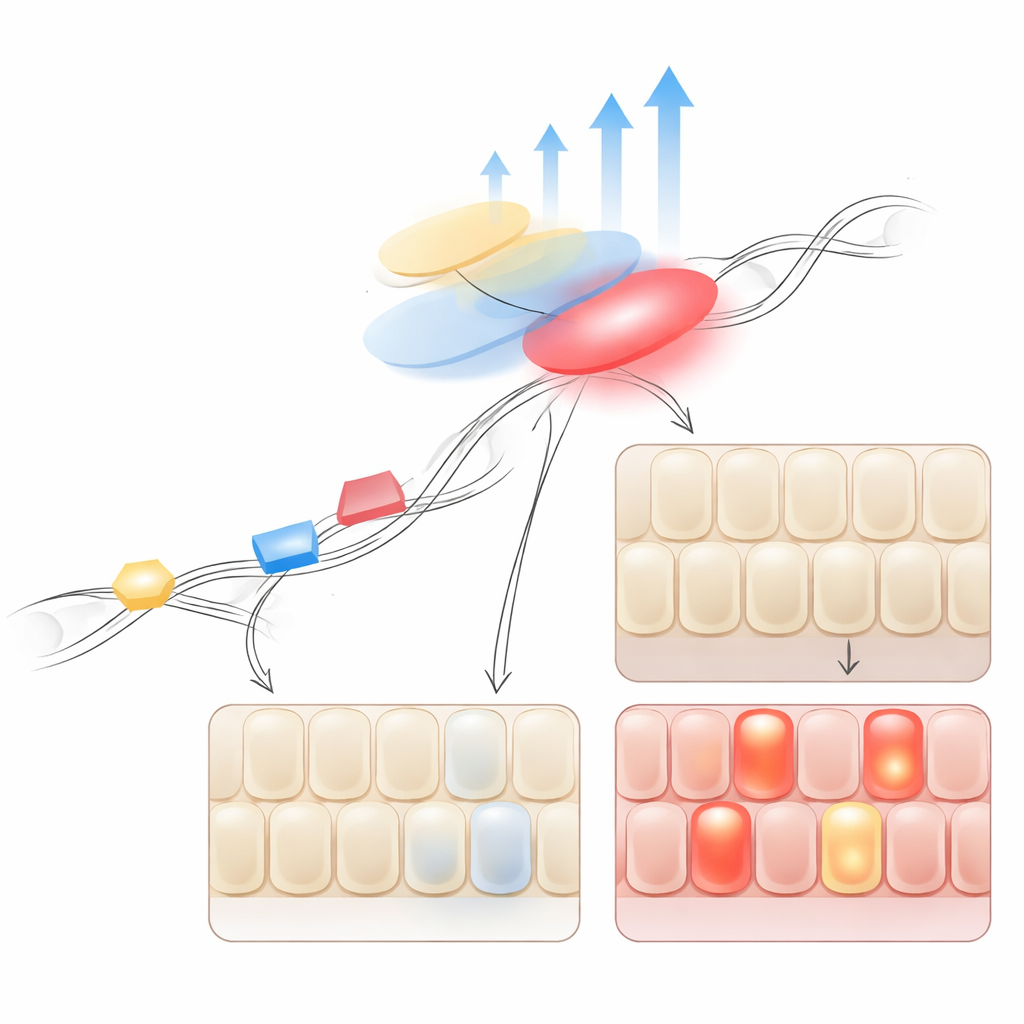
Hoe ziekte genetische effecten herschikt
Kijkend over alle regio’s waar IBD-risicovarianten en eQTL overlappen, vonden de auteurs dat de IBD-specifieke signalen niet alleen verschillend waren maar vaak ook sterker. In ziek colon lagen veel van deze varianten verder van de genen die ze controleerden, in regio’s die waarschijnlijk fungeren als langafstands-enhancers. Toen het team zorgvuldig corrigeerde voor verschillen tussen cohorten, zagen ze dat voor een subset van genen—vooral die betrokken bij immuunreacties en barrière-integriteit—dezelfde variant een groter effect op genactiviteit had in IBD-weefsel dan in gezond weefsel. Dit suggereert dat, zodra ziekte de cellulaire omgeving heeft veranderd, bepaalde regulatoire elementen actiever worden en het effect van bestaande genetische risico’s versterken.
Wat dit betekent voor patiënten en toekomstig onderzoek
Door DNA-informatie te combineren met genactiviteit rechtstreeks in de colons van IBD-patiënten levert deze studie de meest uitgebreide lijst tot nu toe van kandidaatgenen die erfelijk risico voor IBD via hun gedrag in de darm kunnen bemiddelen. Het laat zien dat veel risicovarianten hun impact pas volledig onthullen in de context van ziekte, waar regulatoire circuits verschuiven en sommige genetische effecten vergroot worden. Voor niet-specialisten is de kernboodschap dat weten “waar” in het genoom risico ligt niet genoeg is; we moeten ook weten “wanneer” en “in welke weefseltoestand” die varianten werken. Ziektegerichte kaarten zoals deze zullen onderzoekers helpen genen zoals ABO en TNFRSF14 te prioriteren voor functionele studies en geneesmiddelontwikkeling, en brengen ons dichter bij behandelingen die zijn afgestemd op de specifieke moleculaire bedrading van een ontstoken darm.
Bronvermelding: Nishiyama, N.C., Silverstein, S., Darlington, K. et al. eQTL in diseased colon tissue identifies potential target genes associated with IBD. Nat Commun 17, 2736 (2026). https://doi.org/10.1038/s41467-026-69364-6
Trefwoorden: inflammatoire darmziekte, kolon genetica, genregulatie, IBD-risicovarianten, eQTL