Clear Sky Science · nl
Seq-Scope-eXpanded: ruimtelijke omica voorbij optische resolutie
Cellen scherper zien
Ons lichaam bestaat uit talloze kleine cellen, elk bruisend van activiteit die we meestal niet kunnen zien, zelfs niet met krachtige microscopen. Dit artikel introduceert Seq-Scope-X, een technologie waarmee onderzoekers het binnenste van weefsels met ongekende helderheid kunnen bekijken en in kaart brengen welke genen en eiwitten actief zijn op precieze plekken binnen en tussen cellen. Dat detailniveau kan veranderen hoe we ontwikkeling, het immuunsysteem en ziekten zoals kanker of leverschade bestuderen.
Waarom moleculen op hun plaats in kaart brengen?
Cellen functioneren niet geïsoleerd: ze leven in buurten, vormen lagen en specialiseren zich afhankelijk van hun locatie. Traditionele gen-sequencingmethoden breken weefsels af en verliezen daarmee deze ruimtelijke context. Recente “spatiële omica”-instrumenten houden moleculen op hun plek, maar er is een compromis geweest. Imaging-gebaseerde methoden zien zeer fijne details maar volgen meestal slechts een beperkte set genen. Sequencing-gebaseerde methoden kunnen bijna elk gen tegelijk uitlezen, maar vervagen fijne structuren vaak, waarbij signalen over meerdere micrometers verspreid raken—groter dan veel subcellulaire structuren. De auteurs wilden deze kloof dichten: de rijke, onbevooroordeelde uitlezing van sequencing behouden, terwijl ze de scherpte van moderne microscopen bereiken of zelfs overtreffen.
Weefsel uitrekken om optische grenzen te verslaan
Het kernidee achter Seq-Scope-X is misleidend eenvoudig: vergroot het weefsel zelf voorzichtig zodat elke oorspronkelijke nanometer van structuur makkelijker te onderscheiden wordt. Het team verankert eerst RNA-moleculen—of speciale DNA-tags gekoppeld aan antilichamen—in een zacht hydrogel dat om het weefselplakje heen wordt opgebouwd. Vervolgens verteren ze het oorspronkelijke weefsel en zwelt de gel in een zoutoplossing, waardoor alles fysiek ongeveer drie keer wordt uitgerekt terwijl de relatieve posities nagenoeg intact blijven. Deze uitgezette gel wordt op een ultraschitsequencingchip gelegd die is gecoat met capture-probes. Door de assemblage zorgvuldig te verwarmen, worden de verankerde moleculen uit de gel vrijgegeven en opnieuw aan de chip gehecht, die vervolgens gesequenced kan worden om te onthullen welke genen of eiwitten op elk klein coördinaat aanwezig waren. 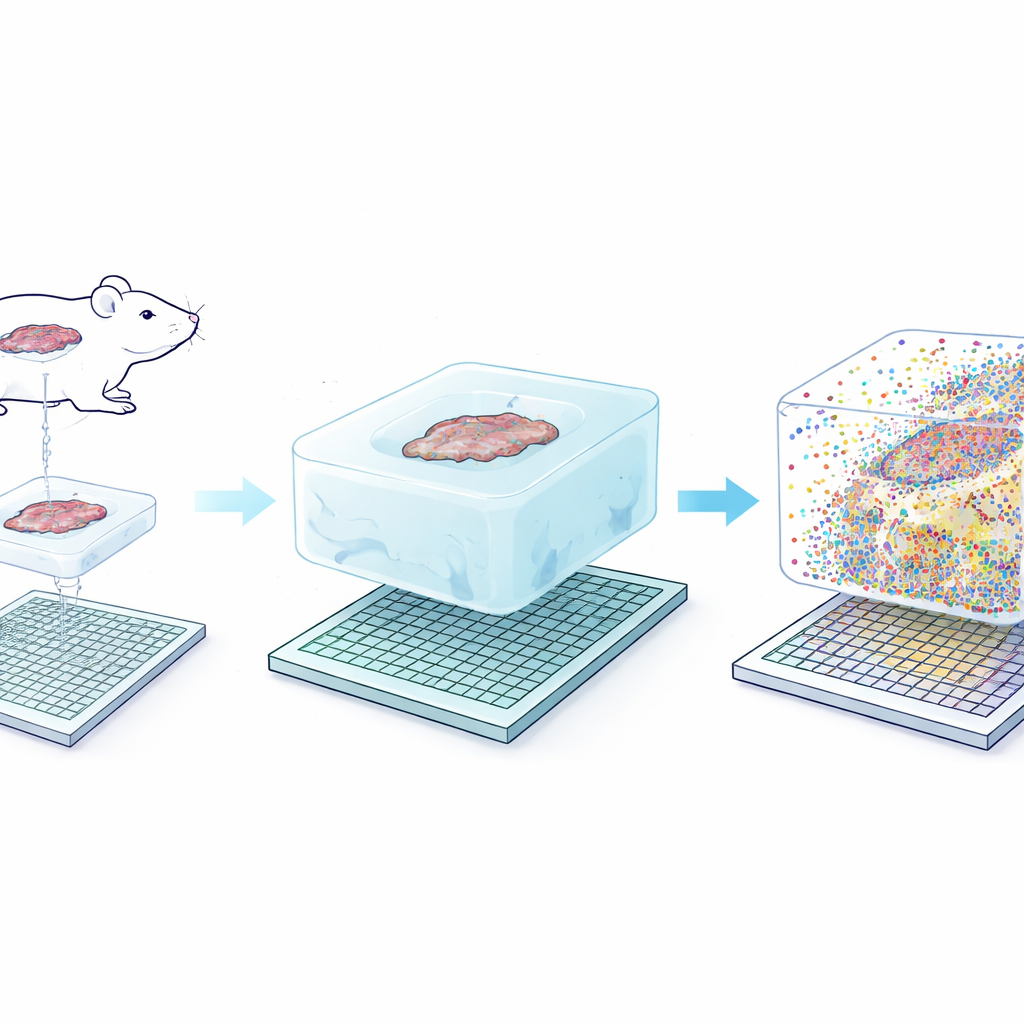
Van vage cellen naar subcellulaire kaarten
Toen de onderzoekers Seq-Scope-X op muislever toepasten, ontdekten ze dat de methode de ruimtelijke resolutie verscherpte van ongeveer 0,6 micrometer naar circa 0,2 micrometer en het aantal meetbare posities per vierkante millimeter bijna tienvoudig verhoogde. In praktische termen resulteerde wat eerder als vage signalen leek nu in heldere omtrekken van individuele cellen. Nog opvallender was dat clusters van RNA die nog niet volledig verwerkt waren (onverwerkt/unspliced) nauw samenvielen met de kernen, terwijl rijp RNA (gespliced) het omringende cytoplasma volgde. Dit stelde de auteurs in staat celgrenzen te tekenen op basis van RNA alleen en kern- en cytoplasmatische genuitkomsten te scheiden voor vrijwel elke hepatocyt in het weefsel—iets waar vorige sequencinggebaseerde methoden slechts naar wezen.
Cellen met verdeelde persoonlijkheden
Met deze nieuwe scherpte ontdekte het team een onverwachte vorm van moleculair “dubbel leven” in levercellen. Langs de bekende gradient van bloedvaten aan de portale zijde van het leverlobje naar die aan de centrale zijde, specialiseren hepatocyten zich in verschillende metabole taken. Seq-Scope-X toonde dat bij veel cellen het patroon van genexpressie in de kern niet overeenkwam met dat in het omringende cytoplasma. Ongeveer een derde van de hepatocyten leek een kernprofiel te hebben dat bij één zone paste, terwijl het cytoplasmatische profiel bij een aangrenzende zone paste. Onafhankelijke imaging-gebaseerde methoden, waaronder MERFISH en single-molecule RNA-fluorescentieassays, bevestigden dat individuele transcripties geconcentreerd kunnen zijn in ofwel de kern of het cytoplasma. Gezamenlijk suggereren deze bevindingen dat hepatocyten hun metabole rollen dynamisch in de tijd kunnen verschuiven, waarbij de kern zich voorbereidt op een toekomstige toestand terwijl het cytoplasma de huidige weerspiegelt. 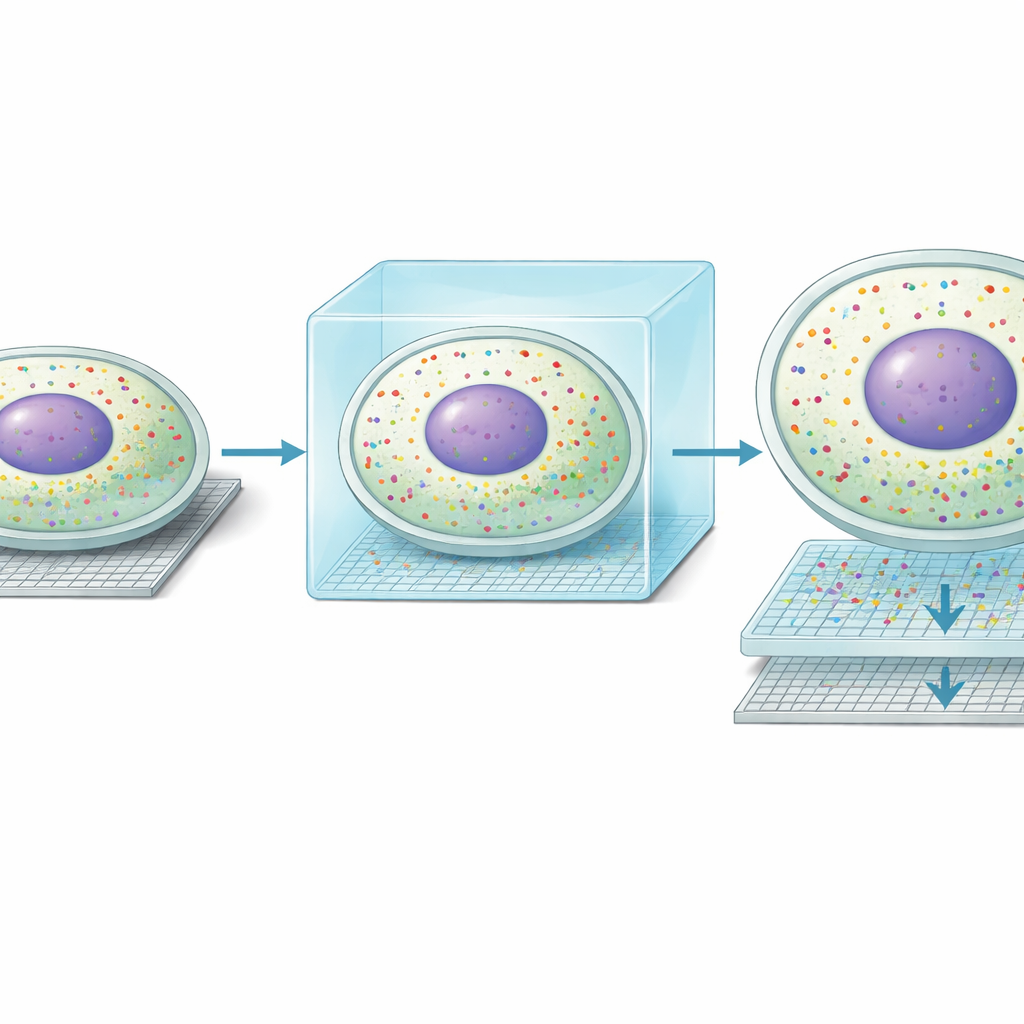
Verder dan de lever: hersen-, darm- en immuunsystemen
De auteurs testten vervolgens of Seq-Scope-X ook in andere organen werkt. In de hersenen onderscheidde het methoden verschillende neuronale typen en ondersteunende cellen en onthulde subcellulaire RNA-patronen rond kernen. In de dikke darm loste het distincte gobletcel-subtypen en lagen van colonocyten langs de crypt-naar-oppervlakte-as op, opnieuw met duidelijke kernsignaturen. Misschien het meest dramatisch paste het team de methode aan voor eiwitten door DNA-gebarcoded antilichamen te gebruiken in muizenspleen en menselijke amandel. Seq-Scope-X kon tegelijkertijd meer dan honderd verschillende celoppervlakmarkers op enkelcelresolutie in kaart brengen, waarmee nauw opeengepakte T- en B-celsubsets en myeloïde cellen te onderscheiden waren. Door over te schakelen op een meer uitbreidbare gelchemie, duwden ze de effectieve resolutie richting het ware nanoschaalbereik, terwijl de weefselarchitectuur voldoende werd behouden voor gedetailleerde kaartlegging.
Wat dit vooruit betekent
Seq-Scope-X laat zien dat het fysiek vergroten van weefsels vóór sequencing lang bestaande resolutiebeperkingen kan overwinnen, bijna microscoopniveau-detail leveren terwijl nog steeds duizenden genen of eiwitlabels tegelijk worden uitgelezen. Voor een niet-specialist betekent dit dat wetenschappers nu "moleculaire atlasen" kunnen bouwen die niet alleen aangeven welke cellen waar zitten, maar ook wat er binnen verschillende delen van elke cel gebeurt. Zulke kaarten kunnen helpen verklaren hoe weefsels op letsel reageren, hoe immuuncellen zich organiseren in lymfoïde organen en tumoren, of hoe subtiele verschuivingen binnen cellen ziekte kunnen voorspellen. Hoewel verdere verfijningen nodig zijn om de dekking op te schalen en sommige kleuringpanelen te verbeteren, opent Seq-Scope-X een krachtig nieuw venster op de microscopische landschappen die gezondheid en ziekte onderbouwen.
Bronvermelding: Anacleto, A., Cheng, W., Feng, Q. et al. Seq-Scope-eXpanded: spatial omics beyond optical resolution. Nat Commun 17, 2564 (2026). https://doi.org/10.1038/s41467-026-69346-8
Trefwoorden: spatiële transcriptomica, weefselexpansie, single-cell omica, spatiële proteomica, leverzonatie