Clear Sky Science · nl
Ontdekking van antimicrobiële peptiden die Acinetobacter baumannii richten via een vooraf getrainde en fijn-afgestelde few-shot learning-pijplijn
Waarom dit belangrijk is voor alledaagse gezondheid
Door medicijnresistente infecties stijgt het aantal gevallen zo snel dat ze halverwege deze eeuw mogelijk meer mensen per jaar kunnen doden dan kanker. Een van de meest zorgwekkende veroorzakers is Acinetobacter baumannii, een taaie ziekenhuisbacterie die veel antibiotica negeert en vaak patiënten op beademing infecteert. Deze studie laat zien hoe onderzoekers kunstmatige intelligentie combineerden met laboratoriumexperimenten om snel nieuwe, kleine kandidaat-geneesmiddelen te vinden die deze bacterie kunnen doden en daarbij veel minder schade aan het lichaam veroorzaken dan onze huidige laatste redmiddelmedicatie.
Een ziekenhuis-superbug die moeilijk te doden is
Acinetobacter baumannii is een Gram-negatieve bacterie die floreert op intensive care-afdelingen, vooral bij patiënten die van beademing afhankelijk zijn. Zijn robuuste buitenlaag en snel evoluerend genoom maken hem resistent tegen veel standaardantibiotica. Tegenwoordig is een van de weinige overgebleven opties een middel genaamd polymyxine B, maar dat kan de nieren ernstig schaden en de bacterie kan toch weerstand ontwikkelen. Tegelijkertijd is een veelbelovende klasse van kleine eiwitfragmenten, antimicrobiële peptiden, onderzocht tegen andere microben, maar er zijn zeer weinig peptiden gevonden die specifiek goed werken tegen A. baumannii. Traditionele trial-and-error screening is simpelweg te traag en te kostbaar om door het astronomisch grote aantal mogelijke korte peptidevolgorden te zoeken.
Gebruik van slimme algoritmen om een enorme ruimte te doorzoeken
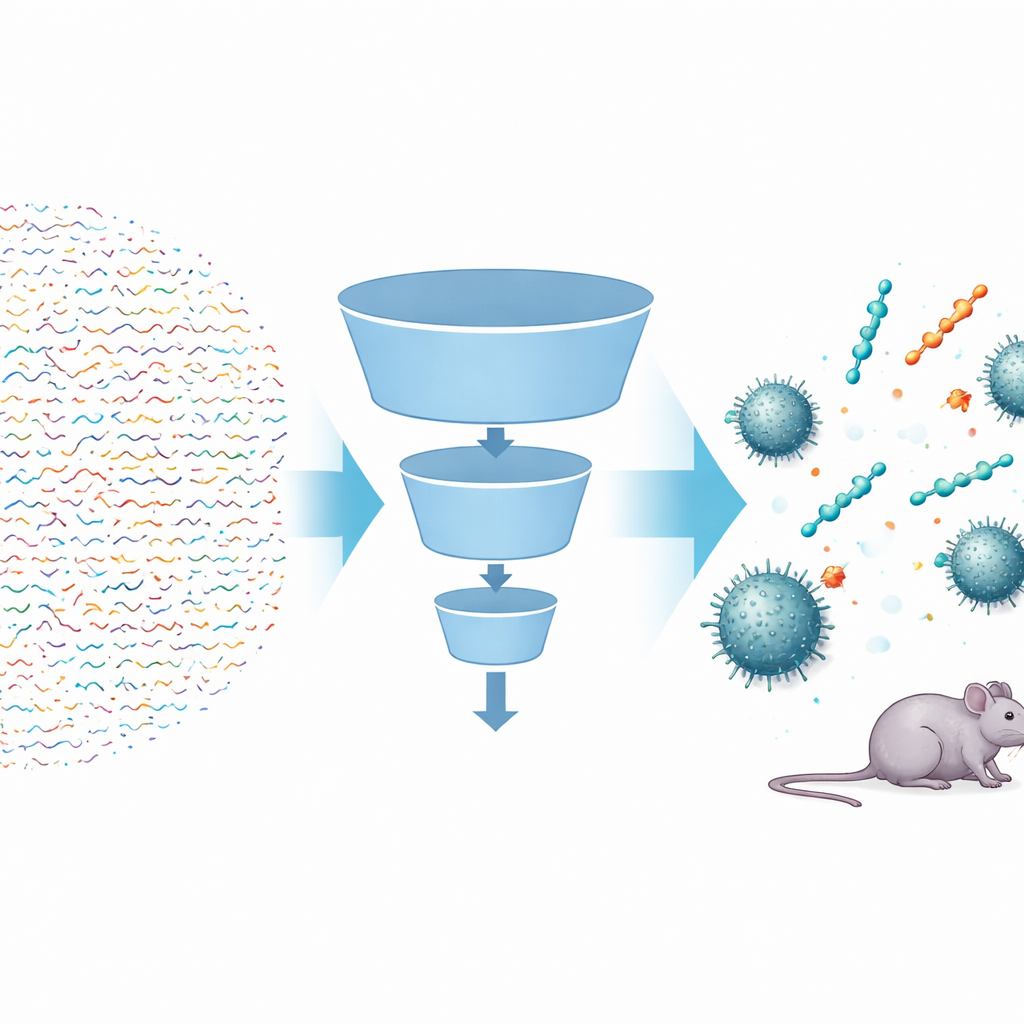
De onderzoekers bouwden een meerstappen kunstmatige-intelligentiepijplijn, genaamd FSLSMEP, om complete bibliotheken van korte peptiden te scannen—peptiden van zes, zeven of acht bouwstenen—wat neerkomt op tientallen miljarden kandidaten. De uitdaging was dat ze slechts 148 bekende peptiden hadden die werken tegen A. baumannii, veel te weinig voor standaard machine-learningmethoden. Om dit te omzeilen begonnen ze met een krachtig voorgetraind model dat al honderden miljoenen natuurlijke eiwitsequenties had “gelezen” en algemene regels had geleerd over hoe dergelijke moleculen zich gedragen. Dit model werd vervolgens in twee stappen fijn-afgesteld: eerst op een grotere set peptiden die actief zijn tegen een verwante bacterie, Pseudomonas aeruginosa, en uiteindelijk op de schaarse A. baumannii-gegevens. Onderweg werkten drie gekoppelde modules—één om waarschijnlijke van onwaarschijnlijke peptiden te scheiden, één om ze te rangschikken, en één om te schatten hoe sterk elk peptide mogelijk is—als opeenvolgende filters in een trechter.
Van computervoorspellingen naar succes in reageerbuizen
Nadat ze eerst de minst veelbelovende peptiden hadden verwijderd met eenvoudige chemische regels, voerde het team bijna vier miljoen kandidaten in hun pijplijn. De classifier sorteerde de meeste sequenties eruit die niet antimicrobieel leken; het rangschikkingsmodel gaf de voorkeur aan die waarvan de eigenschappen sterke activiteit suggereerden; en het regressiemodel voorspelde de minimale concentratie van het middel die nodig is om bacteriegroei te stoppen. Van vierenzestig miljoen zes-eenheidspeptiden stelde het systeem slechts tien topkandidaten voor. Toen die werden gesynthetiseerd en in het lab getest, toonden negen hiervan echte antibacteriële activiteit, een indrukwekkende trefferpercentage in geneesmiddelenontdekking. Dezelfde getrainde modellen werden daarna, zonder opnieuw te trainen, toegepast op veel grotere zeven- en acht-eenheids peptide-ruimtes, waaruit de onderzoekers aanvullende hooggeplaatste sequenties kozen voor testen. Ook nu bleken de meesten actief, inclusief heptapeptiden die tegen sommige stammen net zo krachtig waren als polymyxine B.
Krachtige doodbrengers met een zachtere aanpak
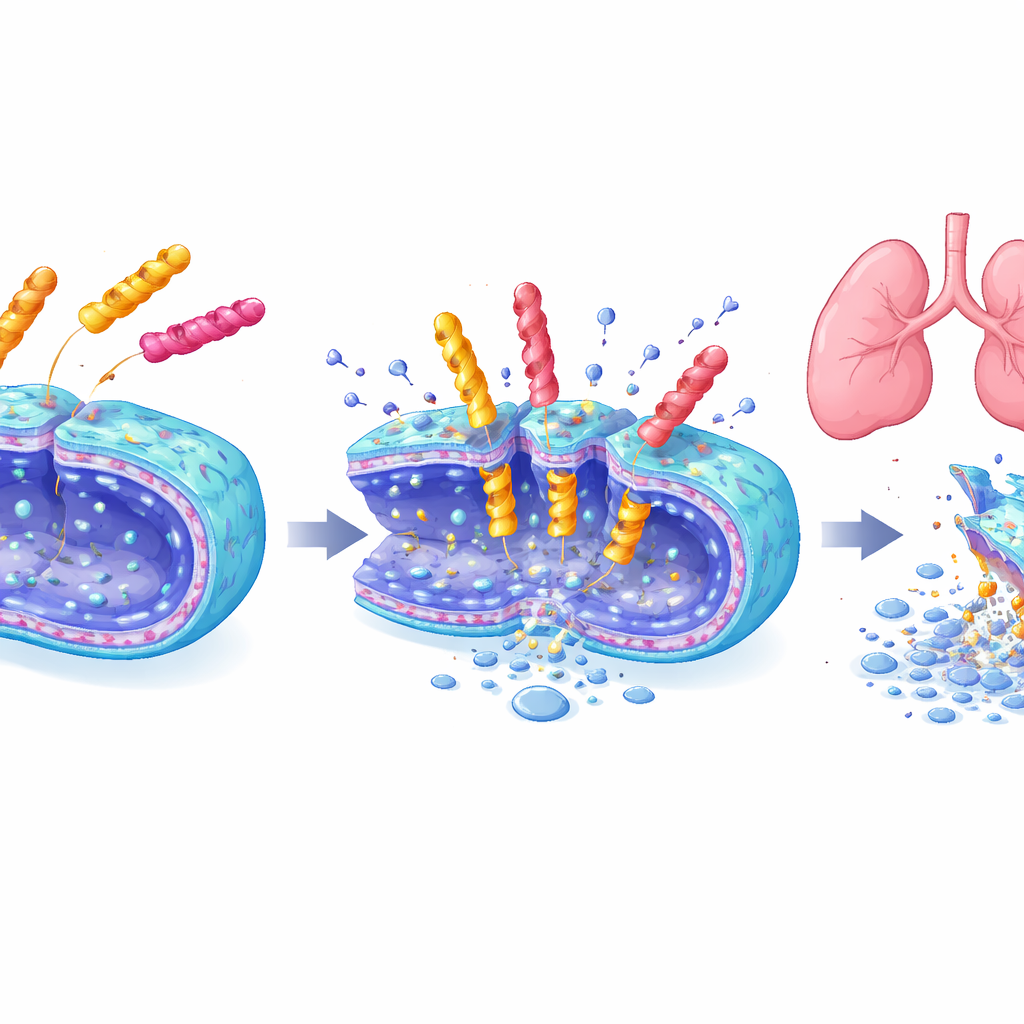
Drie leidende peptiden—één uit elk van de zes-, zeven- en acht-eenheidsbibliotheken—werden in detail onderzocht. Ze maakten populaties van A. baumannii in enkele minuten tot uren snel onschadelijk, beschadigden bacteriële membranen zoals zichtbaar was onder elektronenmicroscopie, en werkten ook tegen verschillende andere gevaarlijke microben. Tegelijk veroorzaakten ze weinig schade aan gekweekte zoogdiercellen of aan rode bloedcellen, in tegenstelling tot sommige bestaande antimicrobiële peptiden. In langetermijnblootstellingstests ontwikkelden bacteriën niet snel weerstand tegen deze nieuwe moleculen, terwijl weerstand tegen polymyxine B snel toenam. Het meest opvallend was dat in een muismodel van longontsteking een geïnhaleerde dosis van het heptapeptide EME7(7) longinfecties even effectief uitroeide als polymyxine B maar de nieren niet beschadigde, terwijl polymyxine B duidelijke nierschade en verhogingen in bloedmarkers van nierstress veroorzaakte.
Wat dit betekent voor toekomstige medicijnen
Dit werk toont aan dat een zorgvuldig ontworpen AI-pijplijn een kleine, onvolledige dataset kan omzetten in een krachtig instrument voor het ontdekken van nieuwe antimicrobiële peptiden. Door brede voortraining, stapsgewijze fijn-afstelling en meerdere lagen filtering te combineren, verkenden de onderzoekers efficiënt complete bibliotheken van korte peptiden en vonden kandidaten die zowel een gevaarlijke ziekenhuis-superbug bestrijden als veiliger lijken voor vitale organen. Dezelfde strategie slaagde er ook in het vinden van peptiden die actief zijn tegen de schimmelpathogeen Candida albicans, wat erop wijst dat het hergebruikt kan worden om naar vele andere typen therapeutische peptiden te zoeken. Voor patiënten zou deze benadering uiteindelijk kunnen leiden tot nieuwe medicijnen die hardnekkige infecties behandelen zonder de zware bijwerkingen en snelle resistentie die de huidige laatste-lijn antibiotica teisteren.
Bronvermelding: Huang, J., Zhang, W., Wang, A. et al. Discovery of antimicrobial peptides targeting Acinetobacter baumannii via a pre-trained and fine-tuned few-shot learning-based pipeline. Nat Commun 17, 2475 (2026). https://doi.org/10.1038/s41467-026-69306-2
Trefwoorden: antimicrobiële peptiden, antibioticaresistentie, Acinetobacter baumannii, machine learning geneesmiddelenontdekking, few-shot learning