Clear Sky Science · nl
TANGO: Analyse en curatie van deeltjes in cryo-elektronentomografie
Cellen in 3D zien en vervolgens de menigte begrijpen
Cryo-elektronentomografie stelt wetenschappers in staat levende cellen in actie te bevriezen en ze in drie dimensies vast te leggen, bijna alsof je een film pauzeert met atomaire detaillering. Maar zodra duizenden kleine moleculaire "stipjes" in een cel zijn gedetecteerd, doet zich een nieuw probleem voor: hoe begrijpen we wie naast wie zit, wie samen teams vormt en waar de belangrijke patronen zich verbergen in deze drukke moleculaire stad? Deze studie introduceert TANGO, een softwarekader dat ruwe 3D-deeltjeskaarten omzet in begrijpelijke verhalen over hoe moleculen gerangschikt zijn en samenwerken.
Van stippen in ijs naar een kaart van moleculaire buren
Cryo-elektronentomografie begint met het kantelen van een bevroren monster in de microscoop om vele 2D-beelden vast te leggen. Deze worden gecombineerd tot een 3D-volume, een tomogram genoemd, waarin individuele moleculaire complexen als wazige vlekken verschijnen. Bestaande methoden gebruiken deze gegevens al om de vormen van moleculen te verscherpen door veel kopieën te middelen, maar ze negeren grotendeels een even rijke bron: de exacte posities en oriëntaties van elk deeltje. TANGO is gebouwd om deze over het hoofd geziene informatie te benutten. Het behandelt al deze deeltjes als punten in de ruimte, elk met een richting, en analyseert hoe ze ten opzichte van elkaar zijn gepositioneerd en georiënteerd. Daarmee gaat het verder dan alleen de vraag "hoe ziet dit molecuul eruit?" naar "hoe zijn deze moleculen samen georganiseerd in de cel?" 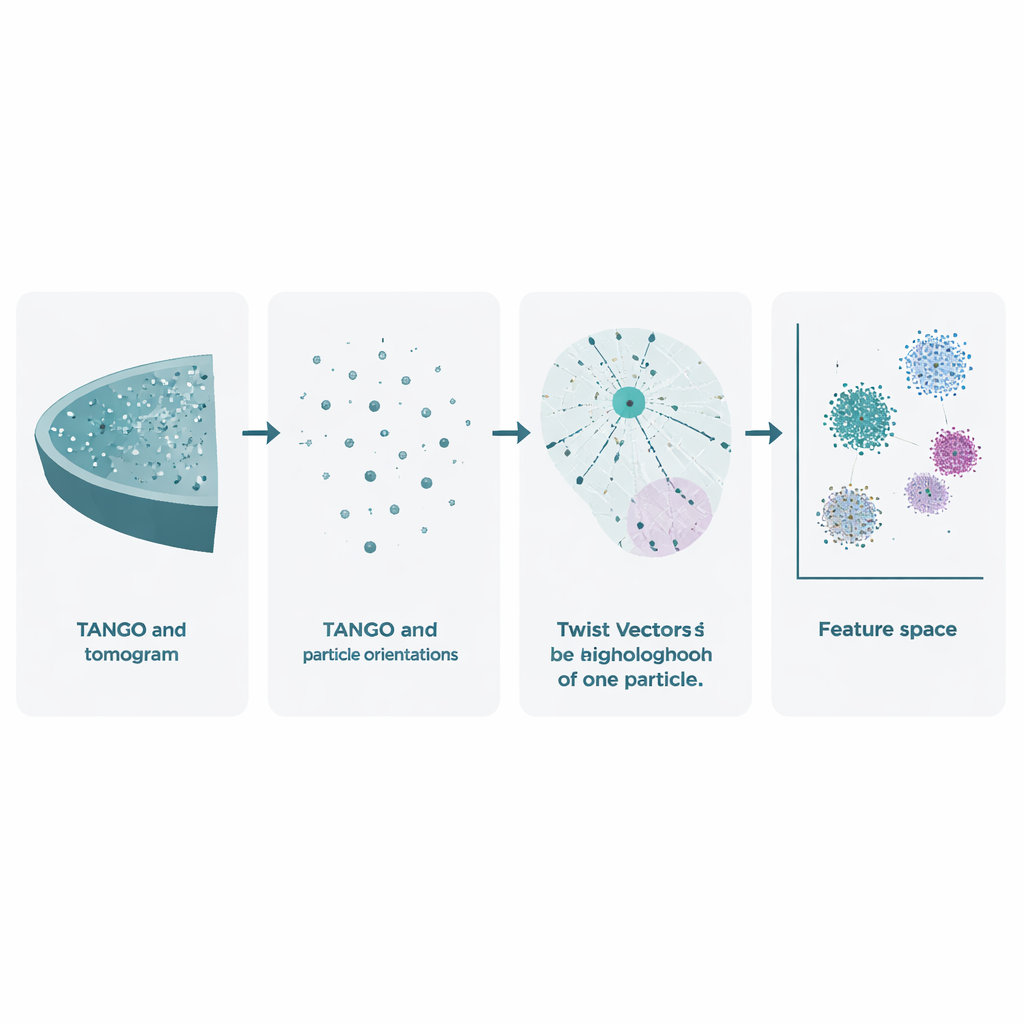
Wendingen en knikken vastleggen met een nieuwe descriptor
Centraal in TANGO staat het idee van "twistvectoren". Voor een gegeven deeltje bekijkt de software alle buren binnen een gekozen straal en registreert twee zaken: waar elke buur in de 3D-ruimte ligt en hoe deze ten opzichte van het centrale deeltje is gedraaid. Deze gecombineerde positie-en-hoekrelaties worden gecodeerd als beknopte numerieke beschrijvingen, bekend als twist-descriptors. Omdat TANGO buurten altijd opnieuw oriënteert naar een gemeenschappelijk referentiekader, zijn deze descriptors ongevoelig voor hoe het hele monster in de microscoop is gedraaid. Dit maakt het mogelijk lokale buurten consistent met elkaar te vergelijken over verschillende tomogrammen en experimenten heen.
Ruis in de data opruimen en moleculaire assemblages herbouwen
Reële experimentele data zijn rommelig: automatische pick-methoden kunnen veel foutieve deeltjes opnemen en uit het oog verliezen welke kleine stukken bij welke grote structuur horen. TANGO pakt dit aan door het netwerk van twist-relaties om te zetten in een graaf, waarbij deeltjes knooppunten zijn en buurverbindingen randen. Door te analyseren hoe knooppunten verbonden zijn, kan TANGO deeltjes weer groeperen tot hun juiste ouderassemblages en uitschieters weggooien die niet in de verwachte geometrie passen. De auteurs tonen aan dat deze aanpak nauwkeurig de ringvormige architectuur van kernporiën in het kernmembraan van de cel terugvindt, de buisvormige ordening van microtubuli en de min of meer bolvormige schillen van onrijpe HIV-achtige deeltjes. In elk geval ruimt TANGO zowel de deeltjeslijsten op als herstelt het welke stukjes bij elkaar horen, vaak overeenkomend met of beter dan zorgvuldige handmatige curatie.
Subtiele defecten en patronen in roosters opsporen
Veel virussen en cellulaire structuren vormen herhalende roosters, zoals moleculair tegelwerk op gebogen oppervlakken. TANGO gebruikt zijn twist-descriptors om te meten hoe regelmatig deze patronen zijn en om plekken te detecteren waar ze buigen of breken. Een cruciale component is een "hoekscore" die oriëntaties vergelijkt terwijl ingebouwde symmetrieën gerespecteerd worden, zoals de zesvoudige symmetrie van hexameren. Toegepast op rijpe HIV-capsids detecteert TANGO pentameren — vijfdelige eenheden die nodig zijn om de kegelvormige schaal te sluiten — verborgen tussen grote velden van hexameren. In onrijpe HIV-roosters scheidt het goed geordende gebieden van vervormde regio's en koppelt lage hoekscores aan onregelmatige, gebroken delen van de schaal. Vergelijkbare analyses op synthetische chromatine- en ribosoomgegevens onthullen gestapelde nucleosomen, spiraalvormige DNA–eiwitordening en terugkerende paren van ribosomen die lijken op eerder beschreven translatiestaten. 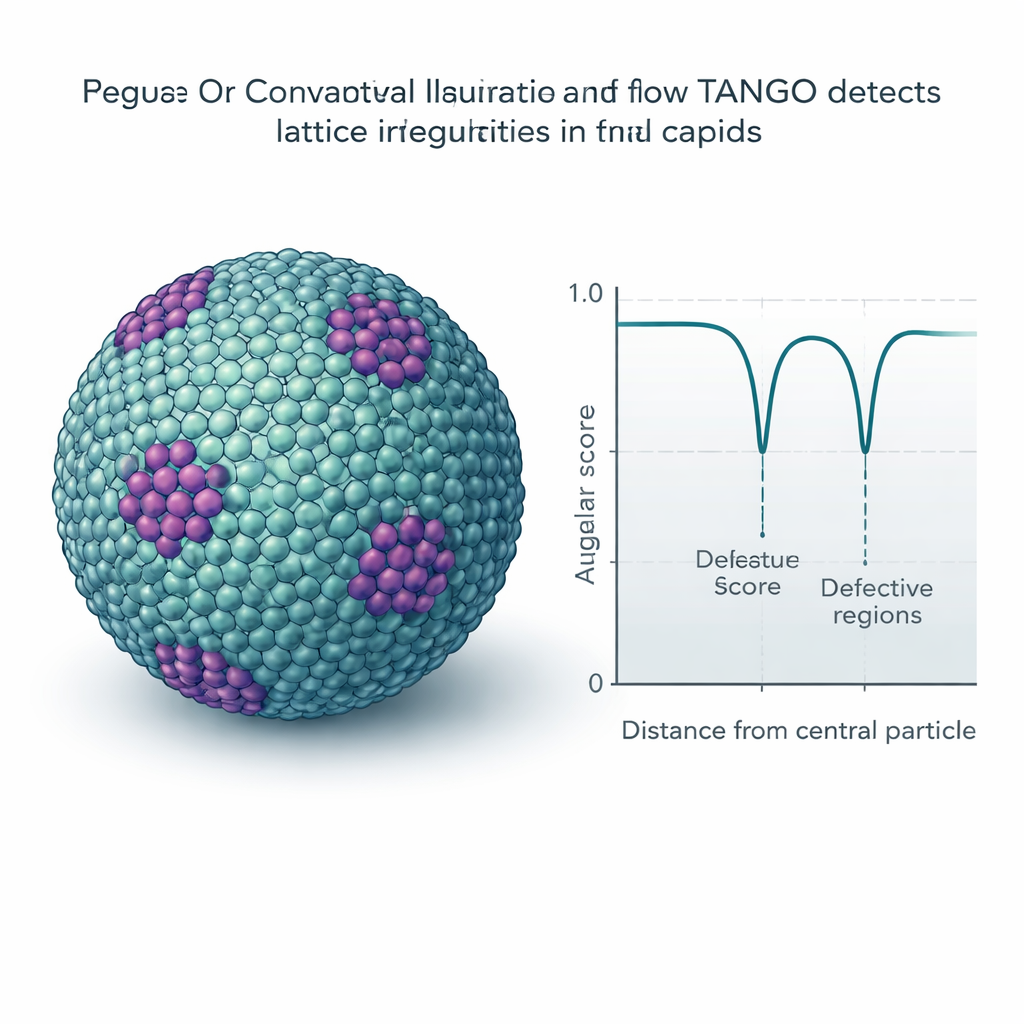
Een flexibele gereedschapskist voor het verkennen van cellulaire architectuur
TANGO is geïmplementeerd als open-source Python-software en wordt geleverd met een grafische interface zodat gebruikers verschillende buurtvormen, filters en features kunnen uitproberen zonder veel te programmeren. Omdat het modulair is, kunnen onderzoekers hun eigen geometrische maten of patroondescriptors invoegen en die direct binnen dezelfde workflow gebruiken. Voor nieuwkomers verlaagt dit de drempel om ruimtelijke organisatie te verkennen; voor experts biedt het een kader dat met nieuwe ideeën en datasets kan meegroeien.
Waarom dit belangrijk is voor het begrijpen van levende cellen
In eenvoudige bewoordingen geeft dit werk biologen een manier om van statische beelden van individuele moleculen te verschuiven naar dynamische kaarten van hoe die moleculen gerangschikt zijn en samenwerken binnen cellen. Door de relaties "wie is dichtbij wie" en "hoe zijn ze georiënteerd" te coderen in robuuste numerieke kenmerken, verandert TANGO ruisrijke 3D-microscopiegegevens in patronen die geclusterd, vergeleken en statistisch getest kunnen worden. Dit kan verborgen assemblages onthullen, defecten in virusomhulsels precies lokaliseren en zeldzame moleculaire ordeningen blootleggen die verband houden met ziekte of medicijnwerking. Naarmate cryo-elektronentomografie vaker gebruikt wordt, zullen tools als TANGO helpen om dichte wolken van deeltjes om te zetten in heldere inzichten over de innerlijke choreografie van het leven.
Bronvermelding: Schreiber, M., Turoňová, B. TANGO: Analysis and curation of particles in cryo-electron tomography. Nat Commun 17, 1557 (2026). https://doi.org/10.1038/s41467-026-69195-5
Trefwoorden: cryo-elektronentomografie, ruimtelijke organisatie, moleculaire roosters, virale capsids, ribosomen