Clear Sky Science · nl
Eiwit-eiwitinteracties zijn een belangrijke bron van epistasie in genetische interactienetwerken
Waarom dit belangrijk is voor het begrijpen van genen
Wanneer artsen of genetische tests zeggen dat een bepaald gen een ziekte "veroorzaakt", klinkt dat eenvoudig. In werkelijkheid hangt het effect van een enkel gen vaak sterk af van wat andere genen tegelijkertijd doen. Dit artikel onderzoekt waarom combinaties van genveranderingen onvoorspelbaar kunnen zijn, en laat zien dat veel van deze verrassingen terug te voeren zijn op hoe de door die genen gecodeerde eiwitten daadwerkelijk in de cel aan elkaar hechten. Het begrijpen van deze link kan onze mogelijkheid verbeteren om ziekerisico te voorspellen en om medicijndoelen te vinden die kwetsbaarheden in kanker en andere ziekten benutten.
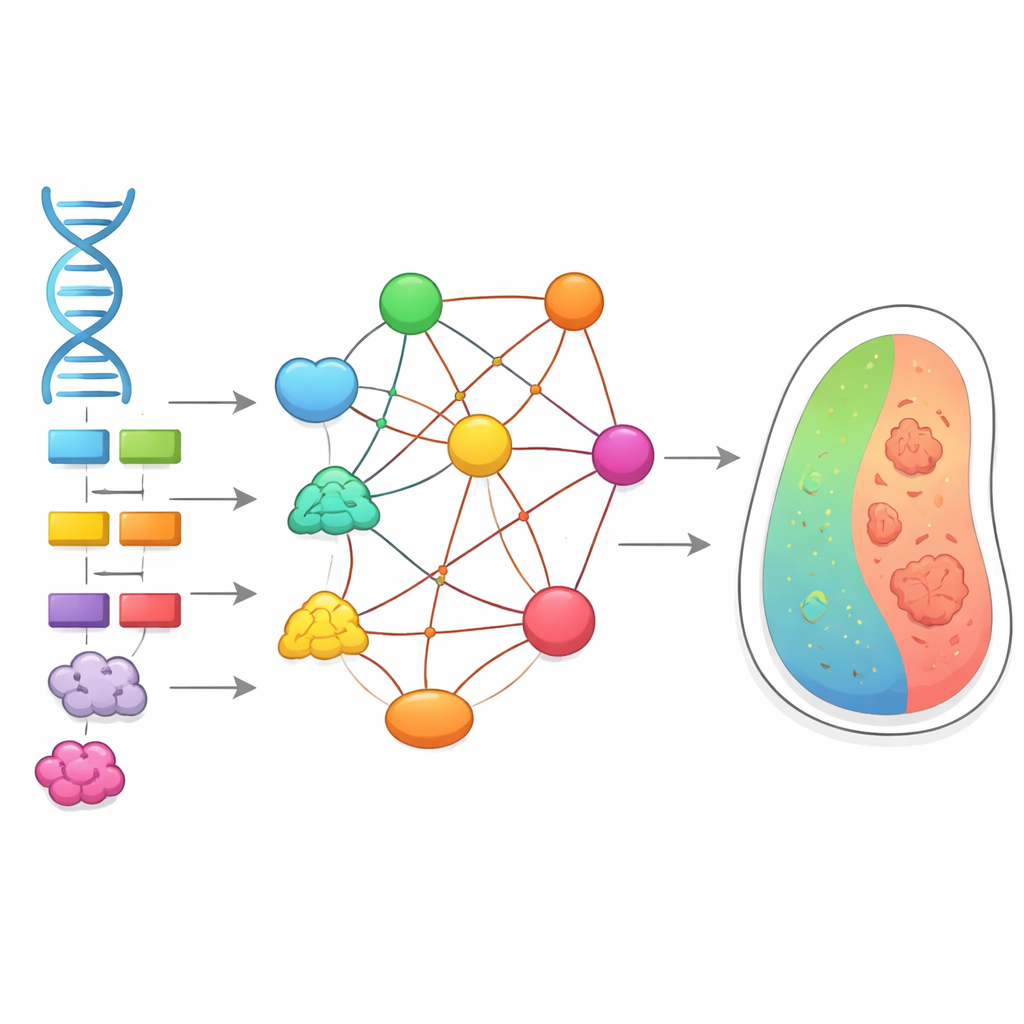
Twee verborgen kaarten in elke cel
Biologen gebruiken twee krachtige soorten kaarten om te begrijpen hoe cellen werken. De ene is de kaart van genetische interacties, die laat zien wat er met een cel gebeurt wanneer twee genen samen worden verstoord: soms is de dubbele verandering veel ernstiger dan verwacht, soms milder. Deze niet-additieve effecten noemen we epistasie en ze maken het moeilijk om eigenschappen alleen uit DNA te voorspellen. De tweede kaart is die van eiwit-eiwitinteracties, die in kaart brengt welke eiwitten fysiek contact maken om complexen en paden te vormen. Tot nu toe werden deze twee kaarten meestal apart bestudeerd, en het was onduidelijk hoe nauw ze met elkaar verbonden zijn.
Hoe sterk eiwitten binden bepaalt gen-gen effecten
De auteurs combineerden grote datasets uit gist en humane cellen die zowel meten hoe vaak eiwitten elkaar tegenkomen als hoe sterk ze binden. Ze legden vervolgens genetische interactiegegevens over dit fysieke landschap heen. Een duidelijk patroon kwam naar voren: genparen waarvan de eiwitten sterke, evenwichtige complexen vormen—waar beide partners in vergelijkbare hoeveelheden aanwezig zijn en ongeveer in 1-op-1-verhoudingen binden—tonen vaak sterke negatieve interacties wanneer beide genen verloren gaan. In praktische termen schaadt het uitschakelen van elk gen afzonderlijk de cel enigszins, maar het verliezen van beide tegelijk is bijzonder schadelijk, wat de centrale rol van het gedeelde eiwitcomplex weerspiegelt. Ter vergelijking: zwakkere of meer onevenwichtige eiwitpartnerschappen gaven mildere en meer gevarieerde genetische effecten.
Bindingsterktes omzetten in netwerkvoorspellingen
Alleen weten welke eiwitten elkaar aanraken is niet genoeg; de sleutel is hoe sterk die contacten zijn. Om dit vast te leggen gebruikten de onderzoekers kwantitatieve massaspectrometrie om bindingsaffiniteiten te schatten—hoe gemakkelijk eiwitparen uit elkaar vallen—voor duizenden interacties. Ze vonden dat, naarmate de binding sterker wordt, de gemiddelde negatieve genetische interactie tussen de overeenkomstige genen een vloeiende, sigmoïde curve volgt, zeer vergelijkbaar met hoe een bindingsplaats zich vult naarmate de concentratie toeneemt. Dit gold voor zowel gist- als menselijke cellen. Met deze kwantitatieve relatie lieten ze zien dat de structuur van een genetisch interactienetwerk gedeeltelijk reconstructeerbaar is uit alleen eiwitbindingsgegevens, waarbij clusters van gerelateerde genen opnieuw tevoorschijn kwamen uit de eiwitmetingen.
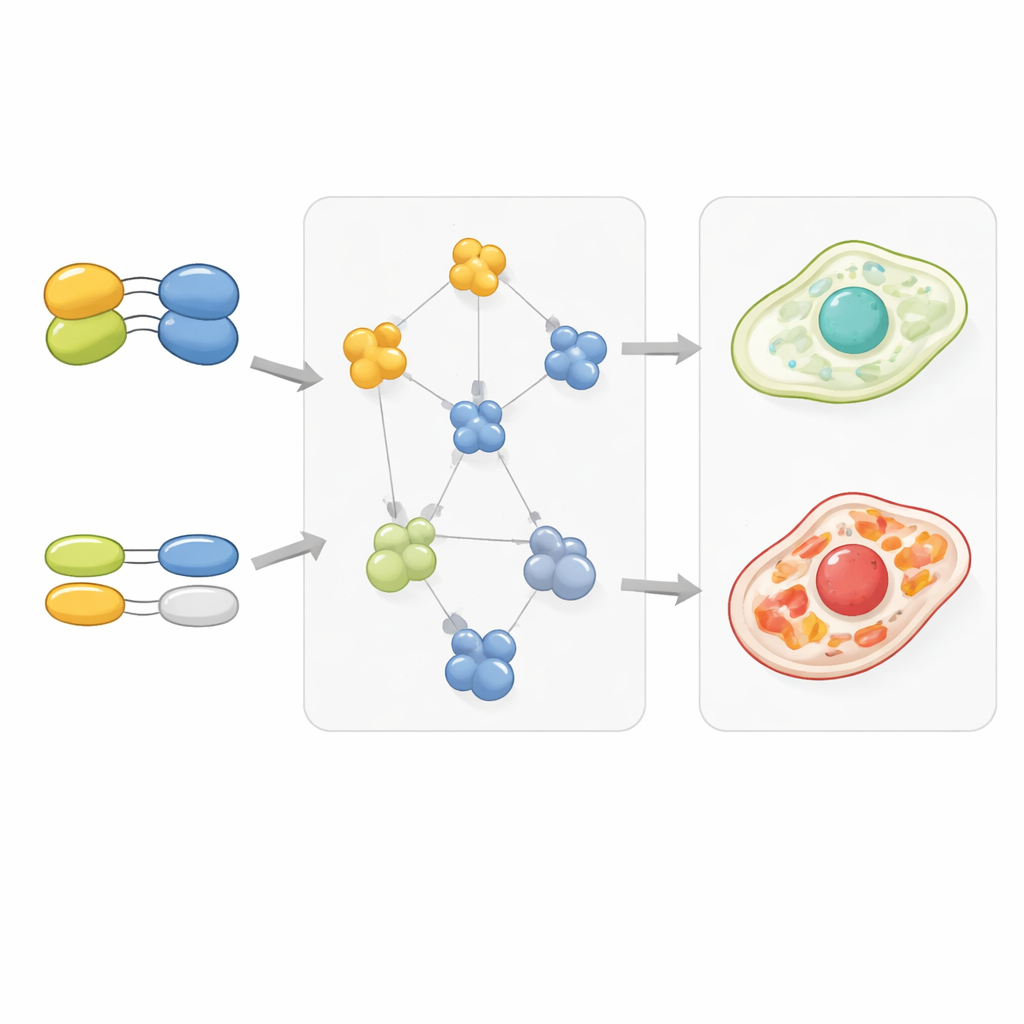
Genduplicaten en patronen in de cellulaire bedrading
De studie keek ook naar genen die duplicaten hebben, bekend als paralogen, die vaak als reserve voor elkaar dienen. Genparen waarbij een of beide partners duplicaten hadden, toonden doorgaans zwakkere genetische interacties met andere genen, wat suggereert dat redundantie de impact van het verliezen van één exemplaar verzacht. Opmerkelijk genoeg hadden eiwitten die door gedupliceerde genen werden gecodeerd ook vaak zwakkere bindingsinteracties met hun partners, alsof evolutie de kleverigheid had teruggeschroefd om het aantal complexen in balans te houden ondanks extra kopieën. Wanneer duplicaten meer uit elkaar gingen in sequentie en functie, behield het ene exemplaar vaak sterke, gerichte interacties terwijl de andere veel van zijn contacten verloor of verzwakte, een patroon dat overeenkomt met veranderingen in hoe die genen genetisch met de rest van de cel interacteerden.
Gedeelde hubs die cellulaire systemen verbinden
Verder dan individuele paren vroegen de auteurs zich af of de grootschalige vormen van de genetische en eiwitkaarten overeenkomen. Ze vonden dat groepen genen die in genetische interactiegegevens samenklonteren vaak nauw overeenkomen met bekende eiwitcomplexen. Even belangrijk is dat dezelfde soorten "connector"-eiwitten vaak deze complexen in beide kaarten met elkaar verbinden, en zo terugkerende module-connector-module-patronen vormen. Bijvoorbeeld transportfactoren die lading door de kernporie verplaatsen en signaaleiwitten zoals Ras treden op als gedeelde connectoren, die verre cellulaire processen verbinden in zowel het fysieke als het genetische netwerk.
Wat dit betekent voor genen, ziekte en therapie
De centrale boodschap voor niet-specialisten is dat veel verwarrende gen-gen effecten helemaal niet zo mysterieus zijn: ze ontstaan omdat de eiwitten die door die genen worden gecodeerd fysiek van elkaar afhankelijk zijn, en de sterkte van die afhankelijkheid kan worden gemeten. Door genetische epistasie te koppelen aan de chemie van eiwitbinding, brengt dit werk ons dichter bij het voorspellen van hoe combinaties van mutaties cellen zullen beïnvloeden, ook bij menselijke ziekten. Op de lange termijn kunnen zulke geïntegreerde kaarten helpen combinaties van genen te identificeren die, wanneer ze samen worden gericht, kankercellen selectief verzwakken of nieuwe manieren onthullen om het evenwicht te herstellen in verstoorde eiwitnetwerken.
Bronvermelding: Castellanos-Girouard, X., Serohijos, A.W.R. & Michnick, S.W. Protein-protein interactions are a major source of epistasis in genetic interaction networks. Nat Commun 17, 2398 (2026). https://doi.org/10.1038/s41467-026-69152-2
Trefwoorden: genetische interacties, proteïnenetwerken, epistasie, eiwitcomplexen, systemenbiologie