Clear Sky Science · nl
Voorspelling van chemische gelijkenis tussen tandem-massaspectra over ionisatiemodi heen in metabolomics
Waarom het verbinden van chemische punten ertoe doet
Elke slok koffie, hap lucht of kuur medicatie laat kleine chemische sporen in ons lichaam achter. Moderne instrumenten kunnen duizenden van deze moleculen tegelijk detecteren, maar die signalen omzetten in biologische inzichten blijft verrassend moeilijk. Deze studie introduceert MS2DeepScore 2.0, een machine-learningtool die onderzoekers helpt te zien hoe die moleculen verwant zijn, zelfs wanneer de signalen op heel verschillende manieren zijn vastgelegd. Daardoor belooft het snellere en vollediger interpretaties van complexe chemische mengsels in geneeskunde, voeding en milieuonderzoek.
Twee manieren om naar hetzelfde molecuul te kijken
Massaspectrometrie is een sleuteltechniek die moleculen weegt en uiteenbreekt om hun identiteit te onthullen. In routinematige experimenten meten onderzoekers een monster vaak in twee modi: één die positieve ionen bevoordeelt en één die negatieve ionen bevoordeelt. Elke modus levert een karakteristieke “streepjescode” van fragmenten op. Zelfs wanneer beide metingen van hetzelfde molecuul komen, kunnen de resulterende patronen zo verschillend zijn dat traditionele vergelijkingsmethoden falen. Daardoor analyseren onderzoekers meestal de twee modi apart, bouwen twee losgekoppelde kaarten van het monster en lopen ze het risico belangrijke relaties tussen stoffen te missen.
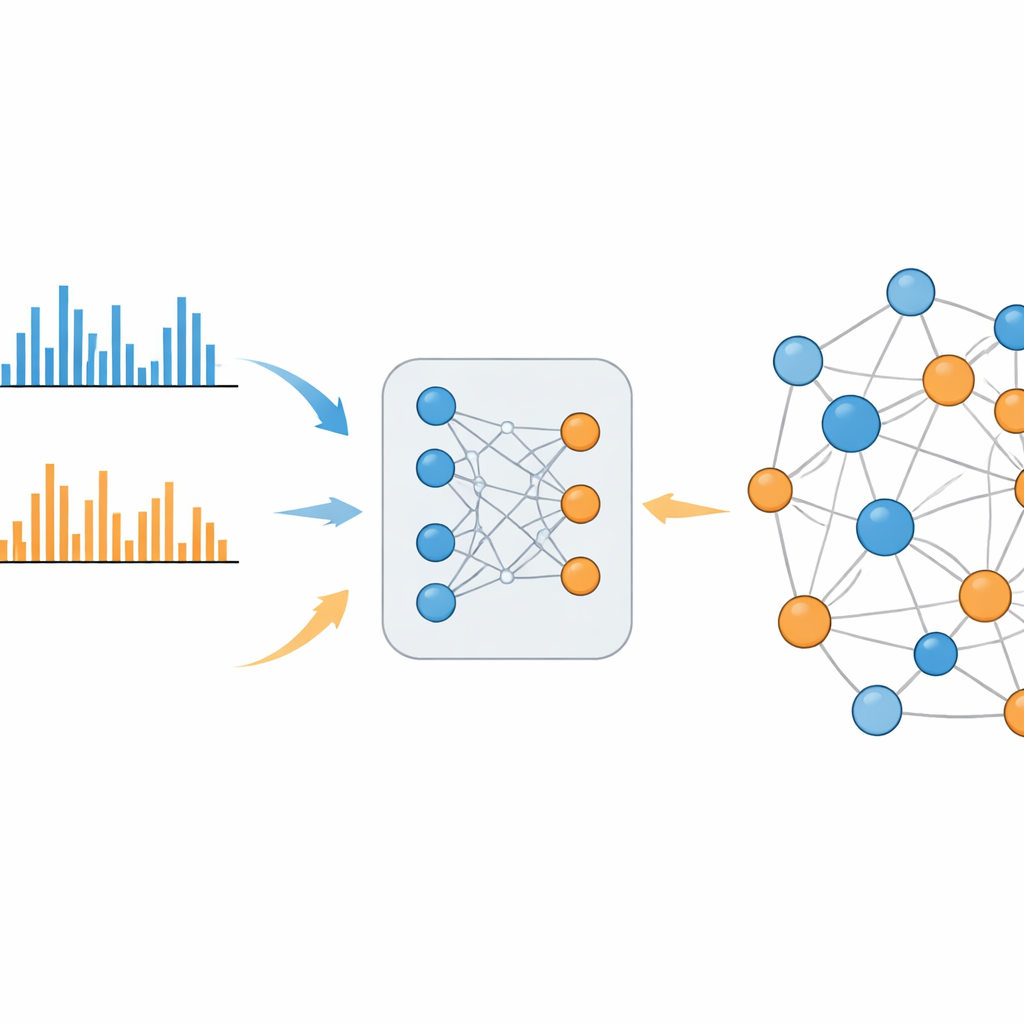
Een lerend systeem dat de kloof overbrugt
MS2DeepScore 2.0 pakt deze kloof aan door chemische gelijkenis direct te leren uit grote bibliotheken met bekende spectra. Het model is gebouwd op een twin-neuraalnetwerkontwerp dat elk fragmentatiepatroon omzet in een 500‑cijferig vingerafdruk, een zogenaamde embedding. Tijdens het trainen ziet het systeem honderden duizenden voorbeelden uit zowel positieve als negatieve modi, samen met hoe vergelijkbaar de onderliggende moleculen daadwerkelijk zijn. Het past zichzelf zo aan dat spectra van verwante moleculen vergelijkbare embeddings krijgen, ongeacht of ze in dezelfde modus of in tegengestelde modi zijn gemeten. De nieuwe versie gaat verder dan zijn voorganger door extra informatie toe te voeren, zoals de massa van het oorspronkelijke molecuul en welke ionisatiemodus werd gebruikt, en door een zorgvuldig gebalanceerd sampelingsschema te gebruiken zodat zeldzame maar informatieve chemische relaties niet worden overstemd door veelvoorkomende, niet-informatieve relaties.
Van verspreide signalen naar eendrachtige kaarten
Eens getraind kan MS2DeepScore 2.0 inschatten hoe chemisch vergelijkbaar twee spectra zijn, inclusief paren van positieve versus negatieve modi. De auteurs tonen aan dat deze voorspellingen goed correleren met gevestigde maten voor structurele gelijkenis, niet alleen binnen elke modus maar ook tussen modi. Met echte data uit menselijke urine, menselijk bloedplasma en een wild eetbaar plantmonster bouwen ze “moleculaire netwerken” waarin elk spectrum een knooppunt is en sterke voorspelde gelijkenis een verbinding creëert. In tegenstelling tot oudere benaderingen mengen deze netwerken op natuurlijke wijze positieve en negatieve modedata in één samenhangende kaart. Door experts samengestelde clusters bevatten bijvoorbeeld groepen cafeïne‑gerelateerde moleculen in urine die over ionisatiemodi heen verbonden zijn en overeenkomen met bekende stofwisselingsroutes.
Het chemische landschap in één oogopslag
Moleculaire netwerken zijn krachtig maar kunnen verward raken als te veel zwakke verbindingen worden opgenomen. Om dit te vermijden gebruiken de auteurs de embeddings van MS2DeepScore rechtstreeks als coördinaten in een tweedimensionale lay-out gemaakt met een techniek genaamd UMAP. Elke stip in deze kaart staat voor één spectrum, en nabijgelegen stippen komen overeen met moleculen die het model als chemisch vergelijkbaar beschouwt. Positieve en negatieve modus‑spectra van hetzelfde verbinding, die visueel heel verschillend lijken, eindigen vaak zij aan zij in deze embeddingruimte. Het team traint ook een aanvullend model dat elke embedding inspecteert en inschat hoe betrouwbaar deze is, waarbij spectra die ruisig, incompleet of onvergelijkbaar met de trainingsdata zijn worden gemarkeerd. Het verwijderen van deze laag‑kwaliteits punten verbetert de algehele nauwkeurigheid en maakt de visualisaties betrouwbaarder.
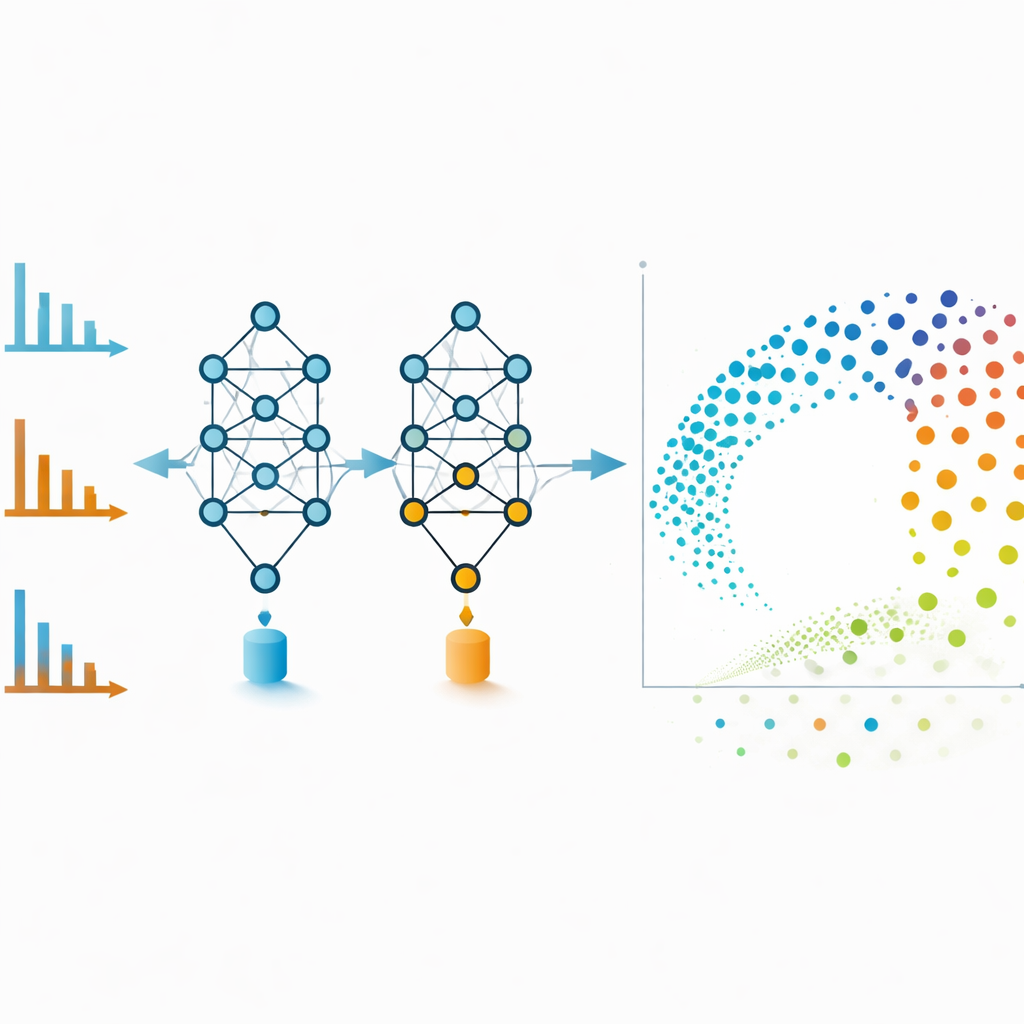
Geavanceerde tools beschikbaar maken voor alledaagse labs
Om ervoor te zorgen dat deze technologie bruikbaar is buiten programmeerexpertise, hebben de auteurs MS2DeepScore 2.0 geïntegreerd in populaire, vrij beschikbare massaspectrometriesoftware. Met deze integratie kunnen onderzoekers features detecteren, moleculaire netwerken bouwen die ionisatiemodusgrenzen negeren, en de resulterende chemische ruimte verkennen via interactieve dashboards. De code, getrainde modellen en voorbeelddatasets worden open gedeeld, en het systeem kan worden bijgetraind of fijn afgestemd voor gespecialiseerde chemische klassen.
Wat dit betekent voor toekomstige ontdekkingen
Voor niet‑specialisten is de kernboodschap dat MS2DeepScore 2.0 helpt gefragmenteerde en modus‑afhankelijke metingen om te zetten in een enkel, beter begrijpelijk beeld van de moleculen in een monster. Door betrouwbaar signalen te verbinden die vroeger in gescheiden analytische werelden leefden, stelt de methode onderzoekers in staat veel grotere referentiebibliotheken te benutten, monsters vollediger te vergelijken en hun aandacht te richten op betekenisvolle clusters van verwante verbindingen. Deze kruisverbinding van data zal naar verwachting het identificeren van biomarkers, voedingsstoffen, natuurlijke producten en verontreinigende stoffen versnellen en uiteindelijk ons begrip verdiepen van hoe chemie gezondheid en milieu vormgeeft.
Bronvermelding: de Jonge, N.F., Chekmeneva, E., Schmid, R. et al. Cross ionization mode chemical similarity prediction between tandem mass spectra in metabolomics. Nat Commun 17, 2483 (2026). https://doi.org/10.1038/s41467-026-69083-y
Trefwoorden: metabolomics, massaspectrometrie, machine learning, moleculair netwerken, chemische gelijkenis