Clear Sky Science · nl
Het detecteren van enhancer–promoter-lussen verbeteren via normalisatiemethoden voor chromatine-interactiegegevens
De verborgen lussen in ons DNA zichtbaar maken
In elke cel vouwen lange DNA-strengen zich en vormen ze driedimensionale lussen, waardoor ver verwijderde gedeelten van het genoom dicht bij elkaar komen. Sommige van deze lussen verbinden fysiek schakelaars, zogenaamde enhancers, met de genen die ze regelen en bepalen zo hoe cellen zich ontwikkelen en hoe ziektes zoals kanker ontstaan. Dit artikel introduceert een nieuwe computationele methode, Raichu, die deze subtiele regulerende lussen veel gemakkelijker detecteerbaar maakt in genoomwijde experimenten en daarmee een scherper venster opent op hoe DNA‑vouwing en genactiviteit met elkaar samenhangen.
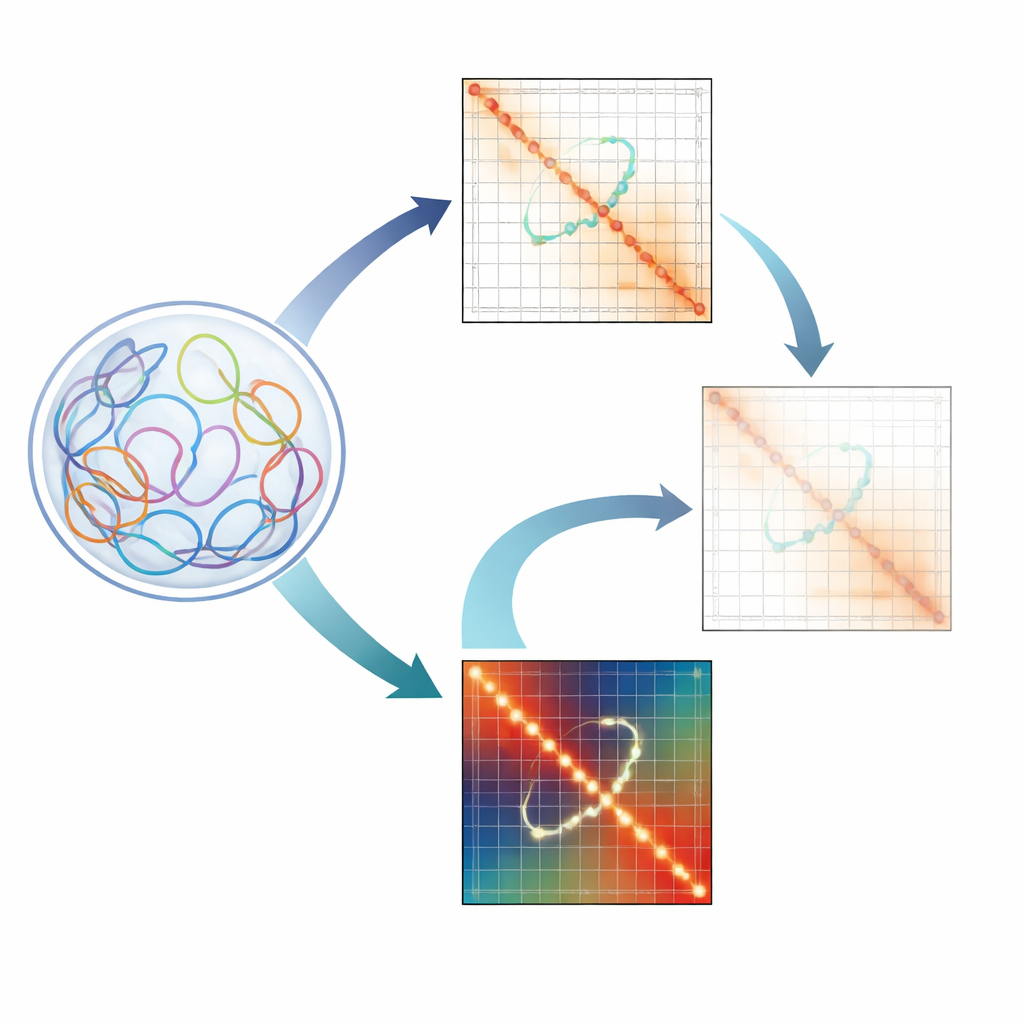
Waarom kleine DNA-lussen ertoe doen
Onze genomen liggen niet als rechte strengen letters geordend. In plaats daarvan plooien ze zich tot een complexe 3D-structuur in de kern. In deze gevouwen staat kunnen verafgelegen regio’s van DNA elkaar raken en chromatine-lussen vormen. Sommige lussen fungeren als steigers die hele buurten van het genoom organiseren. Andere zijn regulerende lussen die promotors van genen verbinden met afstands‑enhancers die hun activiteit versterken. Verstoring van deze regulerende lussen is in verband gebracht met ontwikkelingsstoornissen en kanker, waardoor wetenschappers ze graag gedetailleerd in kaart brengen.
De uitdaging van het lezen van 3D-genoomkaarten
Technieken zoals Hi-C en aanverwante methoden leggen miljoenen tot miljarden DNA–DNA-contacten vast en vatten die samen als heatmaps, waarbij elke pixel weergeeft hoe vaak twee genoomregio’s elkaar ontmoeten. Deze kaarten worden echter gekenmerkt door technische eigenaardigheden: sommige regio’s zijn makkelijker te meten dan andere vanwege sequentiesamenstelling, hoe goed ze uitgelijnd kunnen worden of hoe ze in het experiment worden geknipt. Om dit op te schonen gebruiken onderzoekers normalisatiemethoden zoals ICE en KR die de kaarten balanceren zodat elke regio ogenschijnlijk gelijke zichtbaarheid heeft. Hoewel deze tools grote kenmerken zoals brede domeinen en sterke structurele lussen verscherpen, laten de auteurs zien dat ze onbedoeld de zwakkere, maar biologisch cruciale, enhancer–promoter-lussen wegwassen.
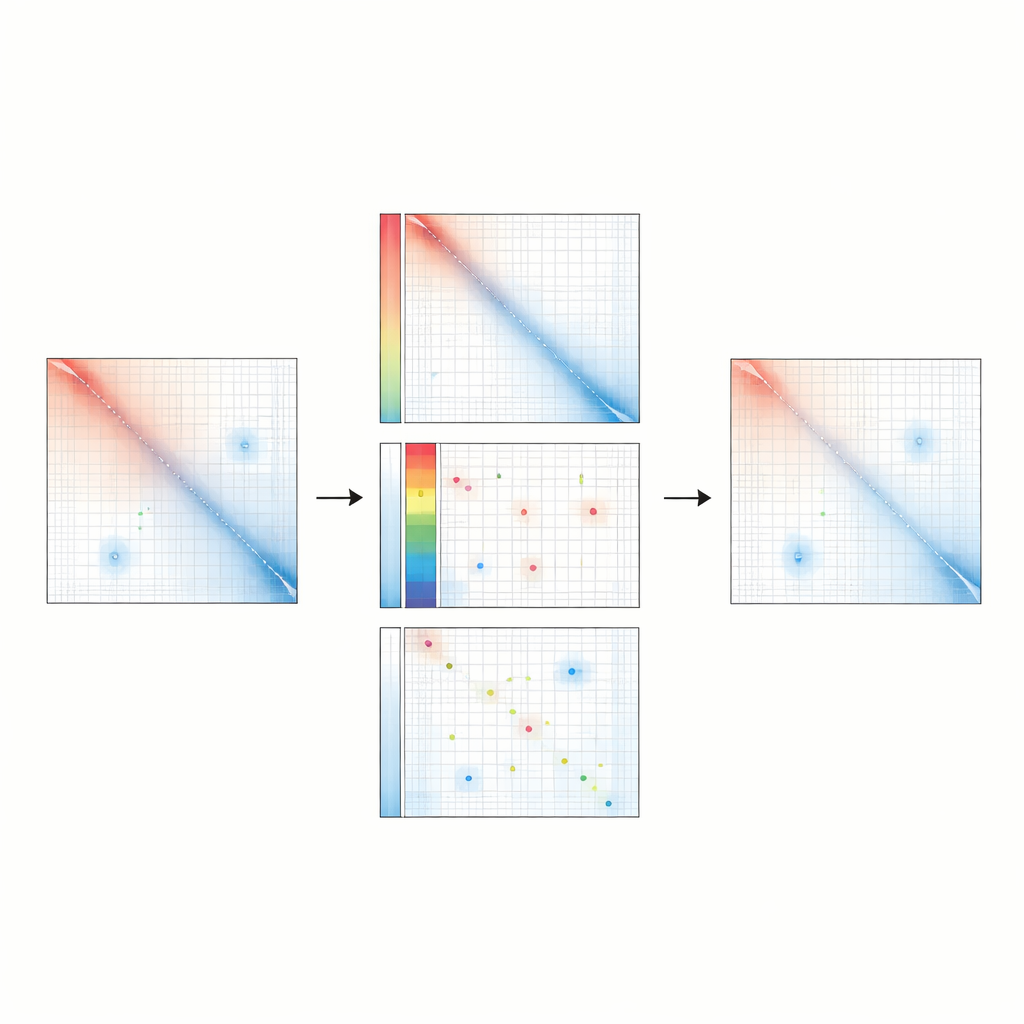
Een nieuwe manier om het signaal te zuiveren
Raichu kiest een andere benadering voor het opschonen van chromatine-contactgegevens. In plaats van te dwingen dat elke genoomregio er even zichtbaar uitziet, modelleert het elke interactie als de som van drie componenten: een algemene afname van contactfrequentie met toenemende afstand langs het chromosoom, een bias die specifiek is voor elke locatie, en een resterend signaal dat specifiek is voor dat contact. Met een optimalisatie-algoritme schat Raichu het biaspatroon dat het best de waargenomen gegevens verklaart, terwijl de globale afstandsafhankelijke trend vastgehouden wordt. De contacten worden vervolgens aangepast door deze biaswaarden eruit te delen. Dit behoudt de natuurlijke globale vervaltrend van interacties terwijl technische vervormingen selectief worden gecorrigeerd, waardoor helderdere signalen van reële, specifieke DNA-contacten overblijven.
Het onthullen van duizenden gemiste regulerende lussen
Toen de auteurs Raichu toepasten op diep-sequencing menselijke en muisdatasets, onthulde het bijna twee keer zoveel chromatine-lussen als standaardmethoden, terwijl het bijna alle eerder bekende lussen bleef terugvinden. De extra lussen die Raichu detecteerde waren sterk verrijkt voor biochemische merkers van actieve enhancers en promotors en voor binding van transcriptiefactoren die genactiviteit regelen. Veel van deze lussen werden onafhankelijk ondersteund door andere 3D-genoomtechnologieën en zelfs door resolutie‑rijke beeldvorming, wat bevestigt dat ze reële fysieke nabijheid in de kern weerspiegelen. Belangrijk is dat Raichu dit voordeel behield zelfs wanneer de gegevens werden verdund om lagere sequenceringsdieptes te simuleren, bij het bestuderen van gespecialiseerde mappingmethoden zoals Micro-C en regiogecapte Micro-C, en zelfs bij het samenvoegen van kleine aantallen enkele cellen.
Subtiele veranderingen en evolutionaire patronen onthullen
Omdat Raichu bijzonder gevoelig is voor regulerende lussen, is het beter in het opsporen van betekenisvolle verschillen tussen condities die anders vergelijkbaar zouden lijken. In een gemodelleerde menselijke cellijn met een leukemierisicovariant ontdekte Raichu nieuwe lussen die alleen in de risicostaat verschenen en sleutelgenen met hun enhancers verbonden, in overeenstemming met verschuivingen in genactiviteit. Over muis- en humane neurale voorlopercellen heen detecteerde Raichu duizenden enhancer–promoter-lussen die tussen soorten geconserveerd waren en vaak verre enhancers verbonden met genen die bij hersenontwikkeling betrokken zijn. Deze bevindingen suggereren dat veel belangrijke regulerende contacten in het zicht hebben verborgen gezeten, gemaskeerd door eerdere normalisatie-aanpakken.
Wat dit betekent voor toekomstig genoomonderzoek
Voor een breed publiek is de kernboodschap dat de manier waarop we grote genoomdatasets verwerken sterk kan beïnvloeden welke biologie we zien. Door de schoonmaakstap voor 3D-genoomkaarten opnieuw te bekijken, herstelt Raichu zwakke maar belangrijke signalen die gen-schakelaars met hun doelwitten verbinden. Dit maakt het eenvoudiger te achterhalen hoe DNA‑vouwing genactiviteit aanstuurt in gezondheid en ziekte, van enkele cellen tot hele weefsels en tussen soorten. Naarmate meer studies Raichu toepassen, kunnen onderzoekers rijkere kaarten van enhancer–promoter‑communicatie verwachten en een duidelijker beeld krijgen van hoe veranderingen in genoomarchitectuur bijdragen aan ontwikkeling, kanker en andere complexe aandoeningen.
Bronvermelding: Wang, X., Shi, D., Xue, F. et al. Boosting the detection of enhancer-promoter loops via normalization methods for chromatin interaction data. Nat Commun 17, 2299 (2026). https://doi.org/10.1038/s41467-026-69082-z
Trefwoorden: 3D-genoomorganisatie, enhancer–promoter-lussen, Hi-C-gegevensanalyse, chromatine-normalisatie, genregulatie