Clear Sky Science · nl
Een atlas voor absolute kwantificatie van kleine niet-coderende RNA 's in diverse zoogdierweefsels en cellijnen
Waarom kleine RNA-moleculen ertoe doen
In elke cel helpen legers van kleine RNA-moleculen bepalen welke genen aan of uit staan. Deze kleine niet-coderende RNA 's werken als dimmers voor onze genetische programma 's en bepalen zo ontwikkeling, orgaanfunctie en ziekte. Ondanks krachtige sequencing-technologieën is het voor wetenschappers moeilijk gebleken precies te meten hoeveel van deze moleculen in verschillende cellen en weefsels aanwezig zijn. Deze studie introduceert een nauwkeurigere manier om ze te tellen en bouwt een gedetailleerde atlas die hun werkelijke abundantie toont over veel zoogdierweefsels en veelgebruikte laboratoriumcellijnen.
Een helderdere manier om kleine RNA's te tellen
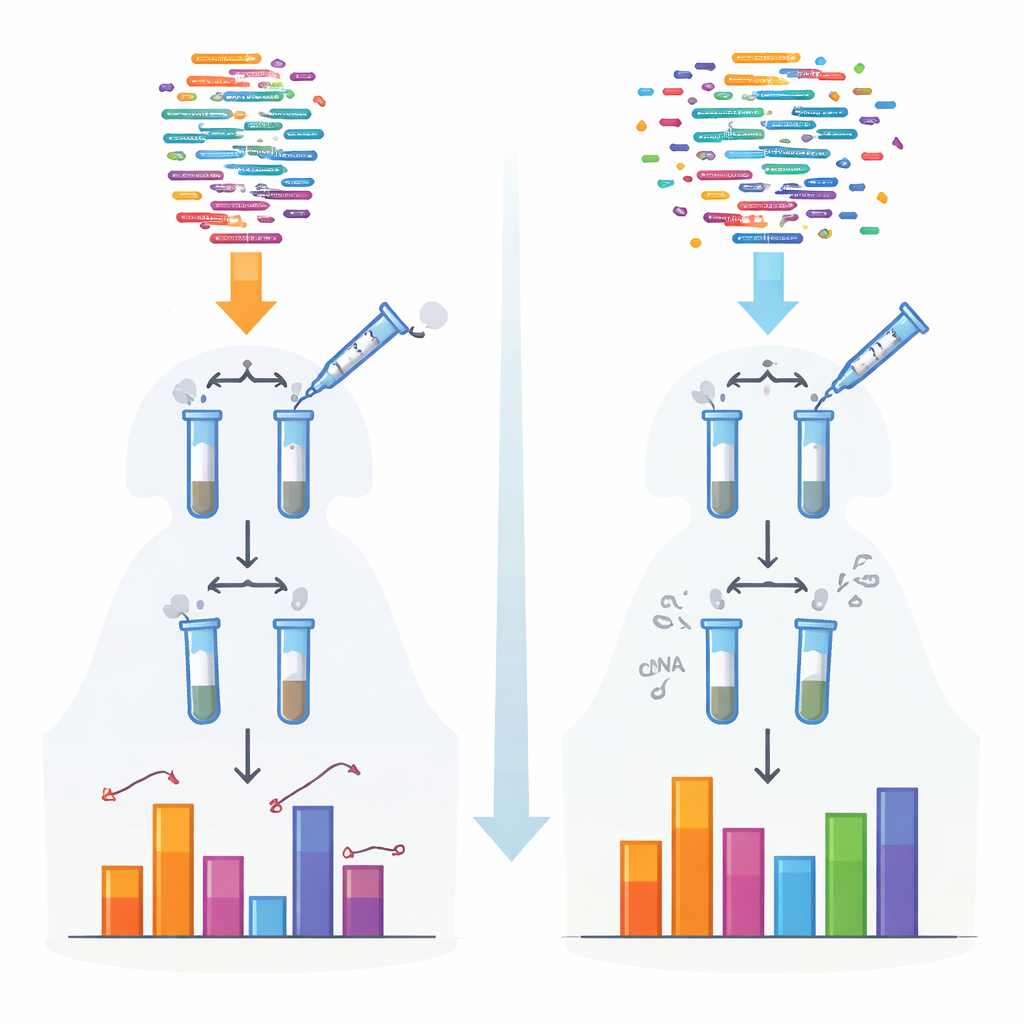
Traditionele methoden voor het sequencen van kleine RNA 's vertrouwen op enzymen die adapters vastmaken voordat de moleculen gelezen worden. Die enzymen hebben voorkeur voor bepaalde vormen en chemische eindgroepen, waardoor sommige RNA 's efficiënt worden gevangen terwijl andere worden gemist of ondergeteld. Deze bias is vooral sterk voor bepaalde klassen zoals piRNA 's en plantaardige kleine RNA 's, die beschermende chemische caps aan hun uiteinden dragen. De auteurs ontwikkelden een nieuw protocol, 4NBoost genoemd, dat de adapters en reactieve voorwaarden herschikt om deze voorkeuren te egaliseren en ingebouwde moleculaire barcodes toevoegt om echte moleculen te onderscheiden van kopieën die tijdens amplificatie zijn gemaakt.
Van protocol naar meetinstrument
Om 4NBoost van een relatieve uitlezing tot een werkelijk meetinstrument te maken, voegde het team zorgvuldig ontworpen synthetische "spike-in" RNA 's toe in bekende concentraties die een zeer breed bereik beslaan. Door te vergelijken hoe vaak elke spike-in door de sequencer werd gelezen met hoeveel er oorspronkelijk was toegevoegd, bouwden ze standaarden die readcounts omzetten in absolute molecuulnummers. Tests met verschillende spike-inmengsels en toegevoegde controlemoleculen toonden aan dat 4NBoost de abundantie nauwkeurig kon volgen over meerdere grootordes, inclusief RNA 's met lastig chemische modificaties. Zelfs bij startmateriaal van slechts één nanogram totaal RNA legde de methode nog steeds het kleine-RNA-landschap getrouw vast.
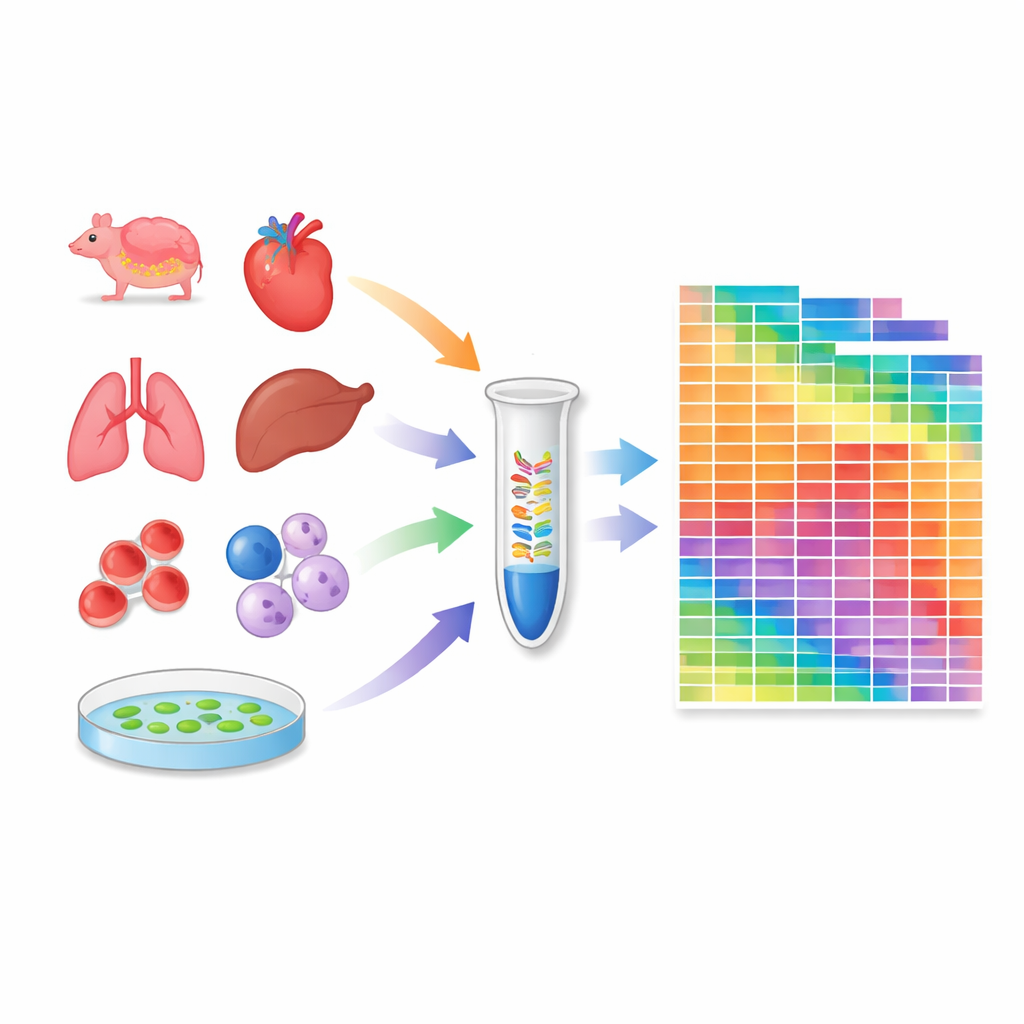
Een atlas opbouwen over weefsels en cellijnen
Gewapend met dit gekalibreerde protocol profileerden de onderzoekers 259 monsters: 20 weefsels van muizen, 18 van krab-etende makaken, 24 veelgebruikte menselijke en muizencellijnen, en verschillende weefsels van de modelplant Arabidopsis. Voor elk monster schatten ze het absolute aantal moleculen voor duizenden microRNA 's en piRNA 's. Dit onthulde hoeveel verschillende microRNA-soorten in elke context voorkomen en hoe hun totale hoeveelheden tussen weefsels en soorten vari�ebren. Sommige cellijnen en organen dragen bijzonder rijke microRNA-repertoires, terwijl andere, zoals bloedcellen, gedomineerd worden door een paar zeer abundant soorten. De atlas toonde ook substanti�eble verschillen tussen muis- en makaakweefsels, wat benadrukt dat kleine-RNA-regulatie soortspecifiek kan zijn.
Oude data corrigeren en gangbare veronderstellingen herzien
Toen de nieuwe atlas werd vergeleken met populaire kleine-RNA-databases die met conventionele methoden zijn opgebouwd, ontstonden opvallende mismatches. Diverse belangrijke microRNA-families — zoals miR-19 en miR-29 — bleken veel overvloediger te zijn dan eerder gedacht, terwijl andere — zoals de veel bestudeerde let-7- en miR-10-families — vaak overschat waren. De studie onderzochte ook opnieuw welke "arm" van elk precursor-hairpin daadwerkelijk in cellen wordt gebruikt en bracht gevallen aan het licht waarin huidige annotaties de verkeerde hoofdstreng vermelden. Om de schat aan bestaande bias-bevattende datasets te redden, trainden de auteurs een machine-learningmodel dat leert hoe conventionele metingen afwijken van 4NBoost en deze vervolgens wiskundig corrigeert om beter de werkelijke abundantie weer te geven.
Een openbare bron voor het verkennen van kleine RNA's
Alle 4NBoost-metingen en het correctiemodel zijn vrij beschikbaar via een online platform genaamd SmRNAQuant. Onderzoekers kunnen absolute kleine-RNA-niveaus voor specifieke weefsels, cellijnen of microRNA 's doorbladeren of downloaden, en ze kunnen hun eigen gegevens die met een gangbare kit zijn voorbereid uploaden om bias-gecorrigeerde waarden te verkrijgen. Voor niet-specialisten is de kernboodschap dat tellen ertoe doet: kleine verschillen in het aantal kopieën van kleine RNA 's kunnen het verschil betekenen tussen actieve genregulatie en geen effect. Door betrouwbaardere getallen te bieden en een manier om oude data te herstellen, legt dit werk een steviger kwantitatief fundament voor het begrijpen hoe kleine RNA 's normale biologie en ziekte vormgeven.
Bronvermelding: Xiao, W., Zheng, Y., Zhang, H. et al. An absolute quantification atlas of small non-coding RNAs across diverse mammalian tissues and cell lines. Nat Commun 17, 2314 (2026). https://doi.org/10.1038/s41467-026-68812-7
Trefwoorden: microRNA-kwantificatie, klein niet-coderend RNA, bias bij RNA-sequencing, weefsel-expressieatlas, machine learning-correctie