Clear Sky Science · nl
HIV-seq onthult verschillen in genexpressie tussen HIV-transcripterende cellen van mensen met viremie en onderdrukte mensen met HIV
Waarom dit onderzoek belangrijk is voor mensen die met HIV leven
Moderne HIV-behandeling kan het virus in het bloed tot ondetecteerbare niveaus terugdringen, waardoor een ooit dodelijke infectie verandert in een chronische, beheersbare aandoening. Toch komt het virus bijna altijd terug als de behandeling stopt. Dit artikel onderzoekt een verborgen groep geïnfecteerde immuuncellen die HIV stilhouden onder de radar, en introduceert een nieuwe technologie, "HIV‑seq", die wetenschappers voor het eerst in staat stelt te zien wat deze cellen afzonderlijk doen. Begrip van deze sluimerende cellen kan toekomstige strategieën informeren die niet alleen gericht zijn op het beheersen van HIV, maar mogelijk ook op genezing.
Het virus ontdekken dat in het volle zicht verstopt zit
HIV blijft in het lichaam aanwezig door zijn genetisch materiaal in langlevende immuuncellen in te bouwen, vooral CD4 T-cellen. Sommige van deze geïnfecteerde cellen blijven stil, terwijl andere actief stukjes viraal RNA of eiwit produceren, zelfs wanneer bloedtesten aangeven dat het virus ondetecteerbaar is. Deze “actieve reservoir”-cellen kunnen chronische ontsteking aanwakkeren en een snelle virale terugkeer veroorzaken wanneer behandeling wordt onderbroken. Standaard enkelcel-RNA-sequencing mist ze echter vaak, omdat HIV-transcripten zeldzaam kunnen zijn en vaak niet de poly-A staart hebben waar de technologie normaal op vertrouwt. De auteurs wilden dit detectieprobleem oplossen zodat ze HIV-producerende cellen konden vergelijken bij mensen met onbeheersbare infectie (viremie) versus mensen met succesvolle antiretrovirale therapie (ART).
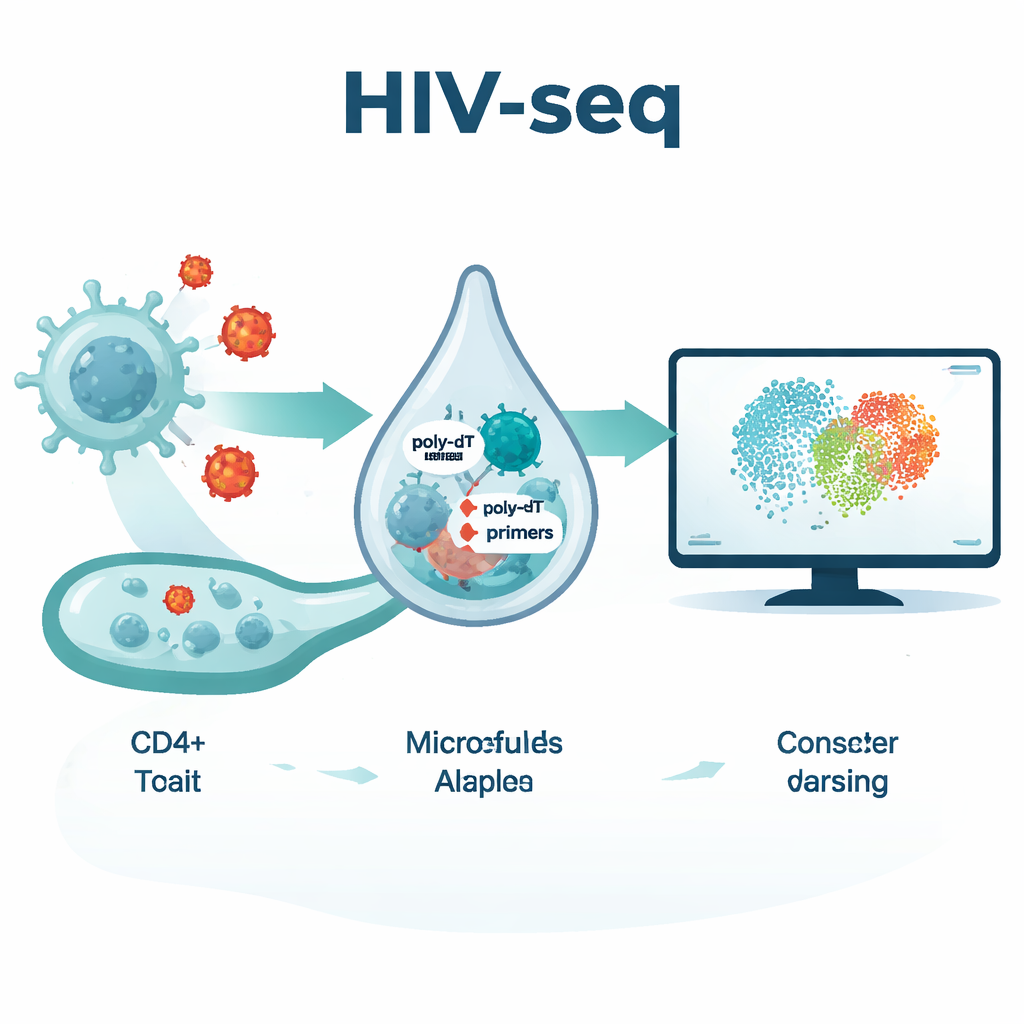
Een nieuwe lens: de HIV‑seq-methode
Het team ontwikkelde HIV‑seq door aan de gebruikelijke enkelcel-sequencingchemie verschillende zorgvuldig ontworpen HIV-specifieke capture-primers toe te voegen. Deze extra primers hechten zich aan geconserveerde regio's van het HIV-genoom, waardoor het terugvinden van viraal RNA wordt versterkt, ongeacht of het een poly-A staart heeft. Ze combineerden dit met DNA-gebarcoded antilichamen die tegelijk tientallen oppervlakte-eiwitten meten, waardoor elke gesequencede cel een rijk moleculair profiel krijgt. In rechtstreekse tests op bloedcellen van mensen met onbehandeld HIV verdubbelde HIV‑seq ruwweg het aantal virale reads per geïnfecteerde cel zonder het genexpressiepatroon van de gastheercel te vervormen of valse signalen te produceren in HIV-negatieve donoren. Dit stelde de onderzoekers in staat HIV-RNA-positieve cellen te definiëren als cellen met ten minste één met vertrouwen gedetecteerd viraal transcrip, en te plaatsen waar die cellen zich bevinden binnen het bredere T-cel-landschap.
Hoe HIV-producerende cellen eruitzien tijdens actieve infectie
Toegepast op vier mensen met onbehandeld HIV analyseerden de auteurs meer dan 85.000 CD4 T-cellen en identificeerden 1.072 cellen die actief HIV transcriberen. Deze geïnfecteerde cellen waren zelden naïeve cellen; in plaats daarvan clusterden ze voornamelijk onder effectorgeheugen T-cellen die al eerder door immuunreacties waren geactiveerd. Een opvallende subset vertoonde een cytotoxisch of "killer"-profiel, met expressie van genen voor granzymes, perforine en andere moleculen die typisch geassocieerd zijn met cellen die geïnfecteerde doelwitten vernietigen. Tegelijkertijd hadden HIV-positieve cellen verminderde niveaus van verschillende natuurlijke antivirale afweermechanismen en restrictiefactoren, wat wijst op een intern milieu dat gunstiger is voor virale replicatie. Padanalyses toonden verhoogde activiteit van signaalroutes die bekend zijn om HIV-genexpressie te stimuleren, waaronder NFAT en proteïnekinase C, evenals chemokine-routegangen die kunnen beïnvloeden waar deze cellen zich door het lichaam verplaatsen.
Hoe HIV-producerende cellen veranderen onder succesvolle behandeling
De onderzoekers onderzochten vervolgens drie van dezelfde individuen na ten minste zes maanden effectieve ART, toen het virus in het bloed was onderdrukt. Zoals verwacht waren HIV-producerende cellen veel zeldzamer, maar HIV‑seq kon nog steeds 25 zulke cellen detecteren onder meer dan 75.000 CD4 T-cellen. Deze cellen waren opnieuw verrijkt onder effectorgeheugen T-cellen, maar hun karakter was anders: ze clusterden niet langer in de hoogcytotoxische groep. In plaats daarvan waren ze geconcentreerd in geheugen-T-celsubsets die worden gemarkeerd door de IL‑7-receptor en andere kenmerken van langlevende, zelfvernieuwende cellen. Velen drukten het overlevingsproteïne BCL‑2 uit, en hun genhandtekeningen wezen op activatie van TGF‑β–gerelateerde routes die bekend staan om ontsteking te dempen en mogelijk helpen HIV in een laag-activiteits, moeilijker te detecteren staat te houden. In vergelijking met de krachtige antivirale en inflammatoire responsen die tijdens viremie werden gezien, vertoonden HIV-positieve cellen onder ART een anti-inflammatoir, meer "tolerant" profiel.
Implicaties voor toekomstige HIV-geneesstrategieën
Voor een niet-deskundige schetsen deze resultaten een beeld van HIV als een vormeveranderaar: tijdens onbehandelde infectie lijken geïnfecteerde cellen op kortlevende strijders die zowel het virus verspreiden als de vlammen van ontsteking aanwakkeren; zodra ART de actieve replicatie tot rust brengt, lijken de overgebleven HIV-producerende cellen op langlevende overlevers die zich verschuilen achter kalmerende, anti-inflammatoire signalen en sterke overlevingsprogramma's. HIV‑seq biedt een krachtig nieuw middel om deze ongrijpbare cellen op enkelcelresolutie te volgen, waardoor onderzoekers kunnen vaststellen welke cellulaire routes hen in stand houden en hoe ze mogelijk blootgelegd of geëlimineerd kunnen worden. Door te verduidelijken hoe HIV-transcripterende cellen verschillen tussen actieve infectie en medicijngedempte toestanden, levert dit werk concrete aanwijzingen voor het ontwerp van "shock‑and‑kill" of "block‑and‑lock" benaderingen die op een dag het virale reservoir zouden kunnen verminderen of zelfs uitroeien.
Bronvermelding: Frouard, J., Telwatte, S., Luo, X. et al. HIV-seq reveals gene expression differences between HIV-transcribing cells from viremic and suppressed people with HIV. Nat Commun 17, 1540 (2026). https://doi.org/10.1038/s41467-026-68797-3
Trefwoorden: HIV-reservoir, single-cell sequencing, antiretrovirale therapie, virale latentie, immunologisch geheugen T-cellen