Clear Sky Science · nl
Geautomatiseerde kaartlegging van DNA-replicatievork-voortgang in menselijke cellen met ForkML
Waarom het volgen van de DNA-kopieersnelheid ertoe doet
Elke keer dat een menselijke cel deelt, moet hij meer dan drie miljard DNA-letters snel en nauwkeurig kopiëren. Als dit kopieerproces vertraagt of stokt, kan het het genoom beschadigen en bijdragen aan kanker en ontwikkelingsstoornissen. Tot nu toe hadden onderzoekers echter geen eenvoudige manier om precies te zien hoe snel individuele DNA-«kopieermachines» zich voortbewegen langs specifieke delen van het menselijke genoom. Dit artikel introduceert ForkML, een nieuwe techniek die nanopore-DNA-sequencing en machine learning combineert om deze taak op ongekende schaal te automatiseren.
De kopieermachines van de cel indirect in beeld brengen
DNA wordt gedupliceerd door kleine moleculaire machines, replicatievorken genaamd, die langs de dubbele helix bewegen en nieuwe strengen vormen. Met ForkML kunnen onderzoekers deze vorken indirect volgen door een onschadelijke chemische marker, BrdU, in nieuw gevormd DNA te introduceren tijdens twee zeer korte pulsen met een vaste tijd tussen beide. Omdat BrdU op individuele DNA-moleculen door nanopore-sequencers gedetecteerd kan worden, zien de wetenschappers twee gemarkeerde «strepen» op elke DNA-streng waar een vork tijdens de twee pulsen langs kwam. Door de afstand tussen de strepen te meten en te delen door het bekende tijdsverschil, kunnen ze berekenen hoe snel elke vork zich in dat genoomgebied bewoog. 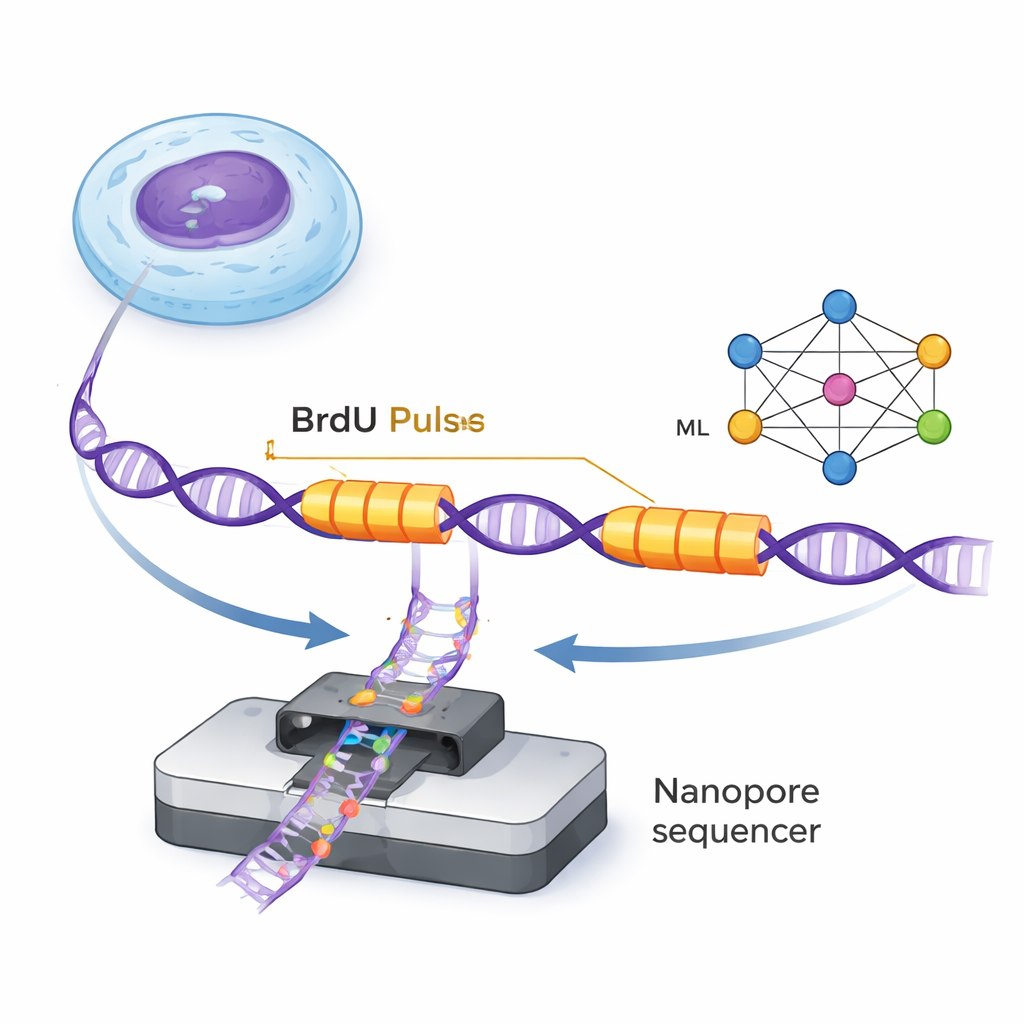
Een computer leren de chemische sporen te lezen
In eerder werk met gist konden de auteurs deze BrdU-sporen met simpele regels detecteren, maar in menselijke cellen zijn de signalen zwakker en complexer. Menselijke experts kunnen nog steeds het karakteristieke patroon herkennen — een scherpe toename in BrdU bij aanvang van de puls, gevolgd door een geleidelijke afname wanneer het wordt weggespoeld — maar dit met het blote oog doen voor miljoenen DNA-fragmenten is onmogelijk. ForkML lost dit op door een neuraal netwerk, een vorm van machine learning, te trainen op duizenden handmatig geannoteerde voorbeelden. Het model leert elk stuk DNA te classificeren als achtergrond of als een naar rechts of links bewegende vork, en de start van elke BrdU-puls met hoge nauwkeurigheid te lokaliseren. Dit maakt volledig geautomatiseerde kaartlegging van duizenden individuele vorksnelheden uit één enkele sequencing-run mogelijk.
Stress meten en verschillen over het genoom heen
Door ForkML toe te passen op een menselijke darmkanker-cellijn, verkreeg het team meer dan 2.000 metingen van vorksnelheid per experiment en vond dat een typische vork zich voortbeweegt met ongeveer 1,2 kilobases per minuut, in overeenstemming met eerdere, lagere-throughput methoden. Toen ze cellen behandelden met geneesmiddelen die de DNA-replicatie vertragen, detecteerde ForkML de vertraging duidelijk, wat aantoont dat het replicatiestress gevoelig kan meten. Omdat elke vork wordt teruggeplaatst op zijn positie in het referentiegenoom, konden de auteurs snelheid relateren aan andere kenmerken, zoals het tijdstip waarop een regio normaal replicateert tijdens de celcyclus, hoe compact het DNA is verpakt en hoe actief het wordt getranscribeerd naar RNA. 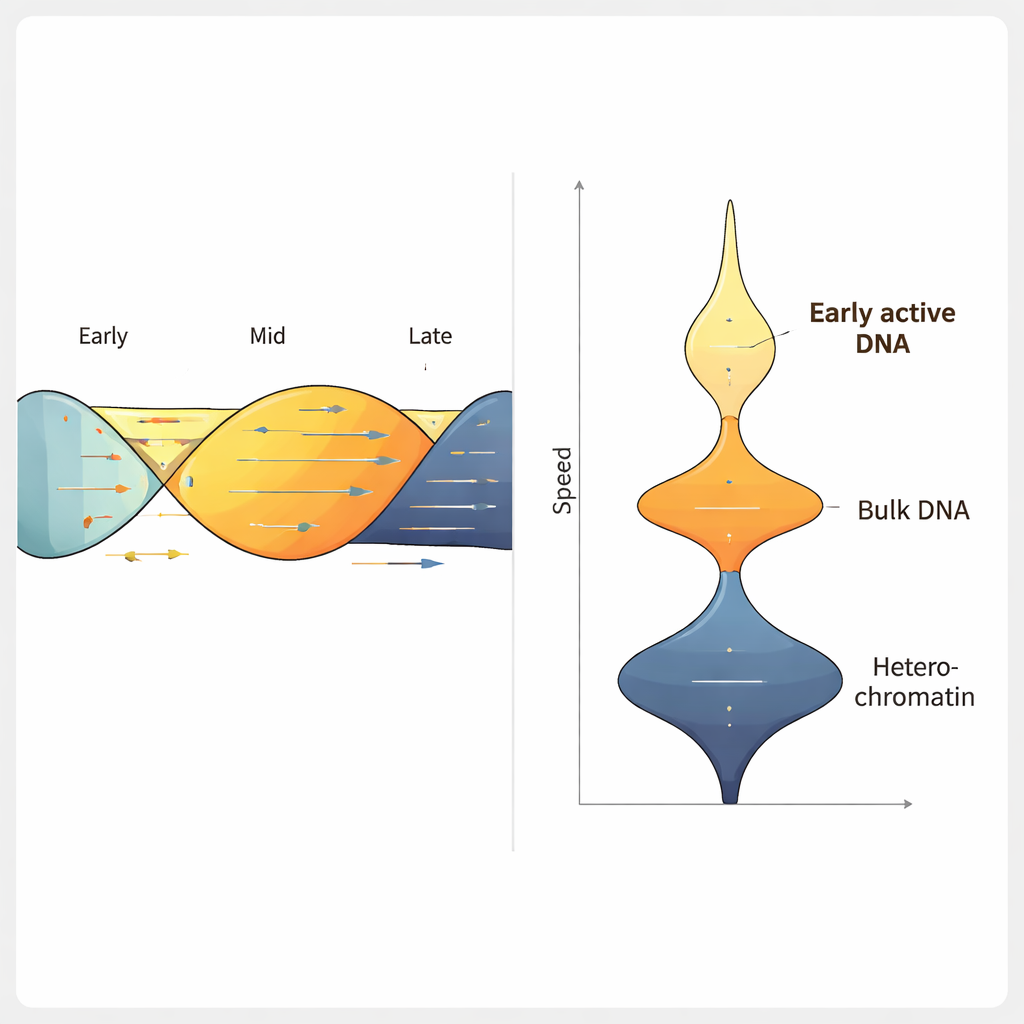
Aanwijzen waar DNA-kopie begint en hoe strengen verschillen
Verder dan snelheid identificeert ForkML ook waar DNA-replicatie begint en stopt, door punten te vinden waar vorken uit elkaar lopen of samenkomen langs hetzelfde molecuul. Door meer dan 20.000 van dergelijke startplaatsen in kaart te brengen, bevestigen de auteurs dat menselijke cellen een gemengde strategie gebruiken: sommige replicaties beginnen in goed omschreven initiatiezones, maar de meeste starten verspreid over het genoom. Door de vorkrichting te combineren met welke DNA-streng door de sequencer gelezen is, kan ForkML ook onderscheid maken tussen de snelheden van leading- en lagging-strandaantrekking, iets wat traditionele vezelgebaseerde assays niet kunnen. Tests in zes verschillende menselijke cellijnen — zowel normaal als kankergezwelachtig — laten zien dat dezelfde eenvoudige BrdU-labelingcondities breed toepasbaar zijn en in elk geval robuuste snelheidschattingen opleveren.
Een digitale upgrade van een klassieke techniek
Voor niet-specialisten kan ForkML worden gezien als een moderne, digitale versie van de klassieke DNA-fiber-assay: het gebruikt een vergelijkbaar labelingsschema, maar vervangt handmatige microscopie door long-read sequencing en machine learning. Dit levert veel hogere throughput, directe plaatsing van elke meting op het genoom en meer gedetailleerde informatie over waar en hoe snel DNA wordt gekopieerd. Omdat het protocol eenvoudig is, compatibel met huidige nanopore-hardware en aanpasbaar aan andere organismen, heeft ForkML het potentieel om een standaardinstrument te worden voor het bestuderen van DNA-replicatie. In praktische zin biedt het onderzoekers een krachtige manier om lokale DNA-kopieersnelheid — normaal of onder stress — te koppelen aan genactiviteit, chromatine-toestand en ziektegerelateerde veranderingen in het genoom.
Bronvermelding: Rojat, V., Ciardo, D., Tourancheau, A. et al. Automated mapping of DNA replication fork progression in human cells with ForkML. Nat Commun 17, 1975 (2026). https://doi.org/10.1038/s41467-026-68750-4
Trefwoorden: DNA-replicatie, snelheid van replicatievork, nanopore-sequencing, BrdU-labeling, machine learning in genomica