Clear Sky Science · nl
Hoge-snelheids blind gestructureerde belichtingsmicroscopie via onbewaakte algoritme-uitrol
Scherpere films van het leven in cellen
Moderne biologie hangt vaak af van het observeren van levende cellen in actie, maar veel belangrijke structuren zijn gewoon te klein en te snel om helder vastgelegd te worden met gewone microscopen. Dit artikel introduceert een nieuwe manier om wazige, snel gemaakte beelden om te zetten in scherpe, supergedetailleerde films in real‑time, zonder perfect afgestemde hardware te vereisen. De methode, unrolled blind structured illumination microscopy (UBSIM) genoemd, belooft geavanceerde, hoge‑snelheids celbeeldvorming toegankelijker te maken voor alledaagse biologische laboratoria.
Waarom gewone microscopen tekortschieten
Traditionele lichtmicroscopen worden beperkt door diffractie, een fundamentele eigenschap van licht die fijne details kleiner dan enkele honderden nanometers vervaagt. Structured illumination microscopy (SIM) pakt dit aan door gepatroniseerd licht op een monster te schijnen en de resulterende interferentie te gebruiken om extra details te achterhalen, wat de resolutie ongeveer verdubbelt. Klassieke SIM vereist echter precies bekende belichtingspatronen en zorgvuldige kalibratie, wat duur en kwetsbaar kan zijn. Een nieuwere variant, blind‑SIM, versoepelt deze hardware‑eisen door willekeurige patronen toe te staan en zowel het monster als de belichting uit de data te reconstrueren. Het nadeel is dat dat reconstructieproces traag en iteratief is, en seconden tot minuten per frame kan vergen—veel te traag voor realtime films van levende cellen.
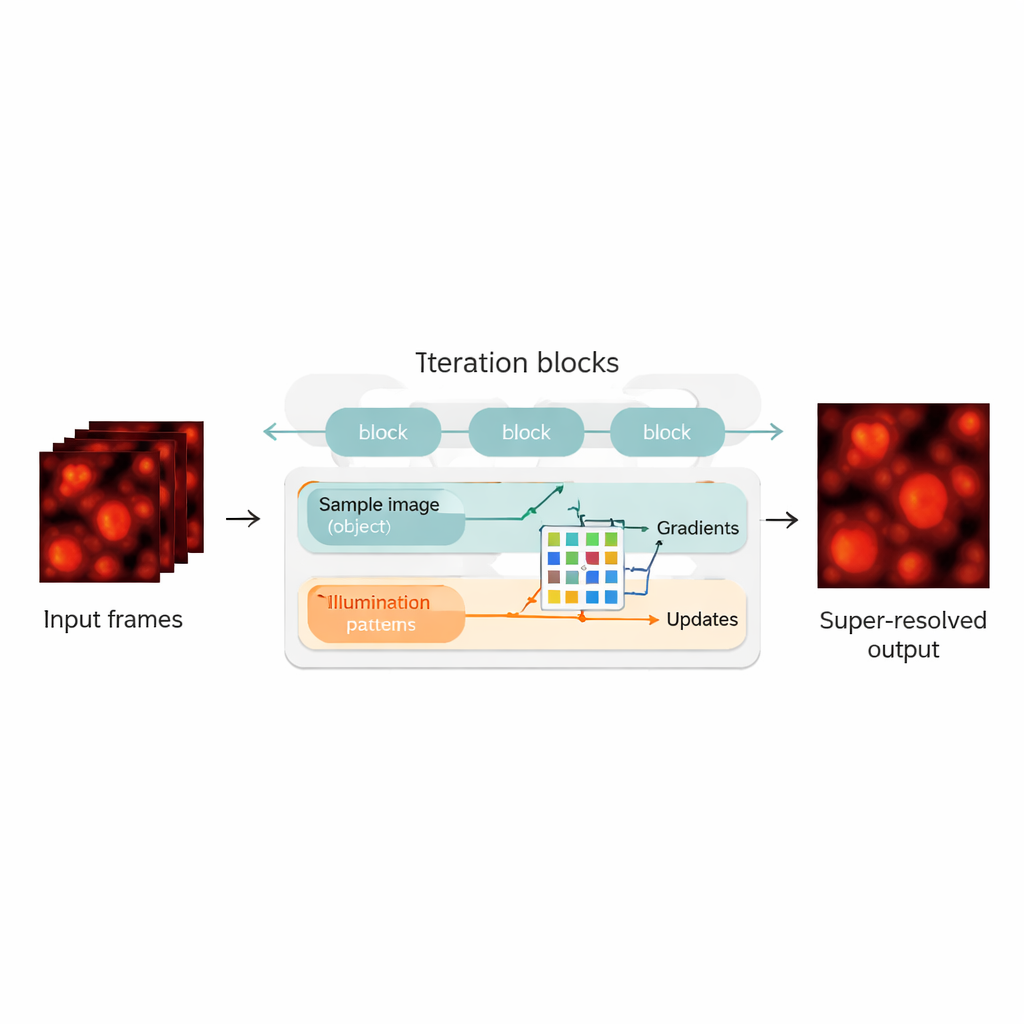
Een mix van fysica en neurale netwerken
De auteurs overbruggen deze kloof door de blind‑SIM reconstructie te herontwerpen als een hybride van een fysisch model en een neuraal netwerk. Ze "rollen" het originele iteratieve algoritme uit—elke iteratie wordt een laag in een neuraal netwerk, en vormt een keten van update‑blokken. Binnen elk blok berekent de methode hoe goed de huidige schatting van het monster en de belichting de gemeten beelden verklaart, berekent gradiënten (richtingen voor verbetering), en voert die vervolgens in een compacte convolutionele neuraal netwerk. Dit netwerk leert slimmer correctiestappen te maken en fungeert als een automatisch afgestemde versneller voor het oorspronkelijke algoritme. Cruciaal is dat UBSIM onbewaakt wordt getraind: in plaats van perfecte voorbeeldbeelden als grondwaarheden te vereisen, heeft het alleen het fysische model van hoe licht door de microscoop gaat nodig. Dat verkleint het risico dat het netwerk plausibel ogende maar onjuiste structuren "hallucineert".
Snel, nauwkeurig en minder vatbaar voor gokwerk
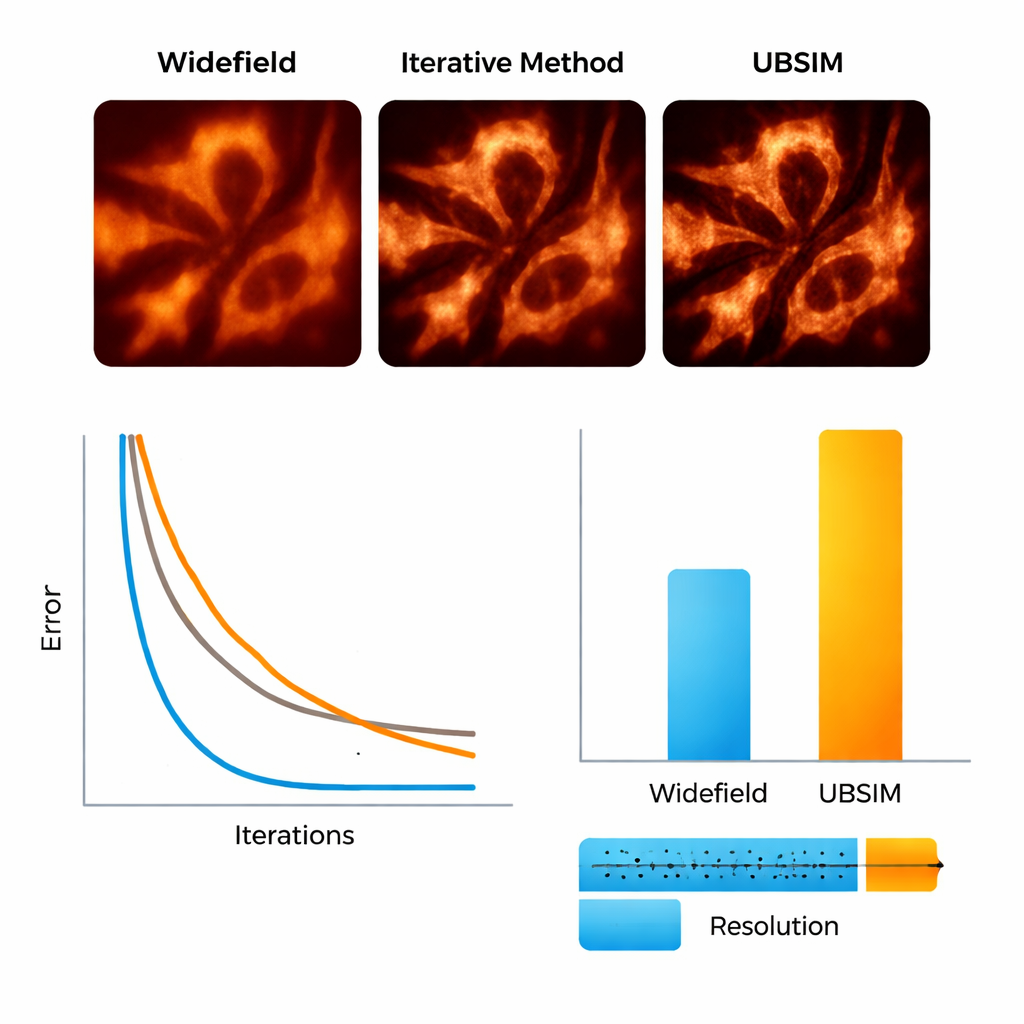
Om UBSIM te testen gebruikte het team eerst gesimuleerde microscopiebeelden waarbij de werkelijke onderliggende structuren bekend waren. Ze lieten zien dat UBSIM ongeveer twee keer de resolutie van gewone widefield‑beelden herstelt, vergelijkbaar met standaard blind‑SIM, maar twee tot drie ordes van grootte sneller werkt—een 256×256 beeld kan in ongeveer 10 milliseconden worden gereconstrueerd in plaats van seconden. Beeldkwaliteitscores, waaronder fout, similariteit en signaal‑tegen‑ruismetingen, verbeterden allemaal aanzienlijk ten opzichte van conventionele beelden. UBSIM bleek ook betrouwbaarder dan populaire deep‑learning superresolutie‑netwerken wanneer het werd geconfronteerd met onbekende data. Terwijl standaardnetwerken die op één type structuur werden getraind geneigd waren dat patroon op nieuwe, verschillende monsters te projecteren—wat subtiele maar misleidende artefacten introduceerde—behield UBSIM consistente trouw, omdat het verankerd is in de onderliggende beeldvormingsfysica in plaats van alleen in visuele voorbeelden.
Cel‑skelet en membranen in beweging zien
De onderzoekers gingen vervolgens over op echte biologische monsters. Met een flexibele opstelling die willekeurige speckle‑patronen op levende cellen projecteert, beeldden ze actinefilamenten—het eiwit"skelet" in de cel—en het endoplasmatisch reticulum (ER) af, een vertakt membraannetwerk betrokken bij eiwitproductie en celstress‑reacties. Met UBSIM werden actinedraden die in gewone beelden als vage banden leken, scherp gescheiden strengen, waarbij de resolutie verbeterde van ongeveer 300 nanometer tot ongeveer 150 nanometer. Het meest opvallend was dat UBSIM video‑snelheids superresolutie mogelijk maakte: door ruwe data vast te leggen tot 100 frames per seconde en te reconstrueren tot 50 super‑resolutie frames per seconde, kon het team ER‑tubuli in real time zien groeien, instorten en zich herorganiseren. Deze dynamiek, die zich afspeelt over fracties van seconden tot enkele seconden, is normaal gesproken moeilijk met voldoende detail te visualiseren.
Wat dit betekent voor toekomstige celbeeldvorming
Voor niet‑specialisten is de belangrijkste conclusie dat UBSIM het veel praktischer maakt om kleine cellulaire structuren in real time te volgen, met duidelijkheid voorbij de normale grenzen van lichtmicroscopen—en dat zonder perfecte hardwarekalibratie of enorme trainingsdatasets. Door de betrouwbaarheid van fysica‑gebaseerde modellen te combineren met de snelheid van moderne neurale netwerken, zet deze aanpak stapels rumoerige, gepatroniseerde beelden snel om in betrouwbare, ultrascherpe films die snel genoeg zijn voor routinematige experimenten. Naarmate de methode verder wordt verfijnd en gecombineerd met betere belichtingsstrategieën, kan het onderzoekers helpen onderzoeken hoe organellen zoals het ER reageren op stress, hoe het cel‑skelet zich herorganiseert tijdens beweging of deling, en hoe ziekten de cellulaire architectuur op nanoschaal veranderen.
Bronvermelding: Burns, Z., Zhao, J., Sahan, A.Z. et al. High-speed blind structured illumination microscopy via unsupervised algorithm unrolling. Nat Commun 17, 1967 (2026). https://doi.org/10.1038/s41467-026-68693-w
Trefwoorden: superresolutie-microscopie, gestructureerde belichting, deep learning, levende-celbeeldvorming, dynamiek van het endoplasmatisch reticulum