Clear Sky Science · nl
Genomisch taalkundig model vermindert chimera-artifacten in nanopore directe RNA-sequencing
Waarom het schoonmaken van RNA‑reads belangrijk is
Onze cellen lezen voortdurend genetische instructies die in RNA zijn vastgelegd, en nieuwe sequentietechnologieën laten onderzoekers dit proces nu in ongekende details zien. Een van de krachtigste instrumenten, nanopore directe RNA‑sequencing, kan hele RNA‑moleculen in één keer uitlezen — maar het introduceert ook fouten die genen lijken te breken en op manieren weer aan elkaar te zetten die in werkelijkheid niet voorkomen. Deze studie introduceert DeepChopper, een softwaretool die fungeert als een taalkundig model voor genomen en deze fouten opruimt zodat onderzoekers de RNA‑gegevens weer kunnen vertrouwen.
Als de sequencer nep‑gencombinaties verzint
Moderne nanopore‑apparaten trekken individuele RNA‑strengen door piepkleine poriën en lezen hun sequentie direct uit. Dat heeft grote voordelen ten opzichte van oudere methoden, zoals het behouden van chemische modificaties en het vastleggen van volledige transcripties in één enkele read. Maar het proces maakt ook gebruik van korte hulpstukjes, adapters, die tijdens de library‑voorbereiding aan RNA‑moleculen worden vastgeplakt. Soms worden twee of meer RNA‑moleculen per ongeluk aan elkaar verbonden door deze adapters, waardoor er ogenschijnlijke chimera ontstaan — hybride moleculen die verschillende genen lijken te fuseren. Standaard analysetools kunnen deze technische resten verkeerd interpreteren als echte biologische gebeurtenissen, zoals kankergerelateerde genfusies of ongebruikelijke splicepatronen, wat leidt tot misleidende conclusies.
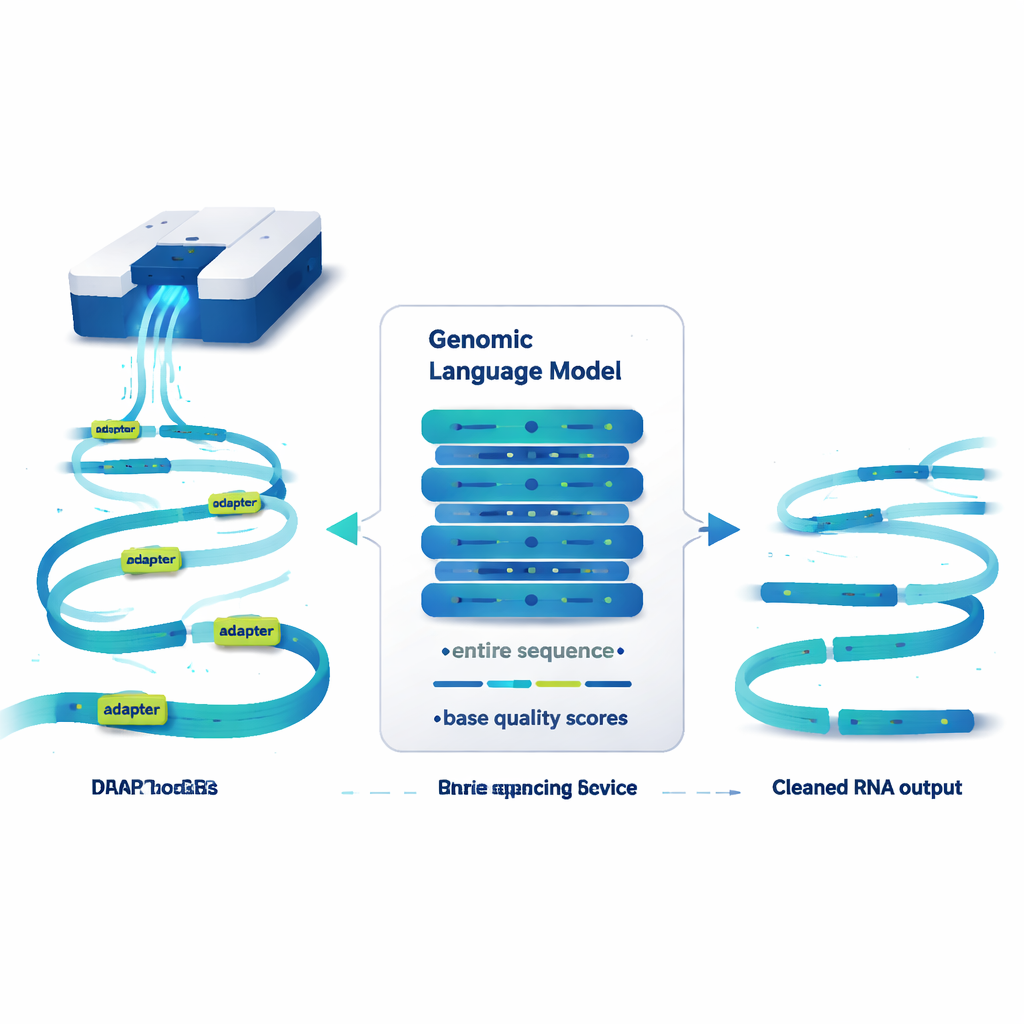
Een taalkundig model dat genomen leest, geen zinnen
DeepChopper behandelt genetische sequenties enigszins zoals tekst en past ideeën uit grote taalkundige modellen daarop toe. In plaats van met woorden te werken, leest het RNA‑sequenties letter voor letter, samen met een kwaliteitscore voor elke letter die aangeeft hoe betrouwbaar de read is. Gebouwd op een compacte architectuur genaamd HyenaDNA, kan het tot 32.000 basen tegelijk scannen — lang genoeg om vrijwel elk menselijk RNA‑molecuul te dekken. Voor elke positie schat DeepChopper of die base deel uitmaakt van een echte RNA‑sequentie of van een adapter. Een verfijningsstap maakt deze voorspellingen vervolgens vloeiender, zodat adapters als aaneengesloten blokken worden gemarkeerd in plaats van als verspreide losse plekken.
De slechte verbindingen wegsnijden zonder data weg te gooien
Als DeepChopper eenmaal adapters binnen een read heeft gevonden, doet het iets cruciaals: in plaats van de hele read weg te gooien, "hakt" het op die adapterplaatsen en behoudt de echte fragmenten. Op die manier kan een kunstmatige fusie van twee RNA’s weer worden opgesplitst in de originele delen. In tests op miljoenen nanopore‑reads van meerdere menselijke kankercellijnen en stamcellen presteerde DeepChopper veel beter dan bestaande adapter‑trimmingtools, die nooit voor deze directe RNA‑instelling waren ontworpen. Het herkende adapters correct met meer dan 99% precisie en recall op synthetische benchmarks, en het schaalt efficiënt naar datasets met meer dan 20 miljoen reads met behulp van grafische processors.
Echte genfusies onderscheiden van sequentie‑illusies
De auteurs onderzochten vervolgens of DeepChopper echte biologische gebeurtenissen kon onderscheiden van artefacten in echte kankergegevens. Door directe RNA‑reads te vergelijken met overeenkomende datasets die met onafhankelijke methoden waren geproduceerd (zoals directe cDNA‑sequencing op zowel Oxford Nanopore als PacBio‑platforms), konden ze labelen welke schijnbare chimera’s werden ondersteund door andere technologieën en welke niet. DeepChopper verminderde niet‑ondersteunde chimerische alignments met 62–91%, terwijl het aandeel dat door andere methoden werd bevestigd sterk toenam. Het sneed ook het aantal verdachte genfusieaanroepen met bijna 90% terug, vooral die involving ribosomale genen die vaak artefacten bleken te zijn. Tegelijkertijd bleven echte fusiegebeurtenissen die door short‑read RNA‑sequencing werden ondersteund behouden.
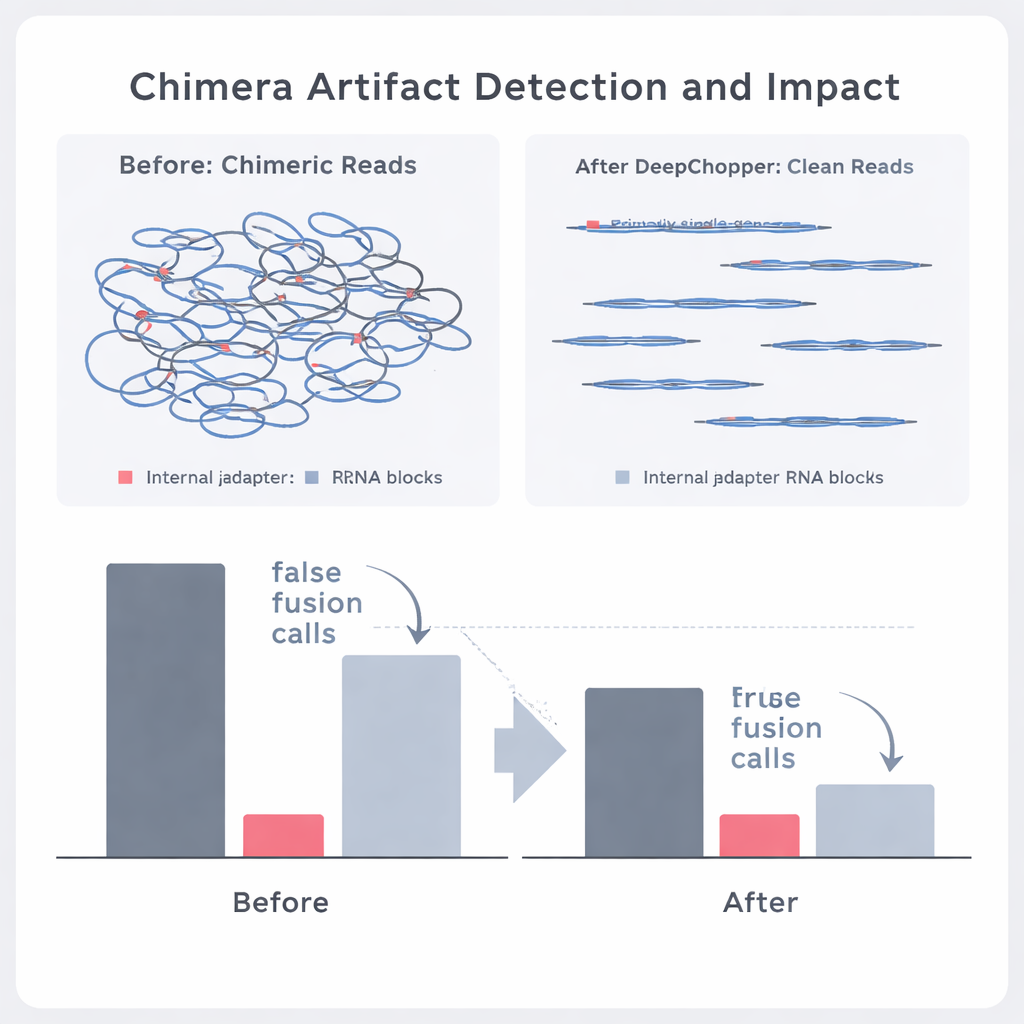
Betere chemie helpt — maar artefacten blijven
Oxford Nanopore bracht onlangs een geüpdatete sequencingkit uit (RNA004) die deels is ontworpen om technische artefacten te verminderen. DeepChopper werd "out of the box" toegepast op gegevens van deze nieuwe chemie en vond toch dat een klein maar belangrijk deel van de reads interne adapters en chimerische verbindingen bevatte. Zelfs zonder extra training verminderde het model het aantal artificiële chimera’s met ongeveer een vijfde; na fijnslijpen op de nieuwe data presteerde het iets beter, terwijl echte signalen intact bleven. Over alle chemieën en celtypen heen maakte het corrigeren van deze artefacten het voor downstream‑tools mogelijk om veel meer full‑length en alternatieve transcripties te detecteren, wat een helderder beeld van het RNA‑landschap van de cel opleverde.
Wat dit betekent voor toekomstige RNA‑studies
Voor niet‑specialisten is de kernboodschap dat niet iedere verrassende RNA‑verbinding die door een sequencer wordt gerapporteerd echte biologie is — sommige zijn bedradingfouten die door de technologie zelf zijn geïntroduceerd. DeepChopper fungeert als een hoogopgeleide corrector voor nanopore RNA‑gegevens, detecteert de typische adaptersequenties die niet‑gerelateerde moleculen aan elkaar koppelen en knipt ze met single‑base precisie uit. Het resultaat zijn schonere, betrouwbaardere kaarten van welke RNA‑moleculen in een cel bestaan en hoe ze zijn samengesteld. Nu laboratoria steeds vaker op lange‑read RNA‑sequencing vertrouwen om kanker, hersenaandoeningen en andere complexe ziekten te bestuderen, zullen tools als DeepChopper essentieel zijn om ruwe, luidruchtige reads om te zetten in betrouwbare biologische inzichten.
Bronvermelding: Li, Y., Wang, TY., Guo, Q. et al. Genomic language model mitigates chimera artifacts in nanopore direct RNA sequencing. Nat Commun 17, 1864 (2026). https://doi.org/10.1038/s41467-026-68571-5
Trefwoorden: nanopore RNA-sequencing, chimerische reads, artefacten van genfusies, genomisch taalkundig model, DeepChopper