Clear Sky Science · nl
Een contextbewuste basecaller met dubbele context voor nanopore direct RNA-sequencing
Waarom het decoderen van RNA-letters ertoe doet
Elke cel in je lichaam leest en herschrijft voortdurend boodschappen die in RNA zijn vastgelegd, de werkende kopie van onze genen. Nieuwe “nanopore”-apparaten kunnen individuele RNA-moleculen direct uitlezen en beloven inzicht te geven in hoe genen worden aan- of uitgezet, hoe RNA’s worden gespliced en hoe chemische markeringen op RNA gezondheid en ziekte beïnvloeden. Er is echter een complicatie: deze apparaten meten in feite uiterst kleine elektrische stroompjes, die vervolgens moeten worden vertaald—“basecalled”—naar de vertrouwde letters A, C, G en U. Als die vertaling fout is, kan het biologische verhaal dat we afleiden ernstig vertekend worden. Dit artikel introduceert Coral, een nieuw kunstmatig-intelligentiesysteem dat deze vertaling veel nauwkeuriger maakt.
Elektriciteit lezen in plaats van letters
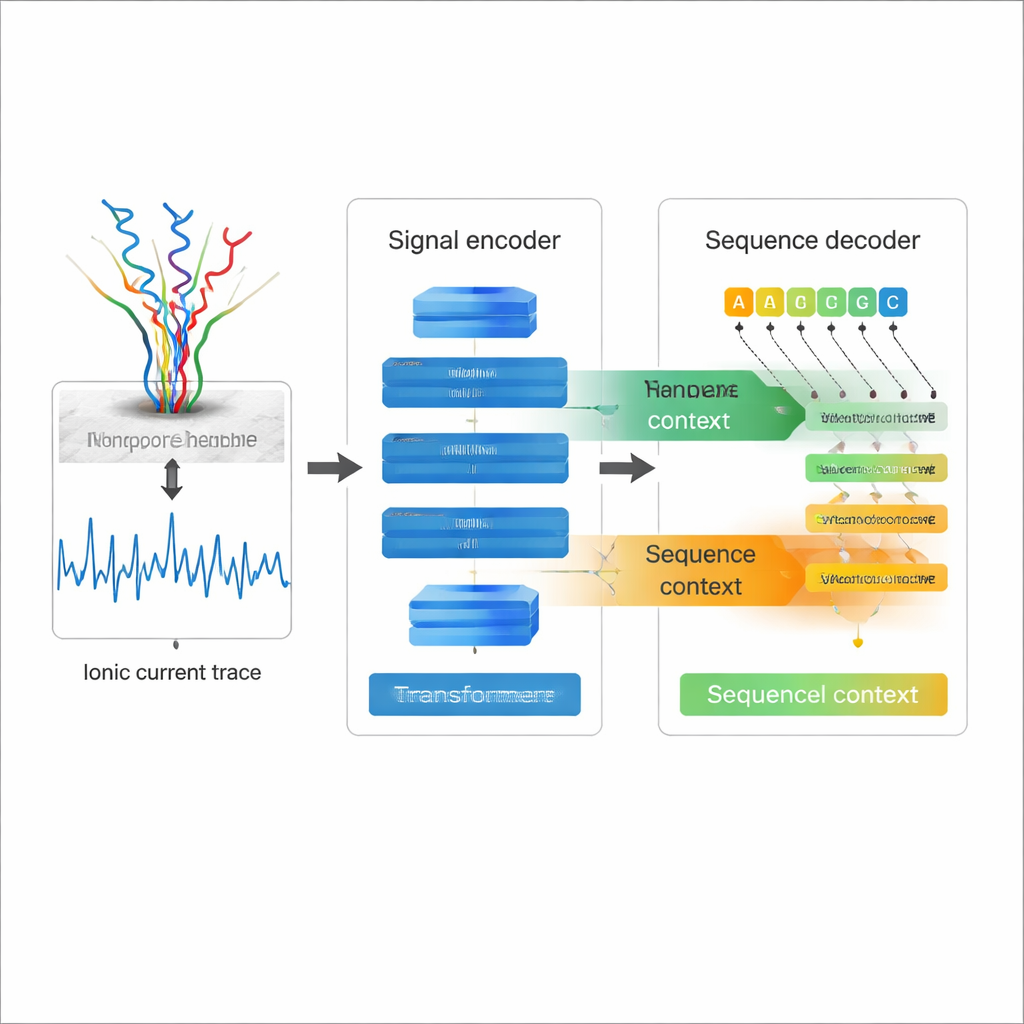
Nanopore direct RNA-sequencing werkt door een enkele RNA-streng door een moleculair gaatje—een nanopore—te leiden terwijl wordt gemeten hoe de elektrische stroom verandert wanneer elk nucleotide passeert. Die kronkelige stroomprofielen bevatten de informatie over de RNA-sequentie en diens chemische modificaties. Traditionele RNA-sequencing zet RNA in plaats daarvan om in DNA en versterkt het, stappen die bias kunnen invoeren en veel natuurlijke chemische markeringen kunnen wissen. Direct RNA-sequencing vermijdt die problemen, maar de prijs was tot nu toe een relatief hoge foutmarge bij het omzetten van stroomtraces naar sequenties, vooral bij lastige kenmerken zoals herhaalde basen en complexe RNA-vormen. Betere basecalling is essentieel als wetenschappers de fijne details van deze lange RNA-reads willen vertrouwen.
Een slimmer vertaalmodel dat twee soorten context gebruikt
De meeste bestaande nanopore-basecallers behandelen het elektrische signaal als de belangrijkste informatiebron en decoderen elke positie min of meer onafhankelijk, wat hun vermogen beperkt om de structuur van de RNA-sequentie zelf te benutten. Coral kiest een andere benadering. Het gebruikt een encoder–decoderarchitectuur op basis van Transformers, verwant aan moderne taalmodellen. Eerst vertaagt een encoder-netwerk, opgebouwd uit convoluties en self-attention-lagen, het ruwe stroomsignaal naar een compacte beschrijving van hoe het signaal in de tijd verandert. Vervolgens voorspelt een decoder elke nieuwe RNA-base stap voor stap, waarbij hij tegelijkertijd terugkijkt naar de al geschreven basen en zijwaarts naar het gecodeerde signaal. Twee soorten attention—binnen de groeiende RNA-sequentie en tussen sequentie en signaal—stellen Coral in staat zowel elektrische als sequentie-context mee te wegen bij het beslissen welke letter volgt.
Scherpere sequenties en minder gemiste moleculen
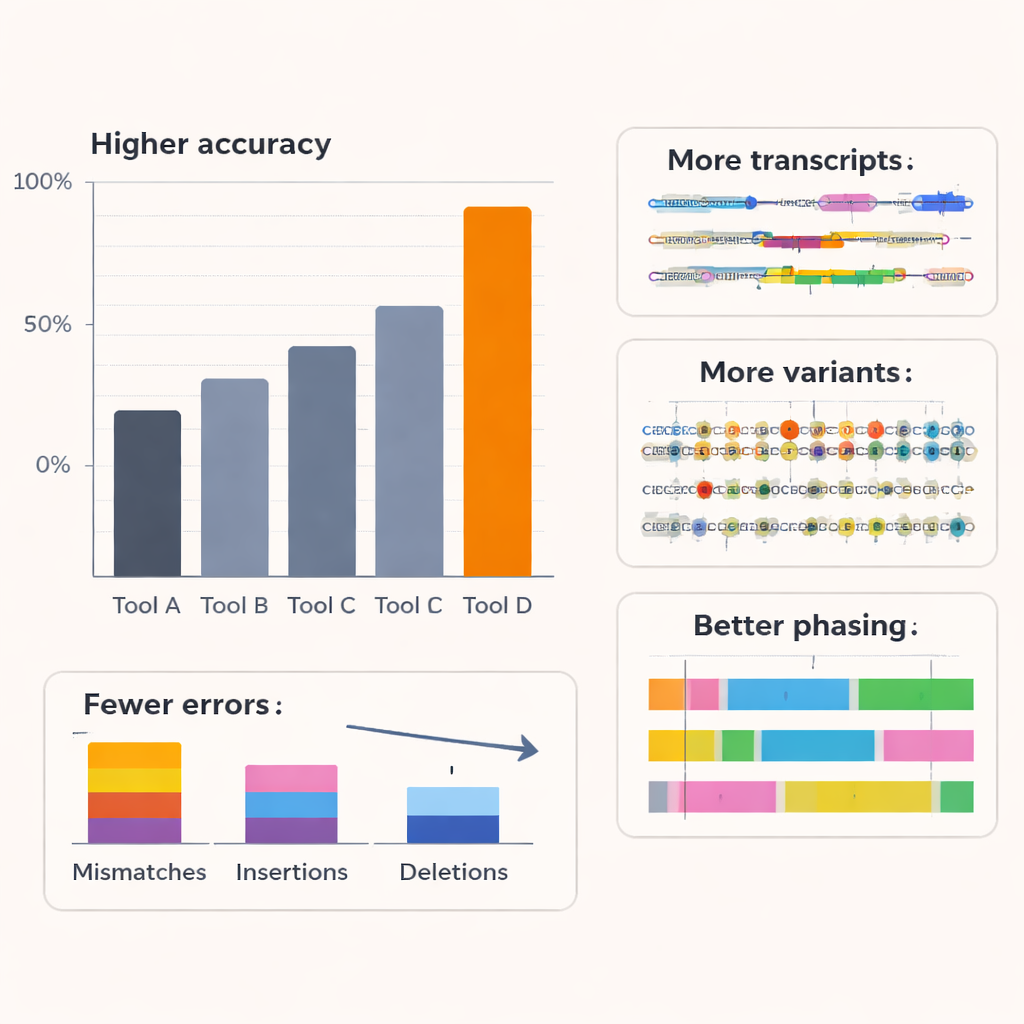
De auteurs testten Coral tegenover verschillende toonaangevende basecallers, waaronder de commerciële tools van Oxford Nanopore, op RNA van mensen en andere organismen en op meerdere nanopore-chemistries. Over zes soorten en oudere RNA-sequencingkits behaalde Coral een typische mediaanreadnauwkeurigheid rond 97%, duidelijk hoger dan concurrerende methoden. Met de nieuwste RNA-kit overtrof de nauwkeurigheid 99%. Coral produceerde minder mismatches, inserties en deleties, en leverde langere, beter uitgelijnde reads met minder sequenties die helemaal niet konden worden gemapt. Het was bijzonder goed in het omgaan met korte reeksen herhaalde basen—zeer veel voorkomend in echte data—die vaak een bron van fouten zijn voor andere tools. Doordat het betrouwbaarder langere stukjes correcte sequentie vastlegt, presteerde Coral ook uitstekend in het voorspellen van korte sequentiepatronen (k-mers) en bleef het robuust, zelfs wanneer eerdere decoderingstappen kleine fouten bevatten.
Meer zicht op verborgen details van het transcriptoom
Verbeterde basecalling is alleen nuttig als het leidt tot betere biologische conclusies. Om dit te testen onderzocht het team hoe de output van Coral downstream-analyses in menselijke cellijnen beïnvloedde. Met een gespecialiseerd hulpmiddel om volledige RNA-isoformen te reconstrueren—de verschillende splice-versies van elk gen—vonden ze dat de reads van Coral meer bekende transcriptstructuren en veel extra, laag-abundante isoformen blootlegden die andere basecallers misten. Veel transcripts die specifiek door Coral werden gevonden, werden ondersteund door onafhankelijke short-read-data, wat aangeeft dat ze reëel zijn en geen artefacten. Coral detecteerde ook meer kunstmatige referentietranscripten met bekende concentraties in een spike-in-experiment en schatte hun abundantie nauwkeuriger. Verder dan transcriptontdekking verbeterde Coral de detectie van genfusies in een borstkankercellijn en verhoogde het aantal en de betrouwbaarheid van genen met allelspecifieke expressie, waarbij de ene ouderlijke kopie van een gen actiever is dan de andere.
Helderdere genetische varianten en familieverbanden
Aangezien lange RNA-reads verre genetische varianten kunnen overspannen, zijn ze krachtige hulpmiddelen om te bepalen welke varianten samen op dezelfde chromosoomkop voorkomen—een proces dat haplotype-fasering wordt genoemd. Met een goed bestudeerde menselijke sample met een goudstandaard-variantkaart toonden de auteurs aan dat Corals hogere-kwaliteit reads leidden tot nauwkeurigere detectie van enkel-nucleotideveranderingen en veel minder faseringfouten: switch-fouten en de algehele mismatchpercentages binnen gefaseerde blokken daalden met tot ongeveer driekwart vergeleken met andere methoden, terwijl aanzienlijk meer varianten überhaupt gefaseerd konden worden. Simulatiestudies waarin de onderliggende readnauwkeurigheid werd gevarieerd, bevestigden dat zodra basecalling ongeveer 95% nauwkeurigheid nadert, de prestaties in transcriptontdekking, allelspecifieke expressie en fasering sterk verbeteren en daarna stabiliseren. Coral zit in deze zone met hoge baten, wat suggereert dat het het grootste deel van de biologisch relevante informatie in de ruisige nanopore-signalen vastlegt.
Wat dit betekent voor toekomstig RNA-onderzoek
Voor niet-specialisten is de kernboodschap dat Coral functioneert als een veel betrouwbaardere vertaler tussen de elektrische taal van nanopore-sequencers en de genetische taal van RNA. Door context in zowel het signaal als de groeiende sequentie beter te benutten, produceert het schonere reads die meer transcriptvarianten onthullen, zeldzame fusiegenen detecteren en met grotere zekerheid volgen welke varianten van welke ouder komen. De software is open-source, zodat onderzoekers deze kunnen aanpassen aan nieuwe organismen, chemistries of zelfs om chemische markeringen op RNA zelf te bestuderen. Naarmate nanopore-technologie blijft verbeteren, zullen tools zoals Coral helpen ruwe stroomtraces om te zetten in betrouwbare, gedetailleerde kaarten van de RNA-wereld in cellen.
Bronvermelding: Xie, S., Ding, L., Yu, Y. et al. A dual context-aware basecaller for nanopore direct RNA sequencing. Nat Commun 17, 1851 (2026). https://doi.org/10.1038/s41467-026-68566-2
Trefwoorden: nanopore RNA-sequencing, basecalling, Transformer-model, transcript-isoformen, haplotype-fasering