Clear Sky Science · nl
Generatieve AI-ontwerpen op sequentiebasis voor veelzijdige tryptofaan-synthases
Enzymen nieuwe trucs leren met AI
De moderne samenleving draait op moleculen—medicijnen, materialen en specialiteitschemicaliën—die vaak worden geproduceerd met energieverslindende, vervuilende processen. Natuurlijke katalysatoren, enzymen, kunnen soortgelijke taken schoon en efficiënt uitvoeren, maar het vinden of bouwen van het juiste enzym voor een nieuwe industriële toepassing is traag en onzeker. Deze studie toont aan dat generatieve kunstmatige intelligentie, dezelfde klasse technologie achter tekstschrijvende chatbots, kan worden gebruikt om gloednieuwe enzymen te ontwerpen die niet alleen goed werken in het laboratorium maar soms zelfs beter presteren dan de beste exemplaren die evolutie en jaren van engineering hebben opgeleverd.
Waarom enzymen belangrijk zijn in het dagelijks leven
Enzymen zijn kleine eiwitmachines die chemische reacties in levende cellen versnellen. Chemici hebben geleerd ze her te gebruiken om geneesmiddelen, ingrediënten voor voedsel en andere waardevolle producten te maken met minder energie en minder giftige reagentia dan traditionele chemie. Het probleem is dat elke nieuwe toepassing meestal een enzym vereist met precies de juiste eigenschappen—in staat om specifieke beginmaterialen te accepteren, te overleven onder proceseisen en hoge opbrengsten te leveren. Conventionele “gerichte evolutie” verbetert enzymen door veel gemuteerde varianten te maken en te testen, generatie na generatie. Dat werkt goed maar is afhankelijk van een redelijk uitgangsenzym en kan maanden tot jaren van vallen en opstaan vergen, waardoor veel nuttige reacties onontgonnen blijven.
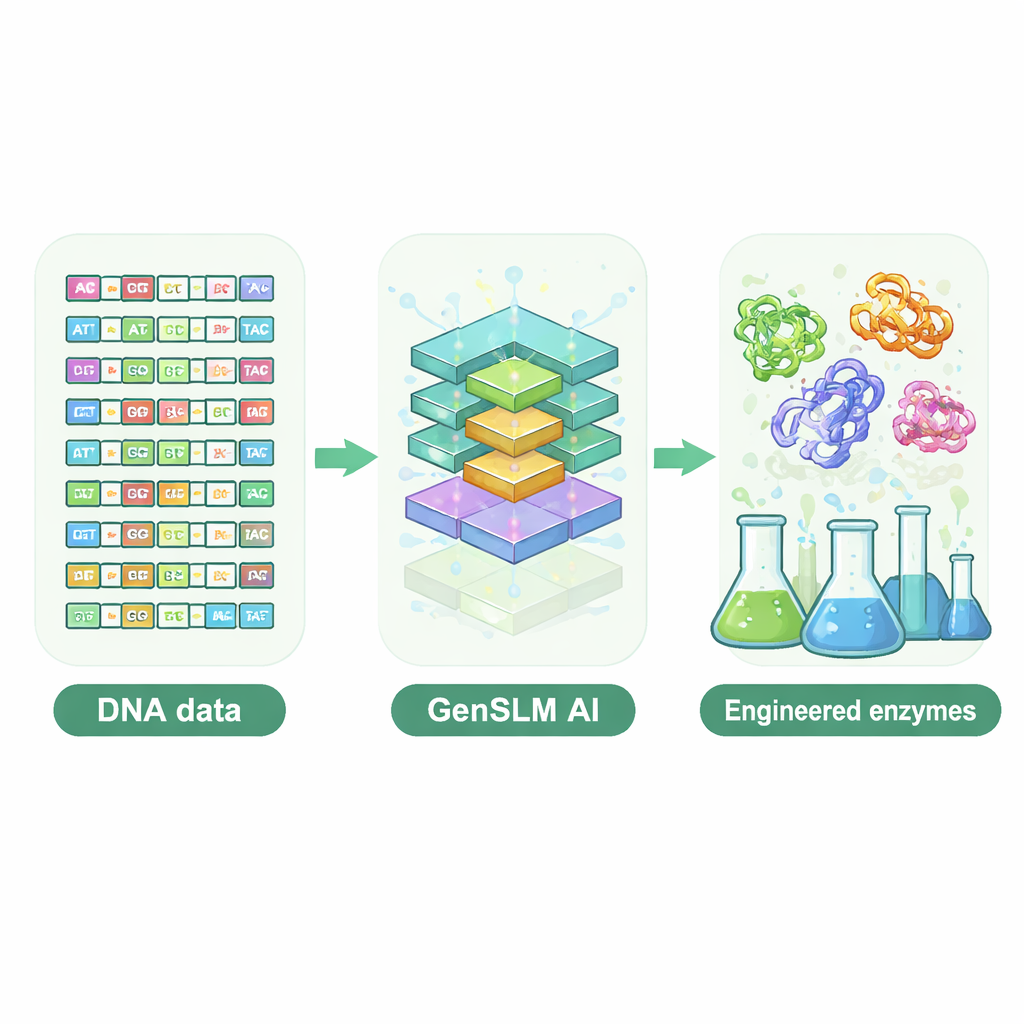
Een taalmodel dna laten schrijven
De onderzoekers grepen naar een genoom-schaal taalmodel genaamd GenSLM, dat patronen in DNA leert zoals een taalmodel grammatica en stijl in tekst leert. In plaats van te werken met voltooide eiwitsequenties, leest en schrijft GenSLM DNA in drielettercodons, overeenkomstig hoe cellen genen naar eiwitten vertalen. Het team verfijnde GenSLM eerst op tienduizenden natuurlijke genen voor één bijzonder complexe enzymsubunit, TrpB genoemd, die helpt bij de biosynthese van het aminozuur tryptofaan. Vervolgens vroeg men het model om duizenden volledig nieuwe trpB-genen te genereren. Eenvoudige computationele filters verwijderden sequenties die te kort of te lang waren, waarschijnlijk niet correct zouden vouwen of bijna identiek waren aan bekende natuurlijke enzymen, wat resulteerde in 105 diverse kandidaten voor experimentele testen in bacteriën.
Van computergestuurde ontwerpen naar werkende katalysatoren
Toen deze 105 AI-ontworpen TrpB-enzymen in E. coli werden geproduceerd, vouwden veel ervan goed en werden ze in hoge hoeveelheden aangemaakt. Tientallen konden hun hoofdtaak uitvoeren: indol en de natuurlijke partner, het aminozuur serine, omzetten in tryptofaan. Sommige werkten robuust zelfs bij verhoogde temperaturen, ondanks dat er geen expliciet ontwerp voor hittebestendigheid was. In vergelijkende tests evenaarden of overtroffen een subset van de GenSLM-TrpBs een referentie-enzym dat jarenlang zorgvuldig in het lab was geëvolueerd om zelfstandig te functioneren bij 75 °C. Eén opvallend ontwerp, gelabeld 230, produceerde meer tryptofaan dan deze industrieel gebruikte referentie zowel bij kamertemperatuur als bij hoge temperatuur, wat laat zien dat een model dat alleen op sequentiegegevens is getraind direct naar topklasseprestaties kan springen.
Nieuwe flexibiliteit voorbij wat de natuur bouwde
Het team daagde de enzymen vervolgens uit met een paneel van niet-natuurlijke substraten—indoolderivaten, een ander alcoholachtig partnermolecuul en een gefluoreerd bestanddeel dat in de geneesmiddelenproductie wordt gebruikt. Natuurlijke varianten van TrpB zijn doorgaans kieskeurig: ze hebben een sterke voorkeur voor hun eigen substraten en vertonen weinig activiteit op dergelijke alternatieven. Opmerkelijk genoeg waren de AI-gegeneerde enzymen vaak avontuurlijker. Voor elk getest niet-natuurlijk substraat toonde ten minste één GenSLM-ontwerp meetbare activiteit, en velen presteerden beter dan natuurlijke enzymen. Wederom stak variant 230 eruit, die alle zeven alternatieve substraten omzet met opbrengsten variërend van bescheiden tot bijna volledig—een breedte aan ‘promiscuïteit’ die eerder niet in deze enzymfamilie werd gezien. Toch vonden de onderzoekers, bij vergelijking van 230 met zijn dichtstbijzijnde natuurlijke verwant—die op slechts 78 van de 400 aminozuurposities verschilde—dat het natuurlijke enzym deze veelzijdigheid niet had, hoewel de algemene structuur en sleutelresiduen in het actieve centrum nagenoeg identiek waren.
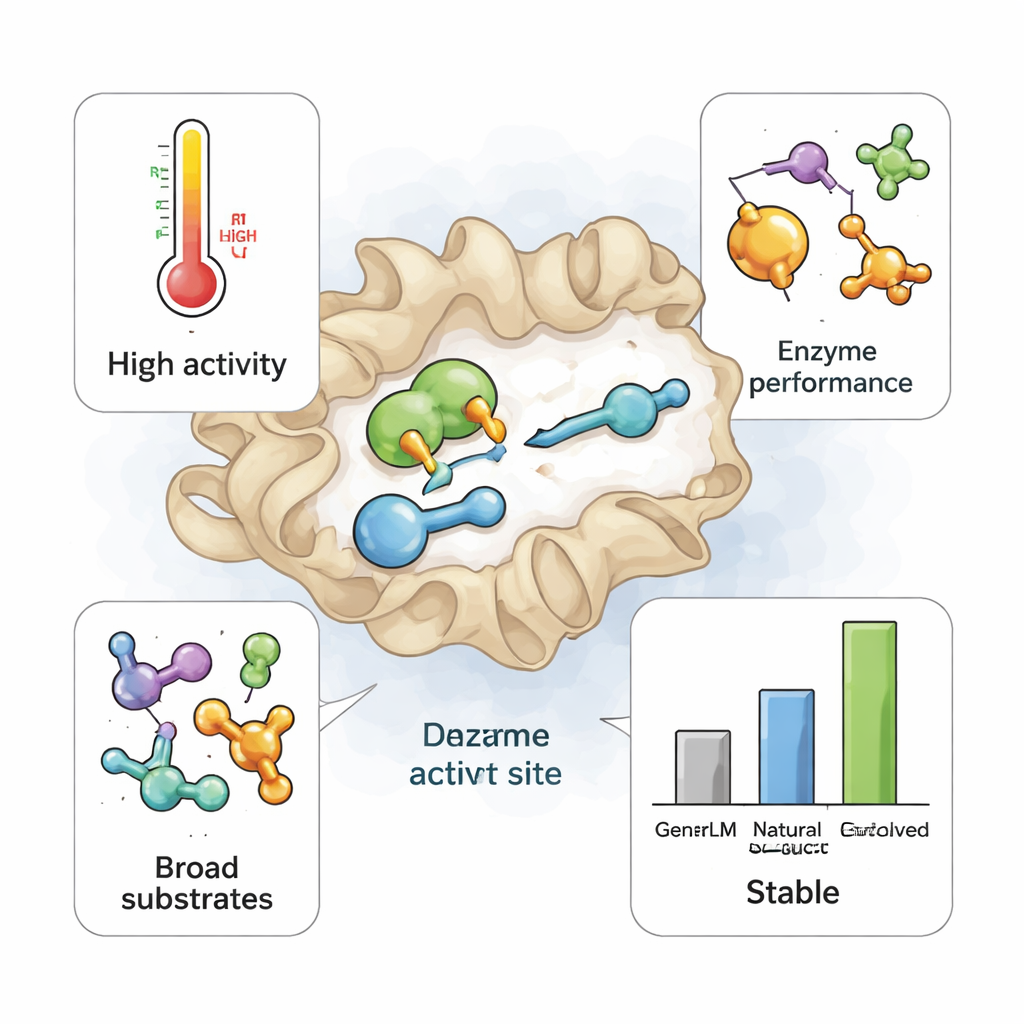
Wat dit betekent voor toekomstige groene chemie
Voor niet‑specialisten is de kernboodschap dat een AI-model, getraind uitsluitend op bestaande DNA-sequenties, realistische nieuwe enzymen kan bedenken die de natuur nooit heeft uitgeprobeerd, waarvan sommige betere gereedschappen voor de chemie zijn dan de momenteel gebruikte. Deze AI-ontworpen TrpB-varianten behouden de essentiële vorm en functie van hun natuurlijke neven maar krijgen een ongebruikelijk vermogen om met veel verschillende beginmaterialen om te gaan. Die flexibiliteit kan de hoeveelheid labwerk die nodig is om enzymgebaseerde routes naar nieuwe geneesmiddelen en andere producten te ontdekken drastisch verminderen. Naarmate ontwerp, DNA-synthese en testen sneller en goedkoper worden, kunnen soortgelijke generatieve modellen de ontdekking van enzymen veranderen van een trage schatzoektocht in een snel, routinematig ontwerpproces en zo meer industriële chemie naar schonere, door enzymen aangedreven processen verschuiven.
Bronvermelding: Lambert, T., Tavakoli, A., Dharuman, G. et al. Sequence-based generative AI design of versatile tryptophan synthases. Nat Commun 17, 1680 (2026). https://doi.org/10.1038/s41467-026-68384-6
Trefwoorden: enzymengineering, generatieve AI, proteïneontwerp, tryptofaan-synthase, biokatalyse